Clear Sky Science · zh
面向百万原子级生物体系的量子力学框架
以电子为视角窥见生命
蛋白质、DNA 和病毒的行为都源于电子的不断运动,但要对如此庞大的分子进行真正的量子级模拟,以往长期仅能在极小体系上运行。本研究提出了一种方法,通过对精度做出谨慎放松,将完整的量子力学引入巨大的生物结构——可达到数千万原子规模——从而使计算变得更快、成本可承受,并在生物学、医学和药物设计问题上出人意料地有用。
为何大分子需要量子视角
许多生物事件——从药物结合到光作用下的视觉——都涉及化学键的断裂与形成以及电子云的重排。经典模拟方法可以跟踪大型蛋白或 DNA 的整体原子运动,但它们只是间接地处理电子,因此会错过一些决定光吸收或药物与靶点结合紧密程度的微妙效应。相比之下,量子力学方法显式追踪电子,能够高保真地预测诸如光学光谱等性质。问题在于,传统量子方法随着体系增大会变得极为缓慢,因此通常只用于小片段,无法覆盖整个病毒或庞大的蛋白组装体。
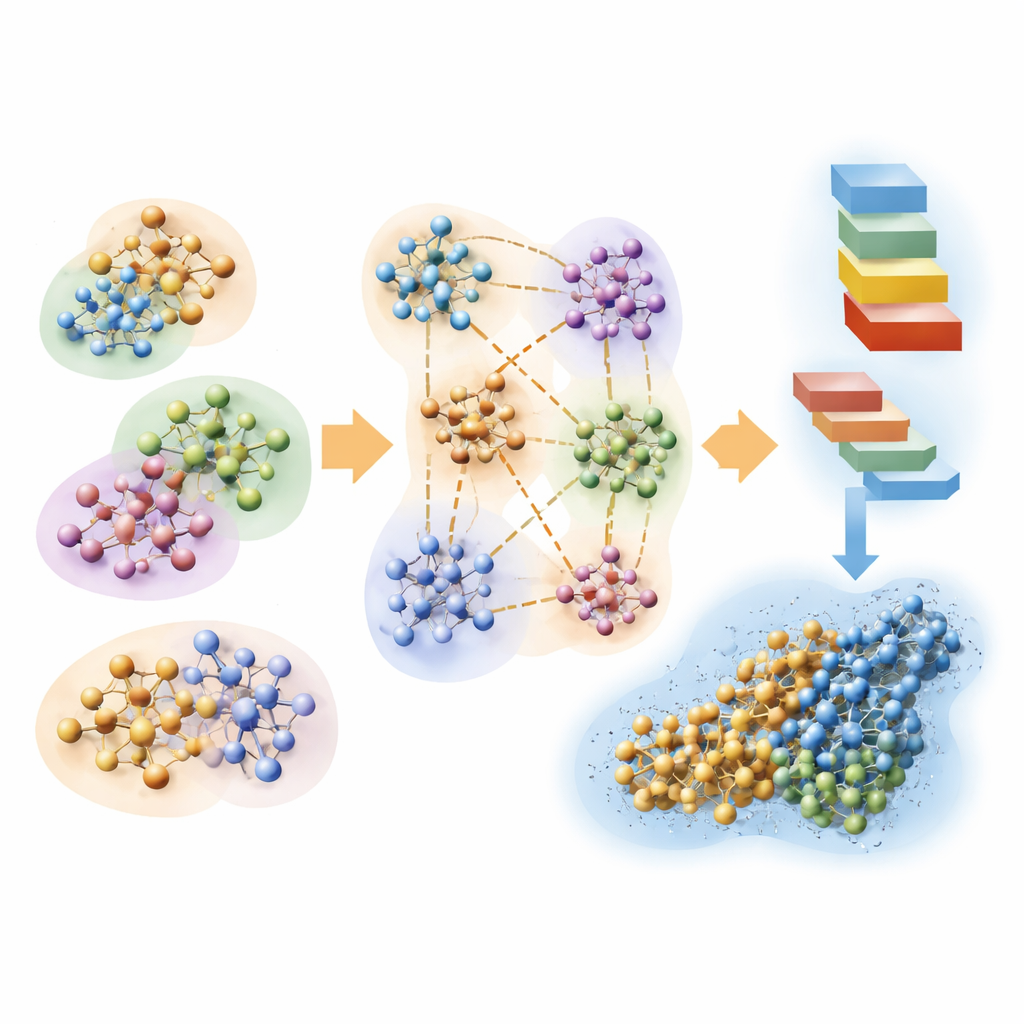
把问题拆成可吞咽的小块
作者基于经典的量子方法——Hartree–Fock,该方法用数学轨道描述电子,并将其改造以追求速度而非极致精度。他们的关键思想是将一个巨大的生物分子及其周围的水环境分割成许多重叠的簇。每个簇具有一个保留量子结果的核心区域和一个模拟邻近原子影响的缓冲区。然后在每个簇上分别进行量子计算,再将各部分拼接以重构体系的整体电子密度。通过同时使用非常紧凑的轨道表示并丢弃对最终结果贡献很小的弱长程相互作用,该方法的计算量大致与原子数成比例增长,而不是呈指数级膨胀。
从病毒到 DNA 与抗癌药物
为展示这一精简框架的能力,研究人员处理了若干示例体系。他们计算了三种大型组装体在水中的完整电子结构,包括一个噬菌体——感染细菌的病毒——连同周围溶剂盒,总计超过4500万原子与超过1.5亿电子。在一台现代计算集群上,此项计算大约在半天内完成,据他们所知,这是迄今为止规模最大的 Hartree–Fock 模拟。随后他们转向光吸收问题:使用方法的时变扩展,他们模拟了长达21碱基对的 DNA 片段以及抗癌药物放线菌素 D(Actinomycin D)自由态与与 DNA 结合态的紫外-可见光谱。预测的光谱与实验测量高度吻合,表明降低精度的方案仍然捕捉到了这些生物分子与光相互作用的核心物理特征。
用物理学检验 AI 预测的蛋白形状
团队还探索了快速量子计算如何帮助评估如 AlphaFold 之类人工智能工具预测的蛋白质结构。蛋白质天然折叠成能量最小化的构型。借助线性可扩展的 Hartree–Fock 方法,作者在若干 AlphaFold 预测蛋白的长度上估算了局部原子能量,并在真实的水环境中进行。当这些基于量子得出的能量模式与 AlphaFold 自身的置信度评分对比时,二者惊人地一致:低能量区域与 AlphaFold 判定为可靠的区域重合,而高能量则标示出不确定或不稳定的片段。这表明现代结构预测网络在某种程度上隐式学习了底层量子能量景观的某些方面,而基于第一性原理的计算可以提供独立的、基于物理的质量检查。
权衡、局限与新可能性
速度提升来自有意识的妥协。使用最小轨道基组并截断弱的长程相互作用必然牺牲一部分精度,分而治之策略并不适合那些对长程效应敏感的量,例如精确的蛋白-配体紧密结合能。作者表明,对于此类高精度任务,必须放宽或移除截断,此时方法更像传统的、较慢的量子代码。然而对于无法进行完全精确量子处理的超大体系而言,他们的方法提供了一个强有力的中间路径:它以适度的计算资源常常给出定性且在许多情况下定量可靠的见解,甚至在单个计算节点上也能处理约百万原子规模的体系。
这对分子科学的未来意味着什么
通过将标准量子方法重新设计以偏向速度,同时与实验保持良好一致,这一框架为对整个病毒、蛋白质机器和大型 DNA–药物复合体进行常规的量子级研究打开了大门。它能够生成可与最前沿晶体学直接比较的详细电子密度图,预测前所未有规模生物分子的现实光学光谱,并对 AI 生成的蛋白结构提供独立的核查。展望未来,相同思路可支撑快速的基于量子的分子动力学研究、研究电场或磁场如何影响生物分子,以及生成用于训练下一代机器学习模型的大规模量子精确数据集。就实践而言,它将曾经遥远的“量子生物学”梦想——以完整电子细节处理生命机械——更接近于日常科学实践。
引用: Wieners, L., Garcia, M.E. A quantum-mechanical framework for million-atom scale biological systems. Commun Chem 9, 170 (2026). https://doi.org/10.1038/s42004-026-02038-y
关键词: 量子生物分子模拟, Hartree–Fock, 蛋白质结构预测, 紫外-可见光谱, 分而治之算法