Clear Sky Science · zh
AMR-GNN:一种多表征图神经网络框架,用于实现基因组抗菌素耐药性预测
为什么预测药物耐药性很重要
抗生素耐药性感染是当代主要的医疗威胁之一,每年导致超过一百万人死亡。医生迫切需要更快捷的方法来判断某种感染对哪些抗生素有效,但传统的实验室检测可能需要数天时间。本研究提出了一种新的人工智能框架,称为 AMR-GNN,它读取细菌的完整 DNA 序列并预测其对不同抗生素是耐药还是敏感,有望推动床边实现同日用药指导。
从缓慢培养到数字化 DNA 检测
目前,大多数医院仍依赖培养法检测:在实验室中培养细菌并暴露于多种药物以观察哪些药物能抑制其生长。尽管这种方法可靠,但速度慢且劳动强度大。与此同时,对细菌全基因组测序变得更便宜、更容易,产生了大量详尽的信息。挑战在于细菌 DNA 的维度极高,包含数百万个构建单元,而且没有单一公认的方法把这些遗传信息转换成计算机能轻松用于耐药性预测的格式。早期工具通常聚焦于少数已知耐药基因或简单模式,当耐药由单一突变引起时效果良好,但在许多微妙变化相互作用时则失效。
将不同的基因组视角合并为一幅图景
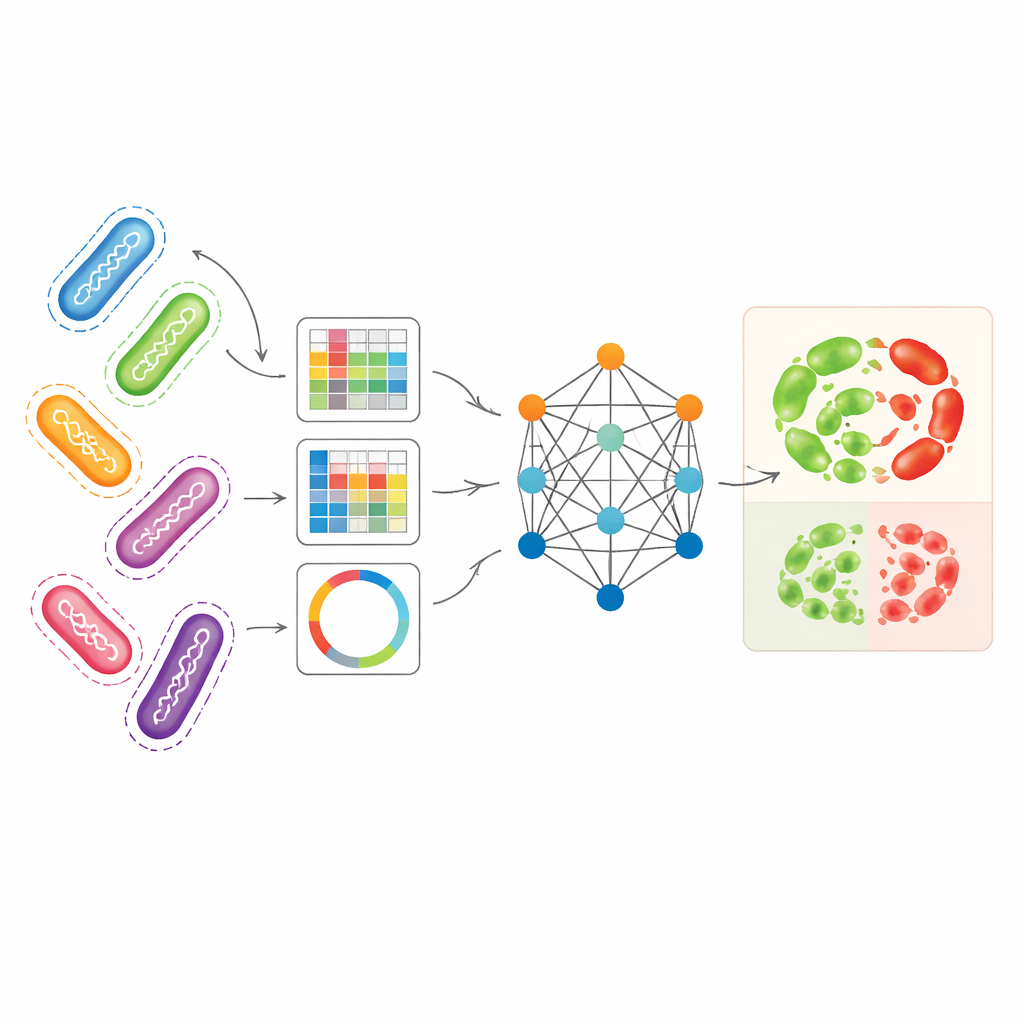
研究人员着手同时利用几种互补的细菌基因组表征方式。以铜绿假单胞菌(Pseudomonas aeruginosa)作为主要测试对象——这是一种院内获得的病原体,具有特别复杂的耐药模式。一种表征称为 unitigs,它在不依赖参考基因组的情况下捕捉重复出现的 DNA 片段。另一种表征跟踪特定位置的小型 DNA 变化,第三种把选定的耐药相关基因转换为类图像的模式,概括短片段 DNA 的排列。单独使用时,这些表征已能让标准机器学习模型以合理的准确度预测耐药性,尤其在某些抗生素上 unitigs 表现突出。但每种视角都遗漏了部分生物学信息,单独使用它们会未充分利用底层基因组数据的丰富性。
基于图的模型如何从相关菌株中学习
AMR-GNN 使用一种称为图神经网络的深度学习形式,它把每个细菌分离株视为一个点(节点),并用连接(边)将基因相似的分离株联结起来。在此设置中,每个分离株详尽的 unitig 描述构成其主要特征向量,而其他基因组视角则决定了图中分离株之间如何连接。模型沿这些连接传递信息,使其能从相关基因组共享的模式中学习。为避免被简单的克隆关系误导——即细菌在谱系上接近但耐药性差异源于模型应发现的具体原因——作者有意移除了将来自同一遗传谱系组的分离株相连的边。这一步“解耦”迫使网络更多关注与耐药性相关的具体 DNA 特征,而不是依赖宽泛的谱系标签作为捷径。
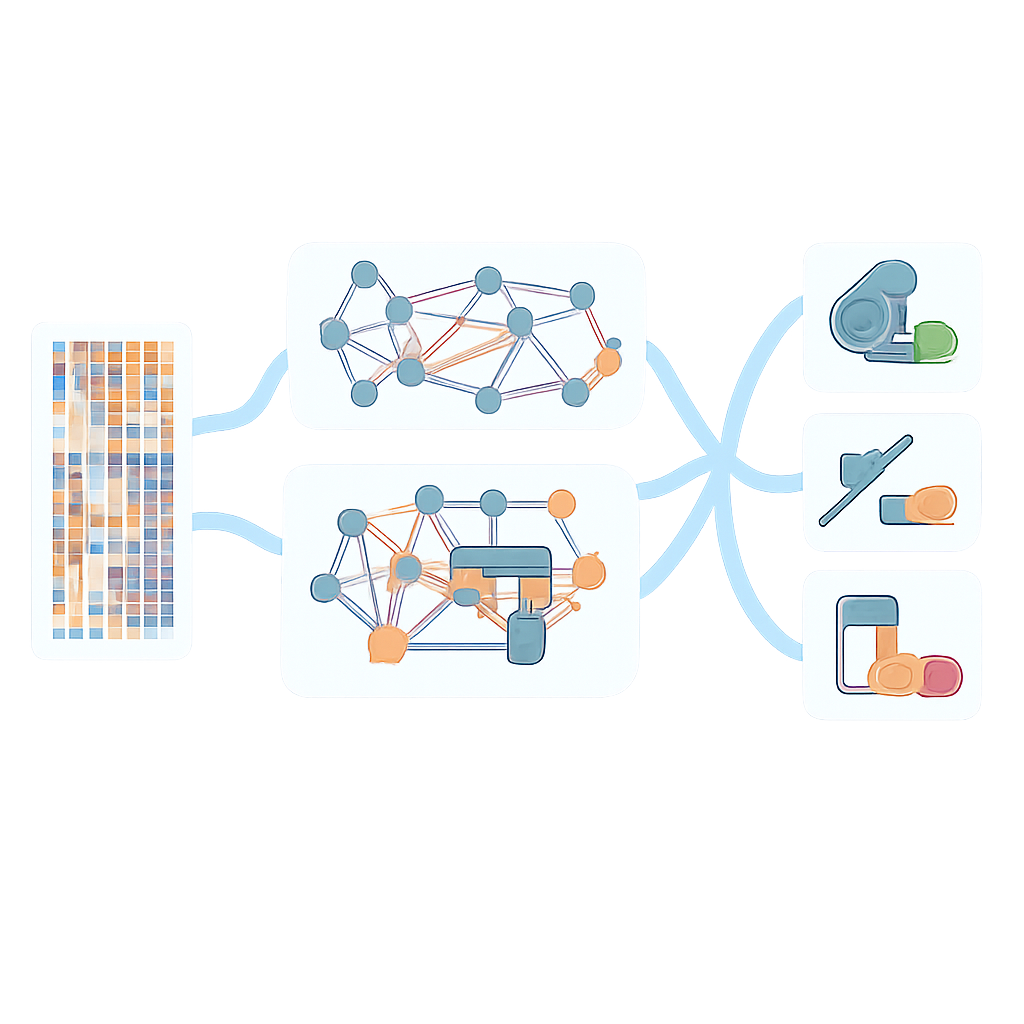
在不同细菌和药物上更强的预测能力
当团队将 AMR-GNN 与依赖单一基因组视角的简单模型比较时,基于图的方法在铜绿假单胞菌测试的 12 种抗生素中几乎全部提高了性能,尤其在先前最难预测的药物上带来最大增益。该模型对独立测试数据集的泛化能力也更好,尽管在训练数据之外性能仍有所下降,这突显出需要更大且更多样化的基因组集合。除铜绿假单胞菌外,研究者还将 AMR-GNN 应用于来自其他主要病原体的超过 23,000 个基因组,包括大肠埃希菌(Escherichia coli)、肺炎克雷伯菌(Klebsiella pneumoniae)、金黄色葡萄球菌(Staphylococcus aureus)和费氏肠球菌(Enterococcus faecium),涵盖多种临床重要的抗生素。在大多数物种—药物组合中,该框架达到很高的准确率,并优于依赖已知耐药基因人工整理列表的广泛使用的基于规则的工具。
让黑箱模型更易解释
对临床使用而言,一个重要关切是此类 AI 系统能否解释其特定预测的原因。团队通过应用可解释性方法来解决这一点,这些方法追踪哪些 DNA 特征对模型决策贡献最大。对于模型表现最好的药物,AMR-GNN 强调了许多已知的耐药基因和突变,例如氟喹诺酮类抗生素的经典靶点。它还指向一些了解较少的基因,其变化与需要更高药物浓度来抑制细菌生长强相关,提示了新的试验室后续研究候选。这种既能预测耐药性又能标示潜在生物学驱动因素的能力,有助于弥合纯预测与机制性理解之间的空白。
这对未来患者护理意味着什么
总的来说,这项工作表明,在图基深度学习模型中结合多种 DNA “视角”可以显著提升从细菌基因组预测抗生素耐药性的能力。AMR-GNN 被呈现为一个灵活且可解释的框架,可扩展到其他数据类型,如基因表达测量或临床信息。尽管仍需更多工作——尤其是更大、地理分布更广的数据集和前瞻性临床试验——但这一方法使我们更接近这样一个未来:从患者样本直接获得的细菌基因组序列,能够快速为医生指引合适用药并帮助减缓耐药性感染的传播。
引用: Nguyen, HA., Peleg, A.Y., Wisniewski, J.A. et al. AMR-GNN: a multi-representation graph neural network framework to enable genomic antimicrobial resistance prediction. Nat Commun 17, 3555 (2026). https://doi.org/10.1038/s41467-026-69934-8
关键词: 抗菌素耐药性, 图神经网络, 细菌基因组学, 机器学习, 抗生素敏感性预测