Clear Sky Science · de
Struktur und Wirkmechanismus der HECT‑Ligase HECTD3
Wie Zellen ihre Proteine für den Einsatz kennzeichnen
In jeder Zelle entscheidet ein winziges Signalsystem, welche Proteine repariert, recycelt oder für neue Aufgaben umprogrammiert werden. Diese Studie konzentriert sich auf eines der Enzyme, das dieses System steuert: ein Protein namens HECTD3. HECTD3 wurde mit Krebs, Entzündungen und Virusinfektionen in Verbindung gebracht, doch wie es auf atomarer Ebene arbeitet, war bislang unklar. Durch die Kombination leistungsfähiger bildgebender und biochemischer Methoden zeigen die Autoren, wie HECTD3 aufgebaut ist, wie es seine molekularen Partner auswählt und wie es andere Proteine mit kleinen Markern versieht, die deren Schicksal verändern können.
Eine zelluläre Markierungsmaschine mit vielen Aufgaben
Zellen modifizieren ihre Proteine häufig mit einem kleinen Molekül namens Ubiquitin, das wie ein Farbetikett in einem Sortierlager wirken kann. Reihen dieser Marker, die unterschiedlich angeordnet sind, senden verschiedene Signale: Manche markieren ein Protein zur Zerstörung, andere regulieren seine Aktivität oder seinen Standort. Enzyme namens E3‑Ligasen sind dafür verantwortlich, welche Proteine markiert werden und wie. HECTD3 gehört zu einer Gruppe von E3‑Ligasen, die zunächst eine vorübergehende chemische Verbindung mit Ubiquitin eingehen, bevor sie es an ein Zielprotein übertragen. Es ist in mehreren Krebsarten ungewöhnlich aktiv und wurde mit Prozessen wie programmierter Zellsterblichkeit, Immunantworten und viraler Replikation in Verbindung gebracht, doch Struktur und Wirkprinzip waren weitgehend unbekannt.
Ein ständig aktives Enzym mit einzigartiger Form
Die Forscher fragten zunächst, ob HECTD3 wie ein Schalter funktioniert, der an‑ oder abgeschaltet werden kann. Viele verwandte Ligasen regulieren sich selbst, indem sie in selbstblockierende Formen falten oder zu größeren Verbünden zusammenlagern. Mit biochemischen Tests und einer Technik zur Bestimmung der Größe von Proteinen in Lösung fanden die Autoren, dass HECTD3 überwiegend als einzelnes Molekül vorkommt und sich offenbar nicht durch Selbsthemmung oder stabile Cluster abschaltet. Sowohl der katalytische Kern als auch das voll‑längliche Protein sind aktiv und zeigen eine deutliche Präferenz für eine Familie von Helferenzymen, die Ubiquitin übergeben. Das bedeutet, dass HECTD3 im Grunde „einsatzbereit“ ist und wahrscheinlich in der Zelle durch Faktoren reguliert wird, die über einfache Selbstblockade hinausgehen.
Enthüllung einer neuen Proteinarchitektur
Um zu verstehen, wie HECTD3 aufgebaut ist, nutzten die Autoren Kryo‑Elektronenmikroskopie, um einzelne Moleküle in dünnem Eis einzufrieren und zu fotografieren. Sie bestimmten Strukturen des Proteins allein und in einem Zustand, in dem ein Ubiquitinmolekül fest an die aktive Stelle gebunden ist. Diese Momentaufnahmen zeigen, dass HECTD3 kompakt und nicht ringförmig ist, mit einer klassischen zweilappigen katalytischen Region an einem Ende und einer zuvor rätselhaften N‑terminalen Region am anderen. Die N‑terminale Hälfte bildet zwei völlig neue Faltungen, die die Autoren D3NA und D3NB nennen, angeordnet als eine helikale Plattform, die ein substratbindendes DOC‑Modul stützt. Wenn Ubiquitin geladen ist, nehmen die katalytischen Lappen eine charakteristische L‑förmige Anordnung ein, und spezifische saure Reste in der Nähe der aktiven Stelle helfen, hereinkommende Proteinseitenketten für die Aufnahme des Markers vorzubereiten. Die Arbeit zeigt, dass HECTD3 zwar den allgemeinen Regeln seiner Enzymfamilie folgt, dabei aber eine eigene Kombination struktureller Elemente verwendet.
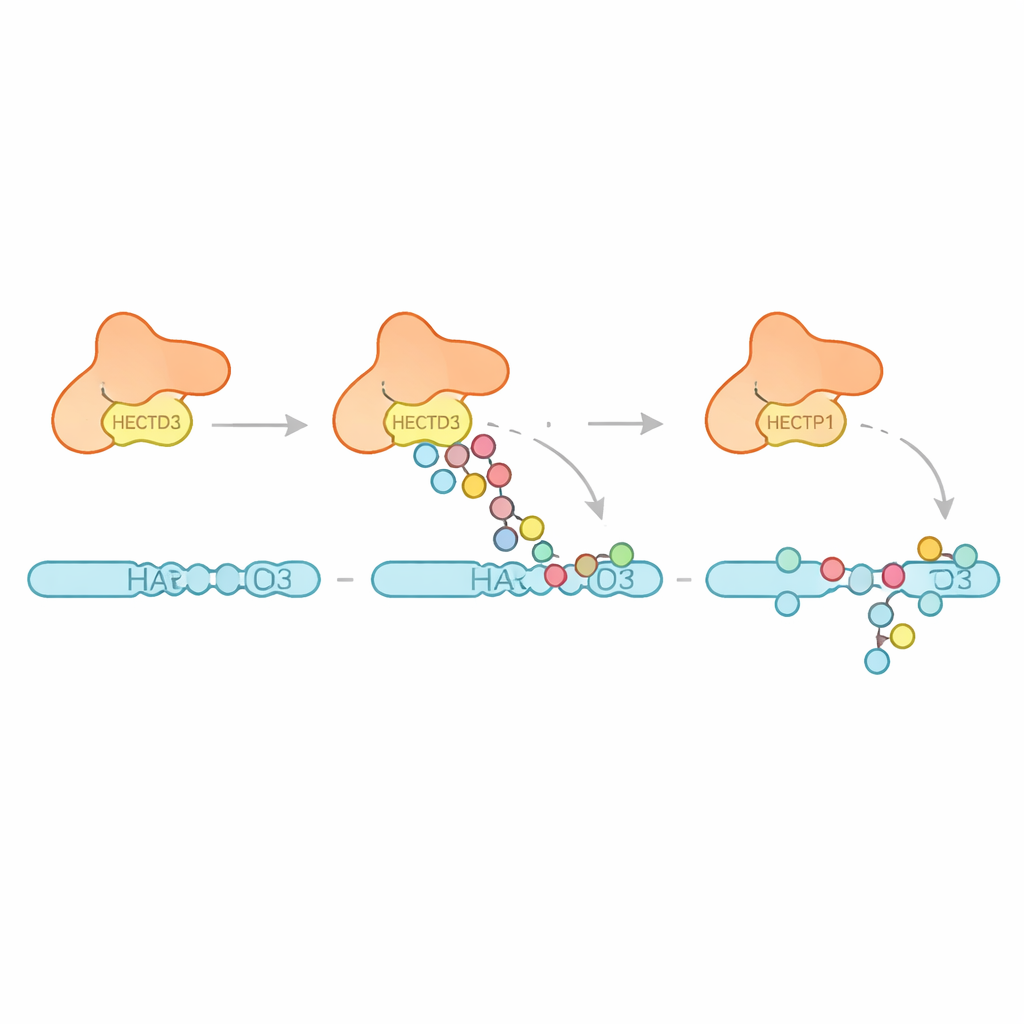
Wie HECTD3 sich selbst und seine Ziele markiert
Anschließend untersuchte das Team, welche Arten von Ubiquitinmustern HECTD3 erzeugt. Statt lange Ketten eines einzigen Typs aufzubauen, hängt das Enzym vor allem mehrere einzelne Ubiquitin‑Einheiten und kurze Ketten an, mit Hinweisen auf einige Verknüpfungen, die für den Proteinabbau förderlich sind. Das legt nahe, dass HECTD3 besser darin ist, Markierungsereignisse zu initiieren, als sie zu langen Signalen zu verlängern. Die Autoren untersuchten dann ein vorgeschlagenes Zielprotein namens PARP1, einen DNA‑Reparaturfaktor, der bereits für seine Bedeutung bei der Antwort auf Krebstherapien bekannt ist. In Reaktionen im Reagenzglas modifizierte HECTD3 PARP1 effizient und versah mehrere Lysinstellen in dessen DNA‑bindender Hälfte mit Markern, einschließlich Ketten, die mit Proteinabbau assoziiert sind. Mithilfe chemischer Quervernetzung und Massenspektrometrie kartierten sie Kontaktpunkte zwischen HECTD3 und PARP1 und bestätigten, dass sowohl das DOC‑Modul als auch die katalytische Region das Substrat positionieren. Die Mutation von zwei exponierten Aminosäuren an der DOC‑Oberfläche reduzierte die PARP1‑Markierung deutlich, ohne die Kernchemie zu beeinträchtigen, und hebt diese als wichtige Verankerungspunkte für die Substraterkennung hervor.
Warum das für Krankheit und Therapie wichtig ist
Insgesamt zeichnen diese Befunde HECTD3 als ständig aktives, aber strukturell anspruchsvolles Markierungswerkzeug, das hauptsächlich das Anstoßen von Ubiquitin‑Marken übernimmt und sich auf eine flexible, einzigartige N‑terminale Region verlässt, um spezifische Partner wie PARP1 zu erkennen. Da die Aktivität von HECTD3 in mehreren Krebsarten erhöht ist und beeinflusst, wie DNA‑Reparaturproteine gehandhabt werden, eröffnet das Verständnis seiner Struktur und seines Mechanismus Möglichkeiten, Moleküle zu entwickeln, die seine Andockflächen oder sein katalytisches Zentrum stören. Solche gezielten Eingriffe könnten theoretisch beeinflussen, wie Zellen über das Schicksal wichtiger Proteine in Krebs, Infektion und entzündlichen Erkrankungen entscheiden.
Zitation: Huber, J., Esposito, D., Maslen, S. et al. Structure and mechanism of the HECT ligase HECTD3. Nat Commun 17, 2783 (2026). https://doi.org/10.1038/s41467-026-69520-y
Schlüsselwörter: Ubiquitin‑Ligase, HECTD3, Proteinmarkierung, PARP1, Krebsbiologie