Clear Sky Science · pt
Perfilagem de modificações pós-traducionais de histonas para identificar assinaturas de resposta a drogas epigenéticas na leucemia linfoblástica aguda de células T
Por que este estudo sobre câncer importa
O tratamento de crianças e adultos com leucemia linfoblástica aguda de células T melhorou consideravelmente, mas muitos pacientes ainda recorrem a recidivas ou sofrem efeitos colaterais graves de quimioterapias intensas. Os médicos precisam de melhores maneiras de prever quais medicamentos funcionarão para cada paciente. Este estudo investiga se pequenas marcas químicas nas proteínas que embalam o DNA das células leucêmicas podem ajudar a prever como essas células respondem a drogas modernas que atuam na maquinaria epigenética da célula.
O código oculto na embalagem do DNA
Dentro de cada célula leucêmica, o DNA está enrolado em torno de proteínas chamadas histonas, formando uma estrutura compacta conhecida como cromatina. As histonas carregam muitas pequenas marcas químicas que funcionam como interruptores, ajudando a ligar ou desligar genes sem alterar a sequência básica do DNA. Como essas marcas são reversíveis, elas são alvos atraentes para drogas. Várias dessas “epidrogas” já são usadas em cânceres hematológicos, mas seu papel na leucemia de células T ainda é incerto, e os médicos não dispõem de marcadores simples para prever quem se beneficiará delas.
Lendo muitas marcas de histona de uma só vez
Os pesquisadores partiram de um esforço anterior no qual mapearam o padrão basal de marcas de histonas em 21 linhagens celulares de leucemia de células T usando espectrometria de massa, uma técnica capaz de medir centenas de marcas químicas simultaneamente. Em seguida, trataram essas linhagens com nove drogas: três antraciclinas de quimioterapia padrão, três drogas que bloqueiam histona desacetilases e três que inibem enzimas de metilação do DNA. Ao comparar a sobrevivência celular após o tratamento com os padrões iniciais de histonas, procuraram “assinaturas” de marcas que acompanhassem sensibilidade ou resistência a cada droga.
O que as linhagens celulares revelaram
Em células cultivadas, surgiram assinaturas distintas de histonas. Para as antraciclinas, certas marcas repressivas, como a chamada H3K27me3, tendiam a ser mais altas nas linhagens mais sensíveis, enquanto outras marcas, especialmente vários grupos dimetil, foram associadas a pior resposta. Para drogas que visam a metilação do DNA, níveis elevados de algumas marcas dimetil novamente apontaram para resistência, enquanto marcas de acetil nas caudas das histonas foram associadas a melhor resposta. Inibidores de histona desacetilase mostraram separação mais fraca entre linhagens sensíveis e resistentes, mas alguns padrões ainda apareceram, incluindo marcas específicas enriquecidas nas células menos ou mais responsivas. No geral, esses achados sugerem que a paisagem combinada de marcas de histonas, em vez de qualquer marca isolada, carrega informação sobre como as células leucêmicas respondem a drogas epigenéticas.
Testando uma única marca
Como trabalhos anteriores haviam sugerido que a aclarubicina funciona especialmente bem em células ricas na marca H3K27me3, a equipe testou essa ideia diretamente. Eles usaram outra droga para bloquear a enzima que escreve essa marca e conseguiram reduzir H3K27me3 em várias linhagens de leucemia de células T. Surpreendentemente, isso não alterou a sensibilidade das células à aclarubicina. Também observaram linhagens que naturalmente apresentavam alto H3K27me3, mas eram resistentes. Isso mostrou que, mesmo quando uma única marca de histona acompanha a resposta a drogas em alguns contextos, ela não é suficiente por si só para explicar a sensibilidade.
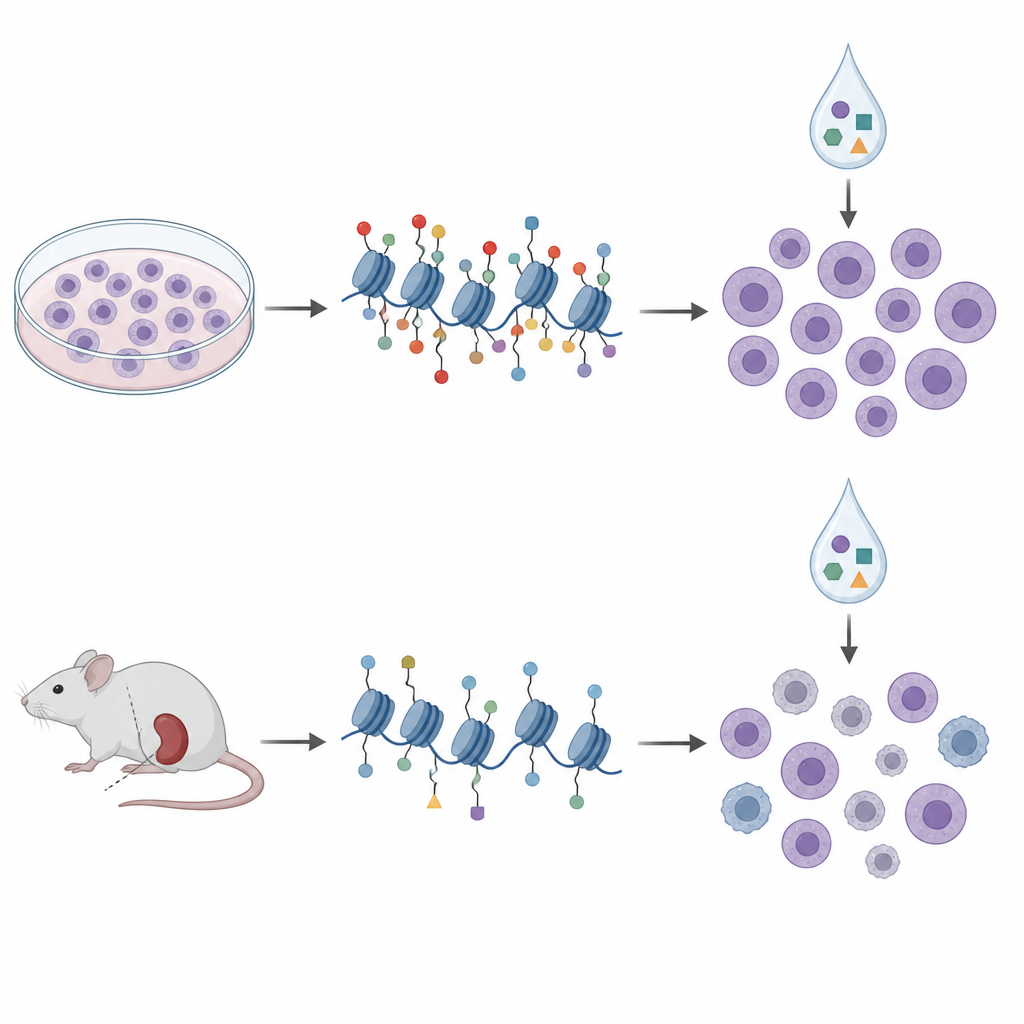
De placas de cultura a modelos em camundongos
Para avançar em direção à clínica, os pesquisadores recorreram a xenotransplantes derivados de pacientes, nos quais células leucêmicas humanas crescem em camundongos imunodeficientes. Eles perfilaram marcas de histonas e metilação do DNA em células de dez desses modelos e as trataram com um painel semelhante de epidrogas fora do organismo. Nesses exemplos, os padrões de histonas se agruparam em quatro clusters que em grande parte refletiam subtipos genéticos conhecidos e estados mais amplos de metilação do DNA, sugerindo que o perfil de histonas captura biologia relevante da doença. Mas, ao comparar novamente marcas de histonas com sensibilidade a drogas, as assinaturas das linhagens celulares não se traduziram. De fato, algumas relações inverteram de direção; a mesma marca H3K27me3 que sugeria sensibilidade à aclarubicina em placas foi ligada a menor sensibilidade nas células derivadas do modelo em camundongo.
Uma rede mutável em vez de um código fixo
Para entender essa discrepância, a equipe estudou como diferentes marcas de histonas sobem e descem em conjunto entre os modelos. Nas amostras derivadas de pacientes, muitas marcas se moveram em coordenação estreita, formando uma rede densa de correlações positivas, enquanto nas linhagens celulares essa rede era mais frouxa e fragmentada. Certas marcas ocupavam nós centrais dessas redes em um sistema, mas não no outro. Esses padrões sustentam a ideia de que as marcas de histonas operam como parte de uma linguagem dependente do contexto, em que o significado de uma marca depende de suas vizinhas e do ambiente celular. Crescimento prolongado em placa parece reconfigurar essa linguagem de maneiras que alteram como os padrões de histonas se relacionam com a resposta a drogas.
O que isso significa para o cuidado futuro da leucemia
Este trabalho delineia um quadro para usar espectrometria de massa para ler a paisagem rica das marcas de histonas na leucemia de células T e vinculá-las à forma como as células respondem a drogas epigenéticas. Também traz uma mensagem de cautela: resultados obtidos em linhagens celulares padrão podem não prever de forma confiável respostas em modelos mais realistas derivados de pacientes, quanto mais em pessoas. Para que biomarcadores baseados em histonas orientem tratamentos personalizados, os pesquisadores precisarão abraçar essa complexidade, focar em combinações de marcas e escolher cuidadosamente modelos de doença que reflitam a biologia dos pacientes o mais fielmente possível.
Citação: Corveleyn, L., Provez, L., Satilmis, O. et al. Profiling histone post-translational modifications to identify signatures of epigenetic drug response in T-cell acute lymphoblastic leukemia. Sci Rep 16, 15029 (2026). https://doi.org/10.1038/s41598-026-44665-4
Palavras-chave: leucemia linfoblástica aguda de células T, drogras epigenéticas, modificações de histonas, xenotransplantes derivados de pacientes, biomarcadores de resposta a drogas