Clear Sky Science · pl
Profilowanie potranslacyjnych modyfikacji histonów w celu identyfikacji sygnatur odpowiedzi na leki epigenetyczne w ostrej białaczce limfoblastycznej z komórek T
Dlaczego to badanie nowotworowe ma znaczenie
Leczenie dzieci i dorosłych z ostrą białaczką limfoblastyczną z komórek T znacznie się poprawiło, jednak wielu pacjentów wciąż doznaje nawrotów lub poważnych skutków ubocznych intensywnej chemioterapii. Lekarze potrzebują lepszych metod przewidywania, które leki zadziałają u konkretnego pacjenta. W tym badaniu sprawdzono, czy drobne chemiczne znaczniki na białkach pakujących DNA w komórkach białaczkowych mogą pomóc prognozować, jak te komórki zareagują na nowoczesne leki przeciwnowotworowe działające na mechanizmy epigenetyczne komórki.
Ukryty kod na białkach pakujących DNA
W każdej komórce białaczkowej DNA jest nawinięte na białka zwane histonami, tworząc zwartą strukturę zwaną chromatyną. Histony noszą wiele małych chemicznych znaczników, które działają jak przełączniki, pomagając włącząć lub wyłączyć geny bez zmiany samej sekwencji DNA. Ponieważ znaczniki te są odwracalne, stanowią atrakcyjne cele dla leków. Kilka takich „lekoopornych” leków epigenetycznych jest już stosowanych w nowotworach krwi, lecz ich rola w białaczce T pozostaje niejasna, a lekarzom brak prostych markerów pozwalających przewidzieć, kto skorzysta z terapii.
Odczytywanie wielu znaków histonowych naraz
Naukowcy rozbudowali wcześniejsze przedsięwzięcie, w którym zmapowali wyjściowy wzorzec znaczników histonowych w 21 liniach białaczki T przy użyciu spektrometrii mas, techniki pozwalającej jednocześnie zmierzyć setki modyfikacji. Następnie poddali te linie leczeniu dziewięcioma lekami: trzema standardowymi antracyklinami chemioterapeutycznymi, trzema inhibitorami histonowych deacetylaz oraz trzema inhibitorami enzymów metylujących DNA. Porównując przeżywalność komórek po leczeniu z początkowymi wzorcami histonowymi, poszukiwali „sygnatur” znaczników powiązanych z wrażliwością lub opornością na każdy lek.
Co ujawniły linie komórkowe
W komórkach hodowanych in vitro ujawniły się odrębne sygnatury histonowe. Dla antracyklin pewne represyjne markery, takie jak H3K27me3, miały tendencję do występowania w wyższych poziomach w liniach bardziej wrażliwych, podczas gdy inne markery, zwłaszcza kilka dimetylacji, wiązały się z gorszą odpowiedzią. W przypadku leków celujących w metylację DNA wysoki poziom niektórych dimetylacji ponownie wskazywał na oporność, podczas gdy markery acetylowe na ogonach histonów kojarzyły się z lepszą odpowiedzią. Inhibitory deacetylaz histonowych wykazywały słabsze różnicowanie między liniami wrażliwymi a opornymi, ale nadal pojawiały się pewne wzorce, w tym konkretne markery wzbogacone w komórkach najmniej lub najbardziej reagujących. Ogólnie te wyniki sugerowały, że to złożony krajobraz znaczników histonowych, a nie pojedynczy marker, niesie informację o tym, jak komórki białaczkowe reagują na leki epigenetyczne.
Weryfikacja pojedynczego znacznika
Ponieważ wcześniejsze prace sugerowały, że aclarubicyna działa szczególnie dobrze w komórkach bogatych w H3K27me3, zespół bezpośrednio przetestował ten pomysł. Użyli innego leku do zablokowania enzymu zapisującego ten znacznik i skutecznie obniżyli poziom H3K27me3 w kilku liniach białaczki T. Ku zaskoczeniu, nie zmieniło to wrażliwości komórek na aclarubicynę. Zaobserwowano też linie, które naturalnie miały wysoki H3K27me3, a mimo to były oporne. Pokazuje to, że nawet gdy pojedynczy znacznik histonowy koreluje z odpowiedzią na lek w niektórych warunkach, sam w sobie nie wystarcza, by wyjaśnić wrażliwość.
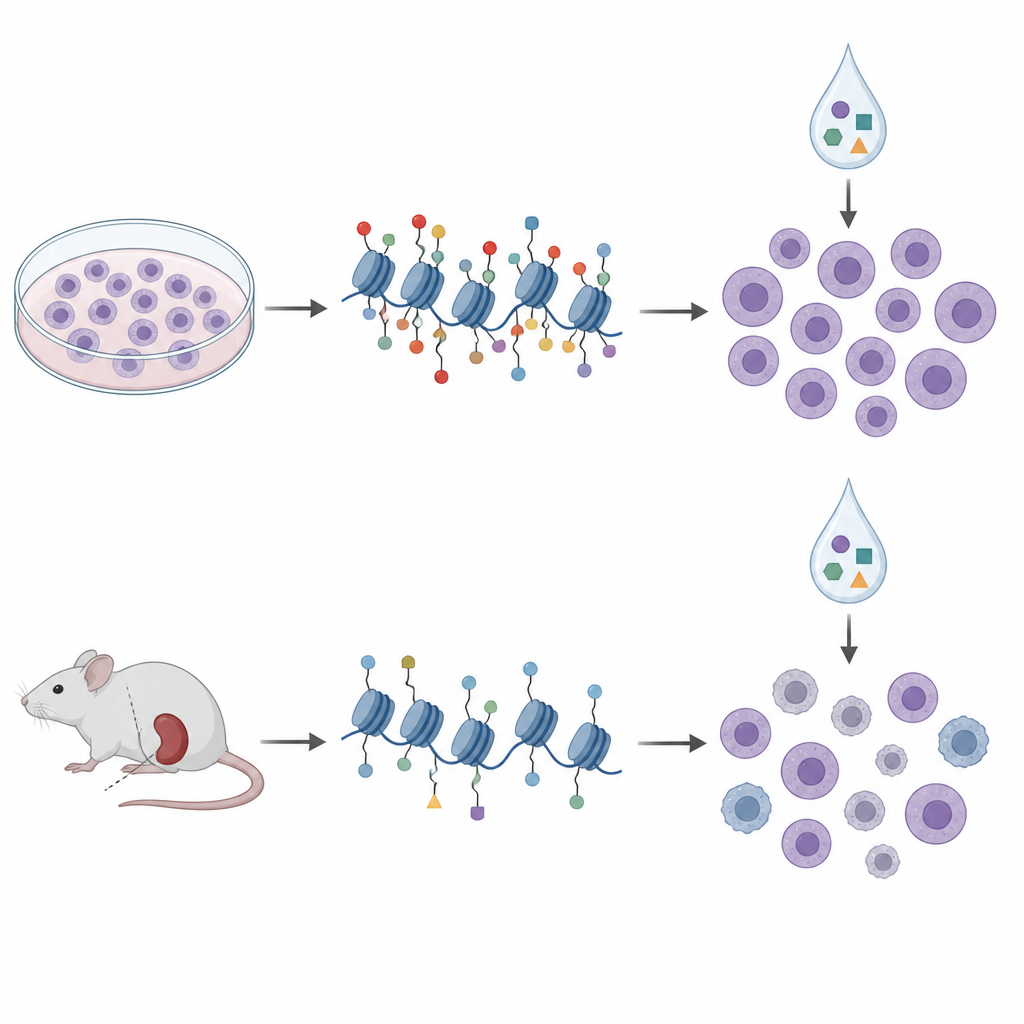
Z hodowli do modeli mysich
Aby zbliżyć się do warunków klinicznych, badacze sięgnęli po xenografty pochodzące od pacjentów (PDX), w których komórki białaczkowe pacjentów rosną w myszach o upośledzonym układzie odpornościowym. Zprofilowali markery histonowe i metylację DNA w komórkach z dziesięciu takich modeli i potraktowali je podobnym zestawem leków epigenetycznych poza organizmem. W tych próbkach wzorce histonowe skupiły się w cztery klastry, które w dużej mierze odzwierciedlały znane podtypy genetyczne i szerokie stany metylacji DNA, co sugeruje, że profilowanie histonów uchwytuje istotną biologię choroby. Jednak gdy ponownie porównano markery histonowe z wrażliwością na leki, sygnatury z linii komórkowych nie przeniosły się. W rzeczywistości niektóre relacje odwróciły się; ten sam znacznik H3K27me3, który sugerował wrażliwość na aclarubicynę w hodowlach, wiązał się z niższą wrażliwością w komórkach pochodzących od myszy.
Dynamiczna sieć zamiast stałego kodu
Aby zrozumieć tę rozbieżność, zespół przeanalizował, jak różne markery histonowe wspólnie wzrastają i opadają w modelach. W próbkach pochodzących od pacjentów wiele znaczników poruszało się w ścisłej koordynacji, tworząc gęstą sieć pozytywnych korelacji, podczas gdy w liniach komórkowych sieć ta była luźniejsza i bardziej rozfragmentowana. Pewne markery zajmowały pozycje centralne w tych sieciach w jednym systemie, ale nie w drugim. Te obserwacje wspierają ideę, że znaczniki histonowe funkcjonują jako część kontekstowo zależnego języka, gdzie sens pojedynczego znacznika zależy od jego sąsiadów i środowiska komórkowego. Długotrwały wzrost w hodowli wydaje się przeprogramowywać ten język w sposób zmieniający związki między wzorcami histonowymi a odpowiedzią na leki.
Co to znaczy dla przyszłej opieki nad białaczką
Praca ta przedstawia ramy wykorzystania spektrometrii mas do odczytywania bogatego krajobrazu znaczników histonowych w białaczce T i łączenia ich z odpowiedzią na leki epigenetyczne. Przynosi też ostrzeżenie: wyniki uzyskane na standardowych liniach komórkowych mogą nie przewidywać wiarygodnie reakcji w bardziej realistycznych modelach pochodzących od pacjentów, a tym bardziej u ludzi. Aby biomarkery oparte na histonach mogły napędzać spersonalizowane terapie, badacze będą musieli uwzględnić tę złożoność, skupić się na kombinacjach znaczników oraz starannie wybierać modele choroby oddające biologię pacjentów jak najwierniej.
Cytowanie: Corveleyn, L., Provez, L., Satilmis, O. et al. Profiling histone post-translational modifications to identify signatures of epigenetic drug response in T-cell acute lymphoblastic leukemia. Sci Rep 16, 15029 (2026). https://doi.org/10.1038/s41598-026-44665-4
Słowa kluczowe: ostra białaczka limfoblastyczna z komórek T, leki epigenetyczne, modyfikacje histonów, pasywne szczepy pochodzące od pacjentów, biomarkery odpowiedzi na leki