Clear Sky Science · it
Profiling delle modificazioni post-traduzionali degli istoni per identificare firme di risposta agli epigenetici nella leucemia linfoblastica acuta T
Perché questo studio sul cancro è importante
Il trattamento per bambini e adulti con leucemia linfoblastica acuta a cellule T è molto migliorato, ma molti pazienti vanno ancora incontro a recidive o subiscono effetti collaterali gravi a causa della chemioterapia intensa. I medici hanno bisogno di modi migliori per prevedere quali terapie funzioneranno per ciascun paziente. Questo studio esplora se piccole etichette chimiche sulle proteine che impacchettano il DNA nelle cellule leucemiche possano aiutare a prevedere come quelle cellule rispondono ai farmaci antitumorali moderni che agiscono sulla macchina epigenetica della cellula.
Il codice nascosto sull’impacchettamento del DNA
All’interno di ogni cellula leucemica, il DNA è avvolto attorno a proteine chiamate istoni, formando una struttura compatta nota come cromatina. Gli istoni portano molte piccole etichette chimiche che agiscono come interruttori, aiutando ad attivare o spegnere i geni senza modificare la sequenza del DNA. Poiché questi segni sono reversibili, rappresentano bersagli attraenti per i farmaci. Diversi di questi “epidrug” sono già impiegati nelle emopatie, ma il loro ruolo nella leucemia T è ancora poco chiaro e i clinici non dispongono di marcatori semplici per prevedere chi ne trarrà beneficio.
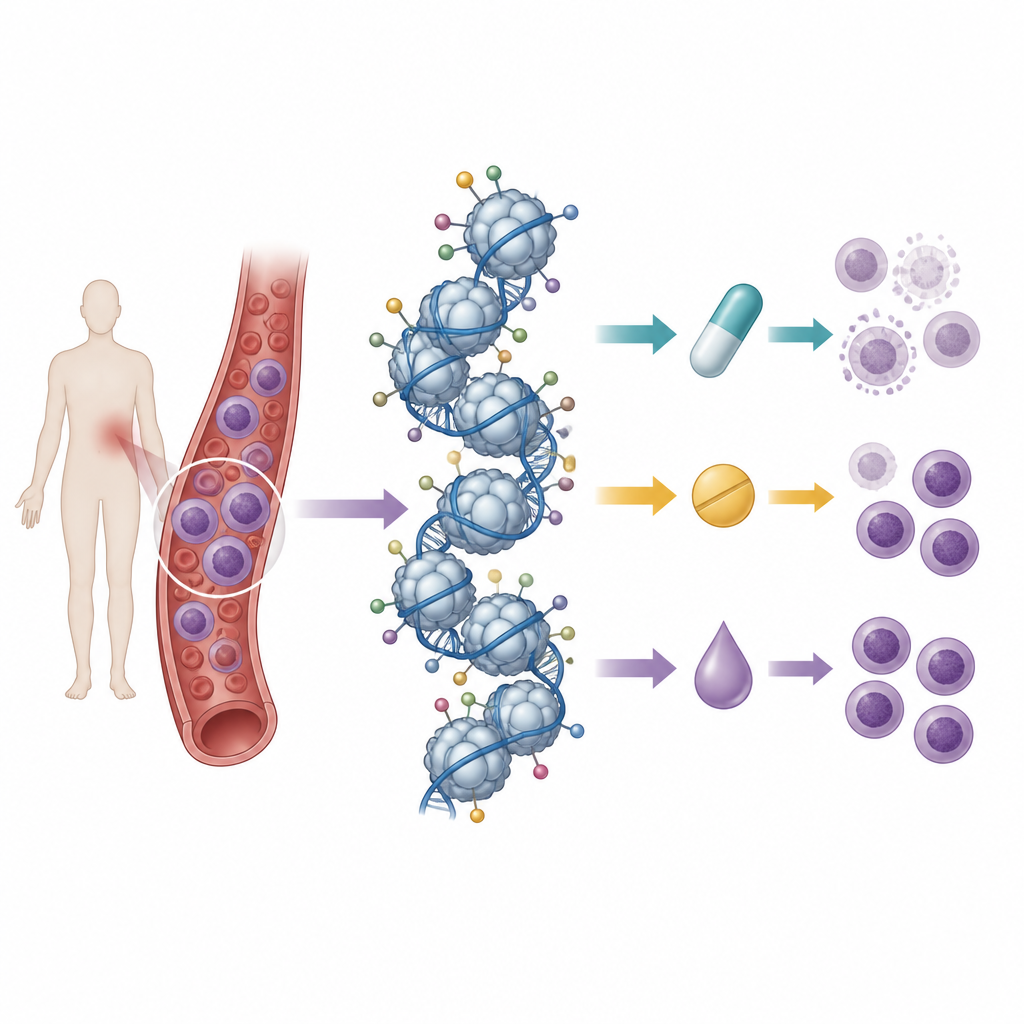
Leggere molti marcatori istonici contemporaneamente
I ricercatori si sono basati su un lavoro precedente in cui avevano mappato il profilo di base dei segni istonici in 21 linee cellulari di leucemia T usando la spettrometria di massa, una tecnica che può misurare centinaia di modificazioni chimiche contemporaneamente. Hanno poi trattato queste linee cellulari con nove farmaci: tre antracicline chemioterapiche standard, tre inibitori delle deacetilasi istoniche e tre inibitori delle DNA metiltransferasi. Confrontando la sopravvivenza cellulare dopo il trattamento con i pattern istonici iniziali, hanno cercato «firme» di segni che si associassero a sensibilità o resistenza a ciascun farmaco.
Ciò che hanno rivelato le linee cellulari
Nelle colture cellulari sono emerse firme istoniche distintive. Per le antracicline, alcuni marcatori repressivi, come H3K27me3, tendevano a essere più elevati nelle linee più sensibili, mentre altri segni, in particolare diverse dimetilazioni, erano associati a risposta peggiore. Per i farmaci che mirano alla metilazione del DNA, alti livelli di alcune dimetilazioni indicavano nuovamente resistenza, mentre i marcatori di acetilazione sulle code degli istoni si associavano a migliore risposta. Gli inibitori delle deacetilasi istoniche mostrarono una separazione più debole tra linee sensibili e resistenti, ma emersero comunque alcuni pattern, inclusi marcatori specifici arricchiti nelle cellule meno o più reattive. Nel complesso, questi risultati suggeriscono che il paesaggio combinato dei segni istonici, più che un singolo marcatore, contiene informazioni su come le cellule leucemiche rispondono agli epigenetici.
Mettere alla prova un singolo marcatore
Poiché lavori precedenti avevano suggerito che l’aclarubicina funzionasse particolarmente bene in cellule ricche del marcatore H3K27me3, il gruppo ha testato direttamente questa ipotesi. Hanno usato un altro farmaco per bloccare l’enzima che scrive questo marcatore e sono riusciti ad abbassare H3K27me3 in diverse linee di leucemia T. Sorprendentemente, ciò non ha modificato la sensibilità delle cellule all’aclarubicina. Hanno inoltre osservato linee cellulari che presentavano naturalmente alti livelli di H3K27me3 ma risultavano resistenti. Questo dimostra che, anche quando un singolo segno istonico si associa alla risposta in alcuni contesti, non è sufficiente da solo a spiegare la sensibilità.
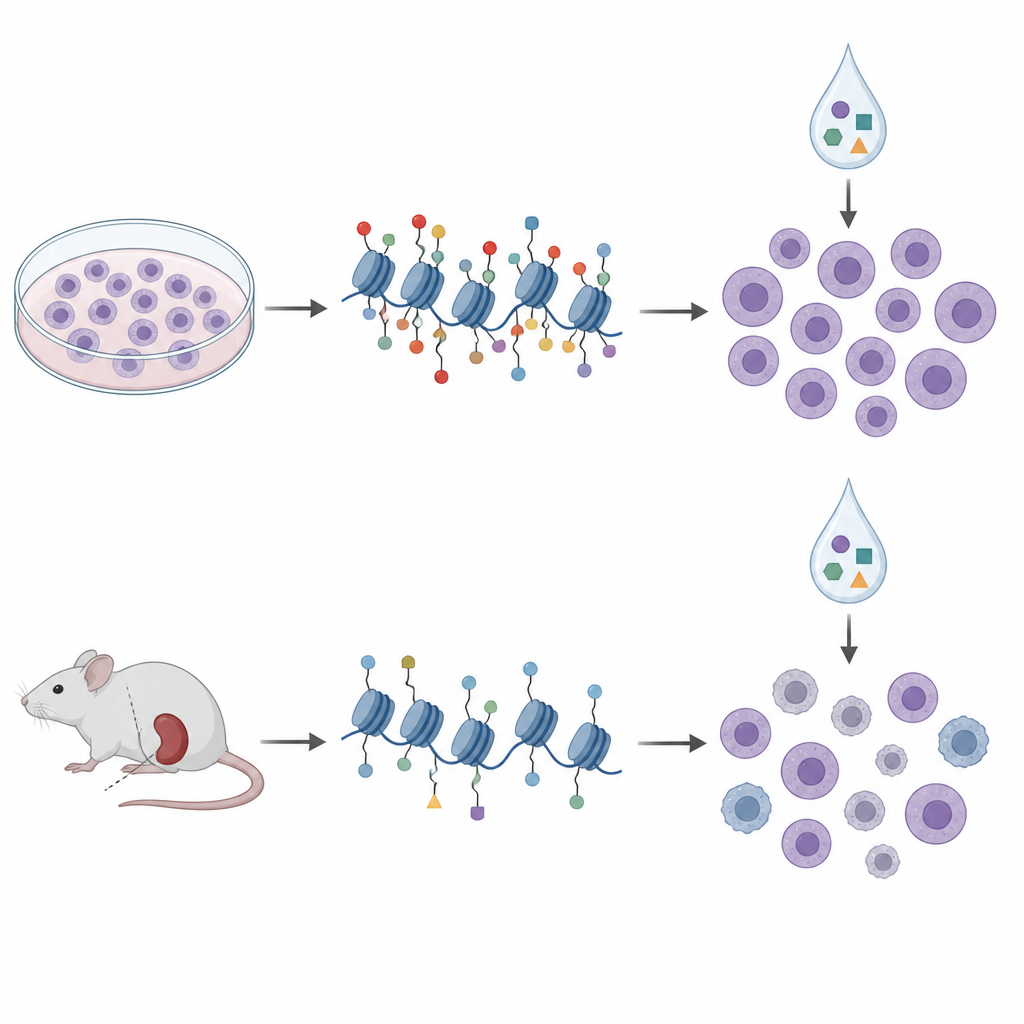
Dalle piastre ai modelli murini
Per avvicinarsi alla clinica, i ricercatori si sono rivolti ai xenotrapianti derivati da pazienti, in cui le cellule leucemiche umane crescono in topi immunodeficienti. Hanno profilato i segni istonici e la metilazione del DNA in cellule provenienti da dieci di questi modelli e le hanno trattate con un pannello simile di farmaci epigenetici ex vivo. In questi campioni, i pattern istonici si raggrupparono in quattro cluster che rispecchiavano in larga parte i sottotipi genetici noti e gli stati più ampi di metilazione del DNA, suggerendo che il profiling degli istoni cattura aspetti biologici rilevanti della malattia. Ma quando hanno nuovamente confrontato i marcatori istonici con la sensibilità ai farmaci, le firme trovate nelle linee cellulari non si sono replicate. Anzi, alcune relazioni si invertirono; lo stesso H3K27me3 che indicava sensibilità all’aclarubicina nelle colture risultava associato a minore sensibilità nelle cellule derivate dai topi.
Una rete che cambia più che un codice fisso
Per capire questo disallineamento, il team ha studiato come diversi marcatori istonici aumentano e diminuiscono insieme nei vari modelli. Nei campioni derivati da pazienti, molti segni si muovevano in stretta coordinazione, formando una densa rete di correlazioni positive, mentre nelle linee cellulari questa rete era più lassa e frammentata. Alcuni marcatori occupavano nodi principali di queste reti in un sistema ma non nell’altro. Questi pattern supportano l’idea che i segni istonici operino come parte di un linguaggio dipendente dal contesto, in cui il significato di un singolo segno dipende dai vicini e dall’ambiente cellulare. La crescita prolungata in coltura sembra riorganizzare questo linguaggio in modi che modificano il rapporto tra i pattern istonici e la risposta ai farmaci.
Cosa significa per la cura futura della leucemia
Questo lavoro delinea un quadro per utilizzare la spettrometria di massa per leggere il ricco paesaggio dei segni istonici nella leucemia T e collegarli alla risposta agli epigenetici. Fornisce anche un avvertimento: i risultati ottenuti con le linee cellulari standard potrebbero non prevedere in modo affidabile le risposte in modelli più realistici derivati dai pazienti, e men che meno negli esseri umani. Perché i biomarcatori basati sugli istoni guidino trattamenti personalizzati, i ricercatori dovranno abbracciare questa complessità, concentrarsi su combinazioni di marcatori e scegliere con attenzione modelli di malattia che riflettano il più possibile la biologia dei pazienti.
Citazione: Corveleyn, L., Provez, L., Satilmis, O. et al. Profiling histone post-translational modifications to identify signatures of epigenetic drug response in T-cell acute lymphoblastic leukemia. Sci Rep 16, 15029 (2026). https://doi.org/10.1038/s41598-026-44665-4
Parole chiave: leucemia linfoblastica acuta a cellule T, farmaci epigenetici, modificazioni degli istoni, xenotrapianti derivati da pazienti, biomarcatori di risposta ai farmaci