Clear Sky Science · nl
Onderzoek naar moleculaire mechanismen van aminoglycoside‑resistentie in Escherichia coli MG1655 met behulp van de antibioticum‑resistentiegroeiplaat
Waarom snel veranderende ziekteverwekkers iedereen aangaan
Antibiotica hebben talloze levens gered, maar bacteriën leren gestaag hoe ze eraan kunnen ontkomen. Dit artikel onderzoekt hoe gewone darmbacteriën, Escherichia coli, binnen slechts enkele dagen resistentie kunnen ontwikkelen tegen een veelgebruikt antibioticum, gentamicine. Door resistentie te volgen op een speciaal ontworpen groeiplaat en vervolgens het DNA en de moleculaire structuren van de bacteriën te onderzoeken, onthullen de onderzoekers nieuwe details over hoe deze microben het middel te slim af kunnen zijn. Hun bevindingen helpen verklaren waarom resistentie zo snel kan ontstaan en wijzen op instrumenten die kunnen voorspellen welke behandelingen waarschijnlijk zullen falen.
Een nieuwe plaat om evolutie in actie te volgen
Om resistentie zichtbaar te maken tijdens het ontstaan, bouwde het team wat zij de Antibiotic Resistance Growth Plate (ARGP) noemen. Stel je een petrischaal voor die verdeeld is in drie concentrische banden: geen middel in het centrum, een matige dosis in de middelste ring, en een zeer hoge dosis rondom de rand. Ze beplaatsten het centrum met een standaard, middelgevoelige stam van E. coli en lieten de bacteriën naar buiten zwemmen door een dunne, semi‑vaste laag. Terwijl de microben zich verspreidden, kwamen ze steeds hogere gentamicineconcentraties tegen. De meesten werden gestopt bij de grenzen tussen zones, maar af en toe slaagden kleine uitlopers erin in de volgende ring door te dringen en verder te groeien. Binnen slechts twee tot drie dagen floreerden sommige lijnen in antibioticaconcentraties die tien keer hoger waren dan de minimumconcentratie die de oorspronkelijke stam stopte. 
Het volgen van de genetische veranderingen achter overleving
Het verschijnen van resistente kolonies was nog maar het begin. De wetenschappers verzamelden cellen uit deze taaie uitlopers en vergeleken hun volledige DNA‑sequentie met die van de oorspronkelijke stam. Na zorgvuldige filtering van artefacten en verontreinigende fragmenten richtten ze zich op veranderingen in genen die bekendstaan om hun rol bij eiwitsynthese binnen de cel. Ze vonden mutaties in delen van de genetische code die de eiwitproducerende machinerie van de cel bouwen: meerdere kopieën van het 16S‑ribosomaal RNA‑gen en een gen genaamd fusA, dat codeert voor een sleutelhulpstof‑eiwit bekend als EF‑G. Beide doelwitten zijn logisch omdat gentamicine werkt door zich vast te hechten aan het bacteriële ribosoom, het complex dat genetische instructies afleest en nieuwe eiwitten aan elkaar zet. Elke aanpassing die deze machinerie verandert zonder haar geheel te vernietigen, kan het effect van het middel verzwakken.
Hoe één scharnierverandering het middel verzwakt
De meest opvallende wijziging was een éénletterverandering in het fusA‑gen die één aminozuur — proline — vervangt door een ander — threonine — op positie 610 in het EF‑G‑eiwit. EF‑G fungeert als een beweegbare arm die helpt transfer‑RNA’s en boodschapper‑RNA door het ribosoom te verplaatsen terwijl elk nieuw eiwit wordt opgebouwd. Met computermodellen van EF‑G’s driedimensionale structuur toonde het team aan dat die positie ligt op een scharnier tussen twee domeinen van EF‑G, waar het eiwit buigt en draait terwijl het het ribosoom voortduwt. De proline op dit scharnier blijkt opvallend sterk geconserveerd te zijn bij veel verwante bacteriën, wat wijst op zijn belang. Wanneer deze wordt vervangen, veranderen de algehele flexibiliteit en compactheid van EF‑G, waardoor de pasvorm tegen het ribosoom subtiel wordt herschikt. Dockingsimulaties die gentamicine virtueel plaatsen op ribosoom–EF‑G‑complexen suggereren dat deze kleine structurele verschuiving de geometrie van het bindingsgebied van het middel wijzigt. In de gemuteerde vorm kan gentamicine het ribosoom niet langer vastzetten in de kwetsbare fase waarin het normaal beweging blokkeert.
Kleine verschuivingen in RNA‑structuur met grote gevolgen
Ook ontstonden mutaties in twee van de meerdere 16S‑rRNA‑genkopieën die de kleinere helft van het ribosoom helpen vormen. Door deze veranderingen in kaart te brengen op bekende RNA‑structuren, vonden de auteurs dat ze allemaal clusterden in het “5′ body”‑gebied, dicht bij waar gentamicine en een naburig ribosomaal eiwit normaal binden. Gedetailleerde computervoorspellingen lieten zien dat de algehele RNA‑vouwing grotendeels behouden bleef, maar dat lokale lussen en helixen nabij de gemuteerde basen subtiel waren herschikt. Deze kleine structurele aanpassingen zijn voldoende om te veranderen hoe het RNA met zowel ribosomale eiwitten als het middel interageert, en kunnen kritieke basen iets wegnudgen van de precieze posities die gentamicine nodig heeft voor strakke binding. Gecombineerd met de EF‑G‑scharniermutatie resulteert dit in een ribosoom dat blijft aflezen, zelfs in aanwezigheid van hoge middelconcentraties. 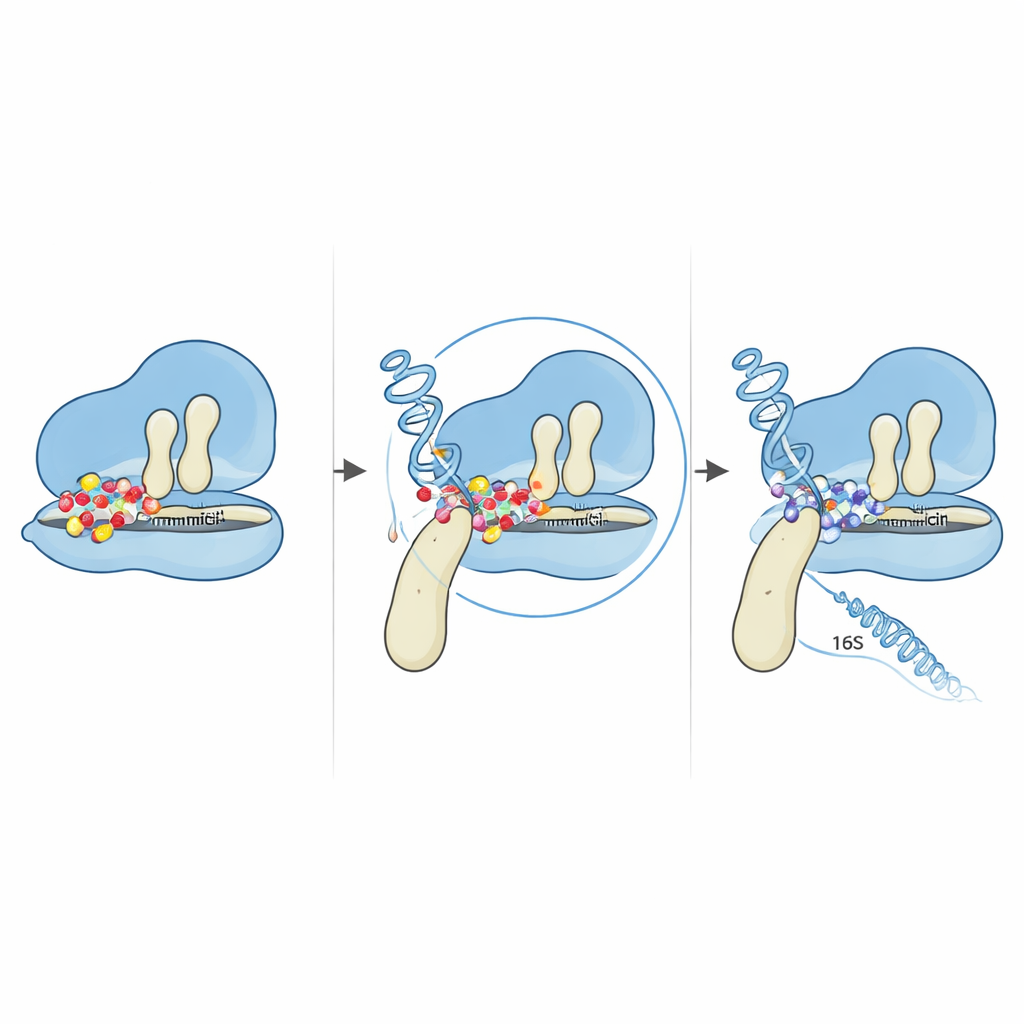
Wat dit betekent voor het bestrijden van resistentie
Gezamenlijk laten de resultaten zien dat E. coli snel een zeer specifieke verdediging tegen gentamicine kan samenstellen door zowel de aanlegplaats van het middel op het ribosomale RNA als een bewegend onderdeel van de eiwitmotor die translatie aandrijft te wijzigen. Deze veranderingen vernietigen de eiwitfabriek niet; ze stellen haar net genoeg bij zodat het antibioticum de werking niet meer kan blokkeren. Het ARGP‑systeem biedt een eenvoudige, visuele manier om dergelijke resistentie‑paden onder gecontroleerde omstandigheden te genereren en te bestuderen, en kan worden aangepast aan andere middelen en pathogenen. Voor niet‑specialisten is de kernboodschap dat resistentie geen vaag, traag fenomeen is — het kan snel ontstaan door precieze moleculaire aanpassingen. Het in detail begrijpen van die aanpassingen is essentieel als we nieuwe antibiotica en behandelingsstrategieën willen ontwerpen die een stap voorblijven op evoluerende bacteriën.
Bronvermelding: Cullen, L., Eldridge, C., Jones, B. et al. Exploring molecular mechanisms of aminoglycoside resistance in Escherichia coli MG1655 using the antibiotic resistance growth plate. Sci Rep 16, 11958 (2026). https://doi.org/10.1038/s41598-026-41386-6
Trefwoorden: antibioticaresistentie, gentamicine, Escherichia coli, ribosoom, experimentële evolutie