Clear Sky Science · tr
STHELAR: mekânsal transkriptomik ile histoloji arasında hücre tipi açıklamasını bağlayan çok dokulu bir veri seti
Neden kanseri mikroskopla görmek tek başına yeterli değil
Onkoloji uzmanları hâlâ büyük ölçüde mikroskop altında gördüklerine güveniyor: hematoksilin ve eozin (H&E) ile boyanmış ince dilimlenmiş, pembemsi‑mor doku görüntüleri. Bu görüntüler şekil ve desenleri ortaya koyar, ancak her hücrenin içinde hangi genlerin aktif olduğunu doğrudan gösteremez. STHELAR adlı yeni bir kaynak bu iki dünyayı bir araya getiriyor; doku lamlarının tanıdık görünümünü gen aktivitesinin en yeni “mekânsal” ölçümleriyle ilişkilendiriyor. Okuyucular için bunun önemi, bir gün sıradan dijital görüntülerden yalnızca moleküler yapı hakkında daha hızlı ve daha ucuz araçların geliştirilebilmesinin yolunu açmasıdır.
Tümörü kalabalık bir mahalle olarak görmek
Tümörler yalnızca kontrolsüz kanser hücrelerinden ibaret değildir; bağışıklık hücreleri, kan damarları, destek hücreleri ve normal doku ile dolu kalabalık mahallelerdir. Bu bileşenlerin karışımı ve düzeni—tümör mikroçevresi—kanserin nasıl büyüdüğünü ve tedaviye nasıl yanıt verdiğini şekillendirebilir. Mekânsal transkriptomik, hangi genlerin bireysel hücrelerde açıldığını dokudaki konumlarını koruyarak haritalayabilen yeni bir teknolojidir. Ancak bu deneyler maliyetli ve teknik olarak zordur, bu yüzden henüz rutin bakımın parçası değildir. Buna karşın H&E lamlarının yüksek çözünürlüklü taramaları artık yaygın, saklaması ucuz ve dünya çapında kullanılıyor. STHELAR’ın temel fikri, standart H&E görüntülerinde görülen milyonlarca hücre için sınırlı sayıda mekânsal transkriptomik deneyini “öğretmen” olarak kullanmaktır.
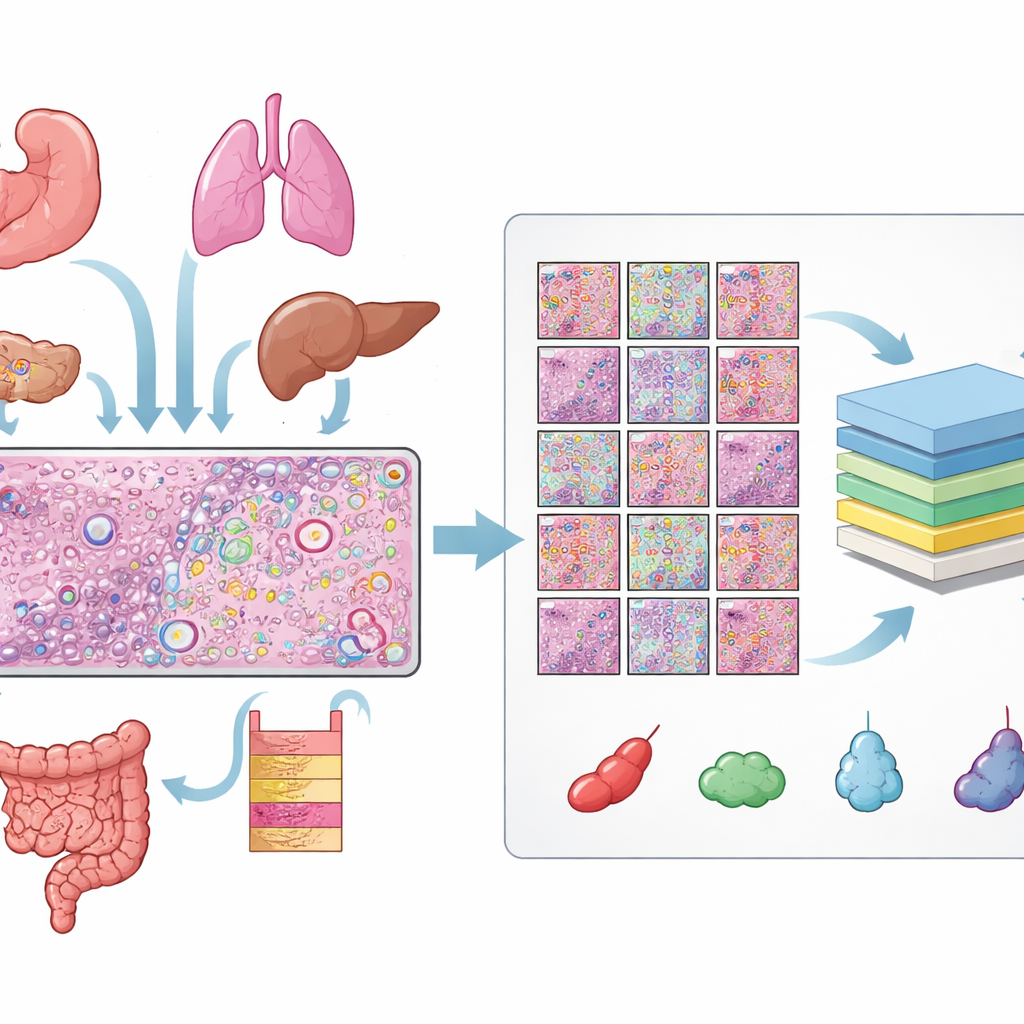
Etiketlenmiş büyük bir hücre kütüphanesi oluşturmak
Yazarlar, 10x Genomics’in Xenium mekânsal transkriptomik platformuyla ölçülmüş 31 doku kesitinden veri topladı; bunlar 16 insan doku türünü ve 22 kanser ile 9 kanser olmayan örneği kapsıyordu. Her kesit için üç eşleştirilmiş görüntü vardı: bir H&E lamı, hücre çekirdeklerini gösteren bir floresan görüntü ve bireysel RNA moleküllerinin bir haritası. Bu görüntüleri hizalamak dikkatli kalite kontrolleri gerektirdi ve birçok lam için floresan görüntüsündeki her çekirdeğin H&E lamındaki karşılık gelen yapıyla örtüşmesi için elle ince ayar yapıldı. Bu hizalanmış görüntülerden 11 milyondan fazla ayrı hücre ve her birinde her çekirdeğin hassas dış hatlarıyla birlikte yarım milyondan fazla küçük H&E yaması elde ettiler.
Bilgisayara her hücre tipinin ne olduğunu öğretmek
Hücrelerin nerede olduğu bilinmesi yeterli değil; asıl önemli adım hangi tür hücre olduklarını belirlemektir. Bunu yapmak için ekip mekânsal transkriptomikleri mevcut büyük tek hücre RNA kataloglarıyla birleştirdi. Tangram adı verilen bir yöntemle önce bu referans atlaslardan mekânsal verilere muhtemel hücre kimliklerini aktardılar. Ardından bu ön etiketleri, hücreleri gen aktivitelerine göre kümelere ayırıp hangi genlerin her kümeyi ayırt ettiğini inceleyerek geliştirdiler. Marker genler ile Tangram uyum gösterdiğinde etiketler kabul edildi; uyuşmadıklarında dokudaki yerel gen desenleri öncelik kazandı. Son olarak, sonuçları epitelyal, kan damarı, bağışıklık hücre grupları, fibroblastlar, melanositler ve genel bir “diğer” grubu gibi on geniş kategoriye uyumlu hale getirdiler. Bir patolog, etiketlerin biyolojik açıdan anlamlı olduğunu doğrulamak için H&E görüntüleri üzerinde sonuçları görsel olarak inceledi.
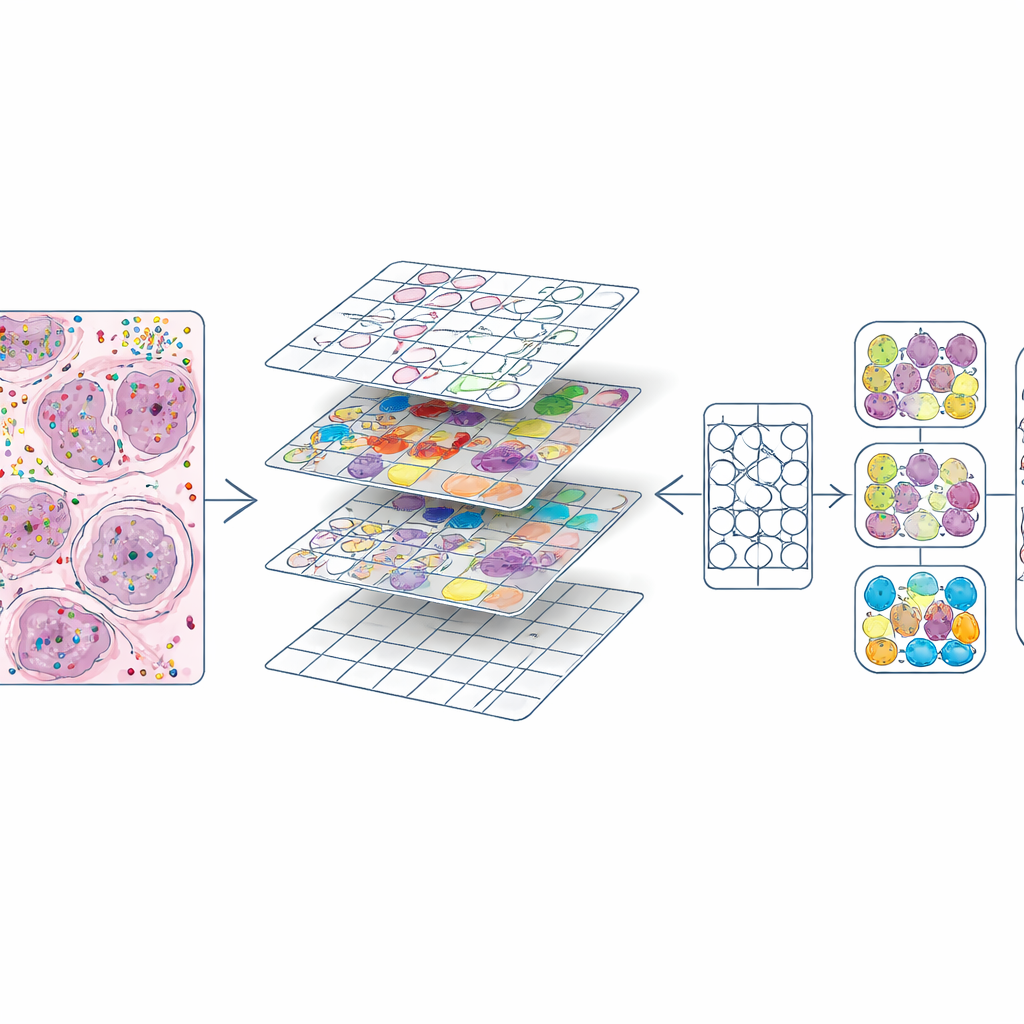
Zengin moleküler haritaları eğitim materyaline dönüştürmek
Her hücrenin hem konumu hem de tipi belirlendikten sonra yazarlar her H&E lamını küçük karelere böldü; bunlar fotoğraf düzenleme programlarındaki görüntü karolarına benziyordu. Her karoya iki temel bileşen ürettiler: her çekirdeği çevreleyen bir maske ve hücre tipini gösteren bir renk kodu. Bu, yüksek büyütmede yaklaşık 587.000 karo ve daha düşük büyütmede biraz daha küçük bir set oluşturdu. Ayrıca çekirdek dış hatlarını mevcut bir derin öğrenme modeli (CellViT) tarafından otomatik üretilenlerle karşılaştırıp uyum skorları hesapladılar; böylece gelecekteki kullanıcılar daha düşük kaliteli bölgeleri filtreleyebilecek. Tüm bu bilgiler—görüntüler, maskeler, gen sayıları, hücre etiketleri ve kalite skorları—araştırmacıların veri setini kolayca keşfetmesi veya yeniden kullanması için standartlaştırılmış veri nesneleri halinde paketlenmiştir.
Bilgisayarların yeni atlasdan öğrenebileceğini göstermek
STHELAR’ın neler mümkün kıldığını göstermek için ekip, H&E görüntülerinde hücre segmentasyonu ve sınıflandırması için tasarlanmış güçlü bir görsel dönüştürücü olan CellViT modelini ince ayarladı. STHELAR etiketlerini gerçek değer (ground truth) olarak kullanarak modeli dokuz ayrıntılı hücre sınıfını ve ikinci bir deneyde daha geniş beş grubu (örneğin birkaç bağışıklık hücresi tipini birleştirerek) tanımak üzere eğittiler. İnce ayarlı model çekirdekleri tespit etme ve dış hatlarını belirlemede güçlü performansını korudu ve epitelyal hücreler ile melanositler gibi görsel olarak ayırt edilebilir hücrelerde iyi doğruluk sağladı; daha ince ayrımlı bağışıklık alt tipleri ise hâlâ zorlukluydu. Ayrıca açıklamalarını bağımsız bir etiketleme yöntemi (SingleR) ve RNA tabanlı alternatif modellerle karşılaştırdılar ve genel olarak iyi uyum buldular.
Geleceğin kanser tanısı için bunun anlamı
STHELAR tek bir algoritmadan çok bir referans atlasıdır: patologların standart H&E lamlarında gördükleri ile mekânsal transkriptomiklerin her hücrede ortaya koyduğu gen aktivitesi arasında açık bir, geniş ölçekli bağlantı. Uzman olmayanlar için çıkarılacak nokta, bu kaynağın rutin görüntülerden doğrudan tümörlerin hücresel bileşimini çıkarabilen bilgisayar modellerini eğitmeyi ve test etmeyi çok daha kolay hale getirmesidir; her hasta için pahalı moleküler testler çalıştırmaya gerek kalmayabilir. Bu tür modeller geliştikçe, sıradan lamlardan tümörlerin içindeki görünmez moleküler “konuşmayı” okumada doktorlara yardımcı olabilir ve daha kesin tanılar ile daha iyi uyarlanmış tedavileri destekleyebilir.
Atıf: Giraud-Sauveur, F., Blampey, Q., Benkirane, H. et al. STHELAR, a multi-tissue dataset linking spatial transcriptomics and histology for cell type annotation. Sci Data 13, 665 (2026). https://doi.org/10.1038/s41597-026-06937-6
Anahtar kelimeler: tümör mikroçevresi, mekânsal transkriptomik, histopatoloji görüntülemesi, hücre tipi açıklaması, kanserde derin öğrenme