Clear Sky Science · ru
STHELAR — многотканевой набор данных, связывающий пространственную транскриптомику и гистологию для аннотации типов клеток
Почему смотреть на рак под микроскопом недостаточно
Онкологи по-прежнему во многом полагаются на то, что видно под микроскопом: тонкие срезы ткани, окрашенные гематоксилином и эозином (H&E), с характерными розово‑фиолетовыми оттенками. Эти изображения показывают формы и рисунки, но не дают прямой информации о том, какие гены активны в каждой клетке. Новый ресурс STHELAR объединяет оба подхода, связывая привычный вид срезов ткани с передовыми «пространственными» измерениями активности генов. Для читателя это важно, потому что такая работа открывает путь к более быстрым и дешёвым инструментам, которые однажды смогут определять молекулярный состав опухолей по обычным цифровым изображениям.
Рассматривать опухоль как переполненный район
Опухоли — это не просто разбушевавшиеся раковые клетки; это густонаселённые «районы», наполненные иммунными клетками, сосудами, поддерживающими клетками и нормальной тканью. Состав и расположение этих обитателей — микросреда опухоли — влияют на рост рака и ответ на лечение. Пространственная транскриптомика позволяет картировать, какие гены включены в отдельных клетках, сохраняя их точное положение в ткани. Однако такие эксперименты дороги и технически сложны, поэтому ещё не стали рутиной. Напротив, высокоразрешающие сканы H&E-срезов теперь повсеместно доступны, недороги в хранении и широко используются. Центральная идея STHELAR — использовать ограниченное число экспериментов по пространственной транскриптомике как «учителя» для миллионов клеток, видимых на стандартных H&E‑изображениях.
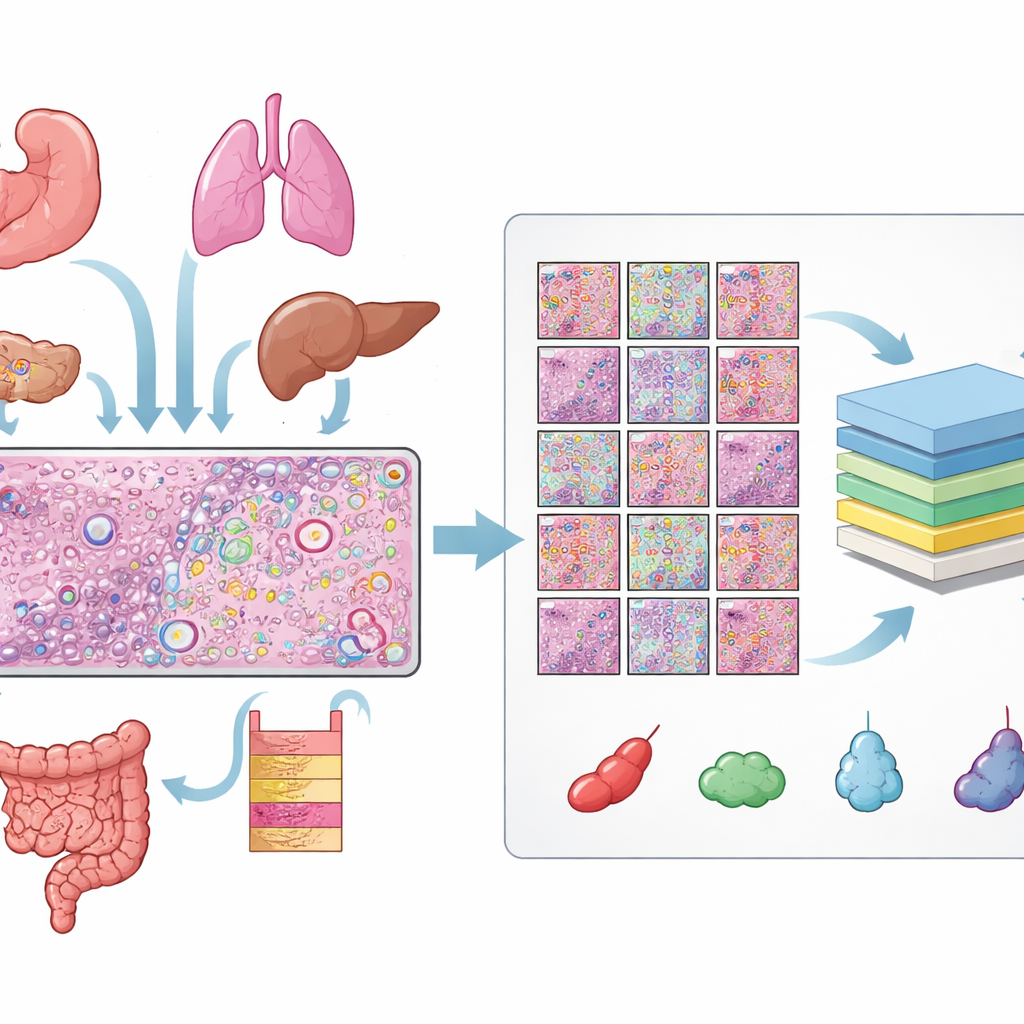
Создание огромной библиотеки размеченных клеток
Авторы собрали данные из 31 среза ткани, измеренного на платформе пространственной транскриптомики Xenium компании 10x Genomics, охватив 16 типов человеческих тканей и 22 образца опухолей и 9 неонкологических образцов. Для каждого среза у них были три согласованных вида: H&E‑слайд, флуоресцентное изображение, показывающее ядра клеток, и карта отдельных молекул РНК. Выровнять эти виды потребовало тщательной проверки качества и, для многих слайдов, ручной донастройки так, чтобы каждое ядро на флуоресцентном изображении совпадало с соответствующей структурой на H&E. Из этих согласованных изображений получили более 11 миллионов различных клеток и более полумиллиона небольших фрагментов H&E, каждый с точными контурами каждого ядра.
Обучение компьютера распознавать типы клеток
Положение клетки само по себе недостаточно; ключевой шаг — определить, какого она типа. Для этого команда объединила пространственную транскриптомику с большими существующими каталогами профилей РНК отдельных клеток. С помощью метода Tangram они сначала перенесли вероятные идентичности клеток из этих эталонных атласов на пространственные данные. Затем они улучшили предварительные метки, группируя клетки в кластеры по активности генов и исследуя, какие гены отличают каждый кластер. Когда маркерные гены и Tangram совпадали, метки принимались; при расхождении приоритет отдавался локальным генным паттернам в ткани. Наконец, результаты были согласованы между всеми слайдами в десять широких категорий, таких как эпителиальные клетки, сосудистые клетки, группы иммунных клеток, фибробласты, меланоциты и универсальная категория «прочее». Патолог визуально проверял результаты на H&E‑изображениях, чтобы убедиться, что метки биологически осмысленны.
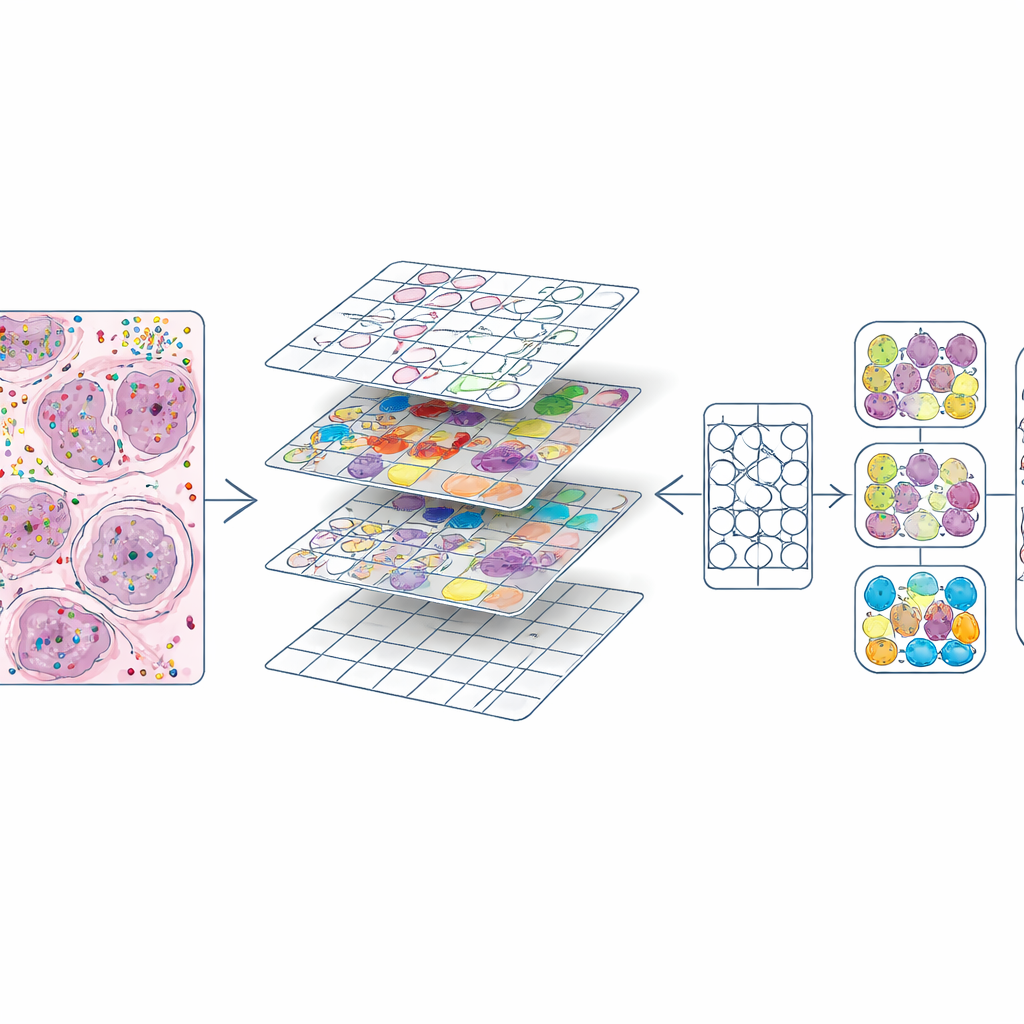
Преобразование богатых молекулярных карт в учебный материал
Когда у каждой клетки были и положение, и тип, авторы разрезали каждый H&E‑слайд на маленькие квадраты, подобные плиткам изображения в графическом редакторе. Для каждой плитки они сгенерировали два ключевых компонента: маску, очерчивающую каждое ядро, и цветовую кодировку, указывающую тип клетки. Это дало около 587 000 плиток при высоком увеличении и немного меньший набор при низком увеличении. Они также сравнили свои контуры ядер с теми, что автоматически сгенерированы существующей моделью глубокого обучения (CellViT), и рассчитали коэффициенты согласия, позволяющие будущим пользователям отфильтровывать участки низкого качества. Вся эта информация — изображения, маски, подсчёты генов, метки клеток и оценки качества — упакована в стандартизованные объекты данных, чтобы исследователи могли легко исследовать или повторно использовать набор данных.
Доказательство того, что компьютеры могут учиться по новому атласу
Чтобы продемонстрировать возможности STHELAR, команда дообучила модель CellViT, мощный визуальный трансформер, предназначенный для сегментации и классификации клеток на H&E‑изображениях. Используя метки STHELAR как эталон, они обучили модель распознавать девять детализированных классов клеток и, в другом эксперименте, пять более широких групп (например, объединяя несколько типов иммунных клеток). Дообученная модель сохранила высокую эффективность в обнаружении и обрисовывании ядер и показала хорошую точность для визуально отличимых клеток, таких как эпителиальные клетки и меланоциты, тогда как более тонкие подтипы иммунных клеток оставались сложной задачей. Они также сверили свои аннотации с независимым методом маркировки (SingleR) и альтернативными моделями, основанными на РНК, и в целом обнаружили хорошее согласие.
Что это значит для будущей диагностики рака
STHELAR — это скорее эталонный атлас, чем единый алгоритм: открытая, крупномасштабная связь между тем, что патологи видят на стандартных H&E‑срезах, и тем, что пространственная транскриптомика показывает о генетической активности в каждой клетке. Для неспециалистов основной вывод в том, что этот ресурс значительно облегчает обучение и тестирование компьютерных моделей, которые могут восстанавливать клеточный состав опухолей непосредственно по рутинным изображениям, без проведения дорогостоящих молекулярных анализов для каждого пациента. По мере улучшения таких моделей они смогут помогать врачам читать невидимый молекулярный «диалог» внутри опухолей по обычным слайдам, поддерживая более точную диагностику и лучше персонализированное лечение.
Цитирование: Giraud-Sauveur, F., Blampey, Q., Benkirane, H. et al. STHELAR, a multi-tissue dataset linking spatial transcriptomics and histology for cell type annotation. Sci Data 13, 665 (2026). https://doi.org/10.1038/s41597-026-06937-6
Ключевые слова: микросреда опухоли, пространственная транскриптомика, гистопатологическая визуализация, аннотация типов клеток, глубокое обучение в онкологии