Clear Sky Science · tr
U6 içsel sap halkasında N2‑metilguanozin’in 2′‑O‑metilasyona bağımlı eklenmesi, etkili spliceozom montajını kolaylaştırır
Neden küçük RNA ince ayarları önemli?
Her insan hücresinin içinde, ham RNA mesajlarını çalışır proteinlere dönüştürülmeden önce düzenleyen karmaşık bir moleküler makine olan spliceozom bulunur. Bu düzenleme hem hızlı hem de doğru olmak zorundadır ve kimyasal etiketlerle yoğun şekilde "ince ayarlanmış" küçük RNAlara dayanır. Bu çalışma, U6 adlı bu RNA'lardan birinde yapılan belirli bir dizi kimyasal değişikliğin spliceozomun doğru biçimde monte olmasına ve özellikle zorlu RNA segmentlerini işlemesine nasıl yardımcı olduğunu ortaya koyuyor; bu durum, hatalı eşleştirmenin rol oynadığı hastalıklar açısından olası çıkarımlara işaret ediyor.
RNA düzenlemede kilit bir yardımcı
Çoğu insan geninde, protein yapılmadan önce RNA’dan çıkarılması gereken kodlamayan diziler (intronlar) bulunur. Spliceozom, bu kesip‑yapıştır işlemini birkaç küçük RNA kullanarak gerçekleştirir; bunların arasında makinenin katalitik çekirdeğinin bir parçasını oluşturan U6 da vardır. U6 tek başına hareket etmez: proteinler ve diğer RNA’larla adım adım bir montaj sürecinde ortaklık kurar. Bu süreçte U6 birçok konumda kimyasal olarak modifiye edilir. Yazarlar, içsel bir halka bölgesinde birkaç şeker metil grubu ve tek bir guanozin baz üzerinde özel bir modifikasyon taşıyan U6 iç halkasına odaklanıyor. Önceki çalışmalar, 72 numaralı pozisyondaki baz metilasyonu olan N2‑metilguanozin'in zayıf eşleşme bölgelerinin ayrılması için gerekli olduğunu ve bu işareti THUMPD2 enziminin yerleştirdiğini göstermişti. Bilinmeyen ise bu işaretin ne zaman eklendiği, enzimin U6’yı nasıl tanıdığı ve bu kimyasal değişikliklerin spliceozom montajı ve eşleştirme üzerinde nasıl etkili olduğuydu.
U6 yaşamının geç bir aşamasında eklenen son rötuş
UV çapraz bağlama ve yüksek verimli dizileme kullanarak araştırmacılar, THUMPD2’nin hücrelerde diğer herhangi bir RNA’ya kıyasla çok daha fazla U6 RNA’sına bağlandığını gösterdi ve U6’yı başlıca hedefi olarak doğruladı. THUMPD2 ile ilişkili U6 moleküllerinin kuyruk uçlarını analiz ederek, enzimin U6’ya ancak 3′ ucunun tam olarak işlenmesinden sonra bağlandığını buldular; bu da 72. pozisyondaki metilasyonun U6 olgunlaşmasında geç bir olay olduğunu gösteriyor. Protein‑etkileşim haritalaması, THUMPD2’nin U6 içeren kompleksler ve erken eşleştirme faktörleri ile ilişkili olduğunu, ancak en erken biyogenez faktörleriyle olmadığını ortaya koydu. Floresan mikroskopi ise THUMPD2’yi spliceozom montajının geç adımlarının gerçekleştiği nükleer altyapılar olan Cajal cisimciklerinde konumlandırdı; bu da guanozin metilasyonunun U6’nın daha büyük spliceozomal yapılara katılmadan önceki son kalite kontrol işaretlerinden biri olduğu fikrini destekliyor.
Şeker ve baz modifikasyonları arasında karşılıklı etkileşim
THUMPD2’nin U6’yı nasıl tanıdığını anlamak için ekip yapısal modelleme, çapraz bağlama kütle spektrometrisi ve mutasyon analizi kombinasyonunu kullandı. U6’nın iç sap halkasının THUMPD2’nin hem THUMP RNA‑bağlayıcı alanına hem de katalitik metiltransferaz alanına yaslandığı ve hedef bazı enzimin aktif bölgesine yakın konumlandırdığı bir model inşa ettiler. Ardından her iki alanın da U6’yı kararlı şekilde kavramak için gerekli olduğunu ve küçük bir ortak protein olan TRMT112’nin THUMPD2’nin katalitik aktivitesi için elzem olduğunu gösterdiler. Çarpıcı biçimde, tüpte yapılan metilasyon denemeleri, THUMPD2’nin modifiye edilmemiş bir U6 halkasını neredeyse metile etmediğini, ancak karşı zindeki iki yakın riboz şekerde 2′‑O‑metil grupları zaten bulunduklarında on katın üzerinde daha verimli çalıştığını ortaya koydu. Hücrelerde, bu şeker metil gruplarını yerleştirmek için gereken bir faktör olan LARP7’nin tükenmesi hem şeker işaretlerini hem de guanozin metilasyonunu azalttı. Yine de THUMPD2 ile U6 arasındaki bağlanma gücü, şeker metilasyonu olsun veya olmasın benzerdi; bu da bu önceki işaretlerin ilk tanımayı değil reaksiyon adımını ayarladığını gösteriyor.
Eşleştirme desenleri ve spliceozom montajı üzerine etkisi
Yazarlar daha sonra bu kimyasal işaretlerin gerçek gen eşleştirmesini nasıl etkilediğini sordu. THUMPD2 eksik hücreler, LARP7 tükenmiş hücreler ve her ikisinden yoksun hücrelerden elde edilen RNA‑sekans verilerini karşılaştırarak, her bir bozulumun alternatif eşleştirme tercihlerini ince ama anlamlı biçimde değiştirdiğini buldular. Sadece guanozin metilasyonunun kaybı esas olarak, zaten verimsiz eşleşen intronlarda artmış intron tutulmasına yol açtı. Buna karşılık, şeker metilasyonlarının kaybı alternatif 3′ ekleme (splice) noktalarının kullanımını daha uzak seçeneklere kaydırdı. Her iki tür modifikasyon bozulduğunda etkilenen eşleştirme olaylarının sayısı en yüksekti ve birleşik etkiler büyük ölçüde bireysel kusurların toplamsal bir karışımıyla açıklanabiliyordu. Nükleer özütlerin biyokimyasal fraksiyonlanması, altında yatan montaj kusurlarını ortaya koydu: baz metilasyonu olmadan U6, ara küçük RNA‑protein komplekslerinde birikti ve tam şekilli spliceozomlara geçişin yavaşladığını düşündürdü. Şeker metilasyonları yokken ise çok daha az U6 küçük nükleer ribonükleoprotein parçacıklarına girdi ve kilit spliceozomal bileşenler yanlış dağıldı; bu da daha temel bir montaj sorunu işaret ediyor.
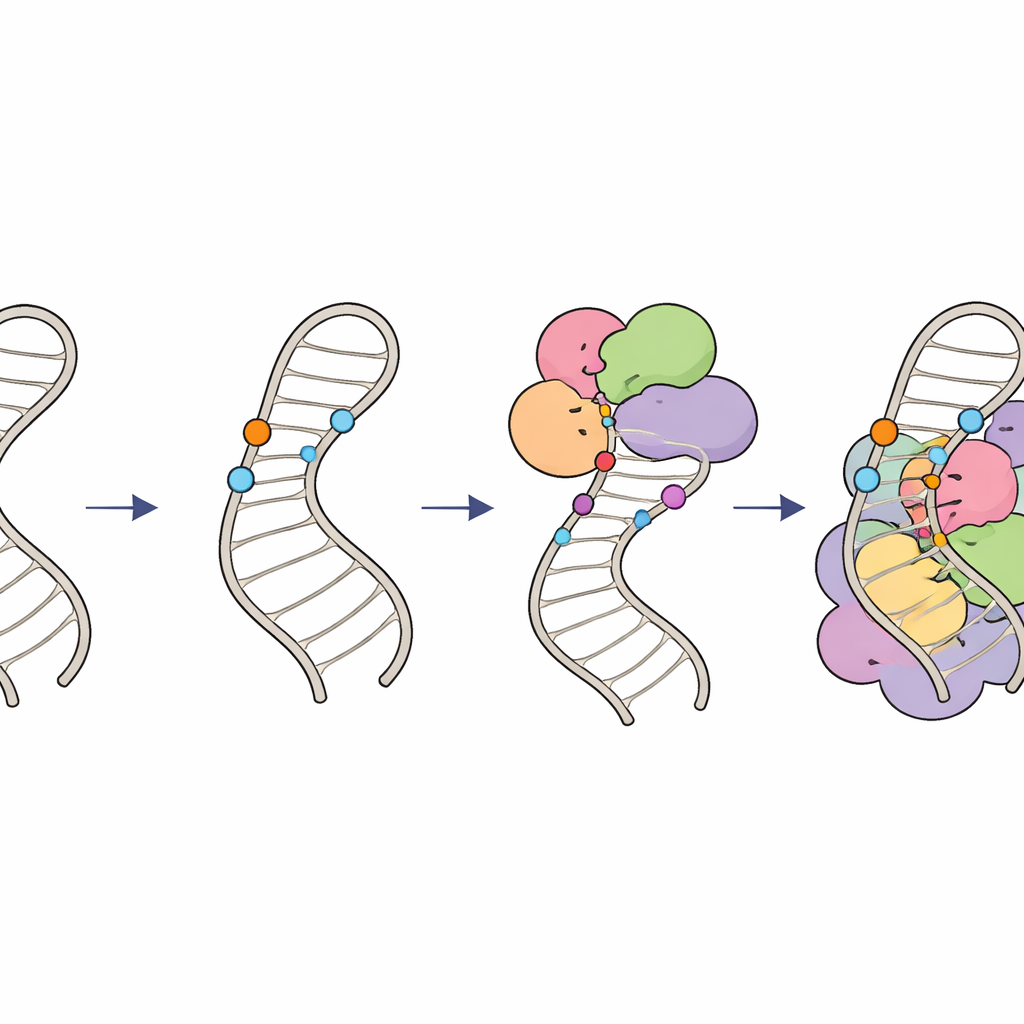
Kimyasal işaretler RNA düzenlemesini nasıl rayında tutar
Bu bulgular, U6 RNA üzerinde hiyerarşik bir "modifikasyon devresi"ni özetliyor. Önce, özel kılavuz RNA’lar ve LARP7 faktörü içsel sap halkasındaki şekerlere 2′‑O‑metil gruplarını yerleştirerek halkanın yapısını şekillendirir ve optimal bir substrat oluşturur. Ardından THUMPD2–TRMT112 enzim kompleksi belirli bir baza son bir metil grubu ekler; muhtemelen U6’nın daha yüksek düzeyde spliceozomal komplekslere ilerlemesi için geç aşama bir lisans görevi görür. Bu küçük kimyasal işaretlerin ne zaman ve nerede ortaya çıktığını koordine ederek hücreler, U6’nın doğru katlanmasını ve spliceozoma tam zamanında entegre olmasını sağlar; böylece doğru ve verimli RNA eşleştirmeyi korurlar. Bu sistemdeki ince kusurlar, genom genelinde eşleştirme desenlerini değiştirebilir ve eşleştirme hatalarına bağlı insan hastalıklarına katkıda bulunabilir.
Atıf: Kleiber, N., Petrosyan, J., Greve, M. et al. 2′-O-methylation-dependent installation of N2-methylguanosine in the U6 internal stem loop facilitates efficient spliceosome assembly. Nat Commun 17, 3793 (2026). https://doi.org/10.1038/s41467-026-72355-2
Anahtar kelimeler: RNA eşleştirmesi (splicing), U6 snRNA, RNA modifikasyonları, spliceozom montajı, THUMPD2