Clear Sky Science · fr
Dépendance à la 2′-O-méthylation pour l’installation de la N2-méthylguanosine dans la boucle interne en tige de l’U6 facilitant l’assemblage efficace du spliceosome
Pourquoi de petites modifications de l’ARN comptent
À l’intérieur de chaque cellule humaine, une machine moléculaire complexe appelée spliceosome édite les messages ARN bruts pour qu’ils puissent être traduits en protéines fonctionnelles. Cette édition doit être à la fois rapide et précise, et elle repose sur de petits ARN fortement « ajustés » par des marques chimiques. Cet article révèle comment une séquence spécifique de modifications chimiques sur un de ces ARN, nommé U6, aide le spliceosome à s’assembler correctement et à traiter des segments d’ARN particulièrement difficiles, avec des implications potentielles pour des maladies liées à des défauts d’épissage.
Un assistant clé dans l’édition de l’ARN
La plupart des gènes humains contiennent des portions non codantes qui doivent être retirées de l’ARN avant la synthèse des protéines. Le spliceosome réalise ce découpage-collage en utilisant plusieurs petits ARN, dont U6, qui fait partie du cœur catalytique de la machine. U6 n’agit pas seul : il s’associe à des protéines et à d’autres ARN au cours d’un assemblage par étapes. En chemin, U6 est chimiquement modifié en de nombreux endroits. Les auteurs se concentrent sur une région en boucle interne de U6 qui porte plusieurs méthylations du sucre et une modification particulière sur une base guanosine. Des travaux antérieurs ont montré que la méthylation de la base, connue sous le nom de N2‑méthylguanosine en position 72, est nécessaire pour épisser des sites faibles et que l’enzyme THUMPD2 installe cette marque. Restait toutefois inconnu le moment où cette marque est ajoutée, comment l’enzyme reconnaît U6, et comment ces modifications chimiques affectent l’assemblage du spliceosome et l’épissage.
Touche finale ajoutée tard dans la vie de l’U6
Grâce à des expériences de réticulation UV et au séquençage haut débit, les chercheurs ont montré que THUMPD2 se lie à l’ARN U6 bien plus qu’à tout autre ARN dans les cellules, confirmant U6 comme sa cible principale. En analysant les extrémités 3′ des molécules d’U6 associées à THUMPD2, ils ont trouvé que l’enzyme n’intervient qu’après le traitement complet de l’extrémité 3′ d’U6, ce qui signifie que la méthylation en position 72 est un événement tardif dans la maturation d’U6. Le cartographie des interactions protéiques a révélé que THUMPD2 s’associe à des complexes contenant U6 et à des facteurs précoces d’épissage, mais pas aux tout premiers facteurs de biogenèse. La microscopie à fluorescence a ensuite localisé THUMPD2 dans les corps de Cajal — des sous-structures nucléaires où se déroulent des étapes tardives de l’assemblage du spliceosome — soutenant l’idée que la méthylation de la guanosine est l’une des marques finales de contrôle qualité avant qu’U6 n’intègre des assemblages spliceosomiques plus importants.
Dialogue entre modifications du sucre et de la base
Pour comprendre comment THUMPD2 reconnaît U6, l’équipe a combiné modélisation structurale, spectrométrie de masse après réticulation et analyses mutagènes. Ils ont construit un modèle où la boucle interne en tige de l’U6 s’appuie à la fois sur le domaine THUMP de liaison à l’ARN et sur le domaine méthyltransférase catalytique de THUMPD2, plaçant la base cible à proximité du site actif de l’enzyme. Ils ont montré que les deux domaines sont nécessaires pour maintenir une fixation stable d’U6, tandis qu’une petite protéine partenaire, TRMT112, est essentielle à l’activité catalytique de THUMPD2. De façon frappante, des essais de méthylation in vitro ont révélé que THUMPD2 modifie à peine une boucle U6 non préalablement modifiée, mais fonctionne plus de dix fois plus efficacement lorsque deux riboses voisines dans le brin opposé sont déjà 2′‑O‑méthylées. Dans les cellules, l’épuisement de LARP7 — un facteur nécessaire à l’installation de ces méthylations du sucre — réduit à la fois les marques sur les sucres et la méthylation de la guanosine. Pourtant, l’affinité de liaison entre THUMPD2 et U6 était similaire avec ou sans les méthylations du sucre, indiquant que ces marques préalables règlent l’étape de la réaction elle‑même, et non la reconnaissance initiale.
Impact sur les profils d’épissage et l’assemblage du spliceosome
Les auteurs ont ensuite cherché à savoir comment ces marques chimiques influencent l’épissage des gènes. En comparant des données de séquençage ARN provenant de cellules dépourvues de THUMPD2, de cellules appauvries en LARP7 et de cellules manquantes pour les deux facteurs, ils ont constaté que chaque perturbation modifiait subtilement mais significativement les choix d’épissage alternatif. La perte de la méthylation de la guanosine seule entraînait principalement une augmentation de la rétention d’introns, en particulier dans des introns déjà épissés de manière inefficace. En revanche, la perte des méthylations du sucre déplaçait l’utilisation des sites d’épissage 3′ alternatifs vers des options plus éloignées. Lorsque les deux types de modifications étaient compromis, le nombre d’événements d’épissage affectés était maximal, et les effets combinés pouvaient être en grande partie expliqués comme la somme additive des défauts individuels. La fractionation biochimique des extraits nucléaires a révélé les défauts d’assemblage sous-jacents : sans la méthylation de la base, U6 s’accumulait dans des complexes intermédiaires ARN–protéines, suggérant un ralentissement de la progression vers des spliceosomes pleinement formés. Sans les méthylations du sucre, beaucoup moins d’U6 intégraient les particules ribonucléoprotéiques nucléaires, et des composants clés du spliceosome étaient mal répartis, indiquant un problème d’assemblage plus fondamental.
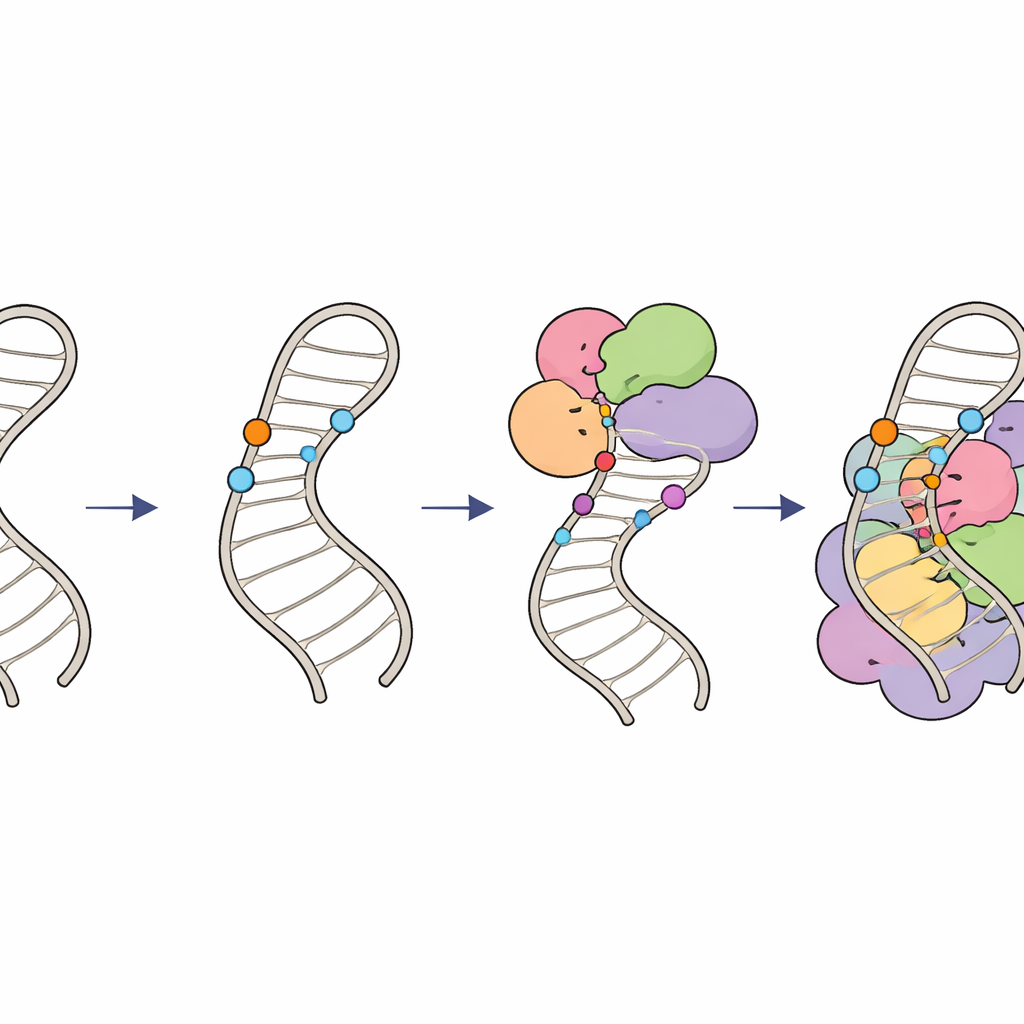
Comment les marques chimiques maintiennent l’édition de l’ARN sur les rails
Ensemble, ces résultats décrivent un « circuit de modifications » hiérarchique sur l’ARN U6. D’abord, des ARN guides spécialisés et le facteur LARP7 placent des groupes 2′‑O‑méthyl sur des sucres au sein de la boucle interne en tige, façonnant sa structure et créant un substrat optimal. Ensuite, le complexe enzymatique THUMPD2–TRMT112 ajoute un groupe méthyle final sur une base spécifique, agissant probablement comme une licence de dernier stade pour permettre à U6 de progresser vers des complexes spliceosomiques de plus haut ordre. En coordonnant le moment et le lieu d’apparition de ces minuscules marques chimiques, les cellules s’assurent qu’U6 se replie correctement et s’intègre au spliceosome avec le bon timing, maintenant un épissage de l’ARN précis et efficace. Des défauts subtils dans ce système peuvent se traduire par des modifications des profils d’épissage à l’échelle du génome et contribuer à des maladies humaines liées à des erreurs d’épissage.
Citation: Kleiber, N., Petrosyan, J., Greve, M. et al. 2′-O-methylation-dependent installation of N2-methylguanosine in the U6 internal stem loop facilitates efficient spliceosome assembly. Nat Commun 17, 3793 (2026). https://doi.org/10.1038/s41467-026-72355-2
Mots-clés: Épissage de l’ARN, ARNsn U6, Modifications de l’ARN, Assemblage du spliceosome, THUMPD2