Clear Sky Science · tr
scTWAS: tek hücre transkriptom çapında ilişkilendirme çalışmalarında güçlü bir istatistiksel çerçeve
Neden tek hücrelere bakmak tıbbı değiştirebilir
Çoğu genetik hastalık çalışması bir kalabalığı dinlemeye benzer: genel bir uğultu duyarlar ama her bireyin ne söylediğini kaçırırlar. Bu makale kulağımızı bireysel seslere nasıl ayarlayacağımızı gösteriyor. Yazarlar, DNA farklılıklarını hastalıklarla bağlayan yeni bir yaklaşım olan scTWAS’i tanıtıyor; bu yaklaşım, tek hücre RNA sekans verisini kullanarak belirli hücre tiplerindeki ve hatta daha ince hücre alt tiplerindeki gen aktivitesine bakıyor. Bu daha keskin görüş, kan hastalıkları, otoimmün hastalıklar ve Alzheimer gibi durumları hangi kesin hücrelerin — ve içlerindeki hangi genlerin — yönlendirdiğini açığa çıkarıyor.
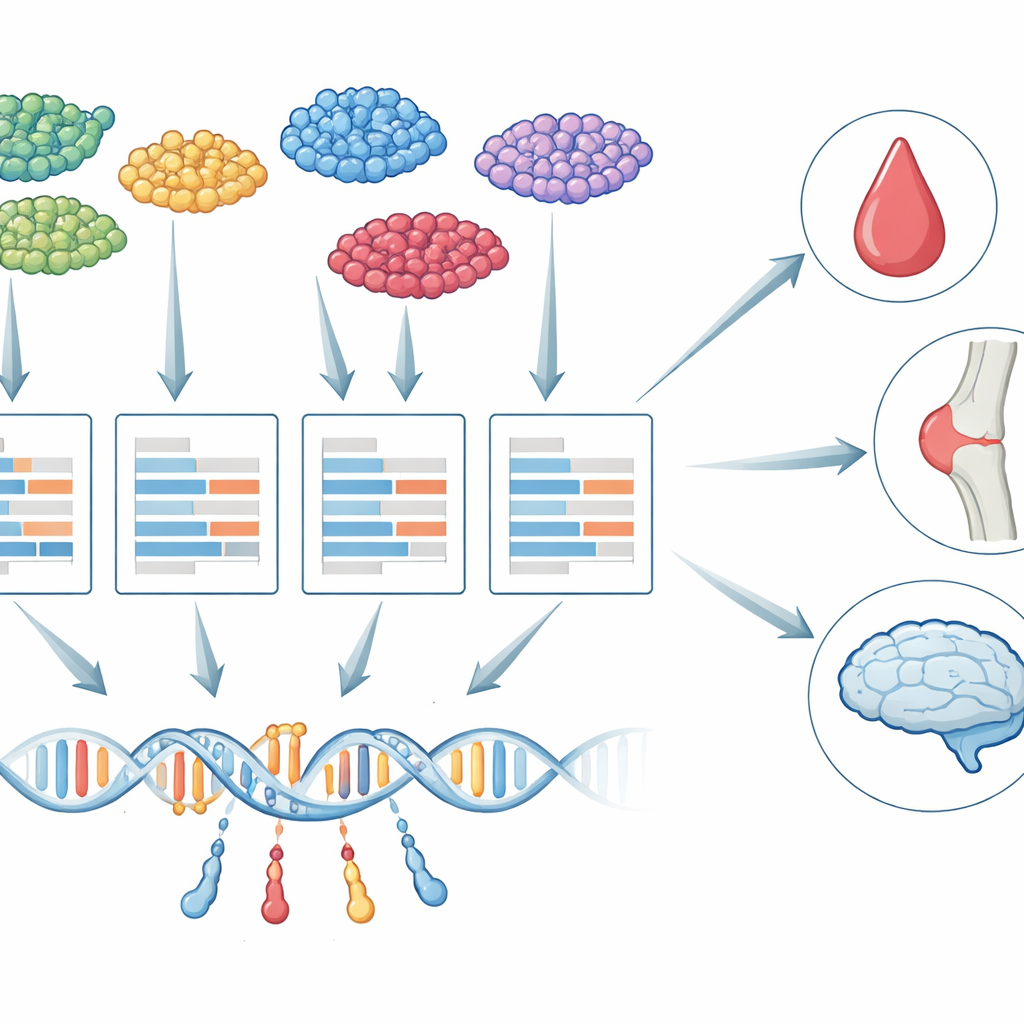
Toplu dokuya karşı tek hücreler
On yılı aşkın bir süredir araştırmacılar, genetik varyantları hastalıklarla ilişkilendirmek için transkriptom-genel ilişkilendirme çalışmaları (TWAS) adlı bir strateji kullanıyorlar. TWAS iki adımda işler: önce DNA değişikliklerinin gen aktivitesini nasıl etkilediğini öğrenir, sonra her bir genin genetik olarak tahmin edilen aktivitesinin trombosit sayısı veya demans riski gibi bir özellik ile ilişkili olup olmadığını test eder. Bugüne dek neredeyse tüm TWAS çalışmaları, birçok hücre tipinin RNA’sının karıştırıldığı “toplu” doku örneklerine dayanıyordu. Bu karışım önemli farklılıkları gizler: örneğin beyindeki bir mikroglial hücrede bir genin genetik kontrolü, aynı genin bir nörondaki kontrolünden oldukça farklı olabilir ve yalnızca bazı hücreler belirli bir hastalık için gerçekten önemli olabilir.
Gürültülü tek hücre verisinin sorunu
Nüfus ölçeğinde yeni tek hücre RNA sekanslaması artık kişi başına binlerce hücreyi ölçmeyi mümkün kılıyor. Ancak bu veriler dağınık: ölçümler seyrek (birçok sıfır), deneyin teknik tuhaflıklarından güçlü şekilde etkileniyor ve biyoloji aynı olsa bile hücreden hücreye büyük değişkenlik gösteriyor. Daha önce tek hücre verisini TWAS’a sokma girişimleri, bu gürültüyü yatıştıracağını umarak toplu RNA yöntemlerinden ödünç alınmış geçici normalizasyon hileleri kullandı. Yazarlar, bu tür kestirme yolların gen aktivitesi üzerindeki gerçek genetik etkileri çarpıtabileceğini, tahminleri zayıflatabileceğini ve özellikle nadir ya da zor hücre tiplerinde daha az gen–hastalık bağlantısının keşfedilmesine yol açabileceğini gösteriyor.
scTWAS sinyali nasıl temizliyor
scTWAS bu zorlukları biyolojiyi ölçüm hatasından açıkça ayırarak ele alır. Önce, tek hücre sayımlarını her kişi ve hücre tipi içinde “sahte-toplu” bir profile toplayarak seyrekliği azaltır ve hücre tipi kimliğini korur. Ardından iki katmanlı bir istatistiksel model kullanır: bir katman DNA varyantlarının ve yaş gibi temel özelliklerin belirli bir hücre tipindeki bir kişinin gerçek altta yatan gen aktivitesini nasıl etkilediğini tanımlar; diğer katman ise dizileme cihazının bu aktiviteyi değişken sayımlara nasıl dönüştürdüğünü, dizileme derinliğinin etkisi dahil, modelleyerek açıklar. Bu modeli özel ağırlıklı regresyon algoritmasıyla uyarak, scTWAS en gürültülü örneklerin ağırlığını azaltır ve her gen için her hücre tipinde genetik olarak düzenlenen ekspresyonu daha doğru tahmin eder.
Hastalık genlerini gerçekten etkiledikleri yerde bulmak
Bu hücre-tipi-spesifik tahmin modelleri eğitildikten sonra, scTWAS bunları geniş çaplı genom çapı ilişki çalışmalarına sokarak gen–özellik bağlantılarını test eder. Gerçek tek hücre deneylerini taklit eden simüle verilerde scTWAS, hem tahmin doğruluğunda hem de güçte mevcut yöntemleri tutarlı şekilde geride bırakmıştır; veri en kıt olduğu nadir hücre tiplerinde özellikle büyük kazanımlar görülmüştür. Çerçeveyi immün hücrelere uyguladıklarında yazarlar, scTWAS’in 29 kan özelliği ile romatoid artrit, lupus ve astım ilişkili olarak önemli ölçüde daha fazla gen tanımladığını gösteriyor. Bu sinyallerin birçoğu belirli monosit veya T hücresi alt kümeleri gibi belirli immün hücre tiplerini, bazı genlerin hastalık riskini etkilediği ana sahne olarak vurguluyor; bazı ilişkiler toplu kan analizleriyle tamamen kaçmıştı.
Alzheimer’da beyin hücre alt tiplerine bakmak
scTWAS beyinde daha da aydınlatıcı hale geliyor. Yüzlerce bağışlanmış insan beyninden elde edilen tek-nükleus verilerini kullanarak yazarlar altı büyük beyin hücre tipi ve 75 daha ince alt tip için tahmin modelleri kurdular. Bunları Alzheimer hastalığı genetik verileriyle birleştirerek risk genlerinin hücresel çözünürlükte nerede muhtemelen etkili olduğunu haritaladılar. Bazı genler birçok hücre tipinde görünerek beyinde geniş roller önermekte, bazıları ise çarpıcı şekilde özgüllük gösteriyor. Örneğin bilinen bir risk geni MS4A6A, yalnızca lipid işleme ile ilişkili hastalık-ilişkili bir mikroglial alt tipte güçlü bir ilişki sergilerken; PPP1R37 yalnızca iyi bilinen APOE risk bölgesine yakın, inflamatuvar bir mikroglial alt tipte ilişkilendirildi. Bu desenler belirli mikroglial durumları, bazı genetik varyantların Alzheimer riskini nasıl yönlendirdiğinde kilit oyuncular olarak işaret ediyor.

Gelecek tedaviler için anlamı
Uzman olmayan birine ana mesaj şudur: bir genin nerede etkili olduğu, genin ne yaptığı kadar önemli olabilir. TWAS’i karışık dokulardan kesin hücre tiplerine ve alt tiplerine indirgeyerek ve tek hücre ölçümlerinin tuhaflıklarını dikkatle modelleyerek, scTWAS daha önce görünmez olan gen–hastalık bağlantılarını açığa çıkarır. Bu daha keskin harita, araştırmacıların kan oluşumu ve bağışıklıktan Alzheimer’da beynin immün hücrelerine kadar yeni ilaçlar veya müdahaleler için hedef alınması gereken tam hücre popülasyonları ve yollar üzerinde yoğunlaşmasına yardımcı olur.
Atıf: Lin, Z., Su, C. scTWAS: a powerful statistical framework for single-cell transcriptome-wide association studies. Nat Commun 17, 3853 (2026). https://doi.org/10.1038/s41467-026-70374-7
Anahtar kelimeler: tek hücre genomikleri, genetik risk eşlemesi, immün hücreler, Alzheimer hastalığı, istatistiksel genetik