Clear Sky Science · tr
EGOLD ile CRISPR gen düzenlemesinin hedef dışı etkilerinde kromatin bağlamının rolünü çözümlemek
Neden küçük DNA değişiklikleri büyük yan etkilere yol açabilir
CRISPR gen düzenleme, hücrelerimizdeki DNA’yı hassas şekilde değiştirerek birçok genetik hastalığın tedavi edilebileceği umudunu doğurdu. Ancak hatalı bir geni düzeltebilen araçlar aynı zamanda genomun diğer bölümlerini yanlışlıkla değiştirebilir ve "hedef dışı" değişiklikler yaratabilir. Bu çalışma, insan hücrelerinde bu istenmeyen düzenlemeleri doğrudan haritalamanın yeni bir yolunu sunuyor ve DNA’nın hücre içinde ne kadar sıkı paketlendiğinin hedef dışı değişikliklerin nerede oluştuğunu büyük ölçüde belirlediğini ortaya koyuyor.
DNA harflerinin ötesine bakmak
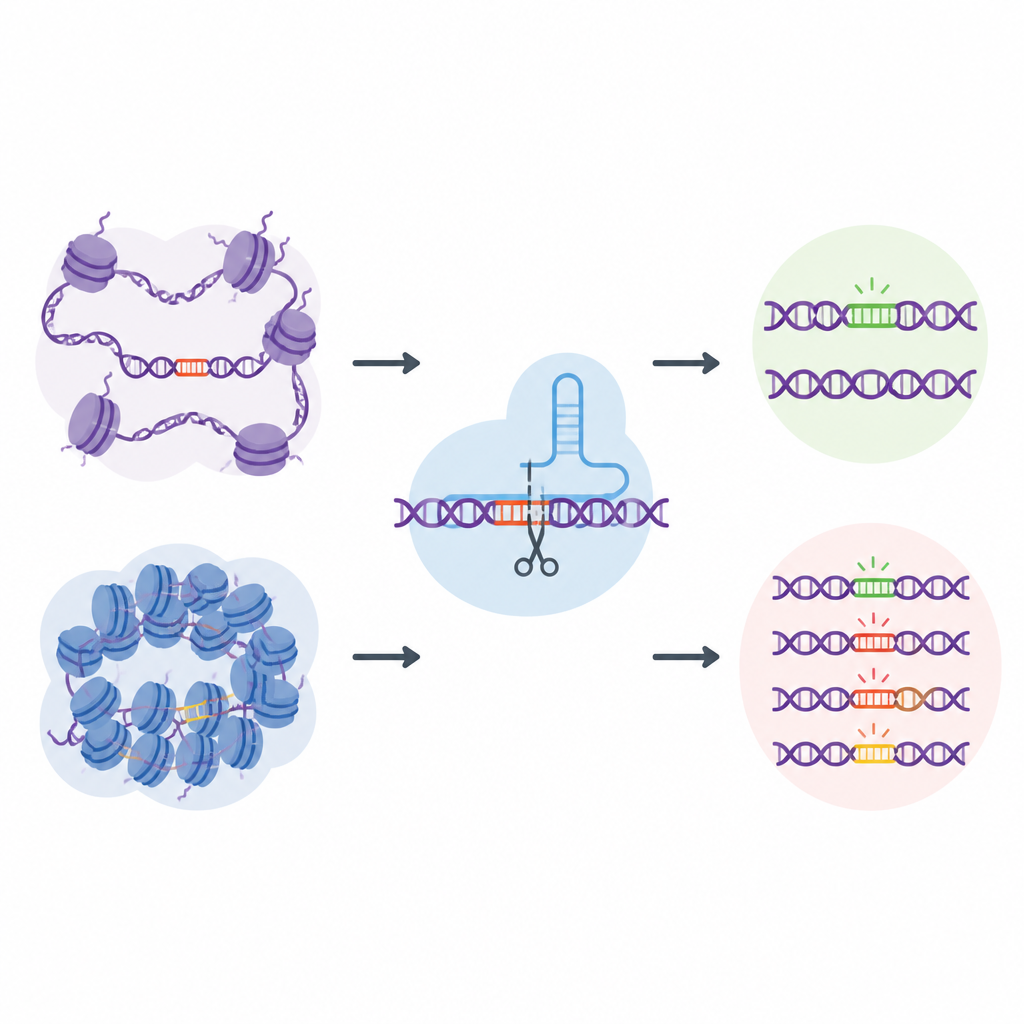
CRISPR güvenliğini anlamaya yönelik çabaların çoğu, hangi A, C, G ve T dizilerinin kesilme veya değiştirilme olasılığının yüksek olduğuna odaklanır. Oysa yaşayan hücrelerde DNA proteinlerin etrafına sarılır ve daha açık ya da kapalı durumlara katlanarak kromatin adı verilen bir manzara oluşturur. Açık bölgeler hücresel makinelerin erişimi için daha elverişliyken kapalı bölgeler daha korunmuş haldedir. Yazarlar, bu yerel DNA paketlemesinin CRISPR araçlarının hata yaptığı yerleri sessizce yönlendirebileceğini şüphelendi, ancak mevcut testler bu etkiyi derinlemesine inceleyecek kadar gerçek genomik siteyi yakalayamıyordu.
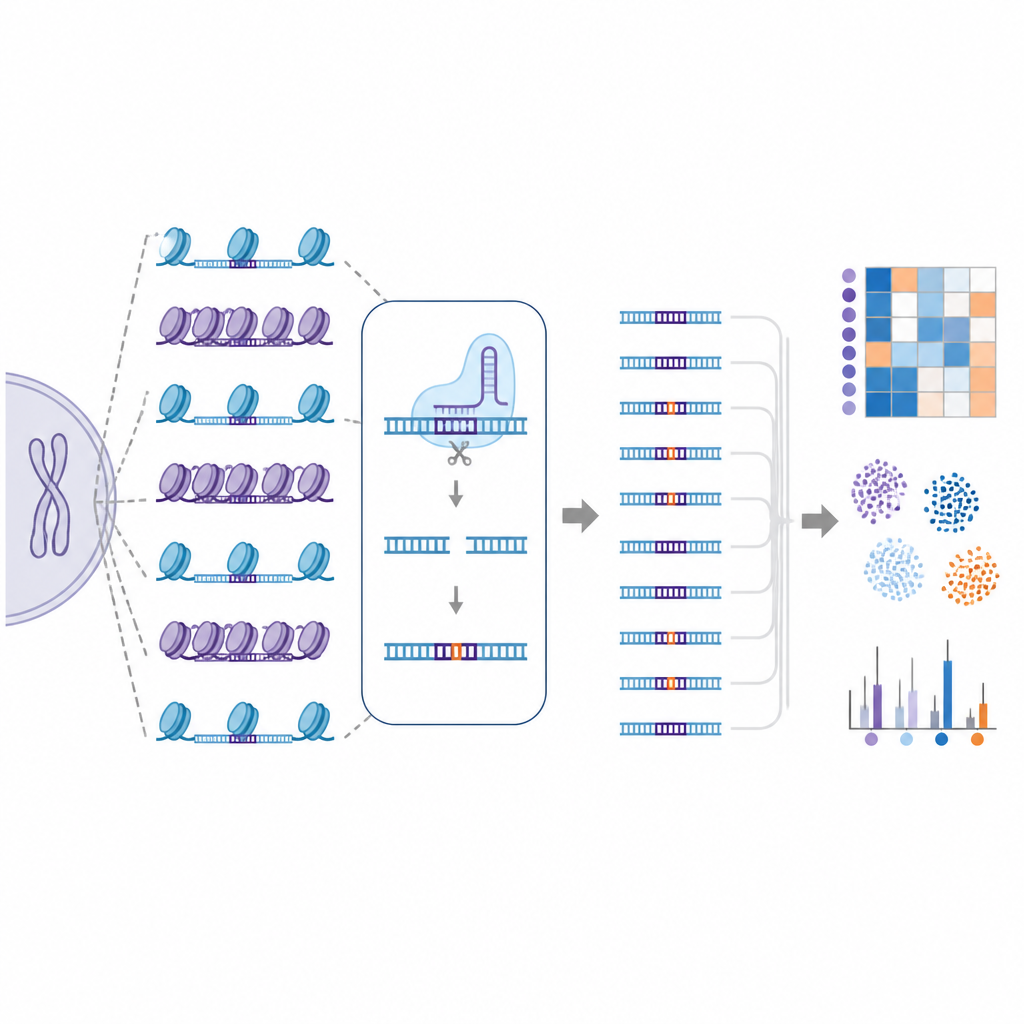
Genom çapında "doğal" bir hedef dışı kütüphane
Bu zorluğun üstesinden gelmek için araştırmacılar EGOLD’u (Endogenous Genome-wide Off-target Library Detection) geliştirdiler. Yapay DNA kütüphaneleri oluşturmak yerine insan genomu boyunca zaten dağılmış yinelenen veya çok benzer dizilerden yararlandılar. Tek bir CRISPR kılavuz RNA’sının binlerce başka konumla yakından eşleştiği, aynı diziyi paylaşan ancak çok farklı kromatin ortamlarında bulunan özel hedef bölgeleri seçtiler. Seçilen bir bölgeyi düzenleyip sonra bütünüyle genomu okuyarak, EGOLD bu benzer sitelerden hangilerinin düzenlendiğini hangilerinin dokunulmadan kaldığını karşılaştırabiliyor; üstelik bunların altında yatan DNA harfleri özdeş kalıyor.
Açık DNA, yanlış düzenlemelere daha açık
EGOLD’u kullanarak ekip, standart çift iplik kesen Cas9 proteinleri ve çift ipliği kesmeden tek harf değiştiren daha yeni baz düzenleyiciler dahil olmak üzere 17 CRISPR tabanlı editörü test etti. İki milyondan fazla tespit edilen hedef dışı olay boyunca belirgin bir desen ortaya çıktı: açık kromatindeki bölgeler, aynı dizinin kapalı, yoğun bölgelerde gömülü hallere göre çok daha yüksek oranda düzenleniyordu. DNA’ya erişim kolaylığını gösteren işaretler ve yakınlardaki proteinlerdeki aktif kimyasal işaretler gibi açık DNA sinyalleri, hedef dışı aktivite ile pozitif ilişki gösterdi. Buna karşılık sıkı paketlenmiş veya kimyasal olarak susturulmuş DNA ile ilişkili özellikler istenmeyen değişikliklere karşı koruma sağlıyordu.
Tüm editörler ve hücreler aynı şekilde davranmıyor
Çalışma ayrıca tanınma açısından ya daha doğru ya da daha esnek olacak şekilde tasarlanmış farklı Cas9 varyantlarını karşılaştırdı. SuperFiCas9 adlı bir varyant, hedeflendiği yerde iyi aktiviteyi korurken özellikle baz düzenleyicilere entegre edildiğinde görece az hedef dışı değişiklik üreterek öne çıktı. Dizideki farklılıklara daha tolerant veya tanıma kuralları daha gevşek olan diğer versiyonlar çok daha yüksek hedef dışı oranlar gösterdi. Aynı editör ve kılavuz RNA kullanılsa bile farklı insan hücre tipleri farklı hedef dışı desenler sergiledi; bu da hücreye özgü kromatin manzaralarının düzenleme sonuçlarını şekillendirdiğini vurguluyor.
Riskli bölgeleri tahmin etmek için bilgisayarlara öğretmek
EGOLD bu kadar büyük ve ayrıntılı hedef dışı haritalar ürettiği için, yazarlar bu verileri makine öğrenimi modellerini eğitmek için kullandılar. Bu bilgisayar modellerine her potansiyel site için hem dizilim bilgisi hem de yerel kromatin özellikleri verildi ve düzenlenen ile düzenlenmeyen konumları çok yüksek doğrulukla ayırt etmeyi öğrendiler. Kromatin bilgisi dizi temelli özelliklere eklendiğinde tahmin performansı iyileşti; bu da DNA paketlemesinin sadece bir ayrıntı değil, hedef dışı riskin ana bir bileşeni olduğunu vurguluyor.
Daha güvenli gen düzenleme için çıkarımlar
Gen terapisinin ilerleyişini takip edenler için bu çalışma, CRISPR’in yanlış gittiği yerin yalnızca DNA yazımına değil aynı zamanda o DNA’nın hücre içinde nasıl katlandığına ve işaretlendiğine de bağlı olduğunu gösteriyor. EGOLD, bu riskleri gerçek genomlarda doğrudan haritalamanın ve kromatin bağlamını dikkate alan daha akıllı tahmin araçları oluşturmanın pratik bir yolunu sunuyor. Uzun vadede bu yaklaşım, araştırmacıların daha güvenli düzenleme stratejileri seçmesine, daha iyi kılavuzlar tasarlamasına ve daha uygun editör varyantlarını tercih etmesine yardımcı olabilir; böylece hayatı değiştiren DNA düzeltmeleri başka yerlerde daha az istenmeyen değişiklikle birlikte gelir.
Atıf: Feng, H., Zheng, J., Li, N. et al. Decoding the role of chromatin context in the off-target effects of CRISPR gene editing with EGOLD. Cell Discov 12, 32 (2026). https://doi.org/10.1038/s41421-026-00889-2
Anahtar kelimeler: CRISPR hedef dışı etkileri, kromatin bağlamı, baz düzenleme, genom güvenliği, makine öğrenimi