Clear Sky Science · pt
Decodificando o papel do contexto da cromatina nos efeitos fora do alvo da edição gênica CRISPR com EGOLD
Por que pequenos ajustes no DNA podem ter grandes efeitos colaterais
A edição gênica com CRISPR despertou expectativas de curar muitas doenças genéticas ao alterar com precisão o DNA dentro de nossas células. Mas as mesmas ferramentas que podem corrigir um gene defeituoso também podem, acidentalmente, alterar outras partes do genoma, gerando mudanças “fora do alvo”. Este estudo introduz uma nova forma de mapear essas edições não intencionais diretamente em células humanas e revela que a forma como o DNA está compactado dentro da célula desempenha um papel importante em onde ocorrem essas alterações fora do alvo.
Indo além das letras do DNA
A maioria dos esforços para compreender a segurança do CRISPR concentra-se na própria sequência de DNA: quais sequências de A, C, G e T têm maior probabilidade de ser cortadas ou alteradas. No entanto, o DNA em células vivas está enrolado em proteínas e dobrado em estados mais abertos ou fechados, um panorama conhecido como cromatina. Regiões abertas são mais fáceis para as máquinas celulares acessarem, enquanto regiões fechadas ficam mais protegidas. Os autores suspeitavam que esse empacotamento local do DNA poderia, silenciosamente, direcionar onde as ferramentas CRISPR cometem erros, mas os testes existentes não capturavam sites genômicos reais suficientes para estudar esse efeito em profundidade.
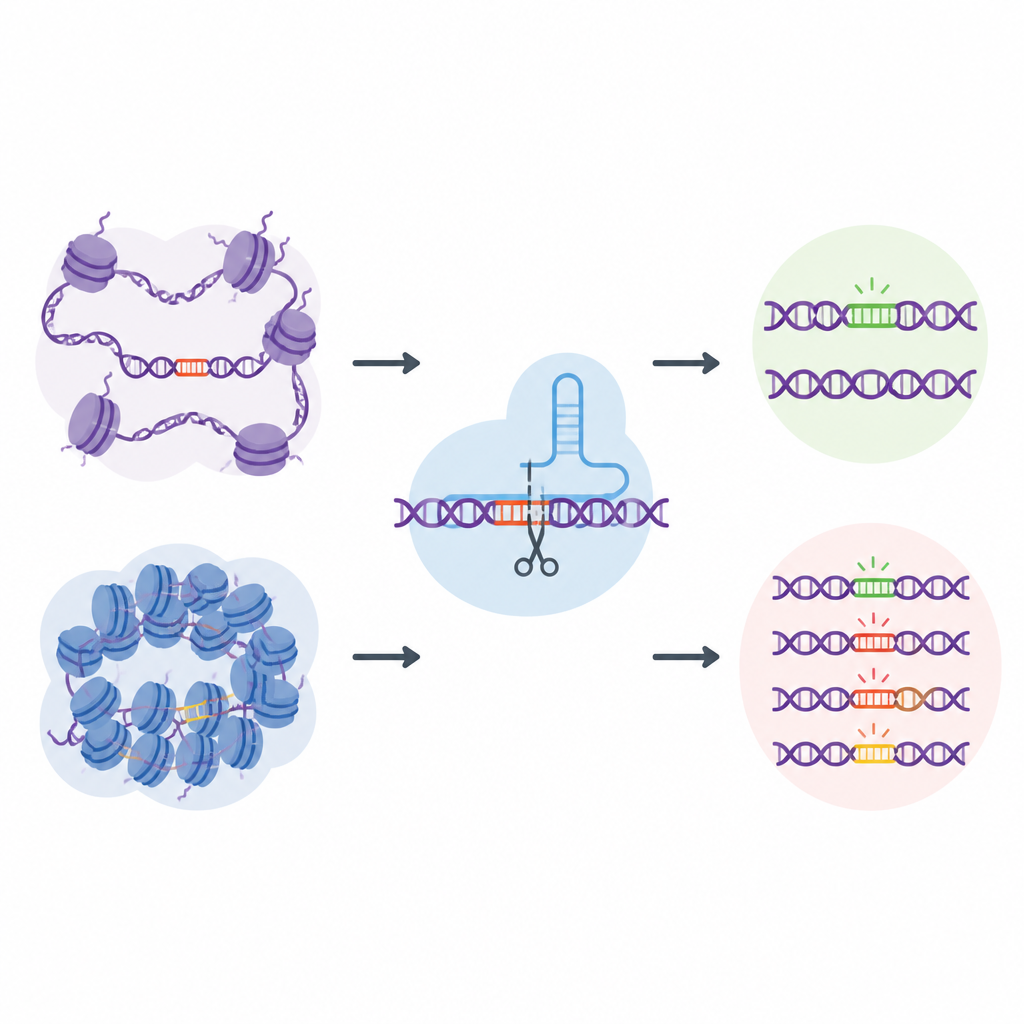
Uma biblioteca “natural” de off-targets em escala genômica
Para enfrentar esse desafio, os pesquisadores criaram o EGOLD, abreviação de Endogenous Genome-wide Off-target Library Detection. Em vez de construir bibliotecas de DNA artificiais, eles aproveitaram sequências repetidas ou muito semelhantes já espalhadas pelo genoma humano. Escolheram sítios-alvo especiais onde um único RNA guia do CRISPR corresponde de perto a milhares de outras localizações que compartilham a mesma sequência, mas estão em ambientes de cromatina muito diferentes. Ao editar um sítio escolhido e depois ler o genoma inteiro, o EGOLD pode comparar quais desses muitos locais semelhantes são editados e quais permanecem intactos, tudo enquanto as letras subjacentes do DNA permanecem idênticas.
DNA aberto é mais vulnerável a edições indesejadas
Usando o EGOLD, a equipe testou 17 editores baseados em CRISPR, incluindo as proteínas Cas9 que cortam o DNA de forma tradicional e editores de base mais recentes que mudam letras individuais sem cortar as duas fitas do DNA. Em mais de dois milhões de eventos fora do alvo detectados, emergiu um padrão claro: sítios em cromatina aberta tinham muito mais probabilidade de serem editados do que a mesma sequência enterrada em regiões fechadas e compactas. Sinais de DNA aberto, como acessibilidade a enzimas que cortam DNA e marcas químicas ativas nas proteínas vizinhas, correlacionaram-se positivamente com atividade fora do alvo. Em contraste, características associadas a DNA fortemente empacotado ou quimicamente silenciado tenderam a proteger contra mudanças indesejadas.
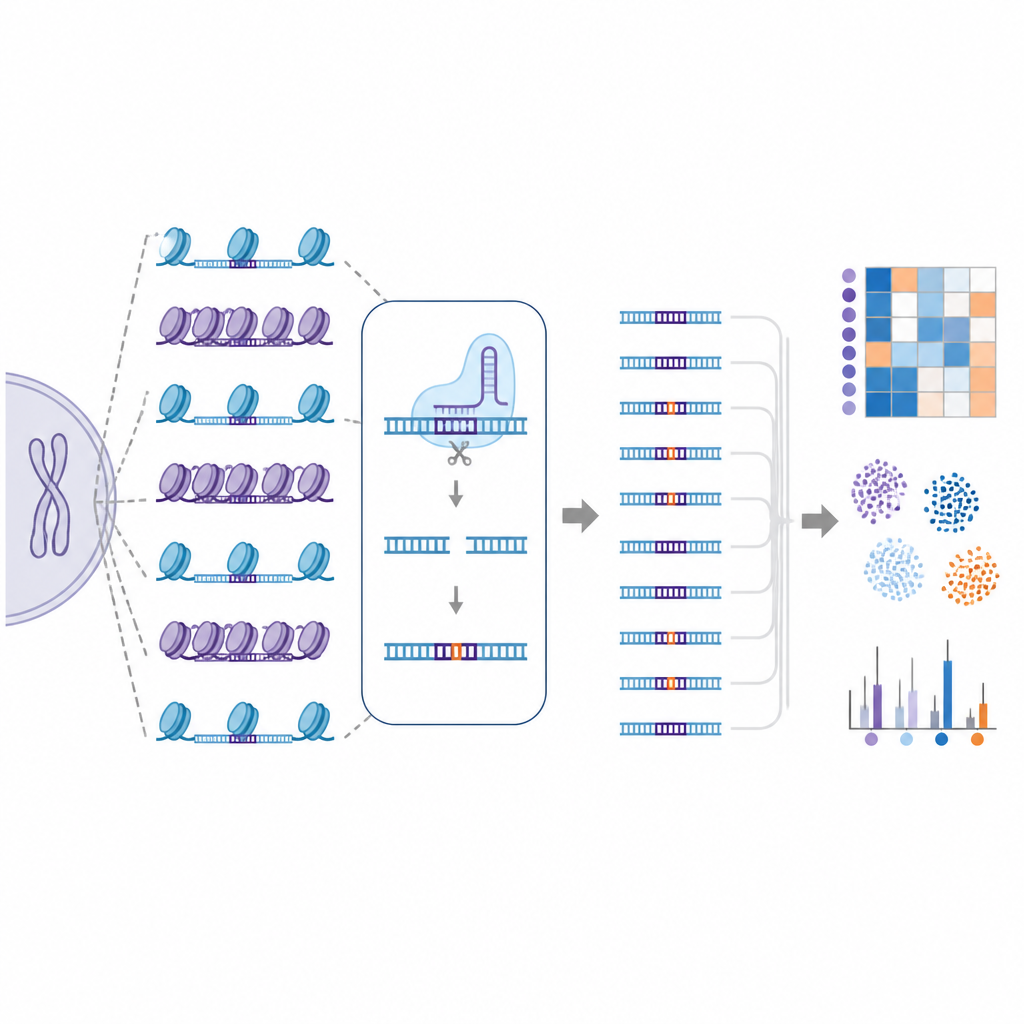
Nem todos os editores e células se comportam da mesma forma
O estudo também comparou diferentes variantes de Cas9 projetadas para serem mais precisas ou mais flexíveis no que reconhecem. Uma variante chamada SuperFiCas9 destacou-se por manter boa atividade no alvo pretendido enquanto produzia relativamente poucas alterações fora do alvo, especialmente quando incorporada a editores de base. Outras versões que toleravam mais diferenças de sequência ou regras de reconhecimento mais relaxadas exibiram taxas de off-target muito mais altas. Mesmo quando o mesmo editor e RNA guia eram usados, diferentes tipos de células humanas exibiram padrões distintos de off-target, ressaltando como os panoramas de cromatina específicos de cada célula moldam os resultados da edição.
Ensinando computadores a prever sítios de risco
Como o EGOLD gera mapas de off-target tão grandes e detalhados, os autores usaram esses dados para treinar modelos de aprendizado de máquina. Esses modelos computacionais foram alimentados com informações de sequência e características de cromatina local para cada sítio potencial e aprenderam a distinguir locais editados de não editados com precisão muito alta. Quando a informação de cromatina foi adicionada às características baseadas na sequência, o desempenho das predições melhorou, ressaltando que o empacotamento do DNA não é apenas um detalhe secundário, mas uma parte chave do risco de off-target.
O que isso significa para edições gênicas mais seguras
Para quem acompanha o progresso da terapia gênica, este trabalho mostra que onde o CRISPR erra é determinado não apenas pela ortografia do DNA, mas também por como esse DNA é dobrado e marcado dentro das células. O EGOLD fornece uma maneira prática de traçar esses riscos diretamente em genomas reais e de construir ferramentas de predição mais inteligentes que levem em conta o contexto da cromatina. A longo prazo, essa abordagem pode ajudar pesquisadores a escolher estratégias de edição mais seguras, projetar guias melhores e selecionar versões de editores mais adequadas para que correções de DNA que mudam vidas ocorram com menos alterações não intencionais em outros locais.
Citação: Feng, H., Zheng, J., Li, N. et al. Decoding the role of chromatin context in the off-target effects of CRISPR gene editing with EGOLD. Cell Discov 12, 32 (2026). https://doi.org/10.1038/s41421-026-00889-2
Palavras-chave: off-targets do CRISPR, contexto de cromatina, edição de bases, segurança genômica, aprendizado de máquina