Clear Sky Science · sv
Avkoda kromatinets roll i CRISPR:s off-target-effekter med EGOLD
Varför små DNA-ändringar kan få stora bieffekter
CRISPR-genterapi har väckt hopp om att bota många genetiska sjukdomar genom att precis förändra DNA i våra celler. Men samma verktyg som kan reparera ett felaktigt gen också kan av misstag ändra andra delar av genomet och skapa så kallade "off-target"-förändringar. Denna studie presenterar ett nytt sätt att kartlägga dessa oavsiktliga redigeringar direkt i humana celler och visar att hur tätt DNA är packat inne i cellen spelar en avgörande roll för var off-target-förändringar uppstår.
Se bortom DNA‑bokstäverna
De flesta försök att förstå CRISPR-säkerhet fokuserar på DNA-sekvensen själv: vilka strängar av A, C, G och T som mest sannolikt blir klippta eller ändrade. Men DNA i levande celler är lindat runt proteiner och veckas till mer öppna eller slutna tillstånd, ett landskap som kallas kromatin. Öppna regioner är lättare för cellens maskineri att nå, medan slutna regioner är mer skyddade. Författarna misstänkte att denna lokala DNA‑packning tyst kan styra var CRISPR-verktygen gör sina misstag, men befintliga tester fångade inte tillräckligt många riktiga genomiska platser för att studera denna effekt på djupet.
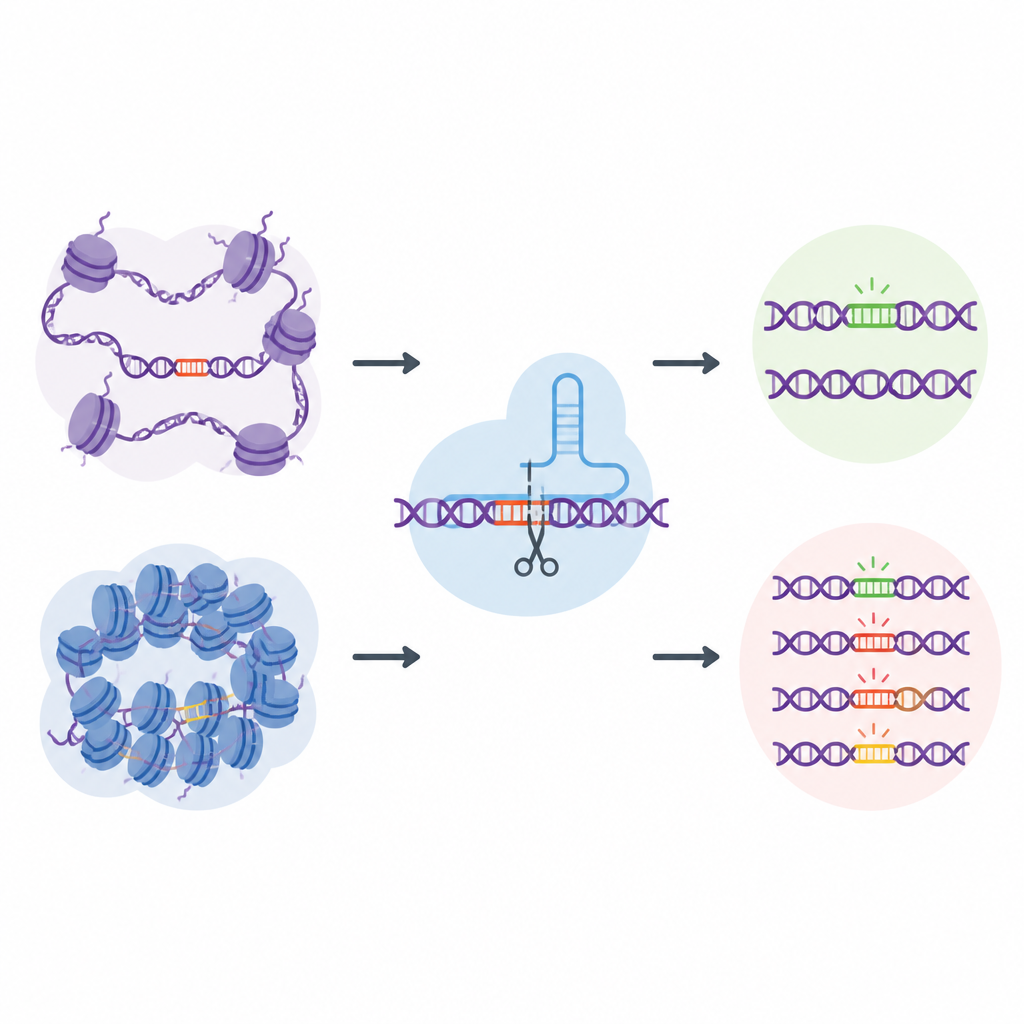
Ett genomomfattande "naturligt" off-target-bibliotek
För att ta sig an denna utmaning skapade forskarna EGOLD, som står för Endogenous Genome-wide Off-target Library Detection. Istället för att bygga artificiella DNA-bibliotek utnyttjade de upprepade eller mycket liknande sekvenser som redan finns utspridda i det humana genomet. De valde särskilda målplatser där en enskild CRISPR-guide-RNA nära nog matchar tusentals andra platser som delar samma sekvens men ligger i mycket olika kromatinmiljöer. Genom att redigera en utvald plats och sedan läsa hela genomet kan EGOLD jämföra vilka av dessa många liknande platser som blir redigerade och vilka som förblir oförändrade, samtidigt som deras underliggande DNA‑bokstäver förblir identiska.
Öppet DNA är mer sårbart för förbipasserande redigeringar
Med EGOLD testade teamet 17 CRISPR-baserade redigerare, inklusive standard Cas9-proteiner som klipper DNA och nyare base editors som byter enstaka bokstäver utan att klippa båda DNA‑strängarna. I mer än två miljoner upptäckta off-target-händelser framträdde ett tydligt mönster: platser i öppet kromatin var avsevärt mer benägna att bli redigerade än samma sekvens begravd i slutna, kompakta regioner. Signaler för öppet DNA, såsom tillgänglighet för DNA-klippande enzymer och aktiva kemiska markörer på närliggande proteiner, var positivt kopplade till off-target-aktivitet. I kontrast tenderade kännetecken för tätt packat eller kemiskt tystat DNA att skydda mot oönskade förändringar.
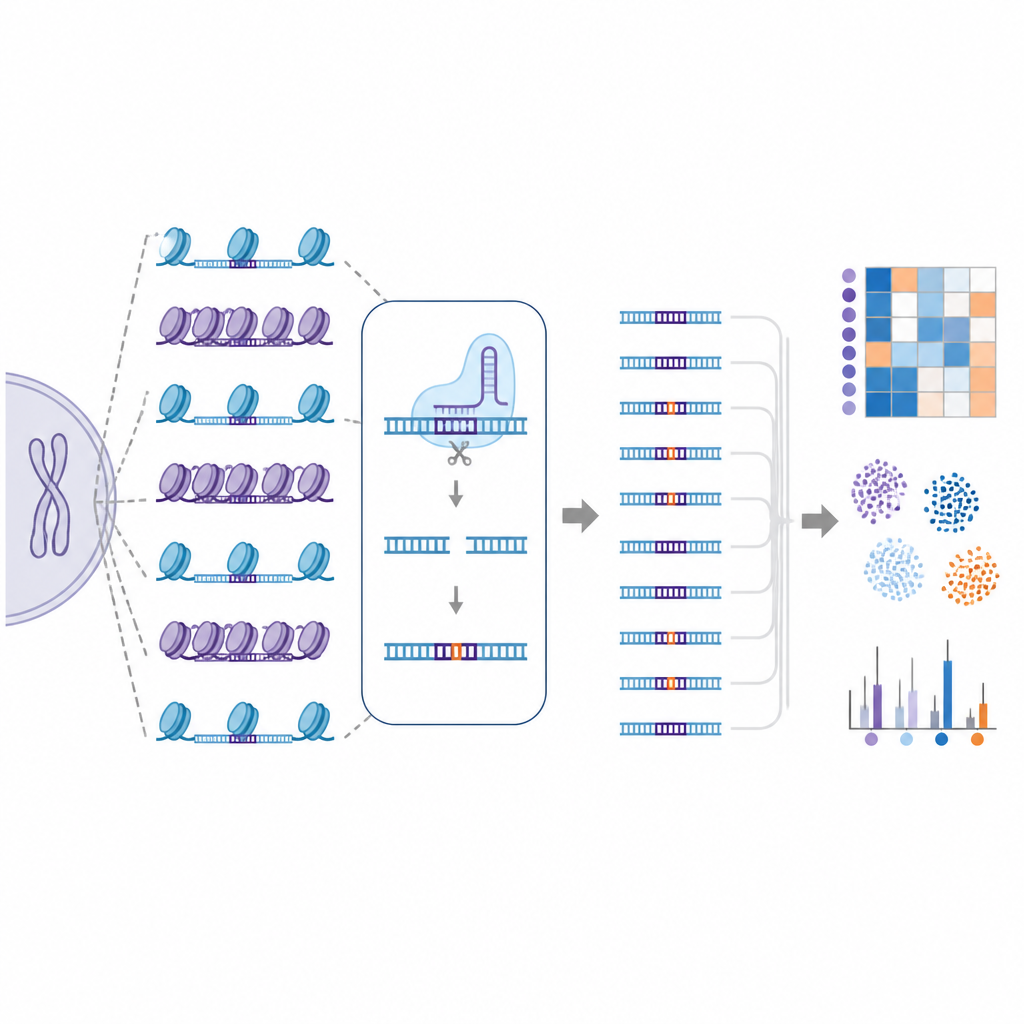
Alla redigerare och celler beter sig inte likadant
Studien jämförde också olika Cas9-varianter som konstruerats för att vara antingen mer precisa eller mer flexibla i vad de känner igen. En variant kallad SuperFiCas9 stack ut genom att behålla god aktivitet vid sitt avsedda mål samtidigt som den gav relativt få off-target-förändringar, särskilt när den byggdes in i base editors. Andra versioner som kunde tolerera fler sekvensskillnader eller mer avslappnade igenkänningsregler visade mycket högre off-target‑nivåer. Även när samma redigerare och guide‑RNA användes visade olika humana celltyper skilda off-target-mönster, vilket understryker hur cellspecifika kromatinlandskap formar redigeringsresultatet.
Att lära datorer att förutse riskfyllda platser
Eftersom EGOLD genererar så stora, detaljerade off-target-kartor använde författarna dessa data för att träna maskininlärningsmodeller. Dessa datorprogram matades med både sekvensinformation och lokala kromatinfunktioner för varje potentiell plats och lärde sig att skilja redigerade från oredigerade platser med mycket hög noggrannhet. När kromatininformation lades till sekvensbaserade egenskaper förbättrades prediktionsprestandan, vilket betonar att DNA‑packning inte bara är en sidoaspekt utan en nyckelkomponent i off-target‑riskbedömning.
Vad detta betyder för säkrare genterapi
För de som följer utvecklingen inom genterapi visar detta arbete att var CRISPR går fel formas inte enbart av DNA‑stavningen utan också av hur det DNA:t är vikt och markerat inne i cellerna. EGOLD erbjuder ett praktiskt sätt att kartlägga dessa risker direkt i verkliga genom och att bygga smartare prediktionsverktyg som tar hänsyn till kromatinkontext. På längre sikt kan detta tillvägagångssätt hjälpa forskare att välja säkrare redigeringsstrategier, designa bättre guider och välja mer lämpliga redigerarversioner så att livsförändrande DNA‑korrigeringar sker med färre oönskade förändringar på andra ställen.
Citering: Feng, H., Zheng, J., Li, N. et al. Decoding the role of chromatin context in the off-target effects of CRISPR gene editing with EGOLD. Cell Discov 12, 32 (2026). https://doi.org/10.1038/s41421-026-00889-2
Nyckelord: CRISPR off-targets, kromatinkontext, base editing, genomsäkerhet, maskininlärning