Clear Sky Science · ja
EGOLDで解明する、CRISPR遺伝子編集のオフターゲット効果におけるクロマチン文脈の役割
なぜ小さなDNAの修正が大きな副作用を招くのか
CRISPRによる遺伝子編集は、細胞内のDNAを正確に変えることで多くの遺伝性疾患を治療する期待を高めてきました。しかし、欠陥のある遺伝子を修復できる同じ道具が、ゲノムの他の部分を誤って変えてしまい、「オフターゲット」と呼ばれる変化を生むことがあります。本研究は、ヒト細胞内で直接これらの意図しない編集をマッピングする新しい方法を紹介し、DNAが細胞内でどれだけ緊密に詰まっているかがオフターゲット変化の発生場所を大きく左右することを明らかにしました。
DNAの文字列を超えて見る
CRISPRの安全性を理解しようとする多くの取り組みは、どの塩基配列(A、C、G、Tの並び)が切断や変化を受けやすいかに注目しています。しかし、生体内のDNAはタンパク質に巻き付けられ、開いた状態や閉じた状態といった折りたたみを示すクロマチンという風景を形成しています。開いた領域は細胞の機構が到達しやすく、閉じた領域はより遮蔽されています。著者らは、この局所的なDNAのパッケージングがCRISPRツールの誤りの発生場所をひそかに左右していると疑っていましたが、既存のテストではこの影響を深く調べるのに十分な実際のゲノム部位を捕らえられていませんでした。
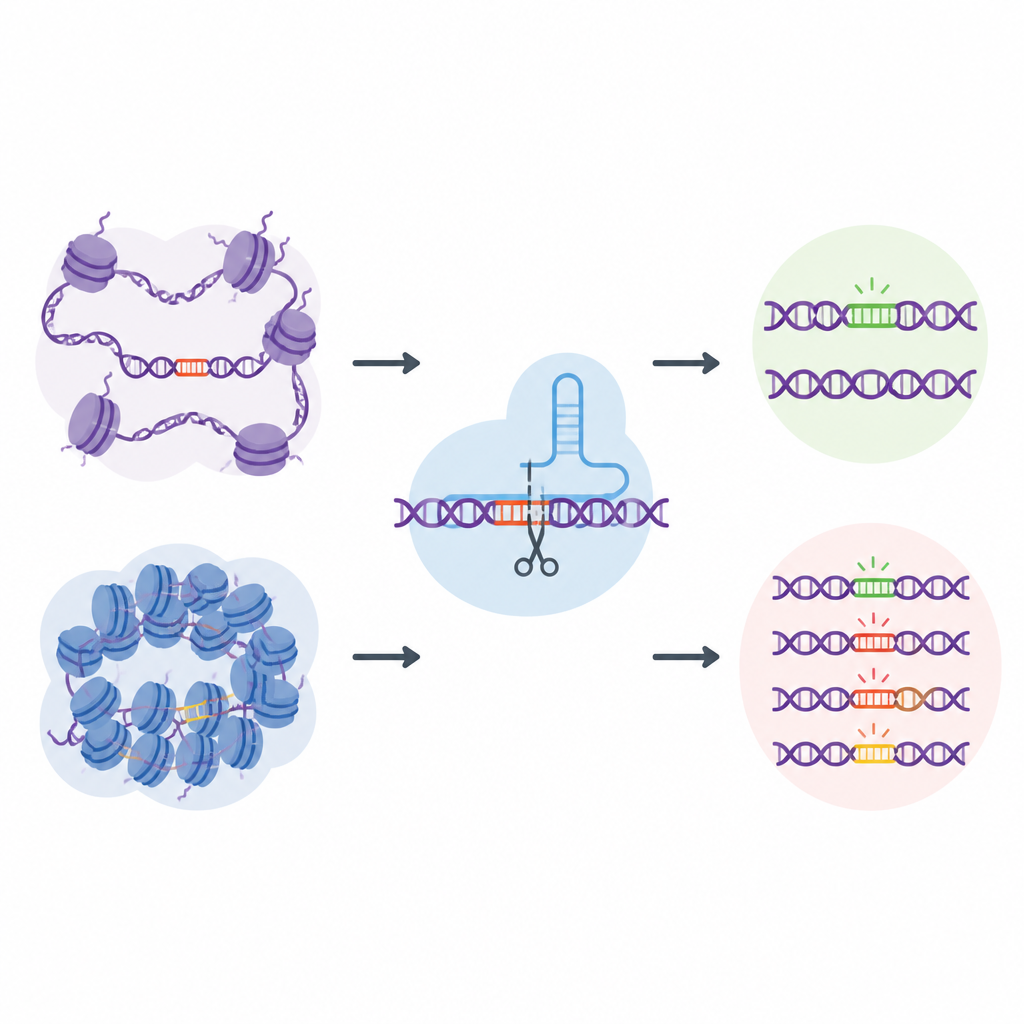
ゲノム全体の“自然な”オフターゲットライブラリ
この課題に取り組むため、研究者らはEGOLD(Endogenous Genome-wide Off-target Library Detection)を作成しました。人工的なDNAライブラリを構築する代わりに、ヒトゲノムに散在する繰り返しや非常によく似た配列を利用しました。1つのCRISPRガイドRNAが数千箇所の類似配列とほぼ一致する特別なターゲット部位を選び、これらは同じ塩基配列を共有しながら異なるクロマチン環境に存在します。選んだ1箇所を編集してからゲノム全体を読み取ることで、EGOLDは多くの見かけ上同一の部位のうちどれが編集され、どれが無傷のままかを比較でき、基礎となるDNAの文字は同一のままです。
開いたDNAは迷い込んだ編集に対して脆弱
EGOLDを用いて、研究チームは標準的なDNA切断Cas9タンパク質や二本鎖を切らずに塩基を変える新しいベースエディターなど、17種類のCRISPRベースのエディターを検査しました。200万件以上の検出されたオフターゲット事象にわたって明確なパターンが見られました:開いたクロマチンにある同一配列の部位は、閉じた密な領域に埋もれた同じ配列よりはるかに編集されやすかったのです。DNA切断酵素へのアクセスのしやすさや近傍タンパク質に付く活性化を示す化学的マークなど、開いたDNAの指標はオフターゲット活性と正の相関がありました。対照的に、密に詰まるか化学的に抑制されたDNAに関連する特徴は、望ましくない変化から保護する傾向がありました。
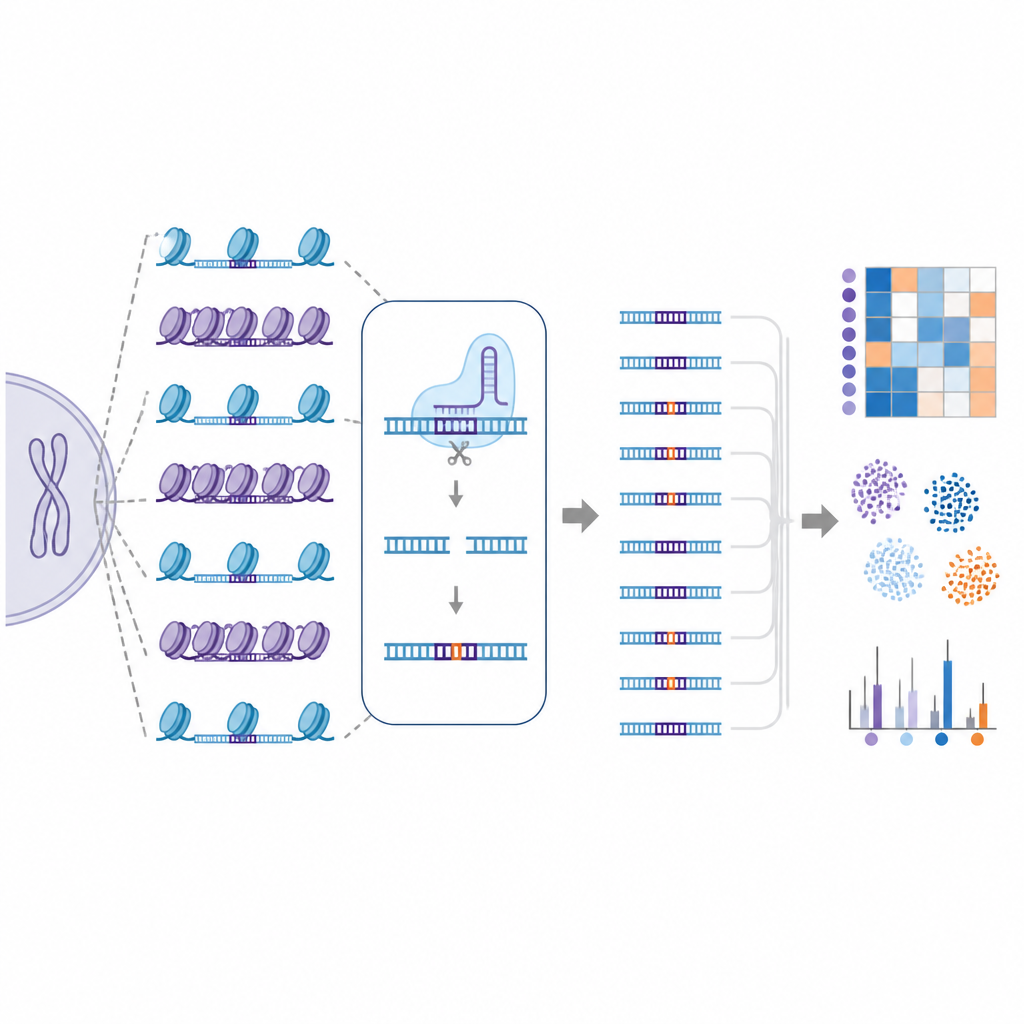
すべてのエディターや細胞が同じ振る舞いをするわけではない
研究ではまた、認識の精度を高めた変異体や認識の柔軟性を持つよう設計されたさまざまなCas9バリアントを比較しました。SuperFiCas9と呼ばれる変異体は、意図したターゲットでの良好な活性を保ちながら、特にベースエディターに組み込んだ場合に比較的少ないオフターゲット変化しか生じなかった点で際立っていました。一方、配列の違いをより許容したり認識ルールが緩い他のバージョンは、はるかに高いオフターゲット率を示しました。同じエディターとガイドRNAを用いても、異なるヒト細胞型ではオフターゲットのパターンが異なり、細胞固有のクロマチン風景が編集結果を形作ることが強調されました。
リスクの高い部位を予測するためにコンピュータを教える
EGOLDは非常に大規模で詳細なオフターゲット地図を生成するため、著者らはこれらのデータを使って機械学習モデルを訓練しました。これらのコンピュータモデルには各潜在的部位について配列情報と局所的なクロマチン特徴が与えられ、編集された場所とされていない場所を非常に高い精度で区別することを学びました。クロマチン情報を配列ベースの特徴に加えると予測性能が向上し、DNAの折りたたみやマーキングが単なる付随的な詳細ではなくオフターゲットリスクの重要な要素であることが裏付けられました。
より安全な遺伝子編集のために意味すること
遺伝子治療の進展を追う人々にとって、この研究はCRISPRの誤りが生じる場所はDNAの綴りだけでなく、そのDNAが細胞内でどのように折りたたまれ、マークされているかによって形作られることを示しています。EGOLDは実際のゲノムでそのリスクを直接描く実用的な手段を提供し、クロマチン文脈を考慮したより賢い予測ツールの構築を可能にします。長期的には、このアプローチは研究者がより安全な編集戦略を選択し、より良いガイドを設計し、適切なエディターのバージョンを選ぶのに役立ち、人生を変えるDNA修正が他の箇所での意図しない変化を減らして実施される助けとなるでしょう。
引用: Feng, H., Zheng, J., Li, N. et al. Decoding the role of chromatin context in the off-target effects of CRISPR gene editing with EGOLD. Cell Discov 12, 32 (2026). https://doi.org/10.1038/s41421-026-00889-2
キーワード: CRISPRのオフターゲット, クロマチン文脈, ベース編集, ゲノム安全性, 機械学習