Clear Sky Science · nl
Ontcijferen van de rol van chromatinecontext bij off-target effecten van CRISPR-genbewerking met EGOLD
Waarom kleine DNA-aanpassingen grote bijwerkingen kunnen hebben
CRISPR-genbewerking wekte de hoop op het genezen van veel genetische aandoeningen door nauwkeurig DNA in onze cellen te veranderen. Maar dezelfde gereedschappen die een defect gen kunnen herstellen, kunnen ook per ongeluk andere delen van het genoom veranderen, en zo “off-target” veranderingen veroorzaken. Deze studie introduceert een nieuwe manier om die onbedoelde bewerkingen direct in menselijke cellen in kaart te brengen en laat zien dat hoe strak DNA in de cel is verpakt een belangrijke rol speelt bij waar off-target veranderingen optreden.
Voorbij de DNA-letters kijken
De meeste pogingen om CRISPR-veiligheid te begrijpen richten zich op de DNA-sequentie zelf: welke reeksen van A, C, G en T het meest waarschijnlijk worden geknipt of veranderd. In levende cellen is DNA echter omgeven door eiwitten en gevouwen in meer open of gesloten toestanden, een landschap dat bekendstaat als chromatine. Open regio’s zijn makkelijker toegankelijk voor cellulaire machines, terwijl gesloten regio’s meer afgeschermd zijn. De auteurs vermoedden dat deze lokale DNA-verpakking stilletjes kan sturen waar CRISPR-gereedschappen fouten maken, maar bestaande tests bevatten niet genoeg echte genomische locaties om dit effect grondig te bestuderen.
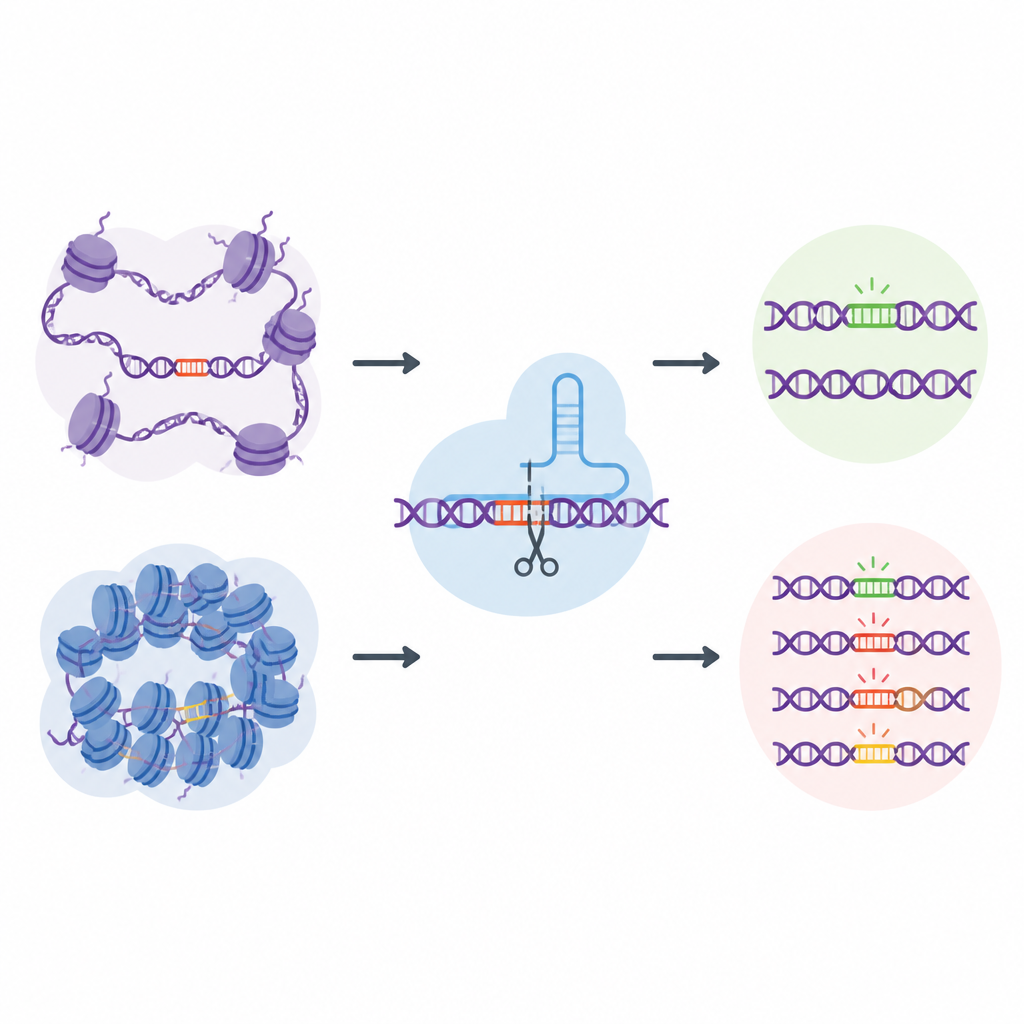
Een genoombrede “natuurlijke” off-target bibliotheek
Om deze uitdaging aan te pakken, ontwikkelden de onderzoekers EGOLD, wat staat voor Endogenous Genome-wide Off-target Library Detection. In plaats van kunstmatige DNA-bibliotheken te bouwen, maakten ze gebruik van herhaalde of zeer vergelijkbare sequenties die al verspreid in het menselijk genoom voorkomen. Ze kozen speciaal doelplaatsen waar één CRISPR-guide RNA nauw overeenkomt met duizenden andere locaties die dezelfde sequentie delen maar in zeer verschillende chromatine-omgevingen liggen. Door één gekozen site te bewerken en vervolgens het hele genoom te lezen, kan EGOLD vergelijken welke van deze vele look-alike sites worden bewerkt en welke onaangetast blijven, terwijl de onderliggende DNA-letters identiek blijven.
Open DNA is kwetsbaarder voor afwijkende bewerkingen
Met EGOLD testte het team 17 CRISPR-gebaseerde editors, waaronder standaard DNA-knippende Cas9-eiwitten en nieuwere base-editors die enkele letters veranderen zonder beide DNA-strengen te knippen. Over meer dan twee miljoen gedetecteerde off-target gebeurtenissen verscheen een duidelijk patroon: locaties in open chromatine werden veel vaker bewerkt dan dezelfde sequentie die begraven ligt in gesloten, compacte regio’s. Kenmerken van open DNA, zoals toegankelijkheid voor DNA-knippende enzymen en actieve chemische merkers op nabijgelegen eiwitten, waren positief gekoppeld aan off-target activiteit. Daarentegen leken kenmerken geassocieerd met strak verpakt of chemisch stilgelegd DNA te beschermen tegen ongewenste veranderingen.
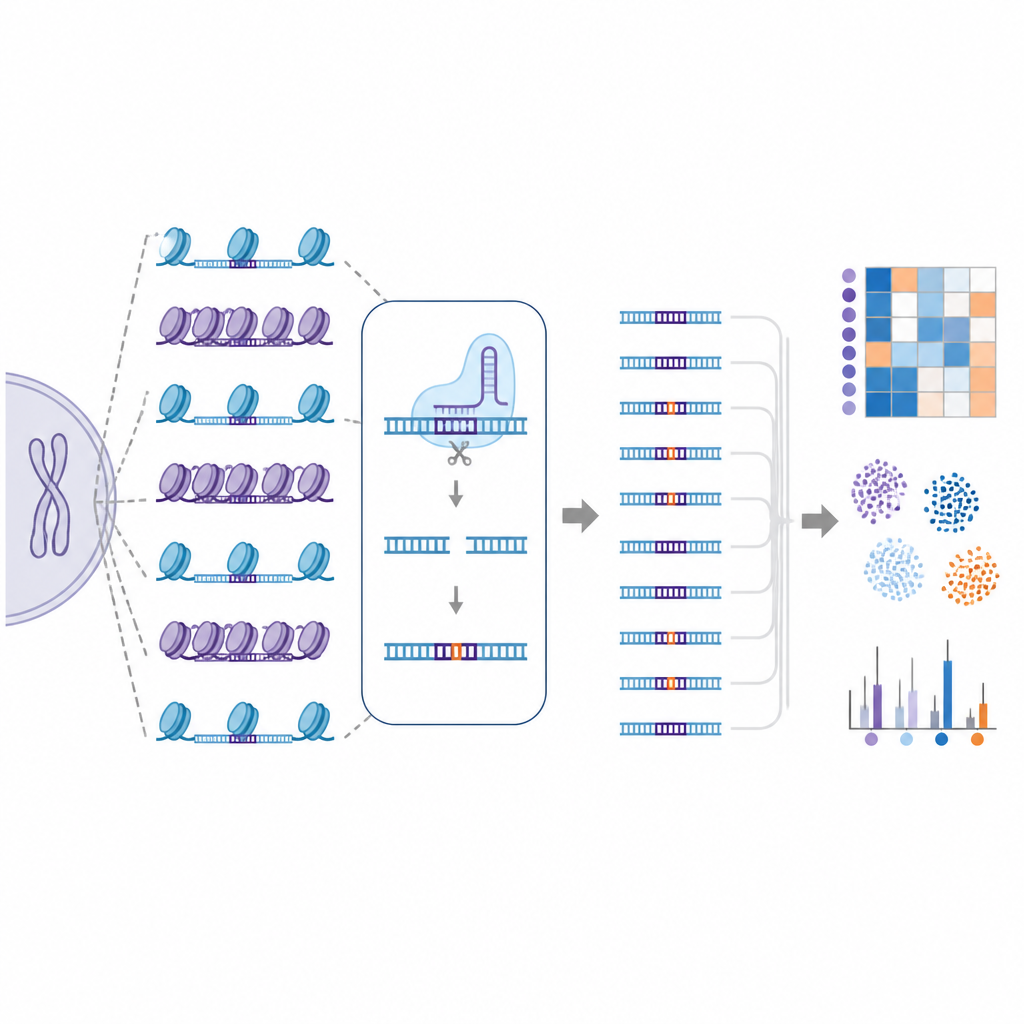
Niet alle editors en cellen gedragen zich hetzelfde
De studie vergeleek ook verschillende Cas9-varianten die zijn ontworpen om ofwel nauwkeuriger te zijn of meer flexibel in wat ze herkennen. Eén variant, SuperFiCas9 genaamd, onderscheidde zich door goede activiteit op het beoogde doel te behouden terwijl relatief weinig off-target veranderingen werden geproduceerd, vooral wanneer ingebouwd in base-editors. Andere versies die meer sequentieverschillen of lossere herkenningsregels konden tolereren, vertoonden veel hogere off-target percentages. Zelfs wanneer dezelfde editor en guide RNA werden gebruikt, toonden verschillende humane celtypes verschillende off-target patronen, wat benadrukt hoe celspecifieke chromatine-landschappen de uitkomst van bewerkingen vormgeven.
Computers leren risicovolle sites te voorspellen
Aangezien EGOLD zulke grote, gedetailleerde off-target kaarten oplevert, gebruikten de auteurs deze data om machine learning-modellen te trainen. Deze computermodellen kregen zowel sequentie-informatie als lokale chromatinekenmerken voor elke potentiële site en leerden bewerkte van onbewerkte locaties met zeer hoge nauwkeurigheid te onderscheiden. Wanneer chromatine-informatie werd toegevoegd aan sequentiegebaseerde kenmerken, verbeterde de voorspellingsprestatie, wat benadrukt dat DNA-verpakking niet slechts een bijzaak is maar een essentieel onderdeel van off-target risico.
Wat dit betekent voor veiligere genbewerking
Voor wie de voortgang van gentherapie volgt, toont dit werk aan dat waar CRISPR fouten maakt niet alleen wordt bepaald door DNA-spelling, maar ook door hoe dat DNA in cellen wordt gevouwen en gemarkeerd. EGOLD biedt een praktische manier om die risico’s rechtstreeks in echte genomen in kaart te brengen en om slimere voorspellingsinstrumenten te bouwen die rekening houden met chromatinecontext. Op de lange termijn kan deze aanpak onderzoekers helpen veiligere bewerkingsstrategieën te kiezen, betere guides te ontwerpen en geschiktere editor-versies te selecteren, zodat levensveranderende DNA-correcties met minder onbedoelde veranderingen elders gepaard gaan.
Bronvermelding: Feng, H., Zheng, J., Li, N. et al. Decoding the role of chromatin context in the off-target effects of CRISPR gene editing with EGOLD. Cell Discov 12, 32 (2026). https://doi.org/10.1038/s41421-026-00889-2
Trefwoorden: CRISPR off-targets, chromatinecontext, base editing, genoomveiligheid, machine learning