Clear Sky Science · sv
Högkvalitativ metagenommontering från nanopore-avläsningar med nanoMDBG
Läsa dold liv i en sked jord
Varje nypa jord eller droppe tarmvätska rymmer tusentals mikrobarter, de flesta omöjliga att odla i laboratoriet. För att förstå vilka de är och vad de gör läser forskare deras DNA direkt från miljön—ett fält som kallas metagenomik. Denna artikel presenterar nanoMDBG, en ny beräkningsmetod som förvandlar råa signaler från en portabel DNA-sekvenserare till högkvalitativa utkast till genom, och därmed gör det möjligt att kartlägga komplexa mikrobiella världar snabbare, billigare och med mycket större detaljrikedom än tidigare.
Varför det är så svårt att bygga upp genom från naturen
Metagenomik fungerar genom att man sönderdelar allt DNA i ett prov till fragment, sekvenserar dessa fragment och sedan använder programvara för att sätta ihop dem till genomen hos de organismer som fanns där. Äldre kortavläsningstekniker gav många små bitar, men de resulterande pusslen blev kraftigt fragmenterade, särskilt i mångfaldiga samhällen som jord. Långavläsningsplattformar, inklusive PacBio HiFi och Oxford Nanopore Technologies (ONT), producerar mycket längre DNA-bitar, vilket i teorin borde göra rekonstruktionen enklare. PacBios avläsningar är extremt precisa men dyrare, medan ONT:s enheter är mer prisvärda och mycket portabla, men historiskt har de gett brusigare data. När ONT-kemier förbättrades till ungefär ett fel per hundra DNA-bokstäver behövde fältet assemblers som fullt ut kunde utnyttja denna nya balans mellan längd, noggrannhet och kostnad.
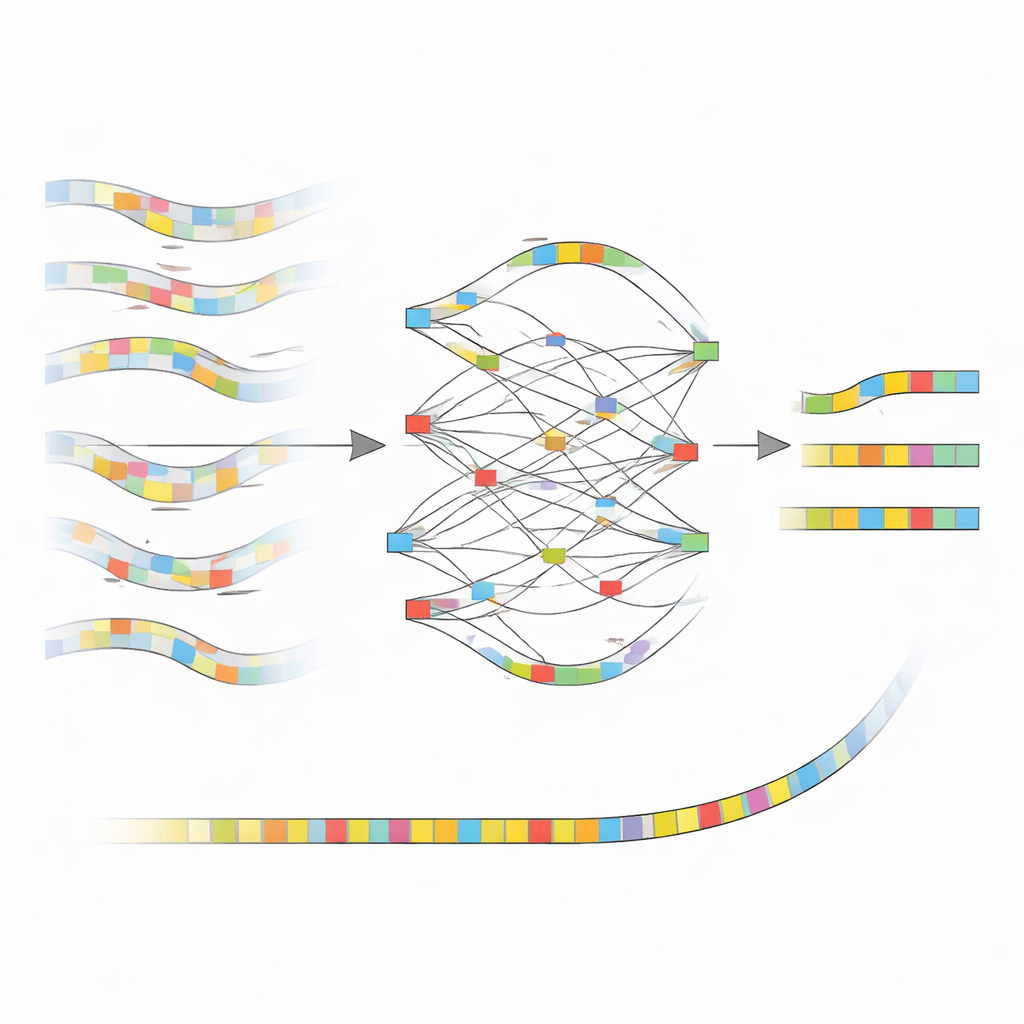
Från brusiga signaler till rena byggstenar
Kärn idén bakom nanoMDBG är att arbeta med en kompakt skiss av varje DNA-fragment istället för varje enskild bokstav. Metoden väljer en gles uppsättning korta DNA-mönster, kallade minimizers, från varje avläsning och behandlar den ordnade listan av dessa mönster som ett lättviktigt fingeravtryck. Tidigare programvara från samma grupp, metaMDBG, använde redan dessa minimizer-fingeravtryck för att effektivt montera mycket precisa PacBio-avläsningar. Men kvarvarande fel i ONT-data tenderade att bryta dessa fingeravtryck och ledde till luckor och felaktiga sammanfogningar. NanoMDBG angriper detta genom att först korrigera ONT-avläsningarna i detta reducerade ”minimizerutrymme.” För varje målavläsning rekryterar algoritmen snabbt ett fåtal av de mest liknande avläsningarna med mycket glesa fingeravtryck, och granskar dem sedan med tätare fingeravtryck för att rensa bort felaktiga matchningar från orelaterade arter.
Hur den nya metoden rensar upp bilden
När nanoMDBG har samlat en pålitlig grupp liknande fingeravtryck överlagrar den dem för att bygga en enkel graf som spårar var mönstren överensstämmer, skiljer sig åt eller visar insättningar och borttagningar. Istället för att titta på varje bas arbetar metoden endast med dessa utvalda mönster, vilket kraftigt reducerar beräkningsbördan. Den mest starkt understödda vägen genom grafen blir ett konsensusfingeravtryck för avläsningen, vilket effektivt jämnar ut många av de ursprungliga sekvenseringsfelen. Alla korrigerade fingeravtryck matas sedan in i den befintliga metaMDBG-assembleraren, som syr ihop dem till längre DNA-bitar och slutligen konverterar dem tillbaka till fullständiga sekvenser, följt av ett poleringssteg för att förfina kvarvarande småfel.
Testning av nanoMDBG i verkliga mikrobiom
Forskarna utvärderade nanoMDBG på flera testfall: en definierad blandning av 21 kända mikrober, ett humant tarmprov, en referensblandning av humant fecesmaterial och en mycket komplex åkerjord. De jämförde dess prestanda med ledande långavläsnings-assemblers, särskilt metaFlye och den tidigare metaMDBG, och tittade på hur många nästan fullständiga genom—kända som metagenom-assemblerade genom, eller MAGs—de kunde återskapa och hur många av dessa som fångades som enstaka kontinuerliga stycken. I alla tre verkliga samhällena producerade nanoMDBG avsevärt fler högkvalitativa MAGs än konkurrerande verktyg, och många fler kompletta, enstaka-kontig-genom. I jorddatasetet på 400 miljarder baspar återvann den till exempel 201 fler nästan fullständiga genomer än metaMDBG och 144 fler än metaFlye, samtidigt som den använde bara en bråkdel av minnet och avslutade bearbetningen på ungefär sex dagar istället för nästan en månad.
Matcha dyr noggrannhet med billigare avläsningar
Eftersom ONT- och PacBio-sekvenserare kördes på samma prover vid matchade djup kunde teamet jämföra teknologierna direkt. För tarm- och standardiserade fecalsamhällen hade PacBio HiFi fortfarande ett försprång i totalt antal förstklassiga genomer, särskilt vid högre sekvenseringsdjup. Ändå kom ONT-data monterade med nanoMDBG förvånansvärt nära, och överträffade till och med HiFi i vissa låg-djups-scenarier. För jordprovet, där tusentals arter samexisterar, var antalet nästan fullständiga genomer från ONT och HiFi i stort sett jämförbara vid högt djup, även om HiFi oftare uppnådde helt kontinuerliga enstaka-kontig-genom. Detaljerade felanalyser visade att nanoMDBG höll felmonteringar och områden med saknad täckning relativt låga och bibehöll fler fullängds proteinkodande gener än konkurrerande ONT-assemblerare, särskilt i det utmanande jorddatasetet.
Vad detta betyder för utforskning av osynliga ekosystem
För icke-specialister är huvudbudskapet att billiga, fältbarbara DNA-sekvenserare nu kan återskapa mikrobiella genom från komplexa miljöer med en kvalitet som närmar sig större, dyrare instrument. NanoMDBG åstadkommer detta genom att listigt förenkla data till återanvändbara mönster, korrigera fel i den kompakta representationen och sedan montera genomer från de rensade mönstren med hög effektivitet. Det gör det möjligt att undersöka många prover, spåra mikrobiella stammar över personer eller platser och utforska den enorma, fortfarande till största delen okända mångfalden av liv i jordar och andra habitat—allt utan superdatorresurser. När algoritmerna fortsätter att förbättras kommer sådana verktyg att föra oss allt närmare rutinmässiga, genomnivå-kartor över hela mikrobiella samhällen.
Citering: Benoit, G., James, R., Raguideau, S. et al. High-quality metagenome assembly from nanopore reads with nanoMDBG. Nat Commun 17, 3556 (2026). https://doi.org/10.1038/s41467-026-69760-y
Nyckelord: metagenomik, nanopore-sekvensering, genommontering, mikrobiom, bioinformatik