Clear Sky Science · es
Ensamblado metagenómico de alta calidad a partir de lecturas nanopore con nanoMDBG
Leer la vida oculta en una cucharada de suelo
Cada pizca de suelo o gota de fluido intestinal está llena de miles de especies microbianas, la mayoría de las cuales no pueden cultivarse en el laboratorio. Para entender qué son y qué hacen, los científicos leen su ADN directamente del ambiente, un campo conocido como metagenómica. Este artículo presenta nanoMDBG, un nuevo método computacional que convierte las señales crudas de un secuenciador de ADN portátil en borradores de genomas de alta calidad, abriendo la puerta a cartografiar mundos microbianos complejos más rápido, más barato y con mucho mayor detalle que antes.
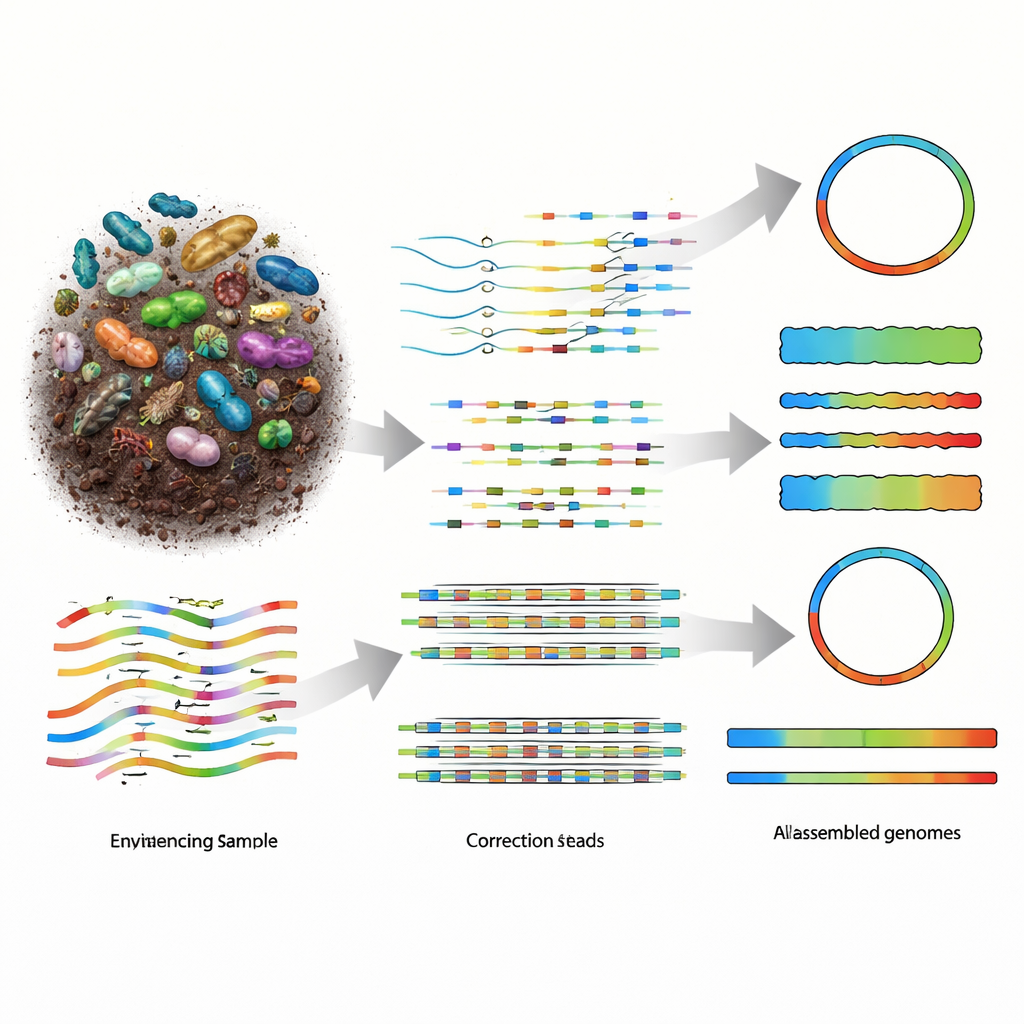
Por qué es tan difícil reconstruir genomas de la naturaleza
La metagenómica funciona fragmentando todo el ADN de una muestra en fragmentos largos, secuenciando esos fragmentos y luego usando software para reensamblarlos en los genomas de los organismos presentes. Las tecnologías antiguas de lecturas cortas proporcionaban muchas piezas pequeñas, pero los rompecabezas resultantes quedaban muy fragmentados, especialmente en comunidades diversas como la del suelo. Las plataformas de lectura larga, incluidas PacBio HiFi y Oxford Nanopore Technologies (ONT), producen piezas de ADN mucho más largas, lo que en teoría facilita la reconstrucción. Las lecturas de PacBio son extremadamente precisas pero más costosas, mientras que los dispositivos de ONT son más asequibles y altamente portátiles, aunque históricamente producían datos más ruidosos. A medida que la química de ONT mejoró hasta aproximadamente un error por cada cien letras de ADN, el campo necesitaba ensambladores que pudieran explotar plenamente este nuevo equilibrio entre longitud, precisión y coste.
De señales ruidosas a bloques de construcción limpios
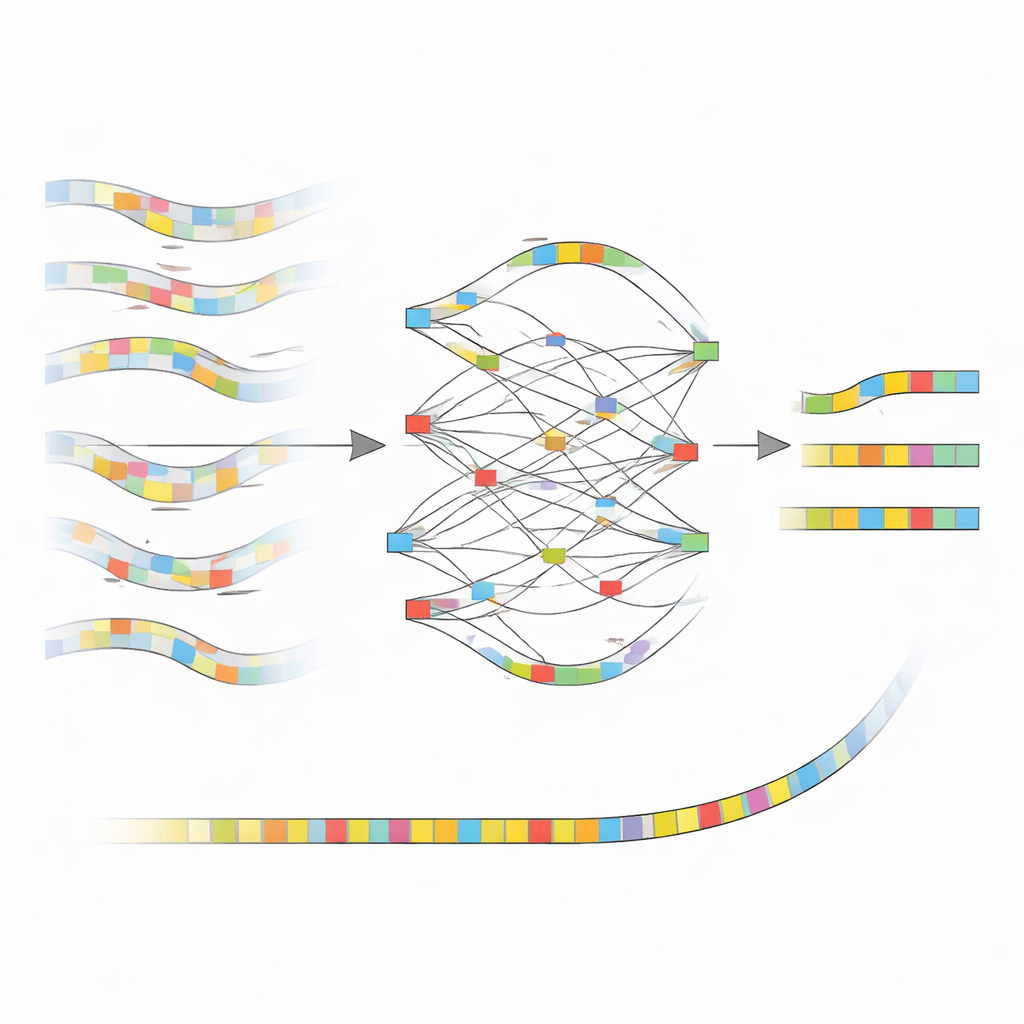
La idea central detrás de nanoMDBG es trabajar con un esbozo compacto de cada fragmento de ADN en lugar de con cada letra. El método selecciona un conjunto disperso de patrones cortos de ADN, llamados minimizadores, de cada lectura y trata la lista ordenada de estos patrones como una huella digital ligera. Software anterior del mismo grupo, metaMDBG, ya utilizaba estas huellas de minimizadores para ensamblar lecturas PacBio muy precisas de forma eficiente. Sin embargo, los errores remanentes en los datos de ONT tendían a romper estas huellas, provocando huecos y empalmes incorrectos. NanoMDBG afronta esto corrigiendo primero las lecturas ONT en este reducido “espacio de minimizadores”. Para cada lectura objetivo, el algoritmo recluta rápidamente un puñado de las lecturas más similares usando huellas muy escasas, y luego las reexamina con huellas más densas para eliminar coincidencias espurias procedentes de especies no relacionadas.
Cómo el nuevo método aclara la imagen
Una vez que nanoMDBG ha reunido un grupo fiable de huellas similares, las sobrepone para construir un grafo sencillo que rastrea dónde los patrones coinciden, discrepan o muestran inserciones y deleciones. En lugar de mirar cada base, trabaja sólo con estos patrones seleccionados, reduciendo enormemente la carga computacional. La ruta con mayor soporte a través de este grafo se convierte en una huella consensuada para la lectura, corrigiendo efectivamente muchos de los errores de secuenciación originales. Todas las huellas corregidas se introducen luego en el ensamblador metaMDBG existente, que las cose en piezas de ADN más largas y finalmente las convierte de nuevo en secuencias completas, seguidas de un paso de pulido para refinar los errores pequeños restantes.
Poniendo a nanoMDBG a prueba en microbiomas reales
Los investigadores evaluaron nanoMDBG en varios escenarios: una mezcla definida de 21 microbios conocidos, una muestra de intestino humano, una mezcla de referencia de material fecal humano y un suelo agrícola muy complejo. Compararon su rendimiento con ensambladores líderes de lecturas largas, en particular metaFlye y el anterior metaMDBG, analizando cuántos genomas casi completos—conocidos como genomas ensamblados de metagenomas, o MAGs—pudieron recuperar y cuántos de esos se capturaron como piezas continuas únicas. En las tres comunidades del mundo real, nanoMDBG produjo sustancialmente más MAGs de alta calidad que las herramientas competidoras, y muchas más genomas completos en un solo contig. En el conjunto de datos de suelo de 400 000 millones de bases, por ejemplo, recuperó 201 genomas casi completos más que metaMDBG y 144 más que metaFlye, mientras usaba sólo una fracción de la memoria y terminaba en unos seis días en vez de casi un mes.
Igualando la precisión cara con lecturas más baratas
Puesto que los secuenciadores ONT y PacBio se ejecutaron en las mismas muestras a profundidades equivalentes, el equipo pudo comparar directamente las tecnologías. Para las comunidades intestinales y fecales estandarizadas, PacBio HiFi aún mantenía una ventaja en el número total de genomas de máxima calidad, especialmente a mayores profundidades de secuenciación. Sin embargo, los datos de ONT ensamblados con nanoMDBG se acercaron sorprendentemente, e incluso superaron a HiFi en algunas condiciones de baja profundidad. Para la muestra de suelo, donde coexisten miles de especies, las cifras de genomas casi completos de ONT y HiFi fueron esencialmente comparables a alta profundidad, aunque HiFi con mayor frecuencia logró genomas completamente continuos en un solo contig. Los análisis detallados de errores mostraron que nanoMDBG mantuvo relativamente bajas las malas ensambladuras y las regiones con cobertura faltante, y conservó más genes codificadores de proteínas de longitud completa que otros ensambladores para ONT, especialmente en el desafiante conjunto de suelo.
Lo que esto significa para explorar ecosistemas invisibles
Para los no especialistas, el mensaje clave es que los secuenciadores de ADN baratos y desplegables en campo pueden ahora reconstruir genomas microbianos de ambientes complejos con una calidad que se aproxima a la de instrumentos más grandes y costosos. NanoMDBG lo logra simplificando inteligentemente los datos en patrones reutilizables, corrigiendo errores en esa representación compacta y luego ensamblando genomas a partir de los patrones limpiados con alta eficiencia. Esto hace factible estudiar muchas muestras, rastrear cepas microbianas entre personas o lugares y explorar la enorme y todavía mayormente inexplorada diversidad de vida en suelos y otros hábitats, todo ello sin recursos de supercomputación. A medida que los algoritmos sigan mejorando, estas herramientas nos acercarán cada vez más a mapas de comunidades microbianas a nivel genómico de uso rutinario.
Cita: Benoit, G., James, R., Raguideau, S. et al. High-quality metagenome assembly from nanopore reads with nanoMDBG. Nat Commun 17, 3556 (2026). https://doi.org/10.1038/s41467-026-69760-y
Palabras clave: metagenómica, secuenciación nanopore, ensamblaje de genomas, microbioma, bioinformática