Clear Sky Science · ar
تجميع متجانسة عالية الجودة للميتاجينوم من قراءات النانوبور باستخدام nanoMDBG
قراءة الحياة الخفية في ملعقة من التربة
كل قبضة من التربة أو قطرة من سائل الأمعاء تعج بآلاف الأنواع الميكروبية، ومعظمها لا يمكن زراعته في المختبر. لفهم ما هي هذه الكائنات وما الذي تفعله، يقرأ العلماء حمضها النووي مباشرة من البيئة، وهو مجال يُعرف بالميتاجينوميكس. تقدم هذه المقالة nanoMDBG، طريقة حسابية جديدة تحول الإشارات الخام من جهاز تسلسل DNA محمول إلى مسودات جينومية عالية الجودة، فاتحة الباب لرسم خرائط العوالم الميكروبية المعقدة بسرعة أكبر وتكلفة أقل وبتفصيل أكبر بكثير مما كان متاحًا من قبل.
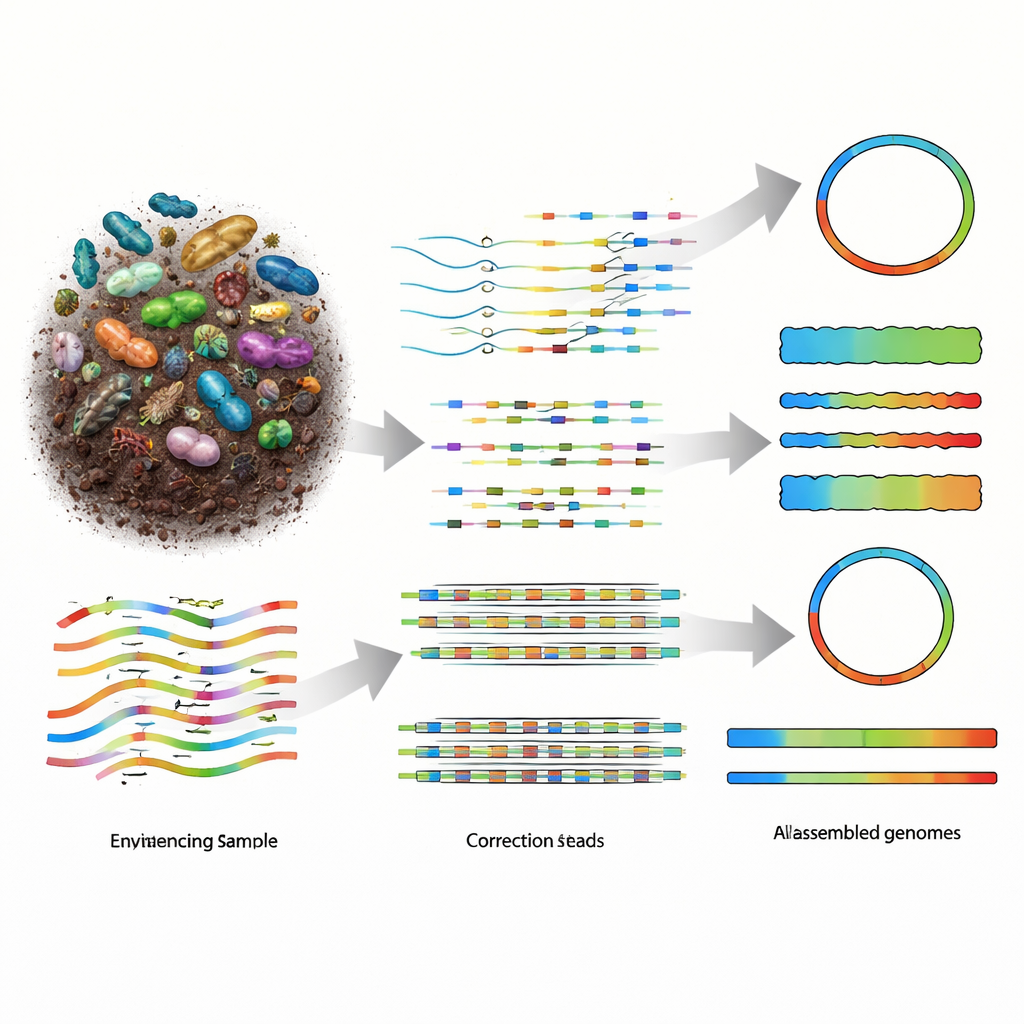
لماذا إعادة بناء الجينومات من الطبيعة صعبة جدًا
تعمل الميتاجينوميكس عن طريق قطع كل الحمض النووي في عينة إلى أجزاء طويلة، وتسلسل تلك الأجزاء، ثم استخدام برامج لإعادة تجميعها إلى جينومات الكائنات التي كانت موجودة. قدمت تقنيات القراءة القصيرة القديمة الكثير من القطع الصغيرة، لكن الألغاز الناتجة كانت متجزئة بشدة، خاصة في مجتمعات متنوعة مثل التربة. تنتج منصات التسلسل طويلة القراءة، بما في ذلك PacBio HiFi وOxford Nanopore Technologies (ONT)، قطعًا أطول بكثير من الحمض النووي، مما ينبغي أن يسهل إعادة البناء. قراءات PacBio دقيقة للغاية لكنها أكثر تكلفة، في حين أن أجهزة ONT أكثر قدرة على التنقل وأرخص، لكنها تاريخيًا أنتجت بيانات أكثر ضوضاء. مع تحسّن كيمياء ONT إلى مستوى يقارب خطأ واحد لكل مئة حرف DNA، احتاج المجال إلى برامج تجميع يمكنها استغلال هذا التوازن الجديد بين الطول والدقة والتكلفة بشكل كامل.
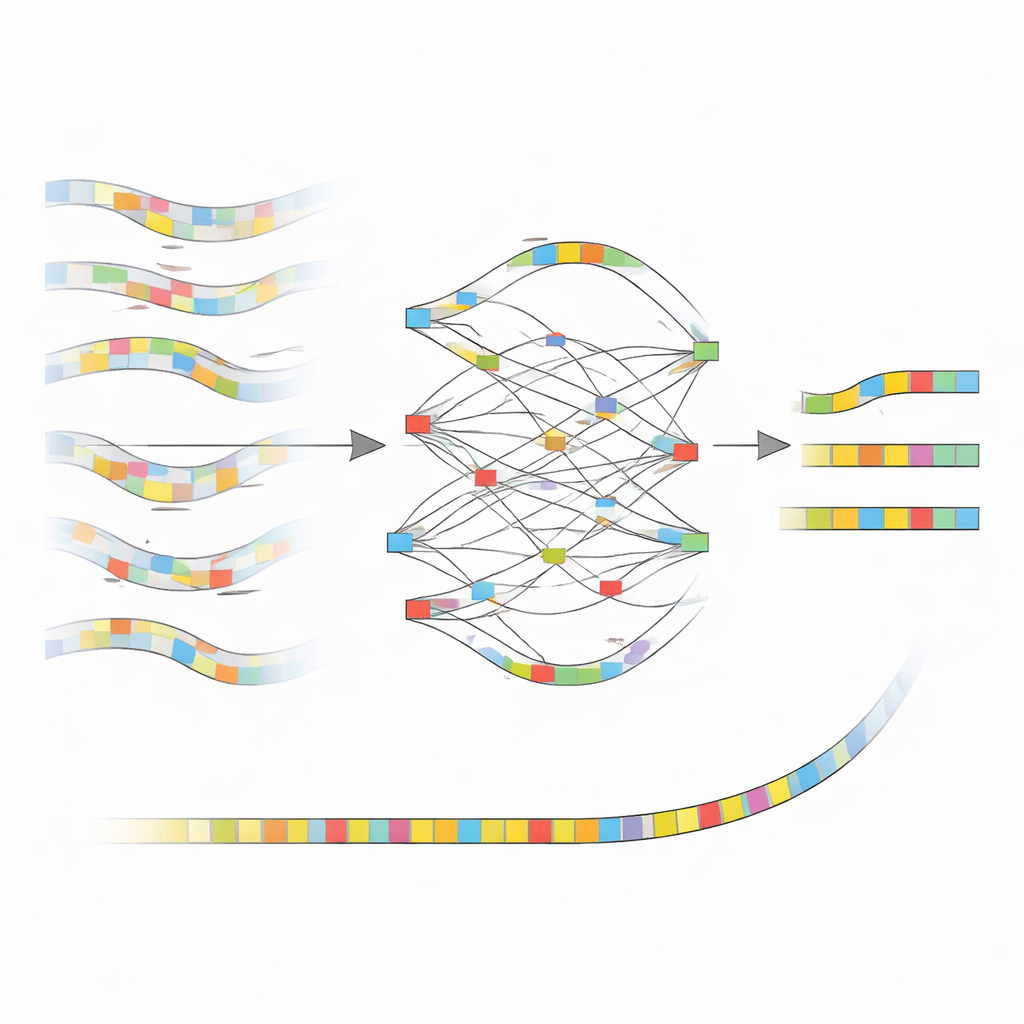
من الإشارات الصاخبة إلى وحدات بناء نظيفة
الفكرة الأساسية وراء nanoMDBG هي العمل بمخطط مضغوط لكل قطعة من الحمض النووي بدلاً من كل حرف منفرد. تختار الطريقة مجموعة متفرقة من أنماط الحمض النووي القصيرة، تُسمى minimizers، من كل قراءة وتتعامل مع القائمة المرتبة لهذه الأنماط كختم بصمة خفيف الوزن. استخدم برنامج سابق من نفس المجموعة، metaMDBG، هذه البصمات القائمة على minimizers لتجميع قراءات PacBio الدقيقة بكفاءة. ومع ذلك، كانت الأخطاء المتبقية في بيانات ONT تميل إلى تمزيق هذه البصمات، مما يؤدي إلى فجوات وارتباطات خاطئة. يتعامل nanoMDBG مع هذا أولًا عن طريق تصحيح قراءات ONT في هذا "فضاء minimizer" المُخفض. لكل قراءة مستهدفة، يستقطب الخوارزم سريعًا عددًا قليلاً من القراءات الأكثر تشابهًا باستخدام بصمات متفرقة جدًا، ثم يعيد فحصها ببصمات أكثر كثافة لاستبعاد المطابقات الزائفة القادمة من أنواع غير ذات صلة.
كيف تنظف الطريقة الجديدة الصورة
بمجرد أن يجمع nanoMDBG مجموعة موثوقة من البصمات المتشابهة، يراكبها لبناء رسم بياني بسيط يتتبع أماكن الاتفاق والاختلاف أو وجود إدخالات وحذف. بدلاً من النظر إلى كل قاعدة، يعمل فقط بهذه الأنماط المختارة، مما يقلل بكثير من عبء الحوسبة. يصبح المسار الأكثر دعمًا عبر هذا الرسم البياني هو بصمة التوافق للقراءة، مما يكوي العديد من أخطاء التسلسل الأصلية. ثم تُغذى كل البصمات المصححة إلى برنامج التجميع الموجود metaMDBG، الذي يخيطها إلى قطع أطول من الحمض النووي ويحولها أخيرًا مرة أخرى إلى تسلسلات كاملة، يتبعها خطوة تلميع لتحسين الأخطاء الصغيرة المتبقية.
تجربة nanoMDBG في ميكروبيومات حقيقية
قيّم الباحثون nanoMDBG على عدة مجموعات اختبار: خليط معرف مكوَّن من 21 ميكروبًا معروفًا، عينة من أمعاء بشرية، خليط مرجعي من مادة برازية بشرية، وتربة زراعية معقدة جدًا. قارنوا أدائه مع أهم مجمِّعات القراءات الطويلة، ولا سيما metaFlye ونسخة metaMDBG السابقة، مع تتبع عدد الجينومات القريبة من الاكتمال—المعروفة باسم الجينومات المجمعة من الميتاجينوم أو MAGs—التي تمكنوا من استرجاعها وعدد تلك التي تم تجميعها كقطع متصلة مفردة. عبر جميع المجتمعات الحقيقية الثلاثة، أنتج nanoMDBG عددًا أكبر بكثير من MAGs عالية الجودة مقارنة بالأدوات المتنافسة، والعديد من الجينومات الكاملة أحادية المقاطع. في مجموعة بيانات التربة التي تضم 400 مليار قاعدة، على سبيل المثال، استعاد 201 جينومًا قريبا من الاكتمال أكثر من metaMDBG و144 أكثر من metaFlye، مع استخدام جزء بسيط فقط من الذاكرة والانتهاء في حوالي ستة أيام بدلًا من ما يقرب من شهر.
مطابقة الدقة المكلفة بقراءات أرخص
بما أن أجهزة ONT وPacBio شغلت على نفس العينات بنفس أعماق التسلسل، تمكن الفريق من مقارنة التقنيات مباشرة. بالنسبة لمجتمعات الأمعاء والمنتجات البرازية المعيارية، لا تزال PacBio HiFi متفوقة في العدد الإجمالي للجينومات ذات الجودة الأعلى، خاصة عند أعماق تسلسل أعلى. ومع ذلك، جاءت بيانات ONT التي جُمعت بواسطة nanoMDBG قريبة بشكل مدهش، وتفوّقت على HiFi في بعض حالات العمق المنخفض. بالنسبة لعينة التربة، حيث تتعايش آلاف الأنواع، كانت أعداد الجينومات القريبة من الاكتمال من ONT وHiFi متقاربة أساسًا عند العمق العالي، رغم أن HiFi حققت في كثير من الأحيان جينومات متصلة تمامًا مفردة أكثر. أظهرت تحليلات الأخطاء التفصيلية أن nanoMDBG حافظ على معدلات التجميع الخاطئ ومناطق التغطية المفقودة منخفضة نسبيًا وحافظ على المزيد من الجينات المشفرة للبروتين كاملة الطول مقارنة بمجمّعات ONT المتنافسة، خاصة في مجموعة بيانات التربة الصعبة.
ماذا يعني هذا لاستكشاف النُظُم البيئية الخفية
بالنسبة لغير المختصين، الرسالة الأساسية هي أن أجهزة تسلسل الحمض النووي الرخيصة والقابلة للاستخدام ميدانيًا يمكنها الآن إعادة بناء جينومات ميكروبية من بيئات معقدة بجودة تقترب من تلك الخاصة بالأجهزة الأكبر والأكثر تكلفة. يحقق nanoMDBG ذلك عن طريق تبسيط البيانات بذكاء إلى أنماط قابلة لإعادة الاستخدام، وتصحيح الأخطاء في هذا التمثيل المدمج، ثم تجميع الجينومات من الأنماط المنقّاة بكفاءة عالية. يجعل هذا من الممكن مسح العديد من العينات، وتتبع سلالات ميكروبية عبر الأشخاص أو المواقع، واستكشاف التنوع الهائل والغالبًا غير المرسوم بعد للحياة في التربة وموائل أخرى، كل ذلك دون الحاجة إلى موارد حوسبة بحجم الحواسيب العملاقة. مع استمرار تحسّن الخوارزميات، ستقربنا هذه الأدوات أكثر فأكثر من خرائط روتينية على مستوى الجينوم للمجتمعات الميكروبية بأكملها.
الاستشهاد: Benoit, G., James, R., Raguideau, S. et al. High-quality metagenome assembly from nanopore reads with nanoMDBG. Nat Commun 17, 3556 (2026). https://doi.org/10.1038/s41467-026-69760-y
الكلمات المفتاحية: الميتاجينوميكس, التسلسل النانوبور, تجميع الجينوم, الميكروبيوم, المعلوماتية الحيوية