Clear Sky Science · pt
Montagem de metagenomas de alta qualidade a partir de leituras nanopore com nanoMDBG
Lendo a vida escondida em uma porção de solo
Cada pitada de solo ou gota de fluido intestinal abriga milhares de espécies microbianas, a maioria das quais não pode ser cultivada em laboratório. Para entender o que são e o que fazem, cientistas leem seu DNA diretamente do ambiente, um campo conhecido como metagenômica. Este artigo apresenta o nanoMDBG, um novo método computacional que transforma sinais brutos de um sequenciador de DNA portátil em rascunhos de genomas de alta qualidade, abrindo a porta para mapear mundos microbianos complexos mais rápido, mais barato e com muito mais detalhe do que antes.
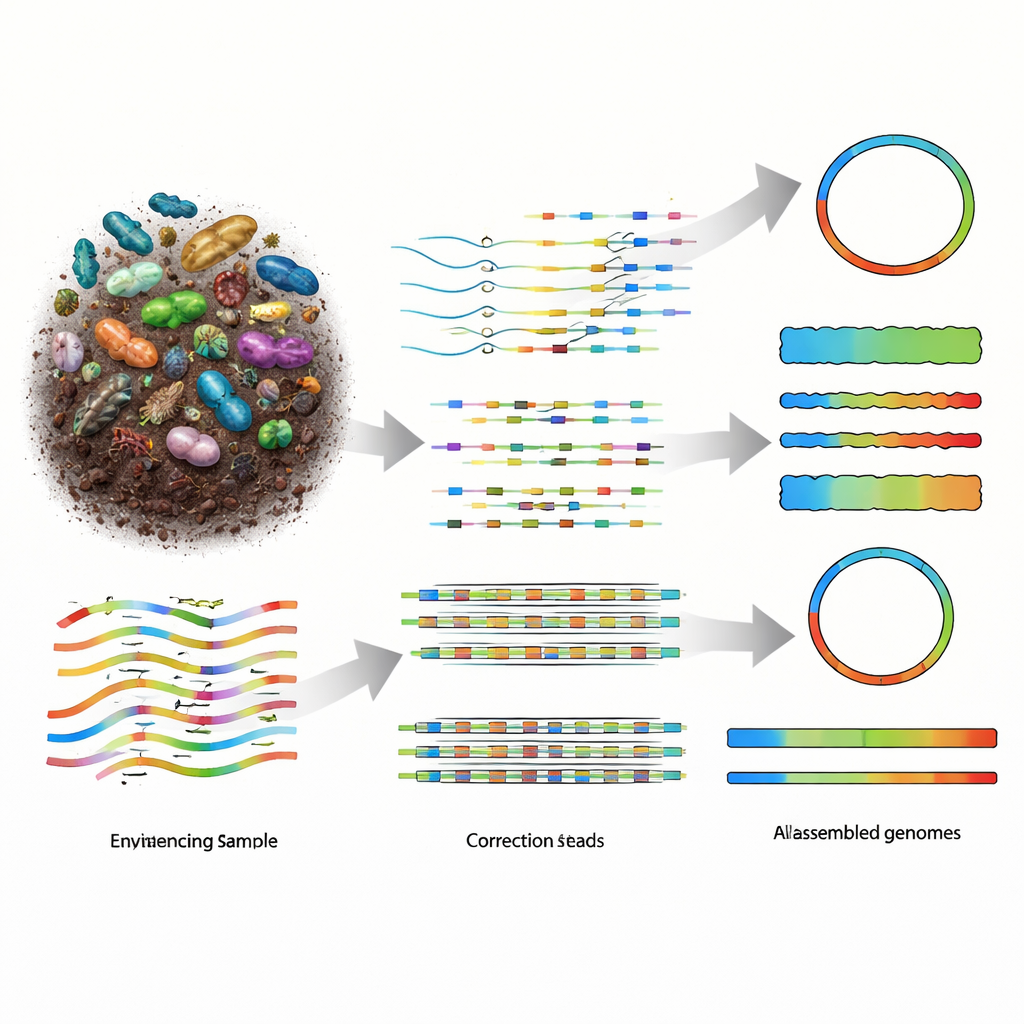
Por que reconstruir genomas da natureza é tão difícil
A metagenômica funciona fragmentando todo o DNA em uma amostra em longos fragmentos, sequenciando esses fragmentos e então usando software para reconstituí-los nos genomas dos organismos presentes. Tecnologias antigas de leituras curtas forneciam muitas peças pequenas, mas os quebra-cabeças resultantes ficavam muito fragmentados, especialmente em comunidades diversas como o solo. Plataformas de sequenciamento de leituras longas, incluindo PacBio HiFi e Oxford Nanopore Technologies (ONT), geram pedaços de DNA muito maiores, o que deveria facilitar a reconstrução. As leituras do PacBio são extremamente precisas, porém mais caras, enquanto os dispositivos ONT são mais acessíveis e altamente portáteis, mas historicamente produziam dados mais ruidosos. À medida que a química da ONT melhorou para cerca de um erro a cada cem letras de DNA, o campo precisou de montadores que pudessem explorar plenamente esse novo equilíbrio entre comprimento, precisão e custo.
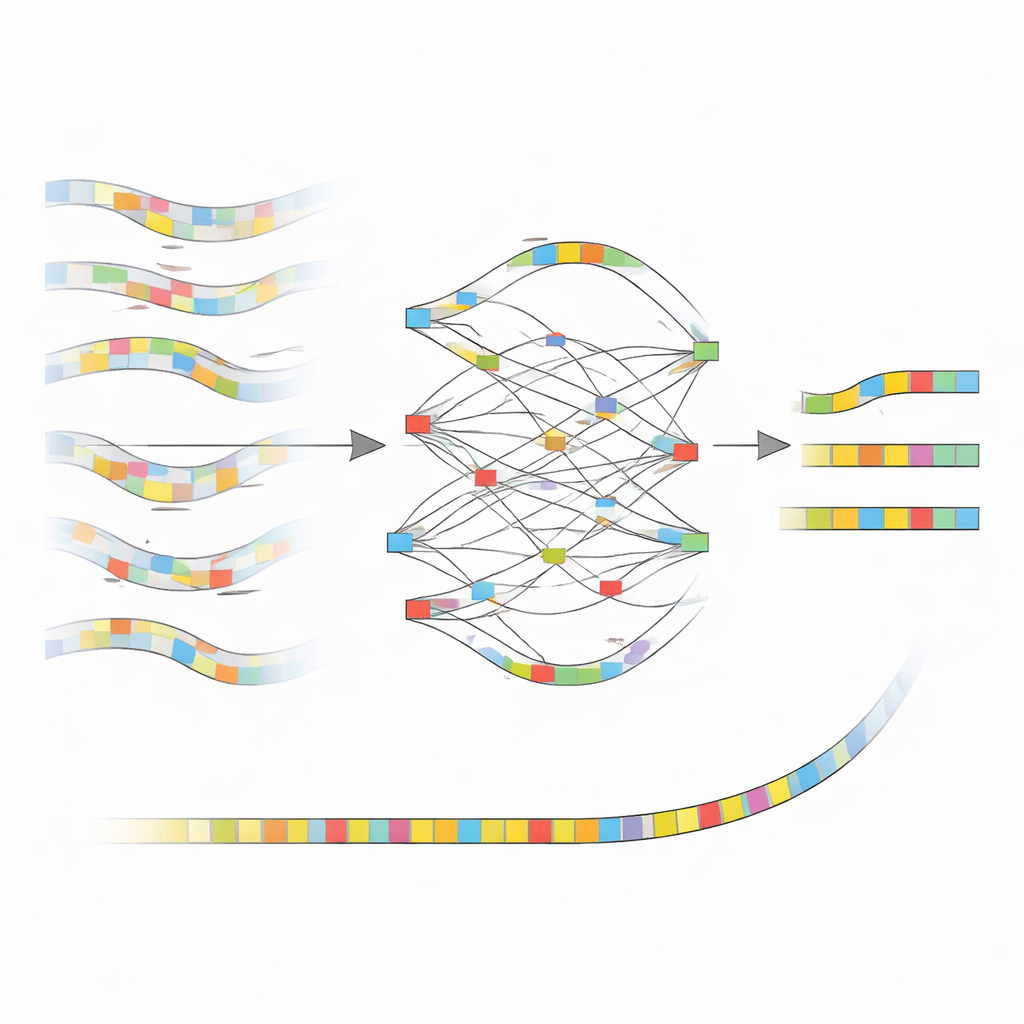
De sinais ruidosos a blocos de construção limpos
A ideia central por trás do nanoMDBG é trabalhar com um esboço compacto de cada fragmento de DNA em vez de cada letra individual. O método seleciona um conjunto esparso de padrões curtos de DNA, chamados minimizadores, de cada leitura e trata a lista ordenada desses padrões como uma impressão digital leve. Softwares anteriores do mesmo grupo, como o metaMDBG, já usavam essas impressões de minimizadores para montar leituras PacBio muito precisas de forma eficiente. Contudo, os erros remanescentes nos dados ONT tendiam a quebrar essas impressões, levando a lacunas e junções incorretas. O nanoMDBG resolve isso corrigindo primeiro as leituras ONT nesse espaço reduzido de “minimizadores”. Para cada leitura-alvo, o algoritmo rapidamente recruta um conjunto pequeno das leituras mais similares usando impressões muito esparsas, então as reexamina com impressões mais densas para eliminar correspondências espúrias de espécies não relacionadas.
Como o novo método limpa o quadro
Uma vez que o nanoMDBG reuniu um grupo confiável de impressões similares, ele as sobrepõe para construir um gráfico simples que rastreia onde os padrões concordam, discordam ou mostram inserções e deleções. Em vez de olhar cada base, trabalha apenas com esses padrões selecionados, reduzindo muito a carga computacional. O caminho mais fortemente suportado através desse gráfico torna-se uma impressão consensual para a leitura, eliminando efetivamente muitos dos erros originais do sequenciamento. Todas as impressões corrigidas são então alimentadas no montador metaMDBG existente, que as costura em fragmentos de DNA mais longos e finalmente as converte de volta em sequências completas, seguidas por uma etapa de polimento para refinar os pequenos erros remanescentes.
Testando o nanoMDBG em microbiomas reais
Os pesquisadores avaliaram o nanoMDBG em vários cenários: uma mistura definida de 21 micróbios conhecidos, uma amostra do intestino humano, uma mistura referência de material fecal humano e um solo agrícola muito complexo. Compararam seu desempenho com montadores de leituras longas líderes, notavelmente metaFlye e o metaMDBG anterior, observando quantos genomas quase completos — conhecidos como genomas montados de metagenoma, ou MAGs — conseguiram recuperar e quantos desses foram obtidos como peças contínuas únicas. Em todas as três comunidades reais, o nanoMDBG produziu substancialmente mais MAGs de alta qualidade do que as ferramentas concorrentes, e muito mais genomas completos em único contig. No conjunto de dados de solo de 400 bilhões de bases, por exemplo, recuperou 201 genomas quase completos a mais que o metaMDBG e 144 a mais que o metaFlye, usando apenas uma fração da memória e terminando em cerca de seis dias em vez de quase um mês.
Igualando a precisão cara com leituras mais baratas
Como os sequenciadores ONT e PacBio foram executados nas mesmas amostras com profundidades equivalentes, a equipe pôde comparar diretamente as tecnologias. Para comunidades intestinais e fecais padronizadas, o PacBio HiFi ainda manteve vantagem no número total de genomas de primeira linha, especialmente em maiores profundidades de sequenciamento. Ainda assim, os dados ONT montados com o nanoMDBG chegaram surpreendentemente perto e até superaram o HiFi em algumas condições de baixa profundidade. Para a amostra de solo, onde milhares de espécies coexistem, os números de genomas quase completos obtidos por ONT e HiFi foram essencialmente comparáveis em alta profundidade, embora o HiFi tenha conseguido com mais frequência genomas totalmente contínuos em único contig. Análises detalhadas de erros mostraram que o nanoMDBG manteve taxas relativamente baixas de montagem incorreta e de regiões com cobertura ausente, e preservou mais genes codificadores de proteína em tamanho integral do que montadores ONT concorrentes, especialmente no exigente conjunto de solo.
O que isso significa para explorar ecossistemas invisíveis
Para não especialistas, a mensagem principal é que sequenciadores de DNA baratos e portáteis agora podem reconstruir genomas microbianos de ambientes complexos com qualidade próxima à de instrumentos maiores e mais caros. O nanoMDBG consegue isso ao simplificar inteligentemente os dados em padrões reutilizáveis, corrigir erros nessa representação compacta e então montar genomas a partir dos padrões limpos com alta eficiência. Isso torna viável investigar muitas amostras, rastrear cepas microbianas entre pessoas ou locais e explorar a enorme e ainda em grande parte inexplorada diversidade da vida em solos e outros habitats, tudo sem recursos de supercomputador. À medida que os algoritmos continuarem a melhorar, tais ferramentas nos aproximarão cada vez mais de mapas rotineiros em nível genômico de comunidades microbianas inteiras.
Citação: Benoit, G., James, R., Raguideau, S. et al. High-quality metagenome assembly from nanopore reads with nanoMDBG. Nat Commun 17, 3556 (2026). https://doi.org/10.1038/s41467-026-69760-y
Palavras-chave: metagenômica, sequenciamento nanopore, montagem de genomas, microbioma, bioinformática