Clear Sky Science · he
הרכבת מטאגנום באיכות גבוהה מקריאות nanopore עם nanoMDBG
לקרוא חיים נסתרים בכפית אדמה
כל קרשוף אדמה או טיפת נוזל מעיים שוקקת באלפי מינים מיקרוביאליים, שרובם אינם ניתנים לגידול במעבדה. כדי להבין מי הם ומה הם עושים, מדענים קוראים את ה‑DNA שלהם ישירות מהסביבה — תחום המוכר כמתאגנומי (מטאגנומיקה). מאמר זה מציג את nanoMDBG, שיטה חישובית חדשה שמשתמשת באותות גולמיים ממכשיר ריצוף DNA נייד כדי לייצר טיוטות גנומים באיכות גבוהה, ופותחת אפשרות למיפוי של עולמות מיקרוביאליים מסובכים מהר יותר, בזול יותר ובפירוט רב הרבה יותר מאי‑פעם.
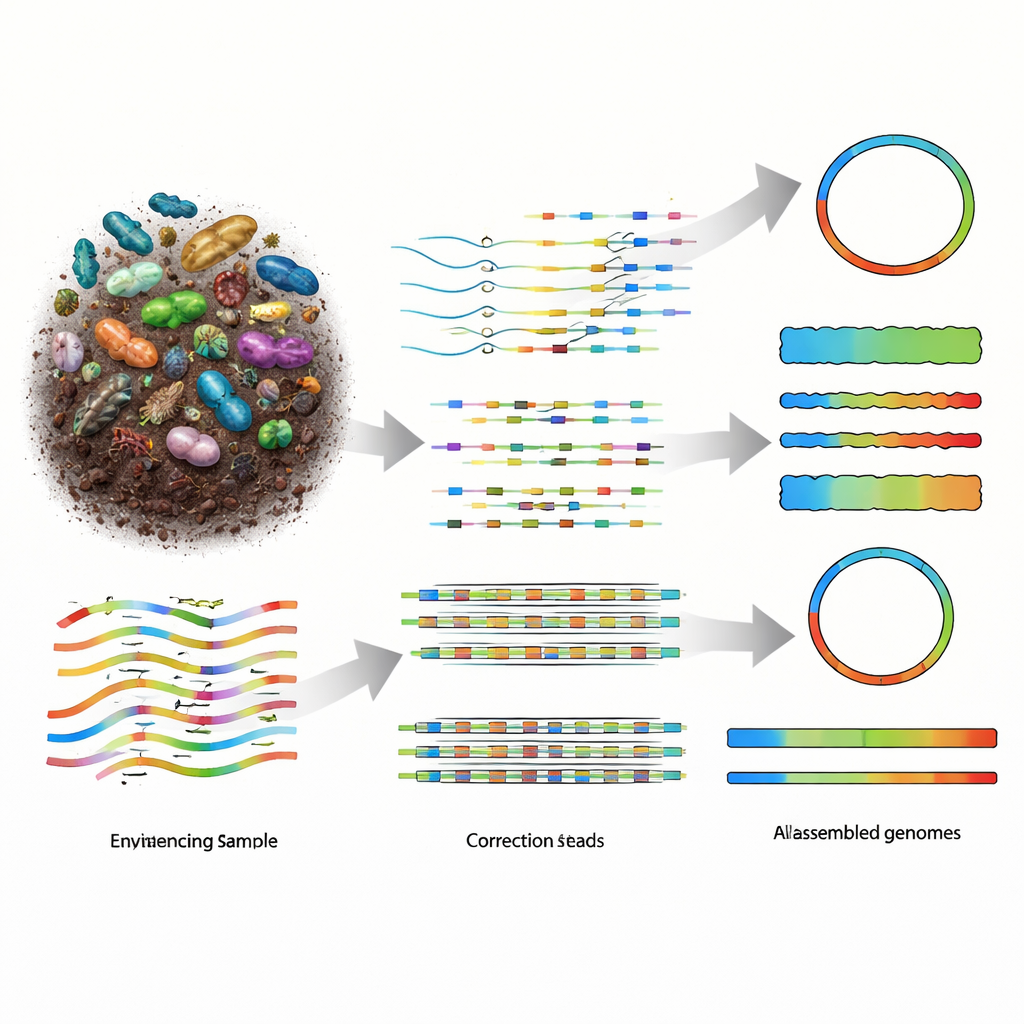
מדוע קשה כל כך לבנות מחדש גנומים מהטבע
מטאגנומיקה פועלת על ידי פירוק כל ה‑DNA בדגימה לקטעים ארוכים, ריצוף הקטעים האלה, ואז שימוש בתוכנה כדי להרכיבם חזרה לגנומים של האורגניזמים שהיו נוכחים. טכנולוגיות ריצוף קצרות ישנות סיפקו הרבה חלקים קטנים, אך הפאזלים שהתגלגלו היו מפורקים מאוד, במיוחד בקהילות מגוונות כמו אדמה. פלטפורמות ריצוף ארוכות־קריאה, כולל PacBio HiFi ו‑Oxford Nanopore Technologies (ONT), מייצרות קטעי DNA ארוכים בהרבה, מה שאמור להקל על השחזור. קריאות ה‑PacBio מדויקות מאוד אך יקרות יותר, בעוד שמכשירי ONT נגישים וזולים יותר לניידות, אך היסטורית נתנו נתונים רעשניים יותר. כאשר הכימיה של ONT השתפרה לכדי שגיאה אחת בערך בכל מאית האותיות, נזקק השדה לאסמבלרים שיכולים לנצל במלואן את השילוב החדש של אורך, דיוק ועלות.
מאותות רועשים לחסימות בנייה נקיות
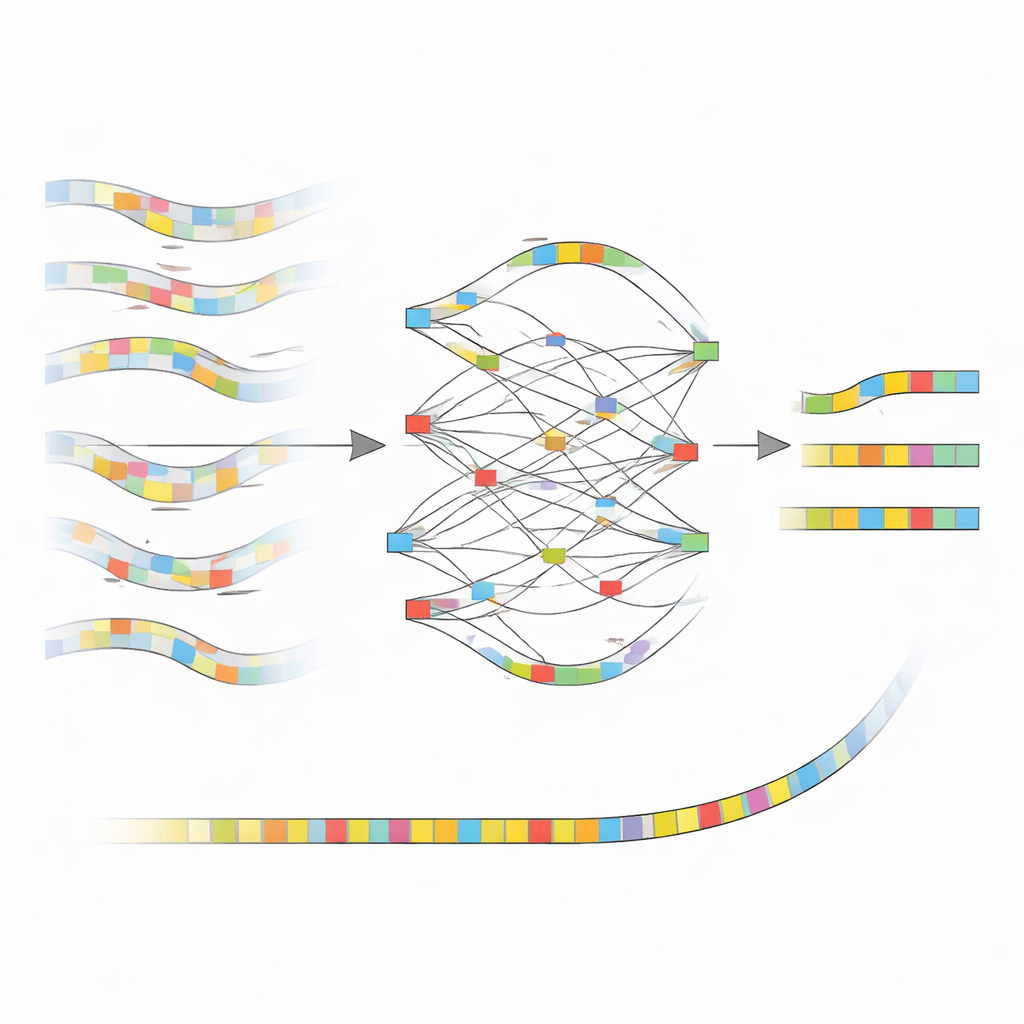
הרעיון המרכזי מאחורי nanoMDBG הוא לעבוד עם טיוטה קומפקטית של כל מקטע DNA במקום עם כל אות ואות. השיטה בוחרת סט דחוס של דפוסי DNA קצרים, הנקראים מינימייזרים, מכל קריאה וטורחת את רשימת הדפוסים הממוינת כטביעת אצבע קלה־משקל. תוכנה קודמת מאותה קבוצת מחקר, metaMDBG, כבר השתמשה בטביעות אצבע של מינימייזרים להרכבת קריאות PacBio מדויקות ביעילות. עם זאת, השגיאות שנותרו בנתוני ONT נטו לשבור את טביעות האצבע הללו, מה שהוביל לפערים ולחיבורים שגויים. NanoMDBG מתמודד עם זה על‑ידי תיקון קריאות ONT במקום המצומצם הזה — "מרחב המינימייזרים". עבור כל קריאה ממוקדת, האלגוריתם מגייס במהירות כמה קריאות שהן הדומות ביותר בעזרת טביעות אצבע דלילות מאוד, ואז בוחן אותן שוב בטביעות צפופות יותר כדי לסנן התאמות מקריות ממינים שאינם קשורים.
כיצד השיטה החדשה מנקה את התמונה
ברגע ש‑nanoMDBG אגרת קבוצה מהימנה של טביעות אצבע דומות, היא משווה ביניהן כדי לבנות גרף פשוט העוקב היכן הדפוסים מסכימים, מתנגשים או מציגים הוספות ומחיקות. במקום להסתכל על כל בסיס ובסיס, היא עובדת רק עם הדפוסים הנבחרים האלה, מה שמקטין משמעותית את העומס החישובי. הנתיב התומך ביותר בגרף הופך לטביעת אצבע קונסנסוס עבור הקריאה, וכך מסדר מחדש רבות מהטעויות של הריצוף המקורי. כל טביעות האצבע המתוקנות מוזנות לאחר מכן לתוכנת metaMDBG הקיימת, שמחברת אותן לחתיכות DNA ארוכות יותר ולבסוף ממירה אותן חזרה לרצפים מלאים, ואחריה שלב ליטוש לשיפור שגיאות קטנות נותרות.
מביאים את nanoMDBG למבחן במיקרוביומות אמיתיות
החוקרים העריכו את nanoMDBG על מספר מערכי מבחן: תערובת מוגדרת של 21 מיקרובים ידועים, דגימת מעי אנושי, תערובת תקנונית של חומר צואתי אנושי, ואדמה חקלאית מורכבת מאוד. הם השוו את הביצועים שלה מול אסמבלרים מובילים לקריאות ארוכות, בייחוד metaFlye והגרסה הקודמת metaMDBG, והתמקדו במספר הגנומים כמעט‑המלאים — שנקראים MAGs (metagenome‑assembled genomes) — שהצליחו לשחזר וכמה מהם הופקו כחתיכה רציפה אחת. בכל שלוש הקהילות בעולם האמיתי, nanoMDBG הניבה מספר גדול משמעותית של MAGs באיכות גבוהה בהשוואה לכלים מתחרים, ורבים יותר של גנומים שלמים בחתיכה יחידה. בדאטהסט של אדמה בגודל כ‑400 מיליארד בסיסים, למשל, היא שחזרה 201 גנומים כמעט‑מלאים יותר מאשר metaMDBG ו‑144 יותר מאשר metaFlye, תוך שימוש בחלק קטן בלבד מהזיכרון והשלמה בכשישה ימים במקום כמעט חודש.
התאמת דיוק יקר לקריאות זולות יותר
מכיוון שמכשירי ONT ו‑PacBio הופעלו על אותם דגימות בעומקים תואמים, הצוות יכל להשוות טכנולוגיות באופן ישיר. עבור קהילות מעי וקהילות צואה תקנוניות, ל‑PacBio HiFi עדיין יש יתרון במספר הכולל של גנומים באיכות הגבוהה ביותר, במיוחד בעומקי ריצוף גבוהים יותר. עם זאת, נתוני ONT שהורכבו עם nanoMDBG התקרבו באופן מפתיע ואף השיגו ביצועים טובים יותר מ‑HiFi בתנאי עומק נמוך בחלק מהמקרים. בדגימת האדמה, שבה מתקיימים אלפי מינים יחד, מספרי הגנומים כמעט‑המלאים שנגזרו מ‑ONT ו‑HiFi היו במידה רבה שניתנים להשוואה בעומק גבוה, אם כי HiFi השיג לעתים קרובות יותר גנומים רציפים לחלוטין בחתיכה יחידה. ניתוחי שגיאות מפורטים הראו ש‑nanoMDBG שמרה על שיעורי חיבורים שגויים ואזורים עם כיסוי חסר יחסית נמוכים ושמרה יותר גנים המקודדים חלבון באורך מלא מאשר אסמבלרים מתחרים ל‑ONT, במיוחד בדגימת האדמה המאתגרת.
מה זה אומר לחקירת מערכות אקולוגיות בלתי נראות
ללא‑מומחים, המסר המרכזי הוא שמכשירי ריצוף DNA זולים וניידים מסוגלים כעת לשחזר גנומי מיקרובים מסביבות מורכבות באיכות שמתקרבת לזו של מכשירים גדולים ויקרים יותר. nanoMDBG משיג זאת על‑ידי פישוט חכם של הנתונים לדפוסים חסכוניים, תיקון שגיאות במיצוג המצומצם הזה, ולאחר מכן הרכבת גנומים מהדפוסים המתוקנים ביעילות גבוהה. זה מאפשר לסרוק דגימות רבות, לעקוב אחרי זני מיקרובים בין אנשים או מקומות, ולחקור את המגוון העצום שעוד רובו ככולו לא מופה בקרקע ובאזורים אחרים — והכל מבלי להזדקק למשאבי מחשוב בסדר גודל של מחשבים-על. ככל שהאלגוריתמים ימשיכו להשתפר, כלים כאלה יקרבו אותנו יותר ויותר למפות שגרתיות ברמת גנום של קהילות מיקרוביאליות שלמות.
ציטוט: Benoit, G., James, R., Raguideau, S. et al. High-quality metagenome assembly from nanopore reads with nanoMDBG. Nat Commun 17, 3556 (2026). https://doi.org/10.1038/s41467-026-69760-y
מילות מפתח: מטאגנומיקה, ריצוף nanopore, הרכבת רצף גנום, מיקרוביום, ביואינפורמטיקה