Clear Sky Science · pt
Detecção versátil e sensível de mono- e poli(ADP-ribosil)ação revela remodelamento dependente de XRCC1 na sinalização de PARP1
Por que pequenas marcas químicas no nosso sistema de reparo do DNA importam
Cada célula do nosso corpo está constantemente reparando danos em seu DNA. Se esse reparo falha, o resultado pode ser câncer, neurodegeneração ou morte celular. Um ator-chave nessa rede de reparo é uma proteína chamada PARP1, que adorna a si mesma e proteínas próximas com pequenas etiquetas semelhantes a açúcares, feitas a partir de NAD+. Essas etiquetas aparecem em formas curtas e longas e funcionam como sinais que recrutam outros fatores de reparo. Até agora, os cientistas careciam de ferramentas precisas para ver e distinguir esses diferentes tipos de marca dentro das células, especialmente em contextos de doença. Este estudo constrói essas ferramentas e as usa para revelar uma mudança inesperada na sinalização de reparo do DNA quando outra proteína de reparo, XRCC1, está ausente.
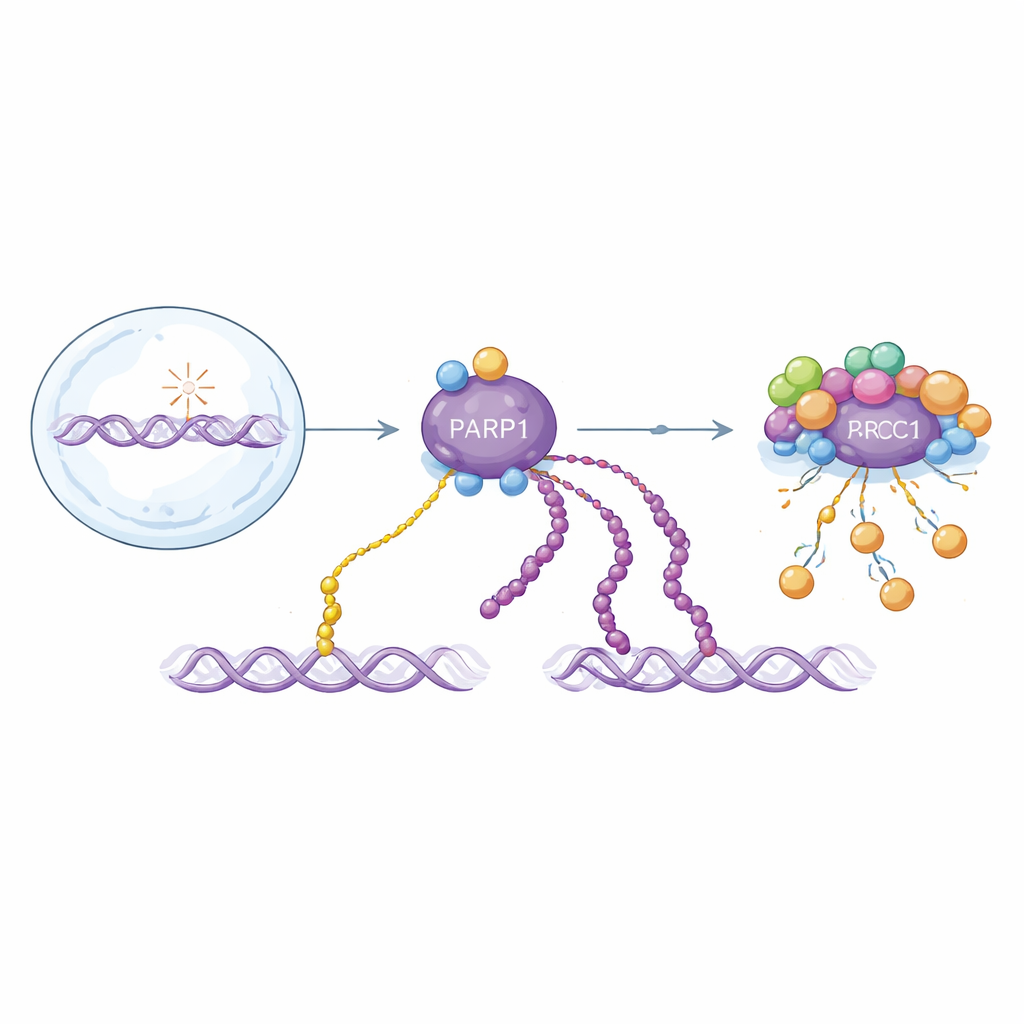
Dois sabores de um sinal crítico de reparo do DNA
PARP1 responde a quebras na fita do DNA ligando unidades de ADP-ribose a si mesmo e a outras proteínas. Essas modificações existem como unidades únicas (mono-ADP-ribosilação) ou como longas cadeias (poli-ADP-ribosilação). Ambas as formas ajudam a organizar o reparo, mas se comportam de forma diferente ao longo do tempo: cadeias longas aparecem em um surto inicial rápido e são rapidamente removidas, enquanto unidades únicas se acumulam mais lentamente e persistem por mais tempo. Como ambas as formas são construídas a partir do mesmo bloco de construção, a maioria dos métodos de detecção existentes as confunde. Isso dificulta entender como cada uma contribui para a saúde e a doença, ou como os medicamentos que têm como alvo PARP1 realmente atuam.
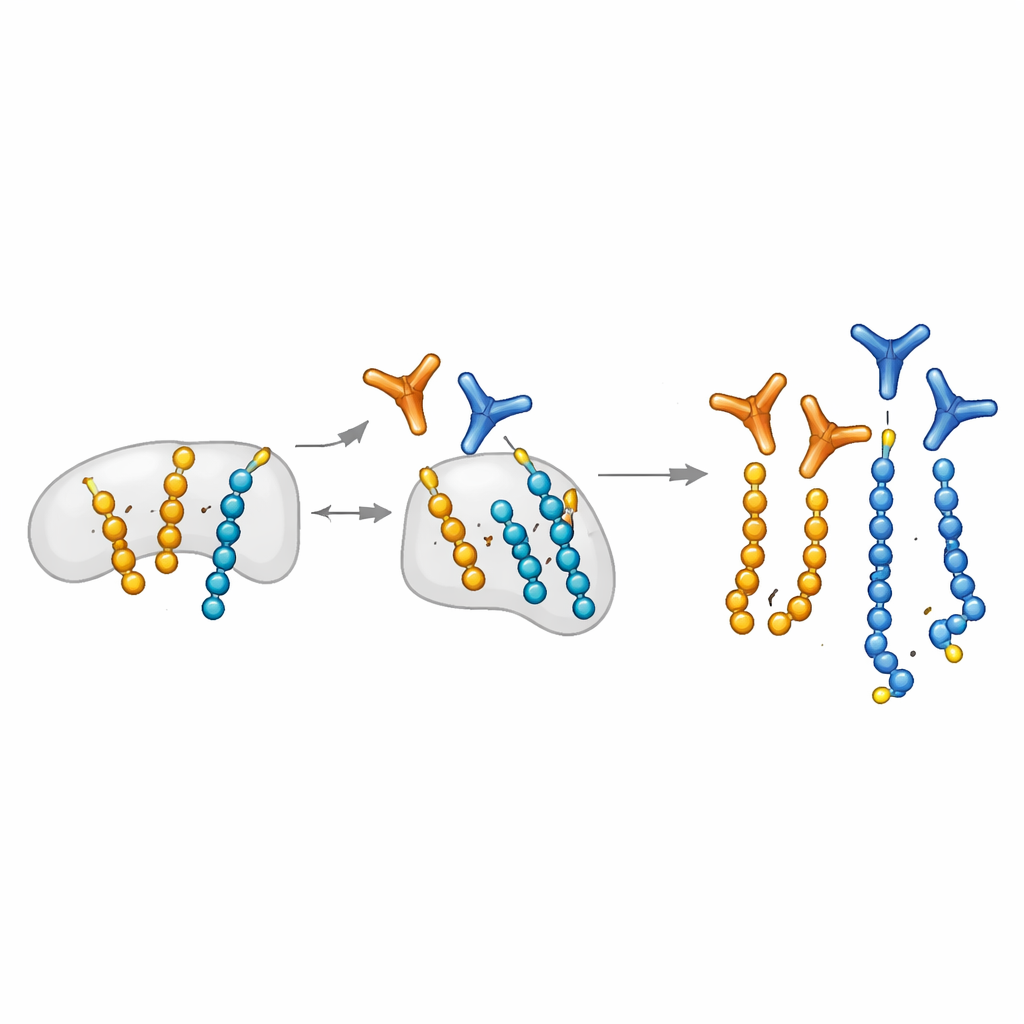
Engenharia de "olhos" moleculares altamente seletivos
Os autores expandem uma plataforma de biologia química que pode posicionar programaticamente ADP-ribose em resíduos de serina específicos de peptídeos curtos. Eles usam esses peptídeos feitos sob medida como isca para selecionar fragmentos de anticorpos de grandes bibliotecas de exibição. De forma crucial, introduzem uma etapa de "bloqueio mono": peptídeos mono-modificados são usados para saturar anticorpos que reconhecem unidades simples, deixando candidatos que preferem cadeias longas. Essa estratégia gera anticorpos modulares que, uma vez montados usando o sistema SpyTag/SpyCatcher, podem ser rapidamente convertidos em diferentes formatos para Western blots, microscopia e puxadas (pull-downs). A equipe também descobre um padrão distintivo de íons de fragmento em espectrometria de massa que marca especificamente peptídeos carregando duas unidades de ADP-ribose, ajudando a mapear corretamente onde ocorrem as poli-modificações nas proteínas.
Vendo sinais sutis onde outros não veem nada
Com suas novas ferramentas, os pesquisadores mostram que os anticorpos poli-específicos detectam cadeias muito curtas, cadeias longas e até polímeros livres de ADP-ribose, e o fazem com sensibilidade muito maior do que reagentes comerciais existentes. Os anticorpos funcionam através de diferentes ligações a aminoácidos, não apenas serina, e podem visualizar poli-ADP-ribose em células em condições onde ferramentas anteriores não detectavam sinal algum, como em células não estressadas ou em crescimento sob baixo oxigênio. Em paralelo, a equipe aperfeiçoa por afinidade anticorpos mono-específicos e específicos por sítio pré-existentes para aumentar sua sensibilidade mantendo a seletividade. Em conjunto, essa caixa de ferramentas permite a imagem simultânea de sinais mono e poli na mesma célula, revelando que a poli-modificação aparece em focos nucleares localizados enquanto a mono-modificação forma uma onda mais difusa e duradoura através da cromatina.
Como a perda de XRCC1 remodela as ondas de reparo do DNA
XRCC1 normalmente atua como um andaime que ajuda PARP1 a se engajar e depois a se desligar de intermediários de reparo do DNA. Quando XRCC1 é perdido, PARP1 torna-se hiperativo e é conhecido por produzir em excesso longas cadeias de ADP-ribose, um estado ligado à neurodegeneração. Usando seu conjunto refinado de anticorpos, os autores mostram que a perda de XRCC1 faz mais do que aumentar as cadeias longas: amplifica dramaticamente também a onda de mono-ADP-ribosilação. Durante danos contínuos ao DNA por diferentes agentes, células sem XRCC1 exibem picos mais altos e precoces de ambas as modificações, longas e curtas, com temporização específica ao tipo de dano. A mono-modificação frequentemente permanece mais estável e distribuída de forma mais homogênea do que o sinal poli, que flutua rapidamente. O trabalho também identifica a histona H1 como um alvo proeminente mono-modificado cuja marcação persistente pode manter a cromatina mais relaxada ao redor das lesões.
De sinais alterados a tráfego proteico alterado
Mono-ADP-ribose em serina pode ser por si só ainda mais decorado por uma ligação química incomum à ubiquitina, formando uma marca híbrida chamada ADP-ribosil-ubiquitinização. A ligase de ubiquitina RNF114 reconhece esse sinal composto e é atraída para locais de dano no DNA onde pode modificar ou movimentar outras proteínas. Usando uma proteína leitora especializada (ZUD) juntamente com seus anticorpos, os autores mostram que a deficiência de XRCC1 aumenta não apenas o mono-ADP-ribose, mas também essa marca híbrida e o recrutamento de RNF114 para quebras. Isso sugere que a desregulação do sinal mono e seu cruzamento com a via da ubiquitina podem contribuir para o estresse celular e os fenótipos de doença observados quando XRCC1 está mutado.
O que isso significa para entender e tratar doenças
Para um não especialista, a mensagem chave é que aquilo que antes parecia um sinal único de reparo do DNA é na verdade duas ondas sobrepostas de pequenas etiquetas químicas, cada uma com seu próprio tempo e consequências. Ao construir ferramentas moleculares altamente seletivas, este estudo separa essas ondas e mostra que a perda de XRCC1 intensifica não só o já conhecido surto de cadeias longas, mas também um aumento sustentado de unidades únicas e de suas marcas de ubiquitina associadas. Essas percepções refinam nossa compreensão de como PARP1 funciona, ajudam a explicar por que defeitos em XRCC1 e enzimas relacionadas causam doenças cerebrais e fornecem um conjunto de ferramentas que outros pesquisadores podem usar para dissecar a ADP-ribosilação no câncer, na imunidade e além — potencialmente levando a um uso mais preciso de medicamentos que têm como alvo PARP.
Citação: Dauben, H., Mihaljević, M., Kolvenbach, A. et al. Versatile and sensitive detection of mono- and poly(ADP-ribosyl)ation reveals XRCC1-dependent remodelling of PARP1 signalling. Nat Commun 17, 3216 (2026). https://doi.org/10.1038/s41467-026-71311-4
Palavras-chave: ADP-ribosilação, reparo de dano no DNA, sinalização PARP1, deficiência de XRCC1, ubiquitinização