Clear Sky Science · pl
Opracowanie kompaktowego, wysokoprecyzyjnego wariantu Cas9 z Staphylococcus aureus o szerszym spektrum celowania i mechanistyczne wglądy w jego aktywację
Mniejsze nożyce do naprawy wadliwych genów
Narzędzia do edycji genów, takie jak CRISPR-Cas9, obiecują terapie chorób dziedzicznych, ale najpopularniejsze wersje są duże i mogą przypadkowo odcinać niewłaściwe fragmenty DNA. W tym badaniu przedstawiono kompaktowe, wysoce precyzyjne „nożyce” DNA oparte na enzymie z Staphylococcus aureus, przeprojektowane tak, by docierać do znacznie większej liczby miejsc w genomie, zachowując jednocześnie precyzyjne cięcie. Ponieważ są na tyle małe, by zmieścić się w powszechnie używanym wirusie do terapii genowej i działają dobrze zarówno w komórkach, jak i u myszy, mogą przybliżyć bezpieczniejszą naprawę DNA do realnych zastosowań medycznych.
Dlaczego wielkość i dokładność mają znaczenie
Oryginalny „koń roboczy” edycji genomu, SpCas9, pochodzi od Streptococcus pyogenes. Jest potężny, ale duży, co utrudnia zapakowanie go do wektorów adeno-związanych wirusów (AAV), szeroko stosowanych do dostarczania terapii genowych. Rozpoznaje też tylko krótkie znaczniki DNA, zwane PAM, w postaci NGG. Te ograniczenia pozostawiają wiele powodujących choroby mutacji poza zasięgiem. Mniejszy kuzyn, SaCas9 z Staphylococcus aureus, mieści się wygodnie w AAV i efektywnie przecina DNA, ale wymaga dłuższego i rzadszego motywu PAM, co radykalnie zawęża liczbę edytowalnych miejsc. Próby poluzowania reguł PAM w różnych wersjach Cas9 często prowadziły do kompromisu: więcej celów, ale też więcej działań pozamiejscowych (off-target).
Opracowanie szerszego i bezpieczniejszego edytora genów
Wykorzystując szczegółową wiedzę strukturalną o SaCas9, autorzy systematycznie zastępowali aminokwasy tworzące bezpośrednie, zależne od nukleotydu kontakty z sekwencją PAM. Następnie wprowadzili nowe dodatnio naładowane reszty, które mocniej chwytają szkielet DNA mniej specyficznie. Uzyskano wariant nazwany SaCas9-NNG, rozpoznający proste PAMy NNG zamiast bardziej restrykcyjnego wzorca NNGRRT, co znacznie powiększyło liczbę potencjalnych miejsc edycji. Dalsze dopracowanie usunęło subtelny konflikt, który osłabiał aktywność w niektórych sekwencjach. W reakcjach poza komórkami i w komórkach ludzkich SaCas9-NNG efektywnie przecinał lub przepisywał DNA w szerokim panelu miejsc NNG, szczególnie tych kończących się na C lub T, których enzym pierwotny nie mógł dotknąć. W wielu celach jego wydajność dorównywała lub przewyższała inne „PAM-poluzowane” edytory, takie jak SpRY, SpG czy iGeoCas9.
Uczynienie edycji bardziej godnej zaufania
Poszerzenie miejsc, w których Cas9 może ciąć, rodzi kluczowe pytanie: czy nadal potrafi unikać niewłaściwych miejsc? Aby to rozwiązać, zespół zaprojektował wersję wysokiej wierności, osłabiając niektóre kontakty, które pozwalają białku tolerować niedopasowania między przewodnikiem RNA a DNA. Dwie kluczowe substytucje w regionie stabilizującym odległy koniec helisy RNA–DNA uczyniły enzym mniej wyrozumiałym wobec niedopasowań, szczególnie tych oddalonych od PAM, będących częstym źródłem cięć poza celem. Ten wariant, nazwany eSaCas9-NNG, zachował silną aktywność na prawidłowych celach, ale zdecydowanie zmniejszył cięcia w miejscach nieidealnych. Porównania w komórkach ludzkich wykazały, że dorównuje lub przewyższa ustalony wysokowiernościowy SaCas9 i ma mniej sfałszowanych cięć niż jego nisko-wiernościowi krewni.
Od probówki do leczenia zaburzeń krzepnięcia
Aby sprawdzić, czy kompaktowy edytor może działać w żywym organizmie, badacze zapakowali SaCas9-NNG i jego przewodnik RNA do pojedynczego wektora AAV8 i wstrzyknięli go do myszy. Celując w ludzki gen czynnika krzepnięcia 9 (F9), ważny w hemofilii B, zaobserwowali efektywne wprowadzenie drobnych zmian DNA (indeli) w miejscach NNG w wątrobie, w tym w miejscach, do których standardowy SaCas9 nie mógł dotrzeć. Stworzyli też wersje do edycji zasad, które zamieniają pojedynczą literę DNA bez przecinania nici. W modelach mysich z ludzkimi mutacjami hemofilii B, edytor adeniny oparty na SaCas9-NNG skorygował zmiany powodujące chorobę zarówno przy klasycznym PAM, jak i przy wcześniej niedostępnym. Leczone zwierzęta wykazały istotny wzrost aktywności czynnika krzepnięcia we krwi, co wskazuje na przywrócenie funkcji.
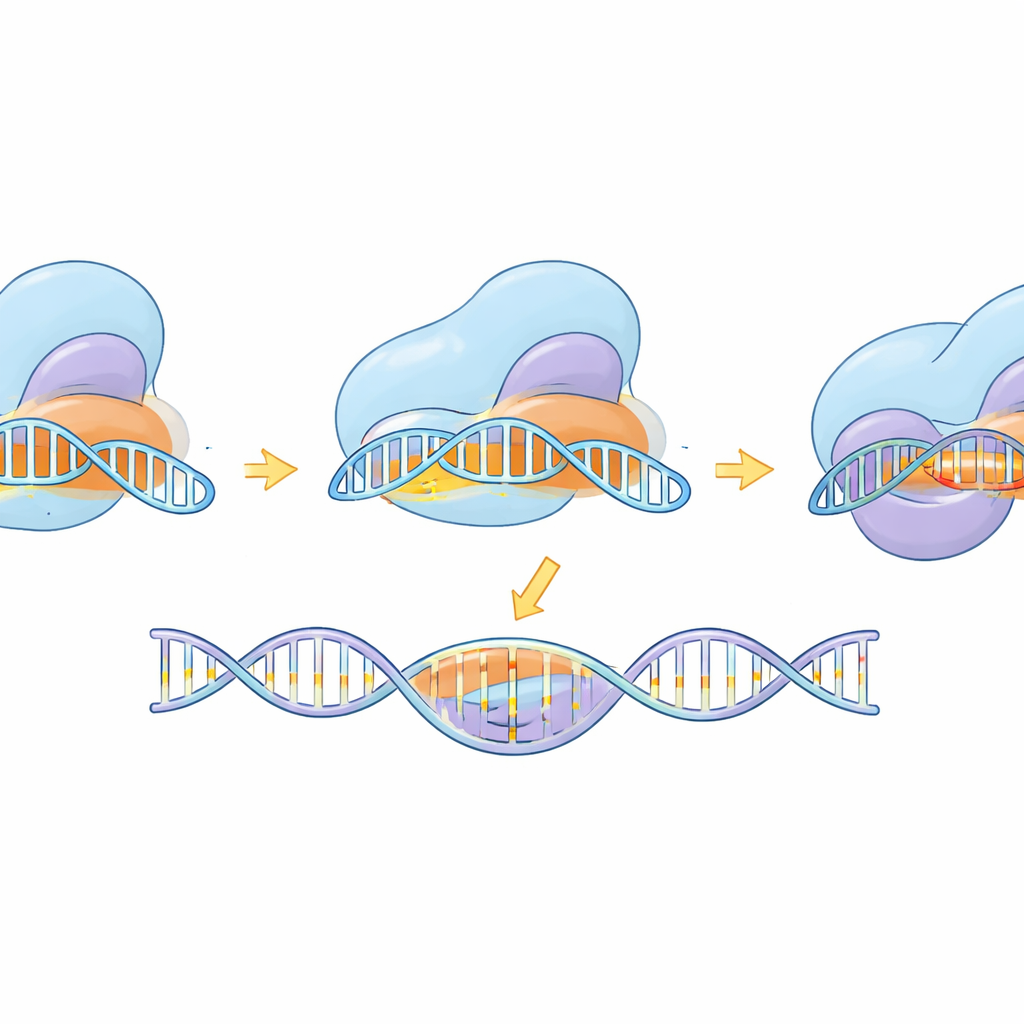
Obserwacja molekularnej maszyny w akcji
Ponad budowaniem narzędzia, badanie wykorzystało krioelektronową mikroskopię do uchwycenia eSaCas9-NNG w wielu migawkach w trakcie jego cyklu pracy — przed związaniem DNA, podczas testowania potencjalnych miejsc, w trakcie częściowego sparowania z celem i w w pełni aktywnej formie gotowej do cięcia. Struktury te pokazują, jak enzym najpierw zaczepia kompatybilny znacznik NNG, potem stopniowo tworzy hybrydową helisę RNA–DNA. Dopiero gdy helisa jest długa i prawidłowo sparowana, wewnętrzne domeny przesuwają się na miejsce i ustawiają centra tnące na obu łańcuchach DNA. Zaprojektowane mutacje poprawiające specyficzność destabilizowały wiązanie z zdeformowanym, niedopasowanym DNA na odległym końcu helisy, faworyzując uwolnienie zamiast błędnego cięcia. Porównanie z pokrewnym, bardziej elastycznym wariantem SpCas9 pokazuje, że mimo różnych kształtów oba podążają za wspólną logiką: pełne, dokładne sparowanie zasad jest wymagane, by odblokować końcowy ruch tnący.
Co to oznacza dla przyszłych terapii genowych
Dla czytelników niebędących specjalistami główne przesłanie jest takie, że autorzy stworzyli mniejsze, bardziej wszechstronne i ostrożniejsze narzędzie do edycji genów. eSaCas9-NNG może celować w znacznie większą część genomu niż oryginalny SaCas9, zachowując przy tym wysoką precyzję, a jednocześnie jest na tyle kompaktowy, by dostarczyć go w pojedynczym opakowaniu AAV — kluczowym wymogu dla wielu terapii in vivo. Jego powodzenie w korygowaniu defektów krzepnięcia w modelach mysich hemofilii B, wraz ze szczegółowym wglądem strukturalnym w to, jak działa i unika błędów, plasuje ten enzym jako obiecujące podłoże dla terapii następnej generacji oraz dalszych udoskonaleń, takich jak jeszcze dokładniejsze edytory zasad i prime editors.
Cytowanie: Omura, S.N., Nakagawa, R., Kajimoto, S. et al. Engineering a compact high-fidelity Staphylococcus aureus Cas9 variant with broader targeting range and mechanistic insights into its activation. Nat Commun 17, 3584 (2026). https://doi.org/10.1038/s41467-026-71626-2
Słowa kluczowe: CRISPR, terapia genowa, Cas9, edytowanie zasad (base editing), hemofilia B