Clear Sky Science · pl
Wydobywanie funkcji przeciwciał za pomocą profilowania strukturalnego nadzorowanego przez sztuczną inteligencję
Dlaczego to badanie ma znaczenie
Szczepionki i leki oparte na przeciwciałach były kluczowymi narzędziami przeciw COVID-19, jednak nasze układy odpornościowe wytwarzają niemal niewyobrażalnie dużą różnorodność przeciwciał, z których większości nigdy nie badamy szczegółowo. Artykuł pokazuje, jak sztuczna inteligencja może odczytywać sekwencje genetyczne przeciwciał i wnioskować, gdzie i jak przyczepiają się one do kolca koronawirusa, pomagając naukowcom szybko wyłowić rzadkie molekuły, które jednocześnie neutralizują wirusa i pozostają aktywne wobec jego mutacji. Ta sama strategia może przyspieszyć poszukiwanie leków przeciwciałowych przeciw wielu przyszłym patogenom.
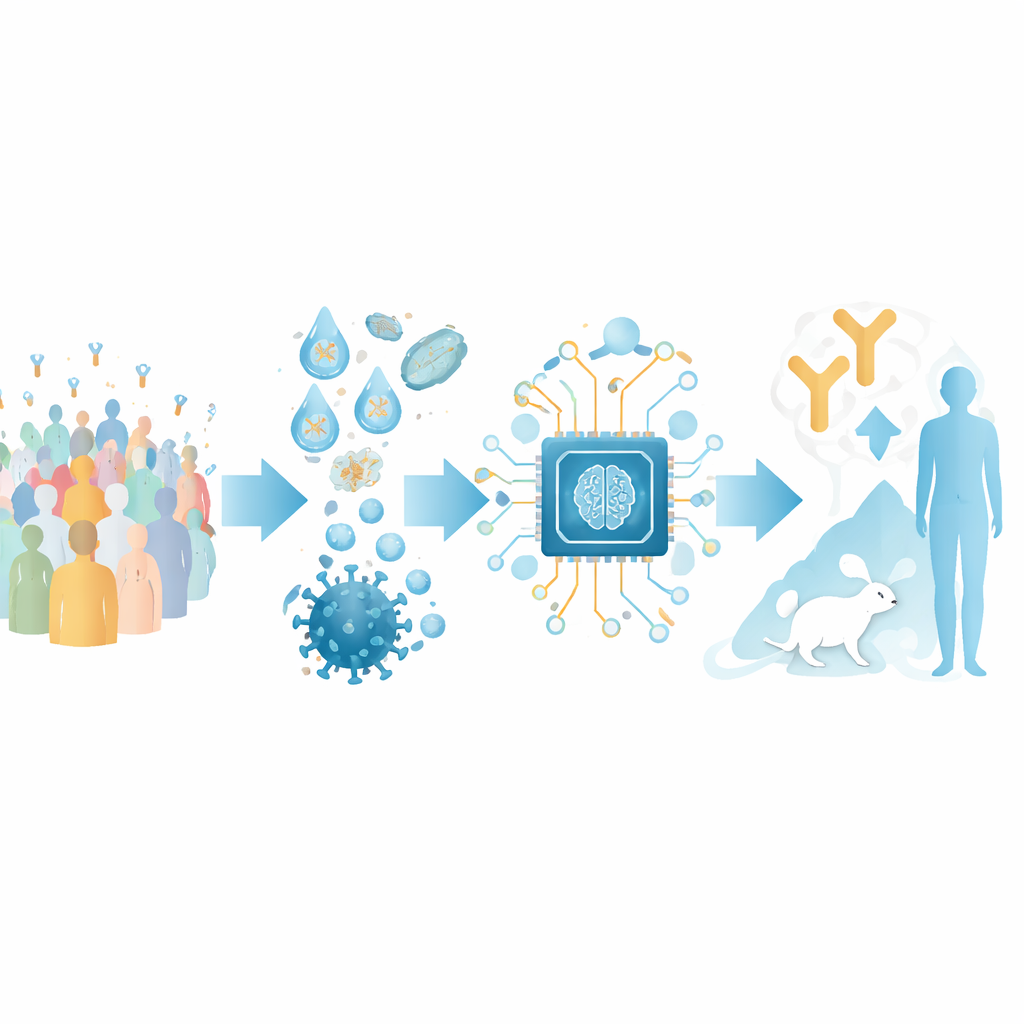
Przekształcanie sekwencji przeciwciał w mapę
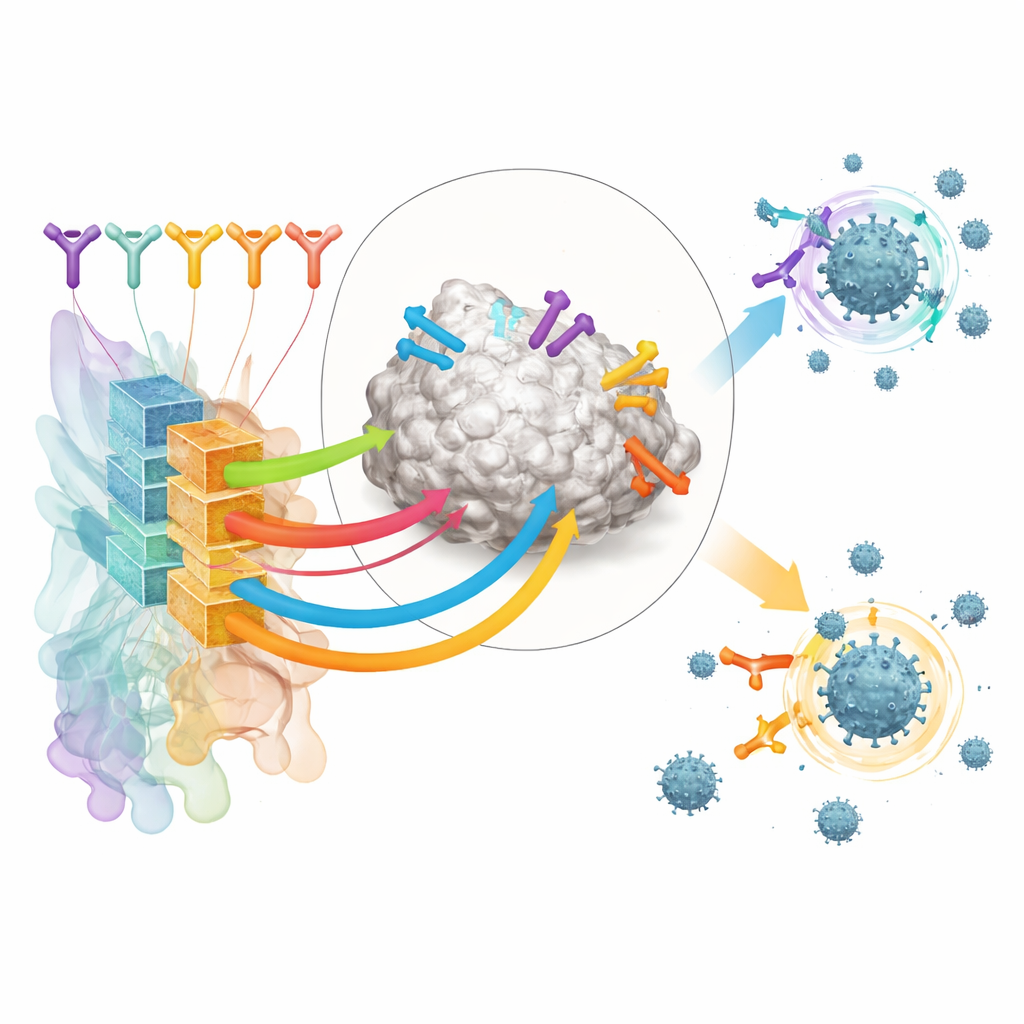
Autorzy koncentrują się na przeciwciałach rozpoznających domenę wiążącą receptor (RBD) białka kolca SARS-CoV-2 — kluczowym uchwycie, którego wirus używa do przyłączania się do komórek ludzkich. Zebrali duży zestaw treningowy z publicznie dostępnych struktur kompleksów przeciwciało–RBD oraz z eksperymentów głębokiego skanowania mutacji, które mapują, jak zmiany w wirusie wpływają na wiązanie przeciwciał. Grupując te dane, zdefiniowali 12 odrębnych „klas epitopów” — nawracających obszarów na RBD, które są celem różnych przeciwciał, z których każda wiąże się z charakterystyczną siłą i zakresem neutralizacji wirusa.
Budowa przewodnika AI dla funkcji przeciwciał
Na bazie tej mapy strukturalnej zespół zbudował narzędzie AI nazwane RBD-AIM. Najpierw model językowy szkolony specjalnie na sekwencjach przeciwciał analizuje kod genetyczny łańcuchów ciężkich i lekkich przeciwciała i przewiduje, do której klasy epitopu należy. Następnie etap przewidywania struktury wykorzystuje znane szablony 3D i nowoczesne algorytmy fałdowania, aby doprecyzować, jak to przeciwciało prawdopodobnie usytuowane jest na RBD. Wskaźnik zaufania wyprowadzony z przewidywanego dopasowania 3D pomaga zdecydować, kiedy zaufać modelowi strukturalnemu zamiast prostszemu klasyfikatorowi opartego na sekwencji. W sumie to połączenie przewyższa tradycyjne wyszukiwania homologicze i kilka nowoczesnych przewidywaczy struktur w zgadywaniu, gdzie przeciwciało się wiąże i jak dobrze prawdopodobnie zablokuje wirusa.
Odtwarzanie rzeczywistych odpowiedzi odpornościowych w laboratorium
Aby przetestować RBD-AIM na realistycznych zbiorach przeciwciał, badacze odtworzyli rodzimy repertuar komórek B od osób zaszczepionych szczepionką mRNA (Pfizer–BioNTech) lub szczepionką wektorową adenowirusową (Sputnik V). Przy użyciu mikroukładów kroplowych uchwycili oryginalne parowania łańcuchów ciężkich i lekkich przeciwciał z pojedynczych komórek B i wyeksponowali powstałe fragmenty na powierzchni drożdży. To zachowało naturalną różnorodność przeciwciał znacznie lepiej niż konwencjonalne metody, które losowo mieszają łańcuchy. Fluorescencyjnie znakowane RBD pozwoliło im sortować komórki drożdżowe niosące wysokowskazywaczowe wiążące RBD, w tym te konkurujące bezpośrednio z ludzkim receptorem ACE2 o ten sam fragment kolca.
Przewidywanie i walidacja, które przeciwciała rzeczywiście działają
Kilkadziesiąt silnie wzbogaconych przeciwciał wiążących RBD od tych zaszczepionych dawców zostało następnie poddanych analizie przez RBD-AIM. Narzędzie przewidziało, którą klasę epitopu każde rozpoznaje, czy prawdopodobnie blokuje ACE2 i jak odporne może być na mutacje kolca występujące w wariantach takich jak Delta i Omikron. Jak można było oczekiwać, przeciwciała celujące w obszar kontaktu z ACE2 miały tendencję do bycia silnymi, lecz wąskimi w zakresie działania, tracąc aktywność wobec Omikronu. W przeciwieństwie do tego, podzbiór przeciwciał z bardziej odległej klasy epitopów (nazwanej przez autorów E221) został przewidziany jako zachowujący zdolność neutralizacji w różnych wariantach. Testy wiązania i neutralizacji wirusa w laboratorium potwierdziły te wzorce, a struktury krystaliczne wykazały, że strukturalne przypuszczenia RBD-AIM często były dokładne nawet do szczegółowych powierzchni kontaktu.
Od przewidywania do ochrony u zwierząt
Aby sprawdzić, czy te priorytetyzowane przez AI przeciwciała mogą działać jako prawdziwe leki, zespół wybrał reprezentatywne molekuły: jedno klasyczne przeciwciało blokujące ACE2 i jedno przeciwciało klasy E221, które neutralizuje w sposób bardziej pośredni. W modelu śmiertelnego zakażenia SARS-CoV-2 u myszy inżynierowanych do ekspresji ludzkiego ACE2 pojedyncza niska dawka dowolnego z tych przeciwciał ochroniła wszystkie leczone zwierzęta, zgodnie z ich przewidywanymi profilami neutralizacyjnymi. Dalsze prace strukturalne i symulacje sugerowały, że szeroko działające przeciwciało klasy E221 działa przez „zamrożenie” elastycznych części RBD potrzebnych do efektywnego angażowania receptora, mechanizm mniej podatny na dokładny kształt miejsca kontaktu z ACE2.
Co to znaczy dla przyszłych pandemii
W praktycznym ujęciu to badanie dostarcza działającego planu łączenia technologii wysokoprzepustowego wyświetlania z AI, aby przekształcić surowe dane sekwencji przeciwciał w wiedzę funkcjonalną. Zamiast mozolnie charakteryzować pojedyncze przeciwciało po kolei, naukowcy mogą teraz szybko przeskanować całe repertuary, uszeregować obiecujących kandydatów pod względem mocy i zakresu oraz zrozumieć, które regiony białka wirusowego są najważniejsze do zaatakowania. Chociaż RBD-AIM był trenowany na SARS-CoV-2, autorzy pokazują, że przy wystarczających danych strukturalnych i mutacyjnych ta sama strategia może rozszerzyć się na inne wirusy, wskazując na przyszłość, w której prowadzone przez AI „profilowanie krajobrazu strukturalnego” pomoże nam wydobywać z własnych odpowiedzi immunologicznych następnej generacji terapie przeciwciałowe.
Cytowanie: Terekhov, S.S., Ivanisenko, N.V., Zhang, N. et al. Mining antibody functionality via AI-guided structural landscape profiling. Nat Commun 17, 4009 (2026). https://doi.org/10.1038/s41467-026-70553-6
Słowa kluczowe: odkrywanie przeciwciał, sztuczna inteligencja, białko kolca SARS-CoV-2, mapowanie epitopów, przeciwciała terapeutyczne