Clear Sky Science · it
Indagare la funzionalità degli anticorpi tramite profilazione strutturale guidata dall'IA
Perché questa ricerca è importante
Vaccini e farmaci a base di anticorpi sono stati armi centrali contro il COVID-19, ma i nostri sistemi immunitari generano una varietà di anticorpi quasi inconcepibilmente ampia, la maggior parte dei quali non studiamo mai nel dettaglio. Questo articolo mostra come l'intelligenza artificiale possa leggere le sequenze genetiche degli anticorpi e inferire dove e come si attaccano alla spike del coronavirus, aiutando gli scienziati a individuare rapidamente le molecole rare che neutralizzano il virus e restano efficaci mentre esso muta. La stessa strategia potrebbe accelerare la ricerca di farmaci a base di anticorpi contro molti patogeni futuri.
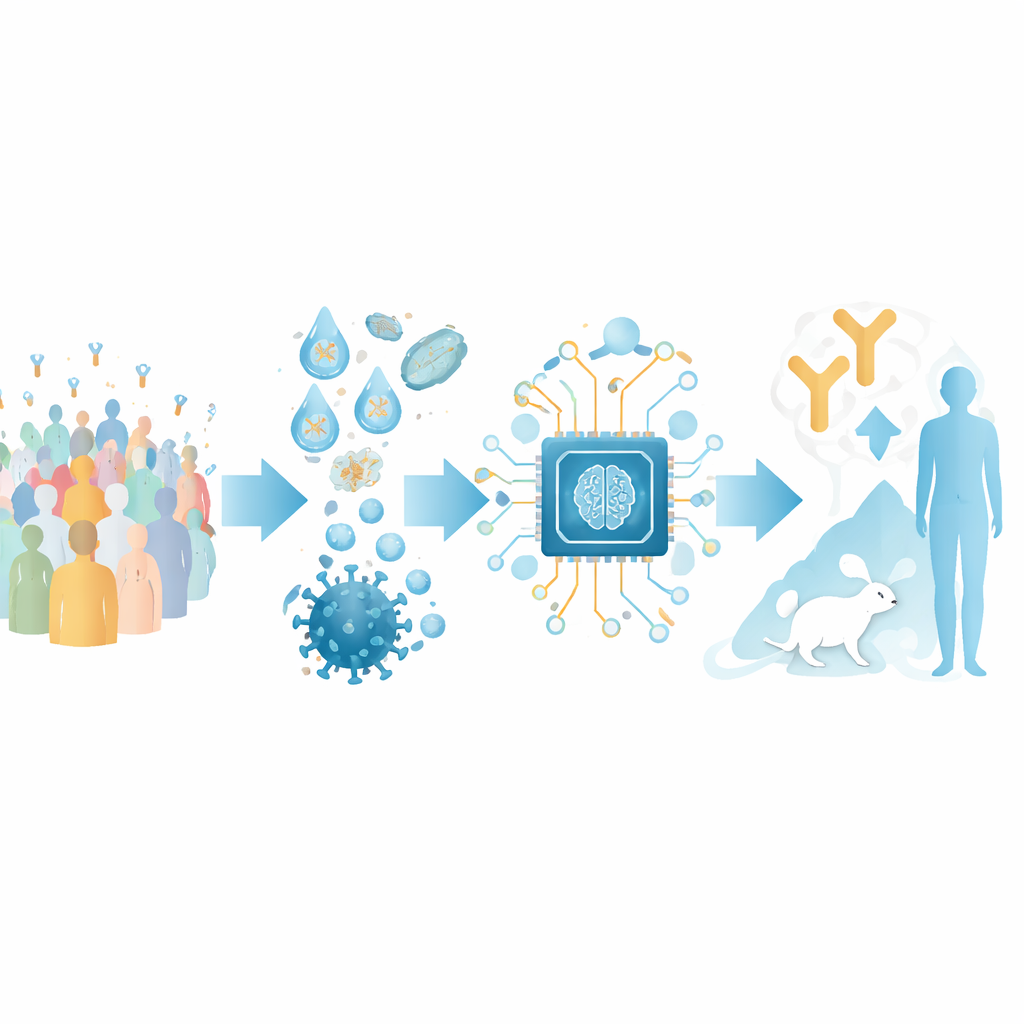
Trasformare le sequenze di anticorpi in una mappa
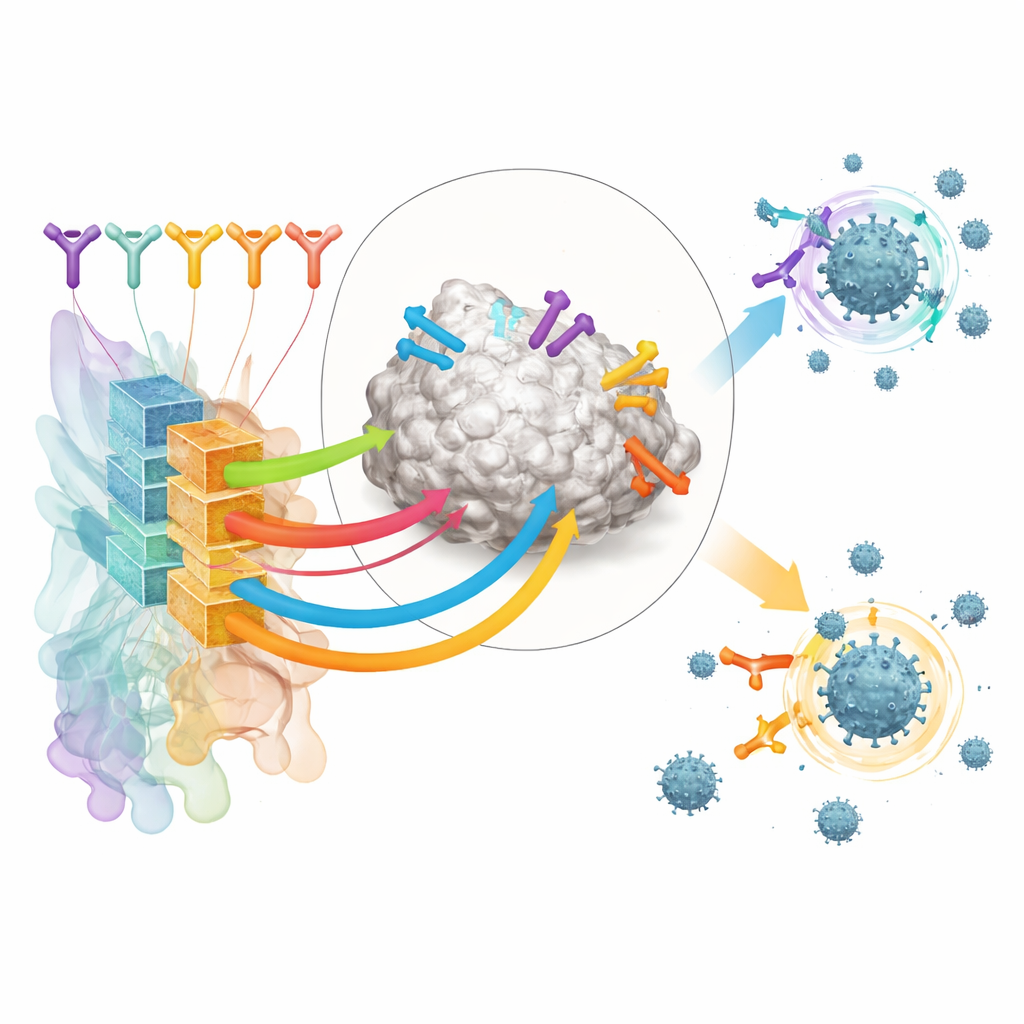
Gli autori si concentrano sugli anticorpi che riconoscono il dominio di legame al recettore (RBD) della proteina spike di SARS-CoV-2, una presa chiave che il virus usa per aggrapparsi alle cellule umane. Hanno assemblato un ampio set di addestramento da strutture pubblicamente disponibili di complessi anticorpo–RBD e da esperimenti di deep mutational scanning che mappano come le variazioni del virus influenzano il legame degli anticorpi. Raggruppando questi dati, hanno definito 12 “classi di epitopi” distinte – regioni ricorrenti sull'RBD verso cui diversi anticorpi convergono, ciascuna associata a caratteristiche tipiche di forza e ampiezza della neutralizzazione virale.
Costruire una guida IA alla funzione degli anticorpi
Sovrapponendo questa mappa strutturale, il team ha creato uno strumento basato sull'IA chiamato RBD-AIM. Innanzitutto, un modello di linguaggio allenato specificamente su sequenze di anticorpi analizza il codice genetico delle catene pesanti e leggere e prevede a quale classe di epitopi appartiene. Successivamente, una fase di predizione strutturale utilizza template 3D noti e algoritmi di folding moderni per raffinare come quell'anticorpo è verosimilmente disposto sull'RBD. Un punteggio di confidenza derivato dall'allineamento 3D previsto aiuta a decidere quando fidarsi del modello strutturale rispetto al più semplice classificatore basato sulla sequenza. Nel complesso, questo approccio combinato supera ricerche di omologia tradizionali e diversi predittori strutturali all'avanguardia nel predire dove un anticorpo si lega e quanto è probabile che blocchi il virus.
Riprodurre risposte immunitarie reali in laboratorio
Per testare RBD-AIM su collezioni realistiche di anticorpi, i ricercatori hanno ricostruito repertori nativi di cellule B provenienti da persone vaccinate con un vaccino a mRNA (Pfizer–BioNTech) o con un vaccino a vettore adenovirale (Sputnik V). Utilizzando microfluidica a goccia, hanno catturato gli abbinamenti originali delle catene pesanti e leggere dagli singoli linfociti B e hanno esposto i frammenti risultanti sulla superficie di cellule di lievito. Questo ha preservato la diversità naturale degli anticorpi molto meglio dei metodi convenzionali che mescolano le catene in modo casuale. L'RBD marcato con fluorescenza ha permesso di selezionare le cellule di lievito che portavano leganti dell'RBD ad alta affinità, inclusi quelli che competono direttamente con il recettore umano ACE2 per lo stesso sito sulla spike.
Predire e convalidare quali anticorpi funzionano davvero
Dozzine di anticorpi fortemente arricchiti e leganti l'RBD provenienti da questi donatori vaccinati sono stati poi analizzati con RBD-AIM. Lo strumento ha previsto quale classe di epitopi ciascuno riconosceva, se probabilmente bloccava ACE2 e quanto potesse essere robusto rispetto alle mutazioni della spike presenti in varianti come Delta e Omicron. Come previsto, gli anticorpi diretti verso l'area di contatto con ACE2 tendevano a essere potenti ma stretti nel raggio d'azione, perdendo attività contro Omicron. Al contrario, un sottoinsieme di anticorpi appartenenti a una classe di epitopi più distante (denominata E221 dagli autori) è stato previsto mantenere potere neutralizzante attraverso le varianti. Test di legame e neutralizzazione virale in laboratorio hanno confermato questi schemi, e strutture cristalline hanno mostrato che le ipotesi strutturali di RBD-AIM erano spesso accurate fino ai dettagli delle superfici di contatto.
Dalla predizione alla protezione negli animali
Per verificare se questi anticorpi prioritizzati dall'IA potessero comportarsi come veri farmaci, il team ha selezionato molecole rappresentative: un anticorpo classico che blocca ACE2 e un anticorpo della classe E221 che neutralizza tramite un meccanismo più indiretto. In un modello letale di sfida con SARS-CoV-2 in topi ingegnerizzati per esprimere ACE2 umano, una singola dose bassa di ciascun anticorpo ha protetto tutti gli animali trattati, in linea con i loro profili di neutralizzazione previsti. Ulteriori lavori strutturali e di simulazione hanno suggerito che l'anticorpo della classe E221, ampiamente attivo, agisce “congelando” parti flessibili dell'RBD necessarie per un'efficace interazione con il recettore, un meccanismo meno vulnerabile alla precisa conformazione della porzione di contatto con ACE2.
Cosa significa per le pandemie future
In termini pratici, questo studio fornisce un progetto operativo per combinare tecnologie di display ad alta resa con l'IA per trasformare dati grezzi di sequenze anticorpali in intuizioni funzionali. Invece di caratterizzare meticolosamente un anticorpo alla volta, i ricercatori possono ora scansionare rapidamente interi repertori, classificare i candidati promettenti per potenza e ampiezza e comprendere quali regioni di una proteina virale sono più importanti da colpire. Pur essendo RBD-AIM addestrato su SARS-CoV-2, gli autori mostrano che con dati strutturali e mutazionali sufficienti la stessa strategia può estendersi ad altri virus, indicando un futuro in cui la “profilazione del paesaggio strutturale” guidata dall'IA ci aiuta a sfruttare le nostre risposte immunitarie per terapie anticorpali di nuova generazione.
Citazione: Terekhov, S.S., Ivanisenko, N.V., Zhang, N. et al. Mining antibody functionality via AI-guided structural landscape profiling. Nat Commun 17, 4009 (2026). https://doi.org/10.1038/s41467-026-70553-6
Parole chiave: scoperta di anticorpi, intelligenza artificiale, spike di SARS-CoV-2, mappatura degli epitopi, anticorpi terapeutici