Clear Sky Science · nl
Van data naar ontdekking: De opkomst van informatietheoretische voorspellende modellen in geneesmiddelenontwikkeling
Waarom snellere geneesmiddelenontwikkeling ertoe doet
Veel ernstige ziekten hebben nog steeds geen doeltreffende behandelingen, en zelfs wanneer veelbelovende geneesmiddelen worden gevonden, is de weg van idee naar apotheekrek lang en kostbaar. Dit artikel onderzoekt hoe slimmer computermodellen enorme verzamelingen chemische en biologische gegevens kunnen doorzoeken om sneller en betrouwbaarder een paar veelbelovende kandidaat-geneesmiddelen te identificeren. Door ideeën uit de informatietheorie — de wiskunde van hoeveel we uit data kunnen leren — te lenen, tonen de auteurs een manier om de zoektocht naar nieuwe medicijnen te verkleinen en beter te begrijpen wat een molecuul waarschijnlijk werkzaam maakt in het lichaam.
Van proef en fout naar datagedreven ontwerp
Traditioneel geneesmiddelenonderzoek steunt op een mix van onderbouwde gokjes, laboratoriumscreening en soms gelukstreffers zoals de ontdekking van penicilline. Tegenwoordig kunnen onderzoekers miljoenen verbindingen in computers testen voordat ze een reageerbuis aanraken. Virtuele screentools classificeren moleculen op basis van hun voorspelde biologische gedrag, waardoor wetenschappers zich op de meest veelbelovende kunnen concentreren. Veel bestaande tools behandelen echter elk molecuul afzonderlijk of geven slechts ruwe kansschattingen, en ze worstelen vaak om vast te leggen hoe reële biologische context — zoals hoe een medicijn door het lichaam beweegt — succes of falen bepaalt.
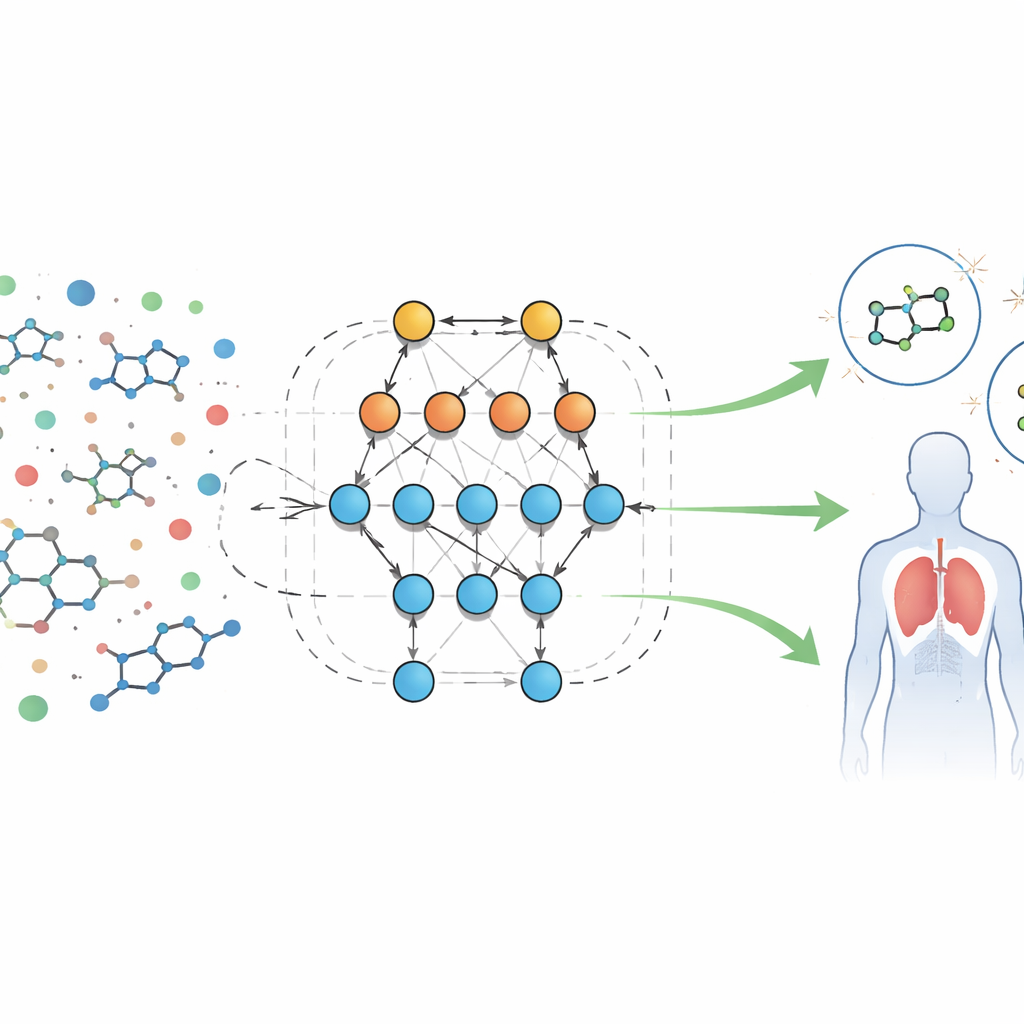
Een nieuwe manier om biologische vingerafdrukken te lezen
De auteurs analyseren een grote openbare dataset van biologische screeningsresultaten voor moleculen gericht op een formylpeptide-receptor, een eiwit dat betrokken is bij ontsteking en immuunafweer. Elk monster heeft tientallen meetbare kenmerken, of “descriptors”, zoals moleculaire grootte, hoe gemakkelijk het oplost in vet of water, het vermogen de bloed-hersenbarrière te passeren en de capaciteit om waterstofbruggen te vormen. In plaats van vaste formules te schrijven voor hoe deze kenmerken zich zouden moeten gedragen, gebruikt het team een geautomatiseerd systeem genaamd Eidos, dat informatietheoretische voorspellende modellen rechtstreeks uit de data bouwt. Deze modellen, aangeduid als ASC (automated system-cognitive) analyse, leren hoe combinaties van kenmerken gekoppeld zijn aan of een monster actief (potentieel nuttig) of inactief is in biologische tests.
De data opschonen en bepalen wat telt
Reële screeninggegevens zijn lawaaierig: metingen kunnen inconsistent zijn en sommige monsters passen in geen enkel duidelijk patroon. Het Eidos-systeem filtert eerst deze “artefacten” weg, verwijdert meer dan duizend twijfelachtige inzendingen en houdt iets meer dan tweeduizend betrouwbare monsters over. Vervolgens onderzoekt het meer dan 300 kenmerken om te zien welke daadwerkelijk helpen actieve van inactieve monsters te onderscheiden. Met concepten uit de informatietheorie wordt ieder kenmerk gescoord op hoeveel het de onzekerheid over de uitkomst vermindert. De analyse laat zien dat slechts een minderheid van de kenmerken het meeste nuttige informatie bevat, wat betekent dat onderzoekers veel metingen veilig kunnen negeren en toch bijna alle voorspellende kracht behouden. Deze verfijning maakt modellen eenvoudiger, beter interpreteerbaar en sneller te draaien.
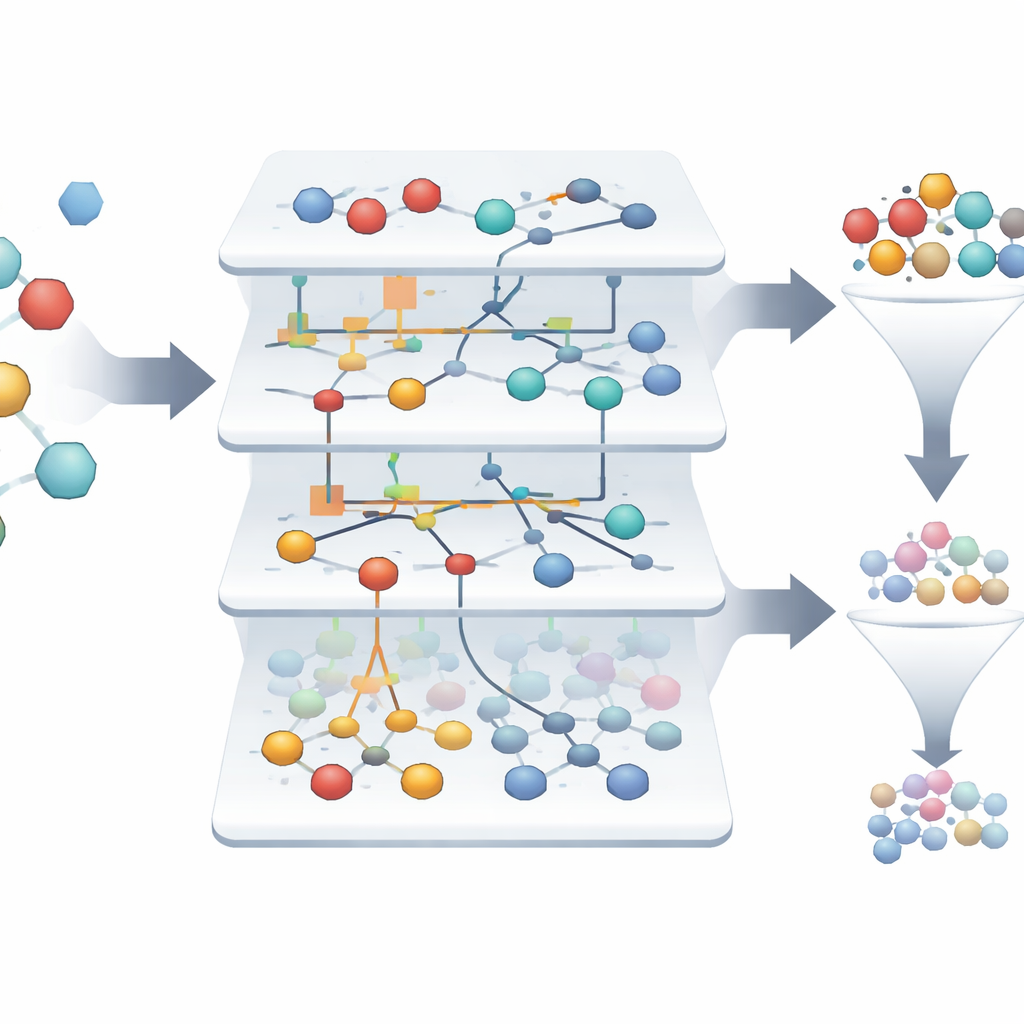
Zeldzame winnaars vinden in een zee van mislukkingen
In de onderzochte dataset is slechts ongeveer 1,4% van de moleculen echt actief, wat het uitdagend maakt om de paar winnaars te vinden tussen duizenden mislukkingen. De op ASC gebaseerde modellen bouwen automatisch “informatieportretten” die laten zien hoe sterk elk kenmerk en elke combinatie van kenmerken een monster naar actief of inactief duwt. Van meer dan drieduizend oorspronkelijke monsters markeert het systeem slechts twee die eruit springen als sterke, betrouwbare kandidaten voor geneesmiddelen gericht op de formylpeptide-receptor, met modelbetrouwbaarheid die in retrospectieve tests richting 99,9% gaat. Visuele netwerkdiagrammen tonen welke moleculaire eigenschappen het sterkst een actieve toestand ondersteunen, en geven wetenschappers een interpreteerbare kaart van wat veelbelovend gedrag aandrijft.
Hoe deze aanpak zich verhoudt en wat volgt
De auteurs vergelijken hun methode met populaire vroege voorspellingshulpmiddelen zoals pkCSM, SwissADME en ADMETlab, die inschatten hoe een geneesmiddel wordt opgenomen, verdeeld, afgebroken en uitgescheiden. Terwijl die systemen vooral vertrouwen op vooraf gedefinieerde regels of algemeen toegepaste machine learning, meet het ASC-kader expliciet hoeveel elk kenmerk bijdraagt aan de verworven kennis over geneesmiddelachtig gedrag en kan het veranderingen in biologische context simuleren. Tegelijkertijd merkt de studie beperkingen op: de dataset is relatief klein en sterk ongebalanceerd, en de methode is tot nu toe op slechts één receptor toegepast. De auteurs suggereren dat toekomstige versies ASC-modellen met deep learning kunnen combineren en kunnen uitbreiden naar meerdere targets.
Wat het betekent voor toekomstige geneesmiddelen
In praktische termen toont dit werk aan dat informatierijke modellen rommelige screeninggegevens kunnen omzetten in heldere, toetsbare voorspellingen over welke moleculen meer aandacht verdienen. Door automatisch data te reinigen, de belangrijkheid van kenmerken te rangschikken en zeldzame maar veelbelovende verbindingen in de schijnwerpers te zetten, kan de aanpak tijd en kosten verminderen die nodig zijn om het laboratorium en uiteindelijk de kliniek te bereiken. Hoewel het dierstudies of menselijke proeven niet vervangt, fungeert het als een krachtig filter en gids, waardoor wetenschappers efficiënter en met meer vertrouwen van ruwe data naar potentiële therapieën kunnen bewegen.
Bronvermelding: Saied, H., Alfahad, O., Aljaffer, A.A. et al. From data to discovery: The rise of information-theoretic predictive models in drug development. Sci Rep 16, 12857 (2026). https://doi.org/10.1038/s41598-026-45644-5
Trefwoorden: geneesmiddelenonderzoek, virtueel screenen, voorspellende modellering, bioassaygegevens, formylpeptide-receptor