Clear Sky Science · zh
MiGPC:来自环境宏基因组学的酶类抗菌剂综合目录
为什么微小的酶对我们的未来至关重要
随着抗生素耐药性上升以及塑料和污染物在空气、水体和土壤中扩散,科学家正在寻求在不损害生态的前提下控制有害微生物的新方法。本研究介绍了 MiGPC,这是一个来自多种环境的天然抗菌酶的大型目录,涵盖从海洋与温泉到动物肠道与塑料垃圾的样本。研究展示了地球隐藏微生物世界在潜在新型抗菌剂方面的丰富性,并为将这些多样性转化为医学、食品安全和环境修复的实用工具提供了一条路线图。 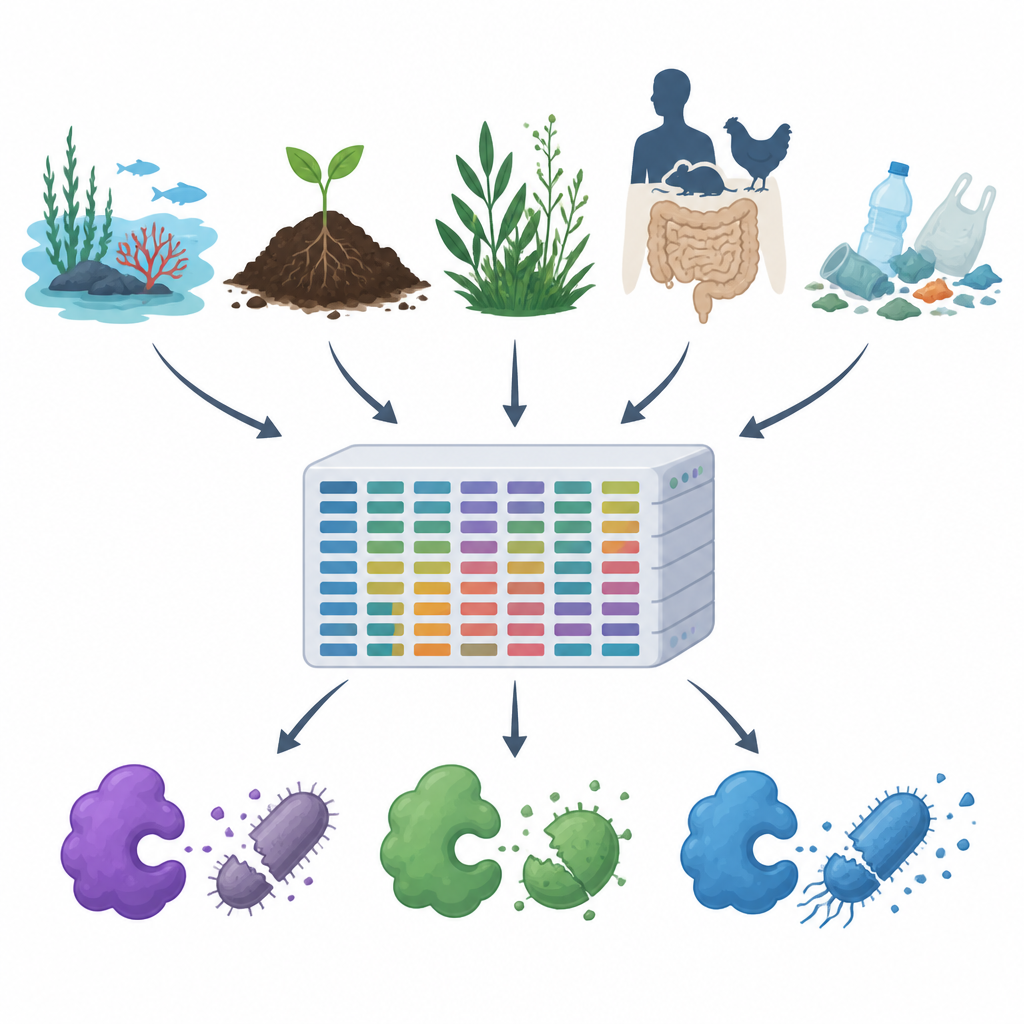
从微生物到天然杀菌剂
传统抗生素往往像粗糙的工具,会同时消灭有益和有害细菌,并随着时间推移促进耐药性的产生。相比之下,许多微生物使用专门的酶以高度精确的方式攻击竞争者,在细胞壁上打孔或在需要处产生有毒分子。这些基于酶的抗微生物剂称为酶类抗菌剂(enzybiotics),它们可以裂解细菌细胞、分解保护性黏液层或扰乱细菌的生存途径。作者旨在找出此类酶在自然界的分布广度,并将其基因蓝图汇集成一个任何人都可探索的有序资源。
构建全球酶类目录
研究团队首先检索了公共蛋白数据库和科学文献,收集了 19 种研究充分的抗菌酶,包括切割细胞壁的酶、蛋白质降解酶以及产生有害活性分子的氧化酶。他们以这些经验证的示例为“诱饵”,扫描来自 15 种截然不同环境的大规模 DNA 数据集,如海水、卤水池、河口、温泉、高山植物、动物与人类肠道,以及受塑料污染的土壤和水体。使用高性能计算流程,他们将约 1.2 TB 的原始 DNA 读取数据清洗并拼接为更长片段,预测基因与蛋白、去重并对相关序列进行分组,最终得到约 1 亿条独特的基因和蛋白序列。
在环境 DNA 中发现隐藏功能
为了理解这些基因可能的功能,研究者将其与主要功能数据库进行比对。即便使用现代工具,约有 62% 的基因无法被赋予已知功能,这暗示着一个深厚且未被探索的生物学宝库。在可识别的功能中,作用于复杂糖类的酶特别常见。两大家族——糖苷水解酶和糖基转移酶尤为突出,其中许多能够削弱细菌细胞壁或生物膜。通过专门工具的定向搜索,发现了近 2 万个可能的抗菌酶。大多数属于两类主要酶群:水解酶(将分子切割开)和氧化还原酶(介导电子反应,可产生损害微生物的活性氧物种)。 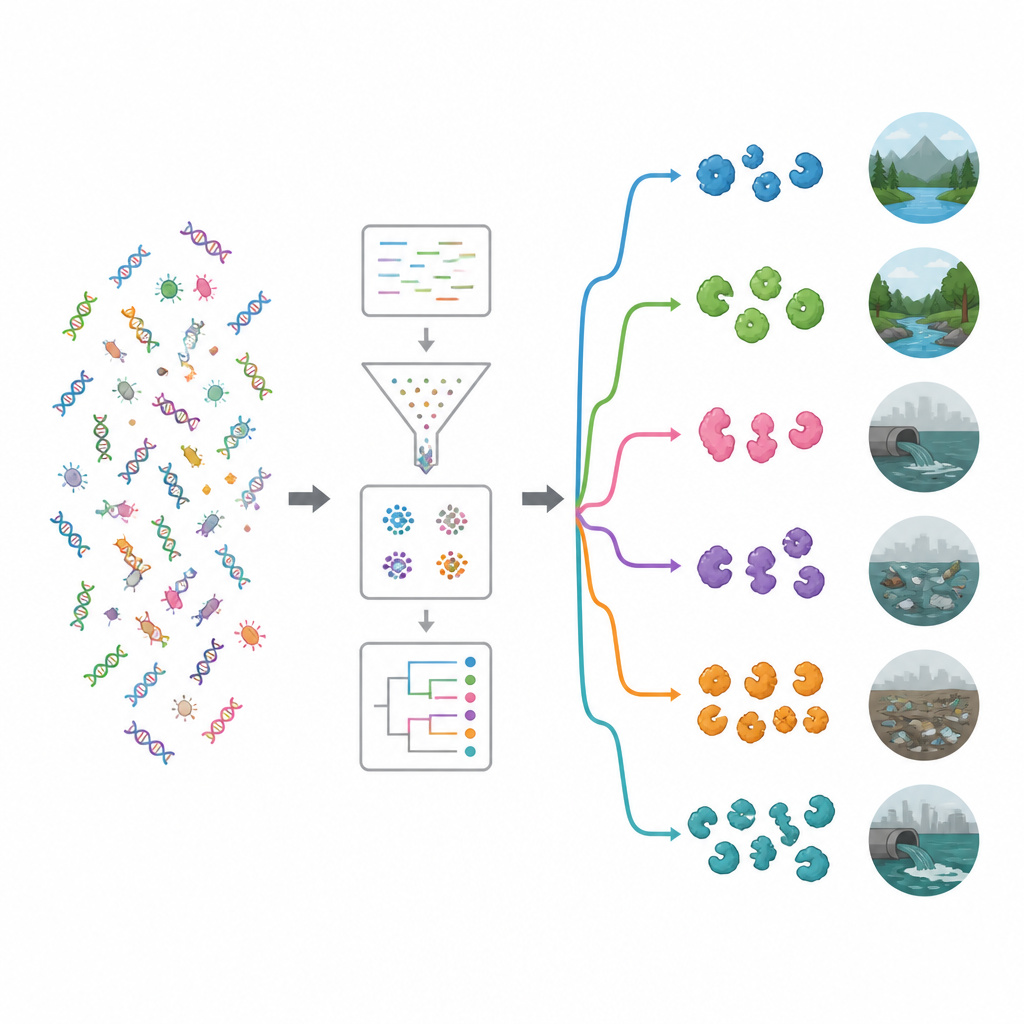
谁在产生这些酶及其适宜栖息地
通过将携带酶基因的序列匹配到其微生物宿主,研究表明许多基因来自已知会产生天然抗菌物质的细菌群体,尤其是假单胞体门(Pseudomonadota)与芽孢杆菌门(Bacillota),以及放线菌门中的链霉菌属(Streptomyces)等。团队随后分析了每种环境中丰富的细菌种类,并使用聚类与机器学习方法将采样点划分为生态学群组。一个群组包含相对原始的环境,例如河流、地下水、植被、卤水和温泉;另一个群组则由更多受人类影响的栖息地组成,包括受塑料污染的地点、污水、蓄水池、靠近农场的海域和粪便样本。受污染的环境往往蕴含更丰富且多样的酶类抗菌基因,这表明剧烈的竞争和化学压力偏向于那些在杀菌工具上投入更多的微生物。
对健康与环境意味着什么
MiGPC 不仅仅是一个庞大的基因清单;它是一张将特定酶、微生物与环境相连接的地图。对非专业读者而言,结论是:无论是受压的环境还是未受干扰的栖息地,都富含能够对抗危险细菌的天然分子,包括那些对常规抗生素已失去敏感性的细菌。许多酶的功能仍然有待揭示,但该目录大大简化了研究者寻找、测试与工程化这些酶的过程。随着时间推移,MiGPC 可为开发新型酶基治疗方法、更安全的食品防腐剂以及用于农场和污染场所的有害微生物管理工具提供指引,帮助社会在不完全依赖传统药物的情况下应对抗微生物耐药性问题。
引用: Afshar Jahanshahi, D., Ariaeenejad, A., Hasannejad, A. et al. MiGPC: a comprehensive catalog of enzybiotics from environmental metagenomes. Sci Rep 16, 15153 (2026). https://doi.org/10.1038/s41598-026-44250-9
关键词: 酶类抗菌剂, 抗微生物酶, 宏基因组学, 微生物生态学, 抗生素耐药性