Clear Sky Science · es
MiGPC: un catálogo exhaustivo de enzifínticos a partir de metagenomas ambientales
Por qué importan las enzimas diminutas para nuestro futuro
A medida que aumenta la resistencia a los antibióticos y los plásticos y contaminantes se extienden por el aire, el agua y el suelo, los científicos buscan nuevas formas de controlar microbios nocivos sin dañar el resto de la naturaleza. Este estudio presenta MiGPC, un vasto catálogo de enzimas naturales que combaten gérmenes extraídas de muchos entornos distintos, desde océanos y fuentes termales hasta intestinos de animales y desechos plásticos. Muestra cuán rica es la mundo microbiano oculto de la Tierra en potenciales nuevos antimicrobianos y ofrece una hoja de ruta para convertir esa diversidad en herramientas prácticas para la medicina, la seguridad alimentaria y la remediación ambiental. 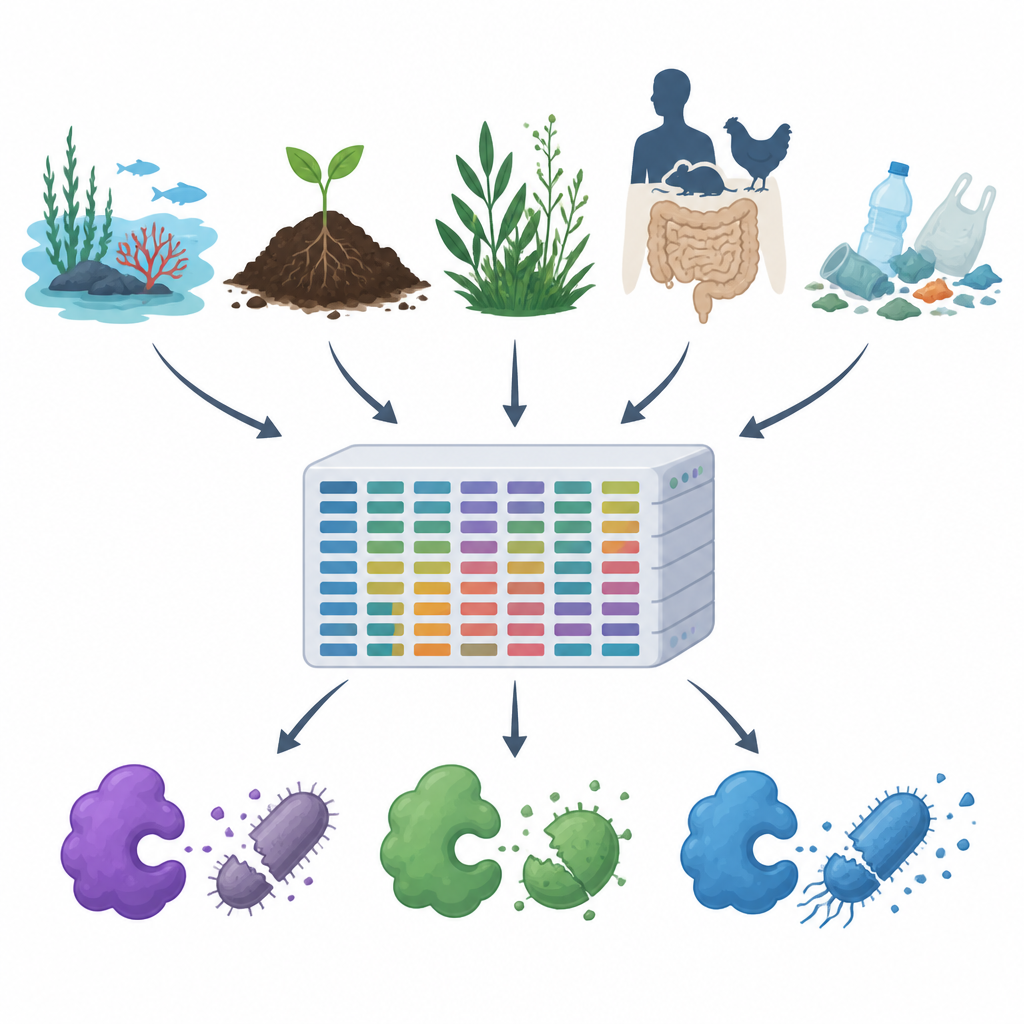
De microbios a agentes naturales contra gérmenes
Los antibióticos tradicionales a menudo actúan como instrumentos toscos, eliminando bacterias útiles junto con las dañinas y fomentando la resistencia con el tiempo. En contraste, muchos microbios emplean enzimas especializadas para atacar rivales con gran precisión, perforando paredes celulares o generando moléculas tóxicas justo donde se necesitan. Estos antimicrobianos basados en enzimas, llamados enzifínticos, pueden hacer estallar células bacterianas, descomponer capas protectoras de mucílago o interrumpir rutas de supervivencia. Los autores se propusieron averiguar cuán extendidas están tales enzimas en la naturaleza y reunir sus planos genéticos en un recurso único y organizado que cualquiera pueda explorar.
Construyendo un catálogo global de enzimas
El equipo primero rastreó bases de datos públicas de proteínas y artículos científicos para recopilar 19 enzimas antimicrobianas bien estudiadas, incluidas cortadoras de paredes celulares, enzimas que digieren proteínas y enzimas oxidantes que generan moléculas reactivas dañinas. Luego usaron estos ejemplos probados como señuelo para escanear grandes conjuntos de datos de ADN procedentes de 15 ambientes muy diferentes, como agua de mar, piscinas hipersalinas, estuarios fluviales, fuentes termales, plantas alpinas, intestinos de animales y humanos, y suelos y aguas contaminados por plástico. Con una canalización computacional de alta potencia limpiaron y ensamblaron alrededor de 1,2 terabytes de lecturas crudas de ADN en fragmentos más largos, predijeron genes y proteínas, eliminaron duplicados y agruparon secuencias relacionadas, terminando con aproximadamente 100 millones de genes y proteínas únicos.
Encontrando funciones ocultas en el ADN ambiental
Para entender qué podrían hacer esos genes, los investigadores los compararon con las principales bases de datos funcionales. Incluso con herramientas modernas, alrededor del 62 por ciento de los genes no pudieron asignarse a una función conocida, lo que insinúa un pozo profundo de biología inexplorada. Entre las funciones reconocibles, las enzimas que actúan sobre azúcares complejos fueron especialmente comunes. Destacaron dos familias: hidrolasas de glicósidos y glicosiltransferasas, muchas de las cuales pueden debilitar paredes celulares bacterianas o biopelículas. Una búsqueda dirigida con una herramienta especializada descubrió casi 20.000 probables enzimas antimicrobianas. La mayoría pertenecía a dos grupos principales: hidrolasas, que cortan moléculas, y oxidorreductasas, que impulsan reacciones electrónicas y pueden generar especies reactivas de oxígeno que dañan a los microbios. 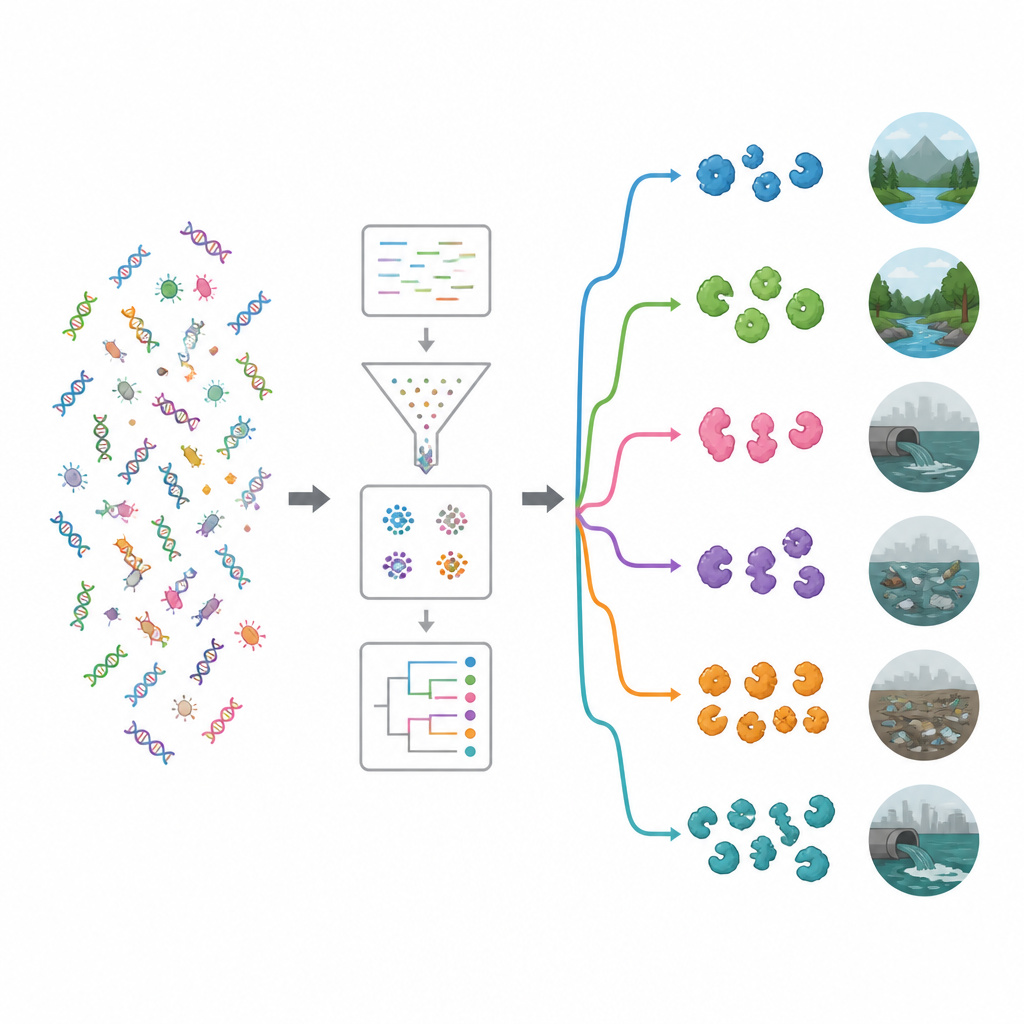
Quién produce estas enzimas y dónde prosperan
Al asociar genes que portan enzimas con sus hospederos microbianos, el estudio mostró que muchos procedían de grupos bacterianos ya conocidos por producir antimicrobianos naturales, en particular Pseudomonadota y Bacillota, así como actinomicetos como Streptomyces. El equipo examinó entonces qué bacterias eran abundantes en cada entorno y usó agrupamiento y aprendizaje automático para clasificar los sitios en grupos ecológicos. Un clúster contenía entornos relativamente prístinos como ríos, aguas subterráneas, vegetación, salmueras y fuentes termales. El otro clúster agrupaba hábitats más influidos por el ser humano, incluidas zonas contaminadas por plástico, aguas residuales, embalses, océanos cercanos a granjas y muestras fecales. Los entornos contaminados tendían a albergar un conjunto más rico y diverso de genes enzifínticos, lo que sugiere que la intensa competencia y el estrés químico favorecen a microbios que invierten mucho en herramientas para matar gérmenes.
Qué significa esto para la salud y el medio ambiente
MiGPC es más que una lista gigantesca de genes; es un mapa que vincula enzimas específicas, microbios y entornos. Para los no especialistas, la conclusión es que tanto los hábitats estresados como los intactos de la Tierra están repletos de moléculas naturales capaces de combatir bacterias peligrosas, incluidas aquellas que ya no responden bien a los antibióticos convencionales. Muchas de estas enzimas siguen siendo funcionalmente misteriosas, pero este catálogo facilita mucho que los investigadores las encuentren, prueben y diseñen. Con el tiempo, MiGPC podría guiar el desarrollo de nuevos tratamientos basados en enzimas, conservantes alimentarios más seguros y herramientas para gestionar microbios nocivos en granjas y sitios contaminados, ayudando a la sociedad a responder a la resistencia antimicrobiana sin depender únicamente de los fármacos tradicionales.
Cita: Afshar Jahanshahi, D., Ariaeenejad, A., Hasannejad, A. et al. MiGPC: a comprehensive catalog of enzybiotics from environmental metagenomes. Sci Rep 16, 15153 (2026). https://doi.org/10.1038/s41598-026-44250-9
Palabras clave: enzifínticos, enzimas antimicrobianas, metagenómica, ecología microbiana, resistencia a los antibióticos