Clear Sky Science · pt
MiGPC: um catálogo abrangente de enziobióticos a partir de metagenomas ambientais
Por que enzimas minúsculas importam para o nosso futuro
À medida que a resistência a antibióticos aumenta e plásticos e poluentes se espalham pelo ar, água e solo, os cientistas buscam maneiras novas de controlar micróbios nocivos sem prejudicar o restante da natureza. Este estudo apresenta o MiGPC, um vasto catálogo de enzimas naturais que combatem germes, extraídas de muitos ambientes diferentes — dos oceanos e fontes termais aos intestinos de animais e detritos plásticos. Ele mostra quão rica é a vida microbiana oculta da Terra em potenciais novos antimicrobianos e oferece um roteiro para transformar essa diversidade em ferramentas práticas para medicina, segurança alimentar e limpeza ambiental. 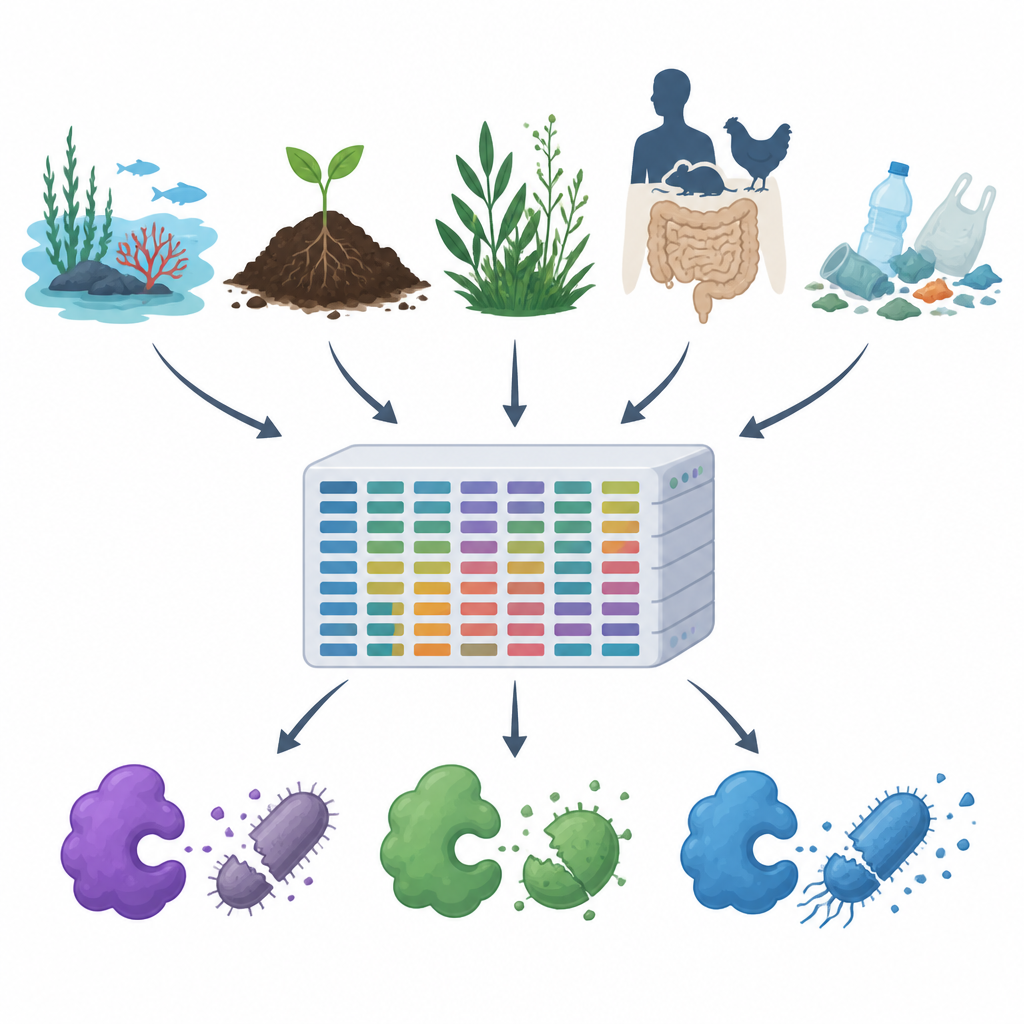
De micróbios a agentes naturais que matam germes
Antibióticos tradicionais muitas vezes atuam como instrumentos de grande impacto, eliminando bactérias úteis junto com as nocivas e incentivando o surgimento de resistência ao longo do tempo. Em contraste, muitos micróbios usam enzimas especializadas para atacar rivais com grande precisão, perfurando paredes celulares ou gerando moléculas tóxicas exatamente onde são necessárias. Esses antimicrobianos à base de enzimas, chamados enziobióticos, podem fazer células bacterianas explodirem, degradar camadas protetoras de muco ou interromper vias de sobrevivência. Os autores buscaram descobrir quão difundidas essas enzimas são na natureza e reunir seus mapas genéticos em um único recurso organizado que qualquer pessoa possa explorar.
Construindo um catálogo global de enzimas
A equipe primeiro vasculhou bancos públicos de proteínas e artigos científicos para coletar 19 enzimas antimicrobianas bem estudadas, incluindo cortadores de parede celular, enzimas que digerem proteínas e enzimas oxidantes que geram moléculas reativas prejudiciais. Em seguida, usaram esses exemplos comprovados como isca para escanear grandes conjuntos de dados de DNA de 15 ambientes muito diferentes, como água do mar, piscinas salinas, estuários de rios, fontes termais, plantas alpinas, intestinos de animais e humanos, e solos e águas contaminados por plástico. Utilizando um pipeline computacional de alto desempenho, limparam e montaram cerca de 1,2 terabytes de leituras brutas de DNA em fragmentos mais longos, previram genes e proteínas, removeram duplicatas e agruparam sequências relacionadas, terminando com aproximadamente 100 milhões de genes e proteínas únicas.
Encontrando funções ocultas no DNA ambiental
Para entender o que esses genes podem fazer, os pesquisadores os compararam com grandes bancos de dados funcionais. Mesmo com ferramentas modernas, cerca de 62% dos genes não puderam ser atribuídos a uma função conhecida, sugerindo um profundo reservatório de biologia inexplorada. Entre as funções reconhecíveis, enzimas que atuam sobre açúcares complexos foram especialmente comuns. Duas famílias — glicossidases e glicosiltransferases — se destacaram, muitas das quais podem enfraquecer paredes celulares bacterianas ou biofilmes. Uma busca direcionada com uma ferramenta especializada revelou quase 20.000 prováveis enzimas antimicrobianas. A maioria pertencia a dois grupos principais: hidrolases, que cortam moléculas, e oxidorredutases, que conduzem reações envolvendo elétrons e podem gerar espécies reativas de oxigênio que danificam micróbios. 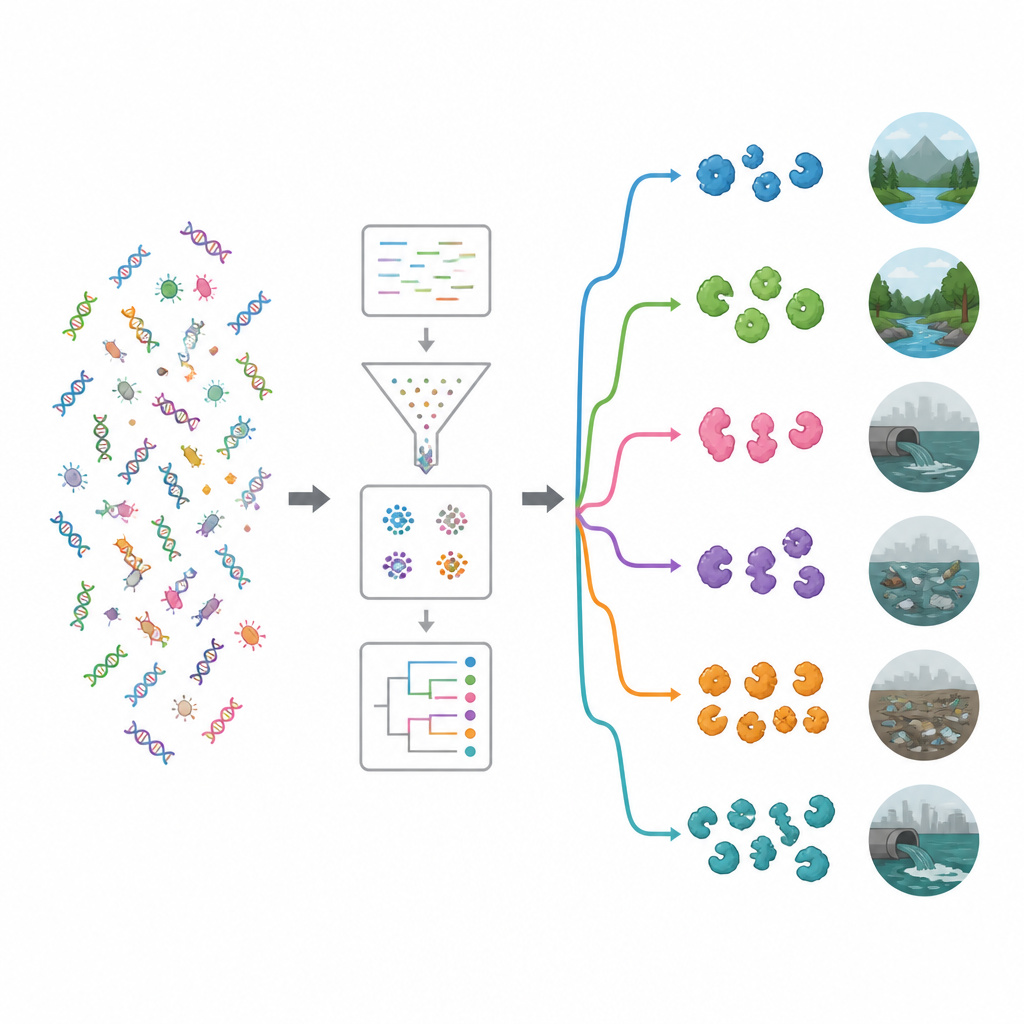
Quem produz essas enzimas e onde elas prosperam
Ao associar genes portadores de enzimas aos seus hospedeiros microbianos, o estudo mostrou que muitos vinham de grupos bacterianos já conhecidos por produzirem antimicrobianos naturais, particularmente Pseudomonadota e Bacillota, além de actinobactérias como Streptomyces. A equipe então examinou quais bactérias eram abundantes em cada ambiente e usou agrupamento e aprendizado de máquina para classificar os locais em grupos ecológicos. Um aglomerado continha ambientes relativamente pristinos, como rios, águas subterrâneas, vegetação, salmouras e fontes termais. O outro agrupava habitats mais influenciados por humanos, incluindo locais poluídos por plástico, estações de tratamento de esgoto, reservatórios, oceanos próximos a fazendas e amostras fecais. Ambientes poluídos tendiam a abrigar um conjunto mais rico e diverso de genes enziobióticos, sugerindo que competição intensa e estresse químico favorecem micróbios que investem pesado em ferramentas para matar germes.
O que isso significa para a saúde e o meio ambiente
O MiGPC é mais que uma lista gigante de genes; é um mapa que conecta enzimas específicas, micróbios e ambientes. Para não especialistas, a conclusão é que tanto habitats estressados quanto intocados da Terra estão repletos de moléculas naturais capazes de combater bactérias perigosas, incluindo aquelas que já não respondem bem aos antibióticos padrão. Muitas dessas enzimas ainda são funcionalmente misteriosas, mas este catálogo facilita muito para os pesquisadores encontrá-las, testá-las e projetá-las. Com o tempo, o MiGPC pode orientar o desenvolvimento de novos tratamentos à base de enzimas, conservantes alimentares mais seguros e ferramentas para gerenciar micróbios nocivos em fazendas e locais poluídos, ajudando a sociedade a responder à resistência antimicrobiana sem depender exclusivamente de fármacos tradicionais.
Citação: Afshar Jahanshahi, D., Ariaeenejad, A., Hasannejad, A. et al. MiGPC: a comprehensive catalog of enzybiotics from environmental metagenomes. Sci Rep 16, 15153 (2026). https://doi.org/10.1038/s41598-026-44250-9
Palavras-chave: enziobióticos, enzimas antimicrobianas, metagenômica, ecologia microbiana, resistência a antibióticos