Clear Sky Science · sv
MiGPC: en omfattande katalog över enzybiotika från miljömetagenomer
Varför små enzymer spelar roll för vår framtid
När antibiotikaresistensen ökar och plaster och föroreningar sprids i vår luft, vatten och jord söker forskare nya sätt att kontrollera skadliga mikrober utan att skada resten av naturen. Denna studie presenterar MiGPC, en omfattande katalog över naturliga bakteriedödande enzymer hämtade från många olika miljöer — från oceaner och varma källor till djurs tarmar och plastavfall. Den visar hur rikt jordens dolda mikrobiella värld är på potentiella nya antimikrobiella ämnen och erbjuder en färdplan för hur den mångfalden kan omvandlas till praktiska verktyg för medicin, livsmedelssäkerhet och miljörengöring. 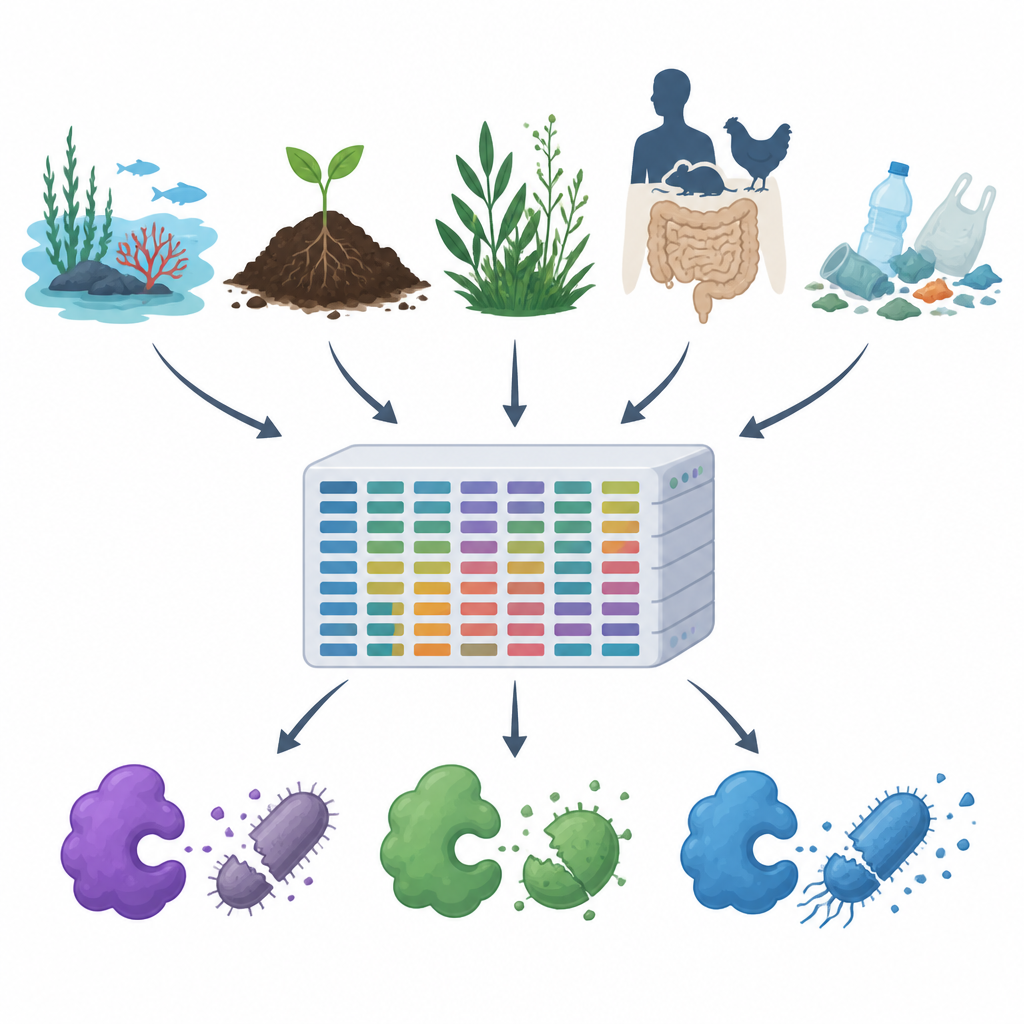
Från mikrober till naturliga bakteriedödare
Traditionella antibiotika fungerar ofta som slöa verktyg, genom att utplåna hjälpsamma bakterier tillsammans med de skadliga och uppmuntra resistens över tid. Många mikrober använder däremot specialiserade enzymer för att angripa rivaler med hög precision, genom att göra hål i cellväggar eller skapa giftiga molekyler precis där de behövs. Dessa enzymbaserade antimikrobiella medel, kallade enzybiotika, kan få bakterieceller att spricka, bryta ner skyddande slemlager eller störa överlevnadsvägar. Författarna ville ta reda på hur utbredda sådana enzymer är i naturen och samla deras genetiska ritningar i en enda, organiserad resurs som vem som helst kan utforska.
Att bygga en global enzymkatalog
Forskargruppen gick först igenom offentliga proteindatabaser och vetenskapliga artiklar för att samla 19 välstuderade antimikrobiella enzymer, inklusive cellväggsklippare, proteinnedbrytande enzymer och oxiderande enzymer som genererar skadliga reaktiva molekyler. De använde sedan dessa beprövade exempel som bete för att söka igenom stora DNA-datamängder från 15 mycket olika miljöer, såsom havsvatten, saltlakebassänger, flodmynningar, varma källor, alpina växter, djur- och människotarmar samt plastförorenade jordar och vatten. Med en högpresterande beräkningspipeline rengjorde och satte de ihop cirka 1,2 terabyte råa DNA-avläsningar till längre fragment, förutsade gener och proteiner, tog bort dubbletter och grupperade relaterade sekvenser, vilket resulterade i ungefär 100 miljoner unika gener och proteiner.
Att hitta dolda funktioner i miljö-DNA
För att förstå vad dessa gener kan göra jämförde forskarna dem med stora funktionella databaser. Även med moderna verktyg kunde cirka 62 procent av generna inte tilldelas en känd funktion, vilket antyder en djup brunn av outforskad biologi. Bland igenkännbara funktioner var enzymer som verkar på komplexa sockerarter särskilt vanliga. Två familjer — glykosidhydrolaser och glykosytransferaser — utmärkte sig, många av vilka kan försvaga bakteriers cellväggar eller biofilmer. En riktad sökning med ett specialiserat verktyg upptäckte nästan 20 000 troliga antimikrobiella enzymer. De flesta tillhörde två huvudgrupper: hydrolaser, som klyver molekyler, och oxidorreductaser, som driver reaktioner som involverar elektroner och kan generera reaktiva syreföreningar som skadar mikrober. 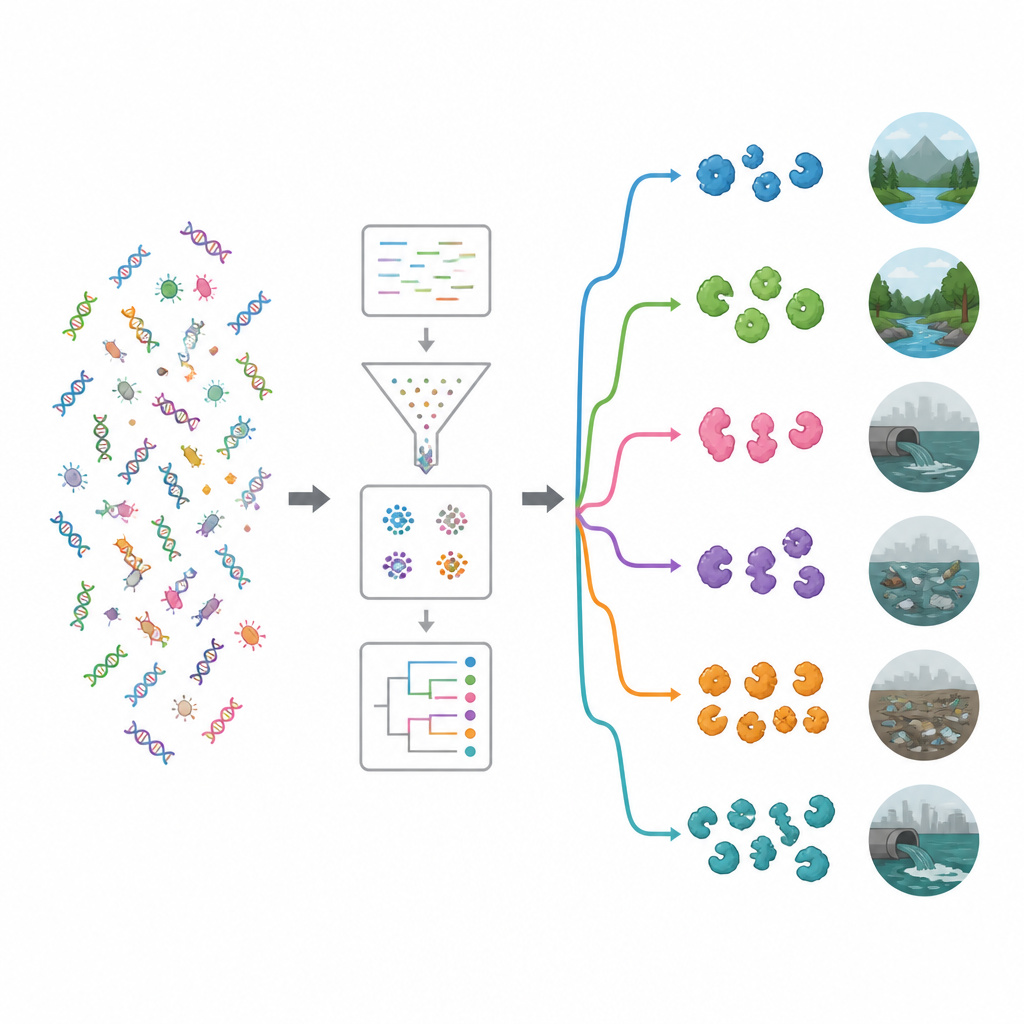
Vem producerar dessa enzymer och var de trivs
Genom att matcha enzymbärande gener till deras mikrobiska värdar visade studien att många kom från bakteriegrupper som redan är kända för att producera naturliga antimikrobiella ämnen, särskilt Pseudomonadota och Bacillota, samt aktinobakterier som Streptomyces. Teamet undersökte sedan vilka bakterier som var vanliga i varje miljö och använde klustring och maskininlärning för att sortera platserna i ekologiska grupper. Ett kluster innehöll relativt opåverkade miljöer såsom floder, grundvatten, vegetation, saltlake och varma källor. Det andra klustret omfattade mer människopåverkade habitat, inklusive plastförorenade platser, avloppsvatten, reservoarer, hav nära jordbruk och fecalprov. Förorenade miljöer tenderade att hysa ett rikare och mer mångsidigt utbud av enzybiotiska gener, vilket tyder på att intensiv konkurrens och kemisk stress gynnar mikrober som satsar mycket på bakteriedödande verktyg.
Vad detta betyder för hälsa och miljö
MiGPC är mer än en jätteförteckning över gener; det är en karta som kopplar specifika enzymer, mikrober och miljöer. För icke-specialister är slutsatsen att både pressade och orörda miljöer är fullpackade med naturliga molekyler som kan bekämpa farliga bakterier, inklusive sådana som inte längre svarar väl på vanliga antibiotika. Många av dessa enzymer är fortfarande funktionellt gåtfulla, men denna katalog gör det mycket enklare för forskare att hitta, testa och konstruera dem. Med tiden kan MiGPC guida utvecklingen av nya enzymbaserade behandlingar, säkrare livsmedelskonserveringsmedel och verktyg för att hantera skadliga mikrober i jordbruk och förorenade områden, vilket hjälper samhället att möta antibiotikaresistens utan att enbart förlita sig på traditionella läkemedel.
Citering: Afshar Jahanshahi, D., Ariaeenejad, A., Hasannejad, A. et al. MiGPC: a comprehensive catalog of enzybiotics from environmental metagenomes. Sci Rep 16, 15153 (2026). https://doi.org/10.1038/s41598-026-44250-9
Nyckelord: enzybiotika, antimikrobiella enzymer, metagenomik, mikrobiell ekologi, antibiotikaresistens