Clear Sky Science · it
MiGPC: un catalogo completo di enzifarmaci da metagenomi ambientali
Perché i piccoli enzimi contano per il nostro futuro
Con l’aumento della resistenza agli antibiotici e la diffusione di plastiche e inquinanti nell’aria, nell’acqua e nel suolo, gli scienziati cercano nuovi modi per controllare i microrganismi nocivi senza danneggiare il resto della natura. Questo studio presenta MiGPC, un vasto catalogo di enzimi naturali che combattono i germi, ricavato da molti ambienti diversi, dagli oceani e dalle sorgenti termali fino agli intestini di animali e ai rifiuti plastici. Mostra quanto sia ricco il mondo microbico nascosto della Terra di potenziali nuovi antimicrobici e offre una roadmap per trasformare quella diversità in strumenti pratici per la medicina, la sicurezza alimentare e il risanamento ambientale. 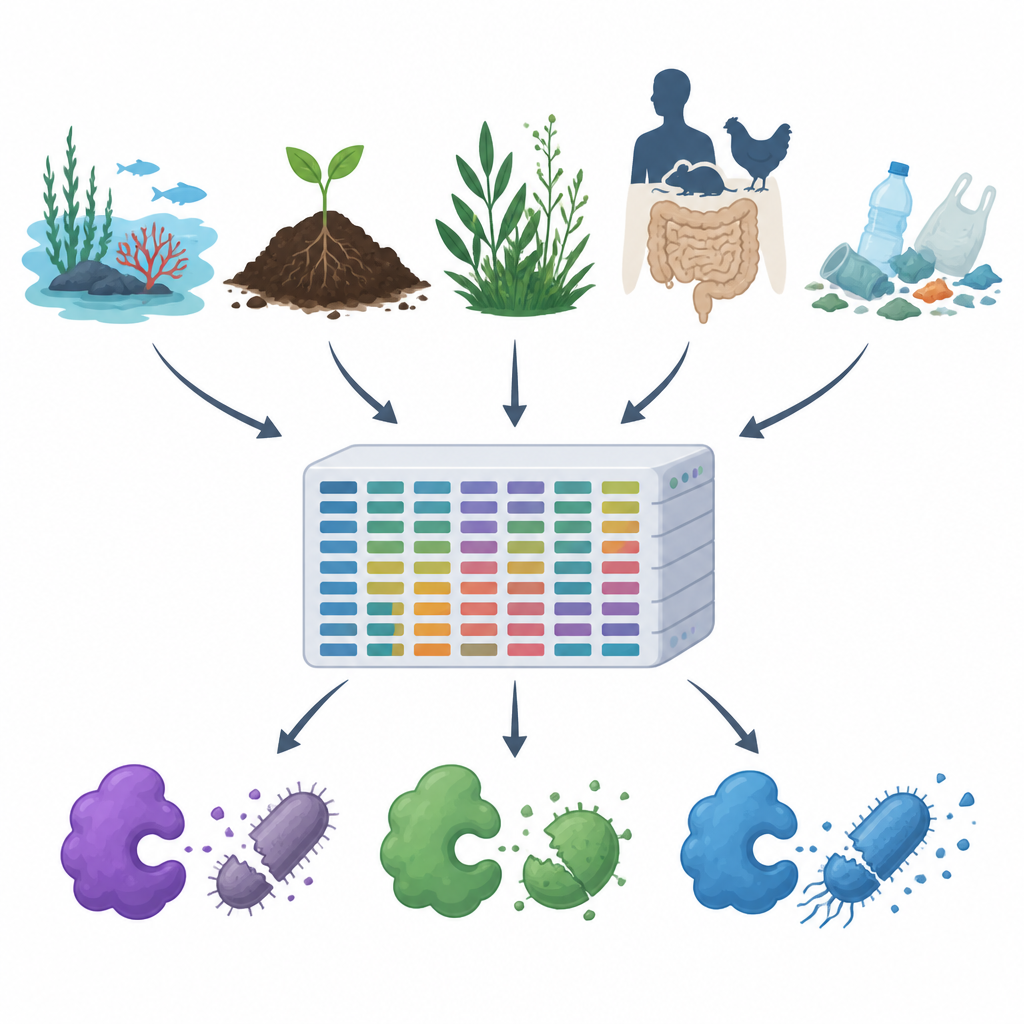
Dai microbi ai killer naturali dei germi
Gli antibiotici tradizionali spesso agiscono come strumenti rozzi, eliminando i batteri utili insieme a quelli dannosi e favorendo nel tempo la comparsa di resistenze. Per contro, molti microbi usano enzimi specializzati per attaccare i rivali con grande precisione, perforando pareti cellulari o generando molecole tossiche proprio dove servono. Questi antimicrobici a base di enzimi, chiamati enzifarmaci, possono far scoppiare cellule batteriche, degradare strati protettivi di muco o interferire con vie di sopravvivenza. Gli autori si sono posti l’obiettivo di stabilire quanto siano diffusi in natura tali enzimi e di raccoglierne i progetti genetici in una risorsa unica e organizzata che chiunque possa esplorare.
Costruire un catalogo globale di enzimi
Il team ha prima setacciato banche dati proteiche pubbliche e articoli scientifici per raccogliere 19 enzimi antimicrobici ben studiati, tra cui taglia-pareti cellulari, enzimi proteolitici e ossidanti che generano molecole reattive dannose. Hanno poi usato questi esempi comprovati come esche per scandagliare grandi dataset di DNA provenienti da 15 ambienti molto diversi, come acqua di mare, pozze salmastre, estuari di fiumi, sorgenti termali, piante alpine, intestini animali e umani e suoli e acque contaminati da plastica. Utilizzando una pipeline computazionale ad alte prestazioni, hanno pulito e assemblato circa 1,2 terabyte di letture di DNA grezze in frammenti più lunghi, predetto geni e proteine, rimosso duplicati e raggruppato sequenze correlate, ottenendo all’incirca 100 milioni di geni e proteine unici.
Trovare funzioni nascoste nel DNA ambientale
Per capire cosa potessero fare questi geni, i ricercatori li hanno confrontati con i principali database funzionali. Anche con strumenti moderni, circa il 62 percento dei geni non è stato assegnabile a una funzione nota, suggerendo un profondo serbatoio di biologia inesplorata. Tra le funzioni riconoscibili, gli enzimi che agiscono su zuccheri complessi erano particolarmente comuni. Sono emerse due famiglie: le glicosidasi idrolitiche e le glicoziltransferasi, molte delle quali possono indebolire pareti cellulari batteriche o biofilm. Una ricerca mirata con uno strumento specializzato ha individuato quasi 20.000 probabili enzimi antimicrobici. La maggior parte apparteneva a due gruppi principali: idrolasi, che tagliano le molecole, e ossidoreduttasi, che guidano reazioni elettroniche e possono generare specie reattive dell’ossigeno che danneggiano i microrganismi. 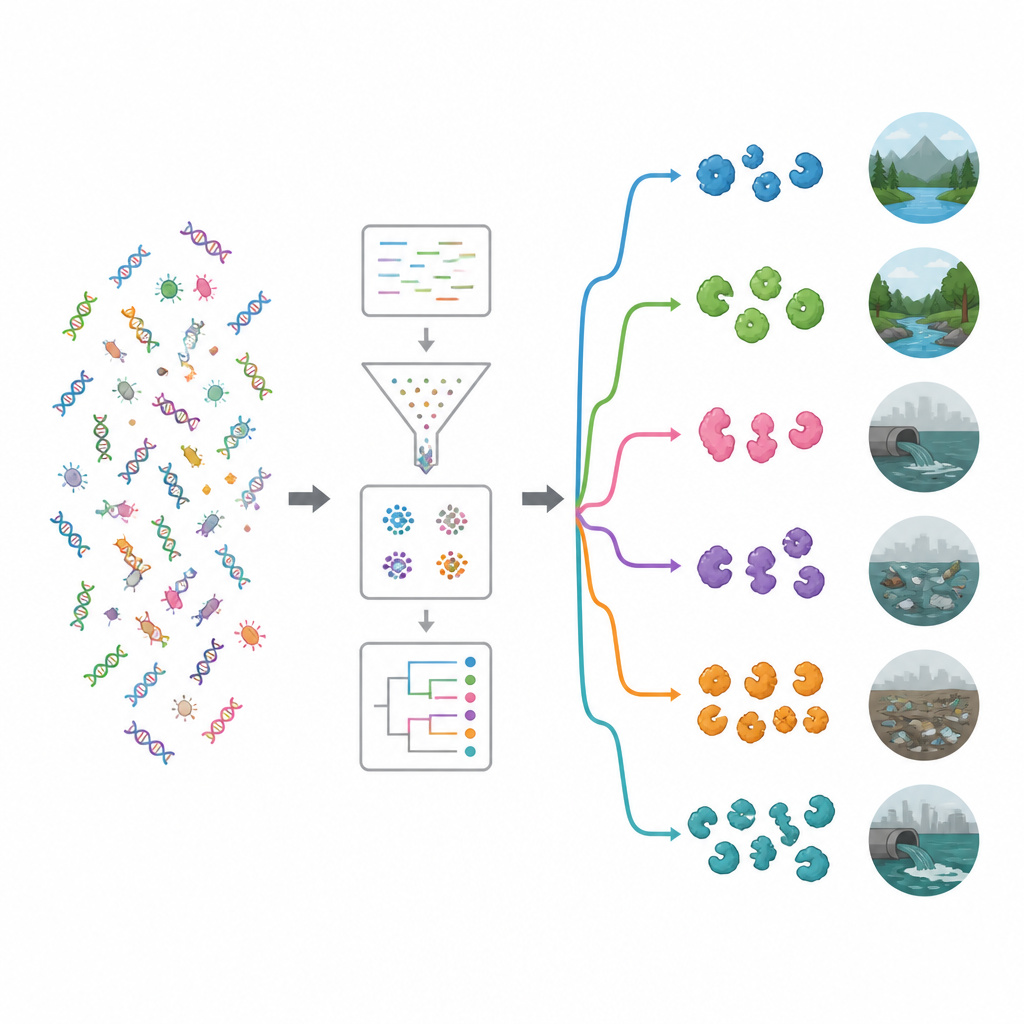
Chi produce questi enzimi e dove prosperano
Abbinando i geni portatori di enzimi ai loro ospiti microbici, lo studio ha mostrato che molti provenivano da gruppi batterici già noti per produrre antimicrobici naturali, in particolare Pseudomonadota e Bacillota, oltre ad actinomiceti come Streptomyces. Il team ha quindi esaminato quali batteri erano abbondanti in ciascun ambiente e ha usato clustering e apprendimento automatico per raggruppare i siti in insiemi ecologici. Un cluster conteneva ambienti relativamente incontaminati come fiumi, falde acquifere, vegetazione, acque salmastre e sorgenti termali. L’altro cluster comprendeva habitat più influenzati dall’uomo, inclusi siti inquinati da plastica, acque reflue, bacini, oceani vicino ad allevamenti e campioni fecali. Gli ambienti inquinati tendevano a ospitare un repertorio più ricco e diversificato di geni enzifarmaci, suggerendo che la competizione intensa e lo stress chimico favoriscano microbi che investono molto in strumenti di lotta contro i germi.
Cosa significa per la salute e l’ambiente
MiGPC è più di una lista gigantesca di geni; è una mappa che collega enzimi specifici, microrganismi e ambienti. Per i non specialisti, il messaggio è che sia gli habitat stressati sia quelli intatti della Terra sono pieni di molecole naturali capaci di combattere batteri pericolosi, inclusi quelli che non rispondono più bene agli antibiotici standard. Molti di questi enzimi restano ancora funzionalmente misteriosi, ma questo catalogo rende molto più semplice per i ricercatori individuarli, testarli e progettarli. Col tempo, MiGPC potrebbe guidare lo sviluppo di nuovi trattamenti a base di enzimi, conservanti alimentari più sicuri e strumenti per gestire microrganismi nocivi in agricoltura e siti inquinati, aiutando la società a rispondere alla resistenza antimicrobica senza fare affidamento esclusivo sui farmaci tradizionali.
Citazione: Afshar Jahanshahi, D., Ariaeenejad, A., Hasannejad, A. et al. MiGPC: a comprehensive catalog of enzybiotics from environmental metagenomes. Sci Rep 16, 15153 (2026). https://doi.org/10.1038/s41598-026-44250-9
Parole chiave: enzifarmaci, enzimi antimicrobici, metagenomica, ecologia microbica, resistenza agli antibiotici