Clear Sky Science · pl
MiGPC: kompleksowy katalog enzybiotyków z metagenomów środowiskowych
Dlaczego małe enzymy mają znaczenie dla naszej przyszłości
W miarę jak rośnie oporność na antybiotyki, a plastiki i zanieczyszczenia rozprzestrzeniają się w powietrzu, wodzie i glebie, naukowcy poszukują nowych sposobów kontrolowania szkodliwych drobnoustrojów bez szkody dla reszty przyrody. W tym badaniu przedstawiono MiGPC, obszerny katalog naturalnych enzymów zwalczających zarazki, pobranych z wielu różnych środowisk — od oceanów i gorących źródeł po przewody pokarmowe zwierząt i odpady z plastiku. Pokazuje on, jak bogaty jest ukryty świat mikroorganizmów Ziemi w potencjalne nowe środki przeciwdrobnoustrojowe i oferuje plan działania umożliwiający przekształcenie tej różnorodności w praktyczne narzędzia dla medycyny, bezpieczeństwa żywności i oczyszczania środowiska. 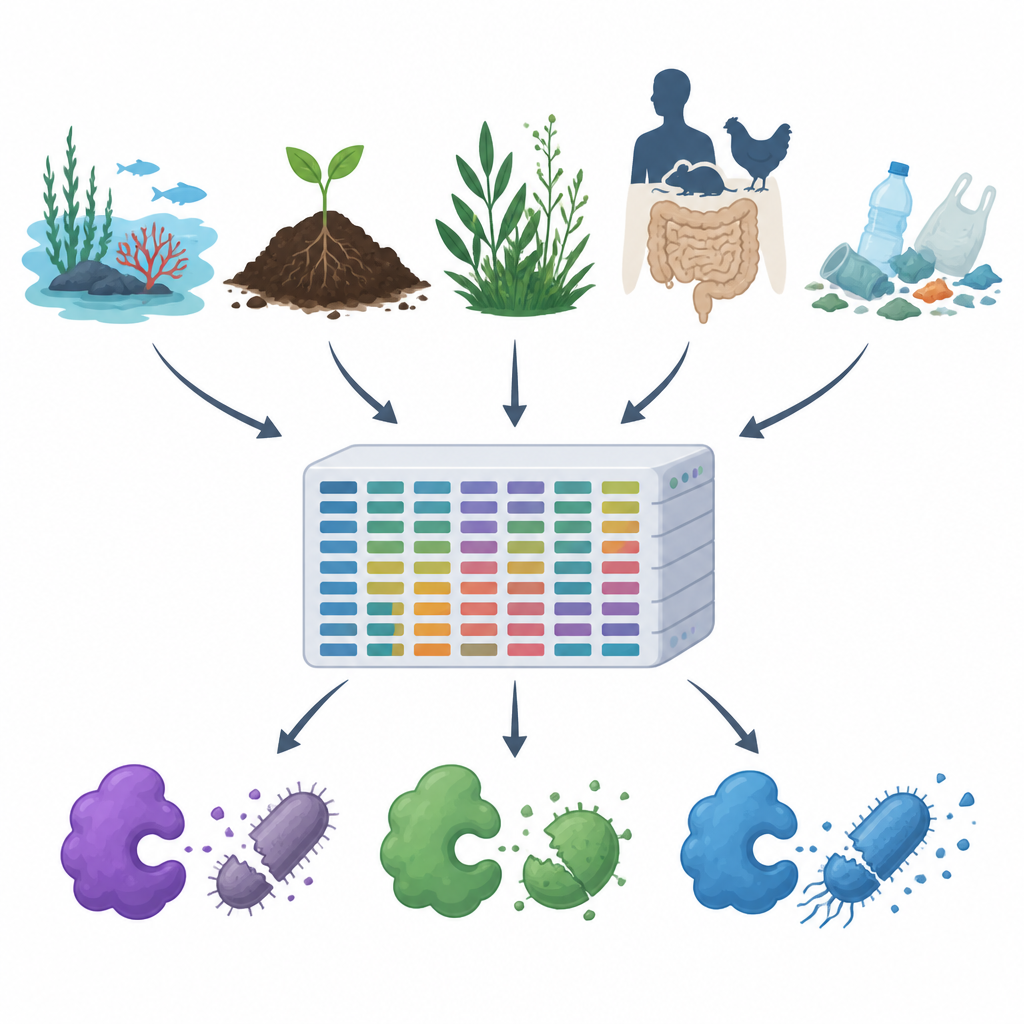
Od mikroorganizmów do naturalnych zabójców zarazków
Tradycyjne antybiotyki często działają jak tępe narzędzia, niszcząc pożyteczne bakterie razem ze szkodliwymi i z czasem sprzyjając powstawaniu oporności. W przeciwieństwie do nich wiele mikroorganizmów używa wyspecjalizowanych enzymów do precyzyjnego atakowania rywali — tworząc dziury w ścianach komórkowych lub generując toksyczne cząsteczki dokładnie tam, gdzie są potrzebne. Te enzymatyczne środki przeciwmikrobowe, zwane enzybiotykami, mogą powodować pękanie komórek bakteryjnych, rozkładać ochronne warstwy śluzu lub zaburzać ścieżki przetrwania. Autorzy postawili sobie za cel ustalić, jak powszechne są takie enzymy w przyrodzie i zgromadzić ich genetyczne plany w jednym, uporządkowanym zasobie, który każdy może przeglądać.
Budowanie globalnego katalogu enzymów
Zespół najpierw przeszukał publiczne bazy białek i literaturę naukową, aby zebrać 19 dobrze scharakteryzowanych enzymów przeciwmikrobowych, w tym enzymy tnące ściany komórkowe, enzymy trawiące białka oraz oksydazy generujące szkodliwe reaktywne cząsteczki. Następnie użyli tych potwierdzonych przykładów jako przynęty do skanowania dużych zestawów danych DNA z 15 bardzo różnych środowisk, takich jak woda morska, zbiorniki solne, ujścia rzek, gorące źródła, roślinność alpejska, przewody pokarmowe zwierząt i ludzi oraz gleby i wody skażone plastikiem. Za pomocą zaawansowanego pipeline’u obliczeniowego oczyszczono i zmontowano około 1,2 terabajta surowych odczytów DNA w dłuższe fragmenty, przewidziano geny i białka, usunięto duplikaty i pogrupowano powiązane sekwencje, co doprowadziło do około 100 milionów unikalnych genów i białek.
Odkrywanie ukrytych funkcji w DNA środowiskowym
Aby zrozumieć, jakie funkcje mogą pełnić te geny, badacze porównali je z głównymi bazami funkcjonalnymi. Nawet przy użyciu nowoczesnych narzędzi około 62 procent genów nie dało się przypisać do znanej roli, co sugeruje głębokie źródło niewykorzystanej biologii. Wśród rozpoznawalnych funkcji szczególnie częste były enzymy działające na złożone cukry. Dwie rodziny — glikozydazy hydrolazy i transferazy glikozydowe — wyróżniały się, z wieloma przedstawicielami mogącymi osłabiać ściany komórkowe bakterii lub biofilmy. Ukierunkowane poszukiwanie za pomocą specjalistycznego narzędzia wykryło niemal 20 000 prawdopodobnych enzymów przeciwmikrobowych. Większość należała do dwóch głównych grup: hydrolaz, które rozcinają cząsteczki, oraz oksydoreduktaz, które napędzają reakcje z udziałem elektronów i mogą generować reaktywne formy tlenu uszkadzające drobnoustroje. 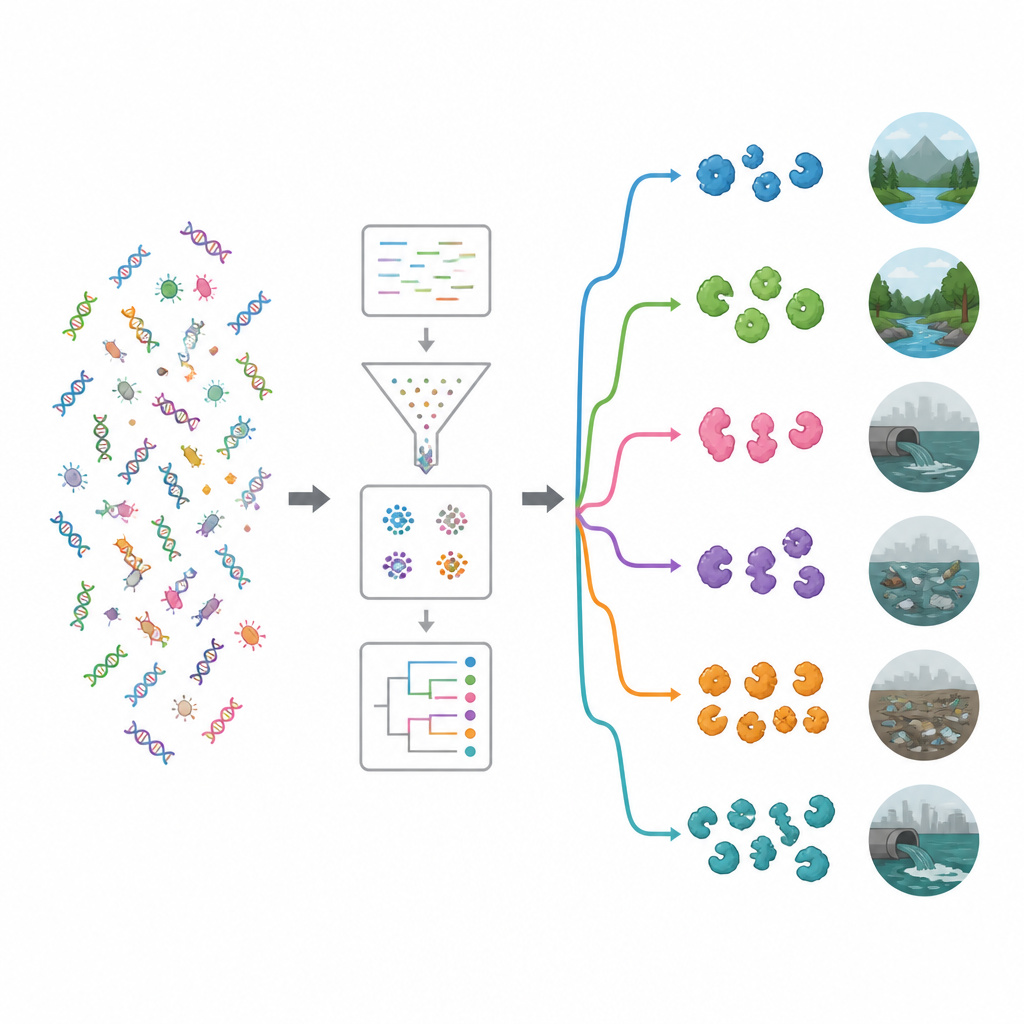
Kto produkuje te enzymy i gdzie się rozwijają
Poprzez dopasowanie genów kodujących enzymy do ich gospodarzy mikrobiologicznych badanie wykazało, że wiele pochodziło z grup bakteryjnych już znanych z produkcji naturalnych środków przeciwmikrobowych, w szczególności Pseudomonadota i Bacillota, a także promieniowców takich jak Streptomyces. Zespół następnie przeanalizował, które bakterie dominują w poszczególnych środowiskach i użył klasteryzacji oraz uczenia maszynowego, aby pogrupować miejsca w grupy ekologiczne. Jeden klaster obejmował stosunkowo nienaruszone środowiska, takie jak rzeki, wody gruntowe, roślinność, słone jeziora i gorące źródła. Drugi klaster obejmował bardziej środowiska pod wpływem człowieka, w tym miejsca zanieczyszczone plastikiem, ścieki, zbiorniki wodne, obszary morskie w pobliżu gospodarstw i próbki kału. Środowiska zanieczyszczone miały tendencję do zawierania bogatszego i bardziej zróżnicowanego zestawu genów enzybiotyków, co sugeruje, że intensywna konkurencja i stres chemiczny sprzyjają mikrobom inwestującym w narzędzia do zwalczania zarazków.
Co to oznacza dla zdrowia i środowiska
MiGPC to więcej niż gigantyczna lista genów; to mapa łącząca konkretne enzymy, mikroby i środowiska. Dla osób niebędących specjalistami kluczowy wniosek jest taki, że zarówno zestresowane, jak i nietknięte siedliska Ziemi są pełne naturalnych cząsteczek zdolnych zwalczać groźne bakterie, w tym te, które przestały reagować na standardowe antybiotyki. Wiele z tych enzymów wciąż pozostaje funkcjonalnie tajemniczych, ale katalog znacznie ułatwia badaczom ich odnalezienie, przetestowanie i zaprojektowanie. Z czasem MiGPC może kierować rozwojem nowych terapii enzymatycznych, bezpieczniejszych konserwantów żywności i narzędzi do zarządzania szkodliwymi mikroorganizmami na farmach i w miejscach zanieczyszczonych, pomagając społeczeństwu radzić sobie z opornością na antybiotyki bez polegania wyłącznie na tradycyjnych lekach.
Cytowanie: Afshar Jahanshahi, D., Ariaeenejad, A., Hasannejad, A. et al. MiGPC: a comprehensive catalog of enzybiotics from environmental metagenomes. Sci Rep 16, 15153 (2026). https://doi.org/10.1038/s41598-026-44250-9
Słowa kluczowe: enzybiotyki, enzymy przeciwmikrobowe, metagenomika, ekologia mikroorganizmów, oporność na antybiotyki