Clear Sky Science · ru
MiGPC: всеобъемлющий каталог энзибиоотиков из метагеномов окружающей среды
Почему крошечные ферменты важны для нашего будущего
По мере роста устойчивости к антибиотикам и распространения пластика и загрязнителей в воздухе, воде и почве ученые ищут новые способы контролировать вредные микробы, не причиняя вреда остальной части природы. В этом исследовании представлен MiGPC — обширный каталог природных антимикробных ферментов, собранных из самых разных сред: от океанов и горячих источников до кишечников животных и мусора из пластика. Он демонстрирует, насколько богата скрытая микробная вселенная Земли потенциально новыми антимикробными средствами, и предлагает дорожную карту превращения этого разнообразия в практические инструменты для медицины, безопасности пищевых продуктов и очистки окружающей среды. 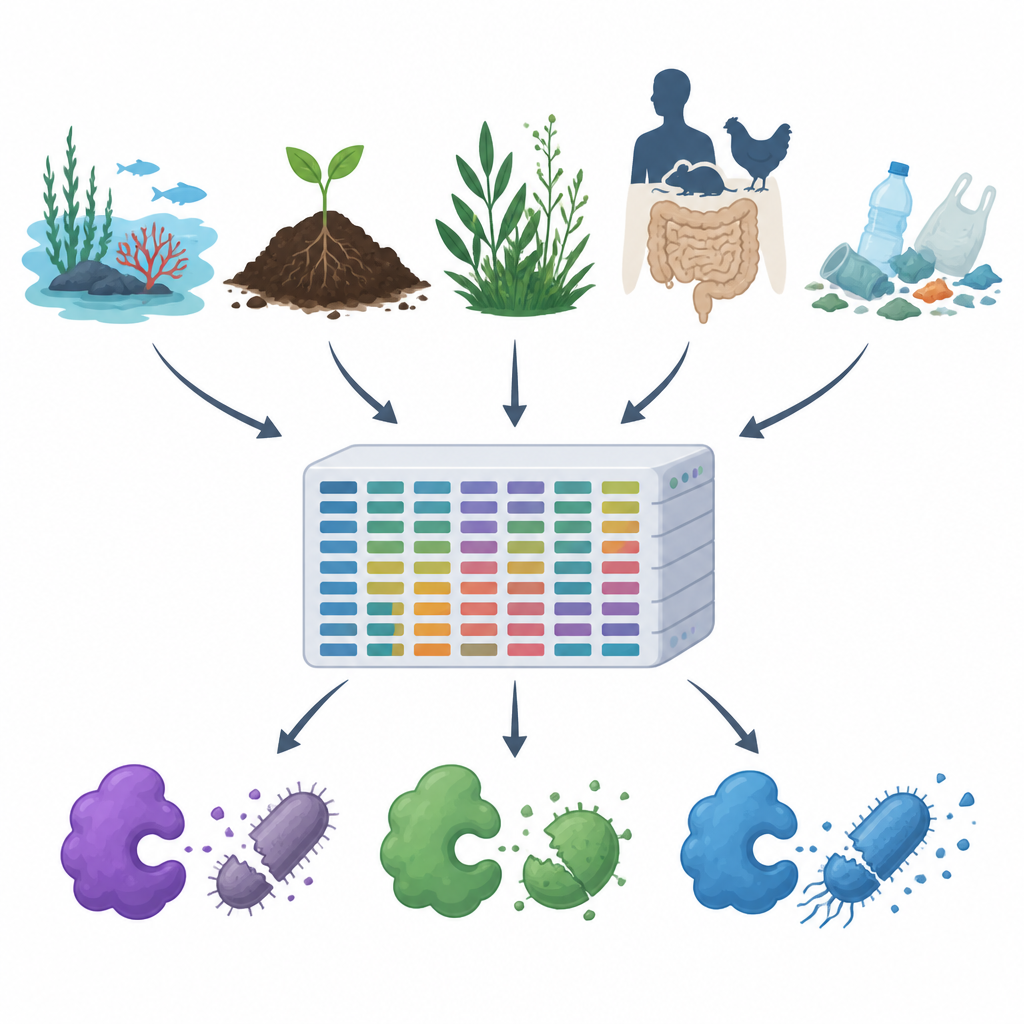
От микробов к природным убийцам микробов
Традиционные антибиотики часто действуют как грубые инструменты, уничтожая полезные бактерии наряду с вредными и способствуя со временем развитию резистентности. Напротив, многие микробы используют специализированные ферменты для точечной атаки соперников, пробивая клеточные стенки или генерируя токсичные молекулы прямо там, где это нужно. Эти ферментные антимикробы, называемые энзибиоотиками, могут разрывать бактериальные клетки, расщеплять защитные слизистые слои или нарушать пути, жизненно важные для выживания. Авторы поставили цель выяснить, насколько широко такие ферменты распространены в природе, и собрать их генетические схемы в единый организованный ресурс, доступный для изучения всем желающим.
Создание глобального каталога ферментов
Команда сначала изучила публичные белковые базы данных и научную литературу, чтобы собрать 19 хорошо изученных антимикробных ферментов, включая ферменты, разрезающие клеточную стенку, протеолитические ферменты и окислители, генерирующие вредные реактивные молекулы. Затем они использовали эти проверенные примеры как приманку для сканирования больших наборов ДНК из 15 очень разных сред — морской воды, солевых бассейнов, устьев рек, горячих источников, альпийских растений, кишечников животных и людей, а также почв и вод, загрязненных пластиком. С помощью мощного вычислительного конвейера они очистили и собрали примерно 1,2 терабайта сырых чтений ДНК в более длинные фрагменты, предсказали гены и белки, удалили дубликаты и сгруппировали родственные последовательности, в итоге получив примерно 100 миллионов уникальных генов и белков.
Поиск скрытых функций в экологической ДНК
Чтобы понять возможные функции этих генов, исследователи сопоставили их с основными функциональными базами данных. Даже при современных инструментах около 62 процентов генов нельзя было отнести к известной функции, что указывает на глубокий запас неисследованной биологии. Среди распознаваемых функций особенно часто встречались ферменты, работающие с сложными сахарами. Две семейства — гликозид-гидролазы и гликозилтрансферазы — выделялись, многие представители которых способны ослаблять бактериальные клеточные стенки или биопленки. Целенаправленный поиск с использованием специализированного инструмента обнаружил почти 20 000 потенциальных антимикробных ферментов. Большинство принадлежало двум основным группам: гидролазам, расщепляющим молекулы, и оксидоредуктазам, приводящим в действие реакции с переносом электронов и способным генерировать реактивные кислородные виды, повреждающие микроорганизмы. 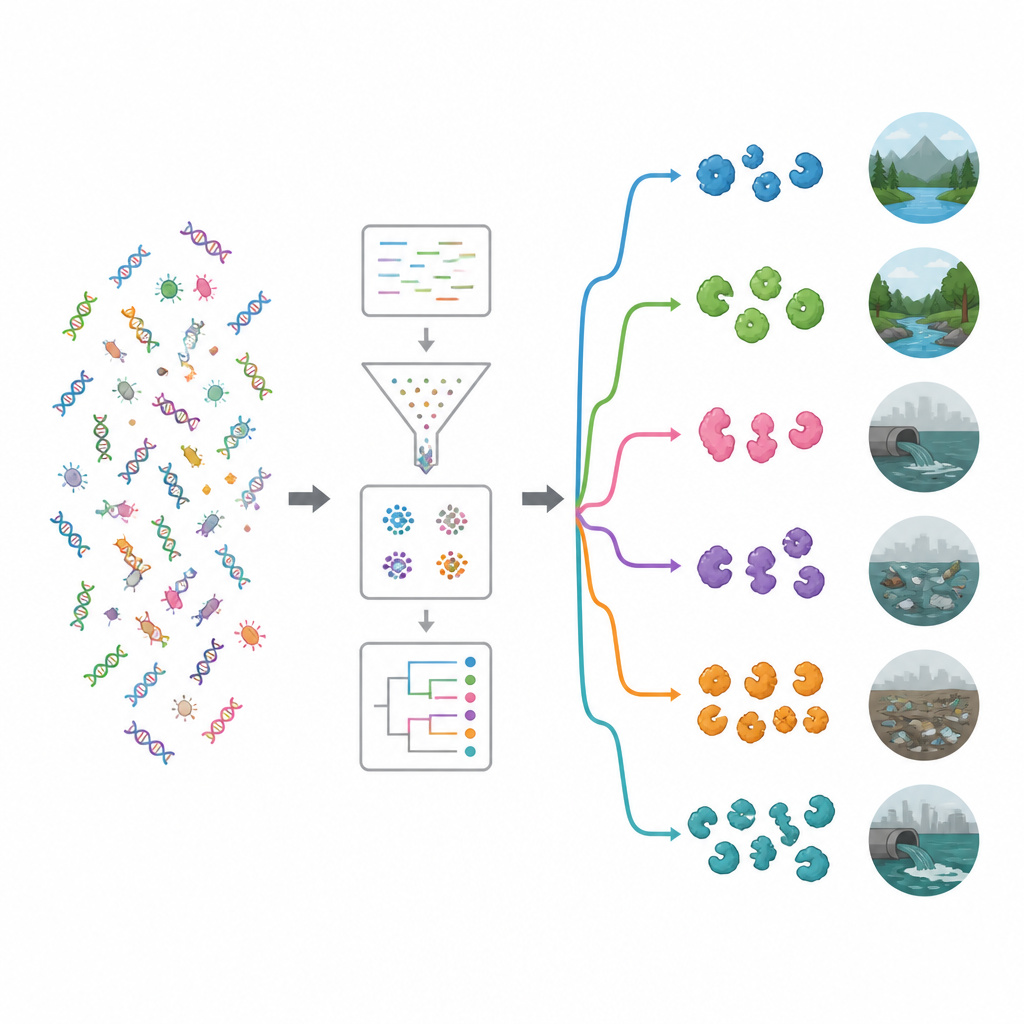
Кто производит эти ферменты и где они преобладают
Сопоставив гены, несущие ферменты, с их микробными хозяевами, исследование показало, что многие происходят от бактериальных групп, уже известных производством природных антимикробных веществ, в частности Pseudomonadota и Bacillota, а также актиномицетов, таких как Streptomyces. Команда затем изучила, какие бактерии доминируют в каждой среде, и с помощью кластеризации и машинного обучения распределила участки по экологическим группам. Один кластер включал относительно нетронутые места, такие как реки, грунтовые воды, растительность, соляные бассейны и горячие источники. Другой кластер объединял среды с более выраженным влиянием человека, включая места, загрязненные пластиком, сточные воды, резервуары, океаны вблизи ферм и фекальные образцы. В загрязненных средах, как правило, обнаруживался более богатый и разнообразный набор генов энзибиоотиков, что говорит о том, что сильная конкуренция и химический стресс благоприятствуют микробам, которые делают ставку на инструменты для уничтожения соперников.
Что это означает для здоровья и окружающей среды
MiGPC — это не просто гигантский список генов; это карта, связывающая конкретные ферменты, микробы и среды. Для неспециалистов главный вывод в том, что как напряженные, так и нетронутые среды Земли полны природных молекул, способных бороться с опасными бактериями, в том числе с теми, которые уже плохо реагируют на стандартные антибиотики. Многие из этих ферментов пока остаются функционально загадочными, но этот каталог значительно упрощает для исследователей поиск, тестирование и инженерную доработку таких молекул. Со временем MiGPC может направлять разработку новых препаратов на основе ферментов, более безопасных пищевых консервантов и инструментов для управления вредными микробами на фермах и в загрязненных зонах, помогая обществу бороться с антимикробной резистентностью без полной опоры на традиционные лекарства.
Цитирование: Afshar Jahanshahi, D., Ariaeenejad, A., Hasannejad, A. et al. MiGPC: a comprehensive catalog of enzybiotics from environmental metagenomes. Sci Rep 16, 15153 (2026). https://doi.org/10.1038/s41598-026-44250-9
Ключевые слова: энзибиоотики, антимикробные ферменты, метагеномика, микробная экология, антибиотикорезистентность