Clear Sky Science · fr
MiGPC : un catalogue complet d’enzybiotiques issus de métagénomes environnementaux
Pourquoi de petites enzymes comptent pour notre avenir
Alors que la résistance aux antibiotiques augmente et que les plastiques et polluants se répandent dans notre air, notre eau et nos sols, les scientifiques cherchent de nouvelles façons de contrôler les microbes nuisibles sans nuire au reste de la nature. Cette étude présente MiGPC, un vaste catalogue d’enzymes naturelles combattant les germes, issu d’un large éventail d’environnements, des océans et sources chaudes aux intestins d’animaux et aux déchets plastiques. Elle montre à quel point le monde microbien caché de la Terre regorge de nouveaux antimicrobiens potentiels et propose une feuille de route pour transformer cette diversité en outils pratiques pour la médecine, la sécurité alimentaire et le dépollution environnementale. 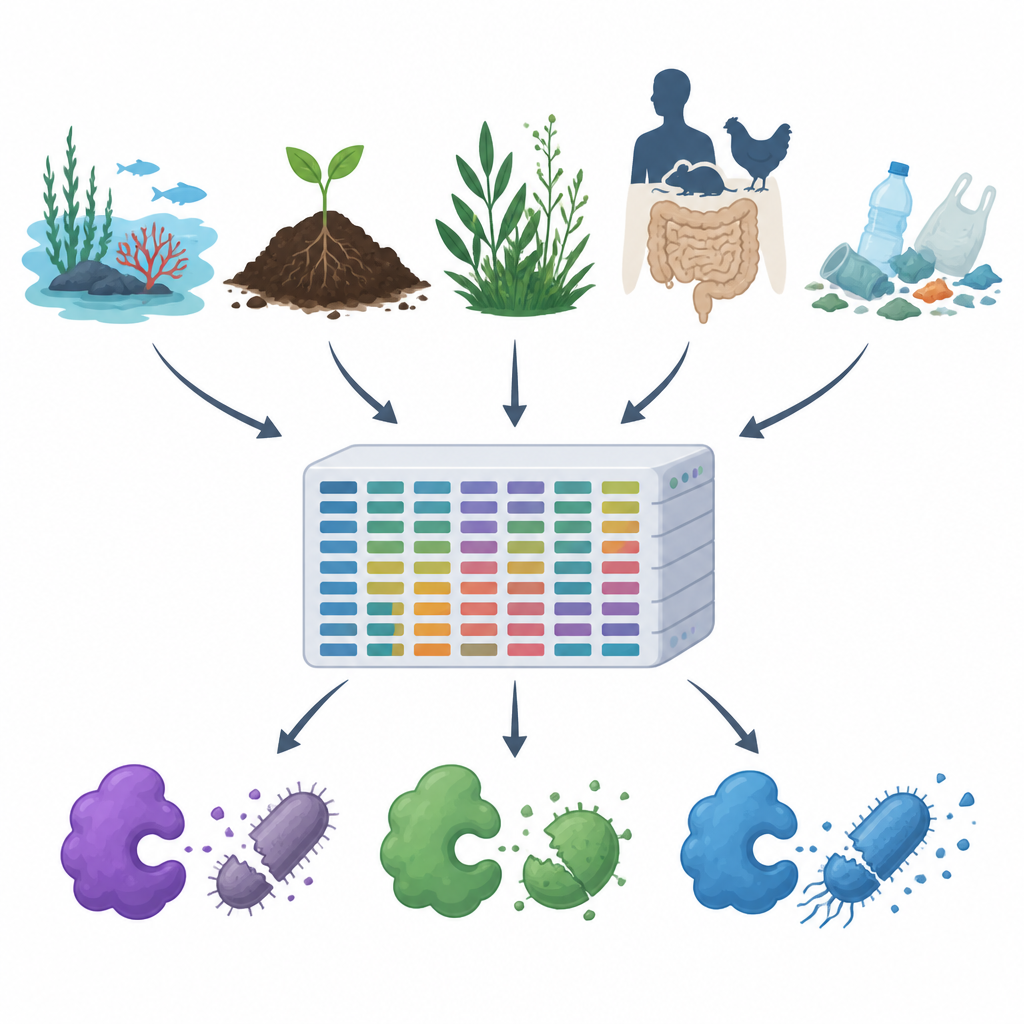
Des microbes aux tueurs naturels de germes
Les antibiotiques traditionnels agissent souvent comme des outils grossiers, éliminant les bactéries utiles avec les nuisibles et favorisant à terme l’apparition de résistances. En revanche, de nombreux microbes utilisent des enzymes spécialisées pour attaquer leurs rivaux avec une grande précision, perçant les parois cellulaires ou générant des molécules toxiques là où elles sont nécessaires. Ces antimicrobiens à base d’enzymes, appelés enzybiotiques, peuvent faire éclater des cellules bactériennes, décomposer des couches protectrices visqueuses ou perturber des voies de survie. Les auteurs ont cherché à savoir à quel point ces enzymes sont répandues dans la nature et à rassembler leurs plans génétiques dans une ressource unique et organisée, accessible à tous.
Construire un catalogue mondial d’enzymes
L’équipe a d’abord passé au crible les bases de données publiques de protéines et la littérature scientifique pour collecter 19 enzymes antimicrobiennes bien étudiées, incluant des coupeurs de paroi, des enzymes protéolytiques et des oxydases générant des molécules réactives nuisibles. Ils ont ensuite utilisé ces exemples éprouvés comme appât pour scanner de vastes jeux de données d’ADN provenant de 15 environnements très différents, tels que l’eau de mer, des piscines de saumure, des estuaires fluviaux, des sources chaudes, des plantes alpines, les intestins d’animaux et d’humains, ainsi que des sols et eaux contaminés par les plastiques. À l’aide d’un pipeline informatique puissant, ils ont nettoyé et assemblé environ 1,2 téraoctet de lectures d’ADN brutes en fragments plus longs, prédit des gènes et des protéines, supprimé les doublons et regroupé les séquences apparentées, obtenant finalement environ 100 millions de gènes et protéines uniques.
Détecter des fonctions cachées dans l’ADN environnemental
Pour comprendre ce que ces gènes pourraient accomplir, les chercheurs les ont comparés aux grandes bases de données fonctionnelles. Même avec des outils modernes, environ 62 % des gènes n’ont pas pu se voir attribuer un rôle connu, suggérant un réservoir profond de biologie encore inexplorée. Parmi les fonctions reconnaissables, les enzymes agissant sur les sucres complexes étaient particulièrement fréquentes. Deux familles, les glycoside hydrolases et les glycosyltransférases, se sont démarquées, dont beaucoup peuvent affaiblir les parois cellulaires bactériennes ou les biofilms. Une recherche ciblée avec un outil spécialisé a révélé près de 20 000 enzymes antimicrobiennes probables. La plupart appartenaient à deux grands groupes : les hydrolases, qui clivent les molécules, et les oxydoréductases, qui conduisent des réactions impliquant des électrons et peuvent générer des espèces réactives de l’oxygène endommageant les microbes. 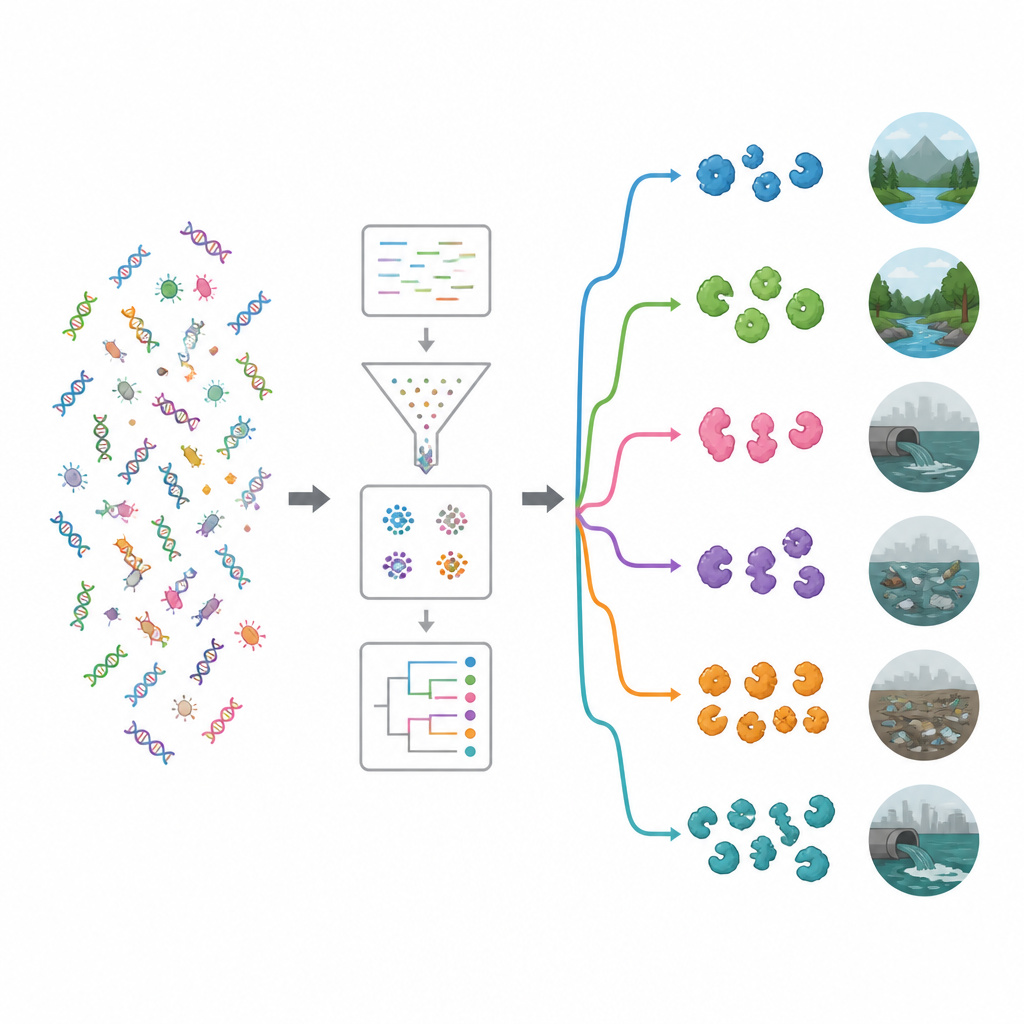
Qui produit ces enzymes et où elles prospèrent
En associant les gènes porteurs d’enzymes à leurs hôtes microbiens, l’étude montre que beaucoup proviennent de groupes bactériens déjà connus pour produire des antimicrobiens naturels, en particulier les Pseudomonadota et Bacillota, ainsi que des actinomycètes comme Streptomyces. L’équipe a ensuite examiné quelles bactéries étaient abondantes dans chaque environnement et a utilisé le regroupement et l’apprentissage machine pour classer les sites en groupes écologiques. Un groupe contenait des milieux relativement préservés comme les rivières, les eaux souterraines, la végétation, la saumure et les sources chaudes. L’autre groupe réunissait des habitats plus influencés par l’homme, incluant des sites pollués par le plastique, les eaux usées, les réservoirs, des zones océaniques proches d’exploitations agricoles et des échantillons fécaux. Les environnements pollués avaient tendance à abriter un ensemble d’enzybiotiques plus riche et plus diversifié, suggérant que la compétition intense et le stress chimique favorisent les microbes qui investissent fortement dans des outils de lutte contre les germes.
Ce que cela signifie pour la santé et l’environnement
MiGPC est plus qu’une simple immense liste de gènes ; c’est une carte qui relie des enzymes spécifiques, des microbes et des environnements. Pour le grand public, l’essentiel est que les habitats stressés comme les milieux intacts regorgent de molécules naturelles capables de combattre des bactéries dangereuses, y compris celles qui ne répondent plus bien aux antibiotiques classiques. Beaucoup de ces enzymes restent encore mystérieuses sur le plan fonctionnel, mais ce catalogue facilite grandement la tâche des chercheurs pour les repérer, les tester et les modifier. Avec le temps, MiGPC pourrait orienter le développement de nouveaux traitements à base d’enzymes, de conservateurs alimentaires plus sûrs et d’outils pour gérer les microbes nuisibles dans les exploitations agricoles et les sites pollués, aidant la société à répondre à la résistance antimicrobienne sans dépendre uniquement des médicaments traditionnels.
Citation: Afshar Jahanshahi, D., Ariaeenejad, A., Hasannejad, A. et al. MiGPC: a comprehensive catalog of enzybiotics from environmental metagenomes. Sci Rep 16, 15153 (2026). https://doi.org/10.1038/s41598-026-44250-9
Mots-clés: enzybiotiques, enzymes antimicrobiennes, métagénomique, écologie microbienne, résistance aux antibiotiques