Clear Sky Science · nl
MiGPC: een uitgebreide catalogus van enzybiotica uit omgevingsmetagenomen
Waarom kleine enzymen van belang zijn voor onze toekomst
Nu antibioticaresistentie toeneemt en kunststoffen en verontreinigingen zich verspreiden door lucht, water en bodem, zoeken wetenschappers naar nieuwe manieren om schadelijke microben te beheersen zonder de rest van de natuur te schaden. Deze studie presenteert MiGPC, een uitgebreide catalogus van natuurlijke microbe‑bestrijdende enzymen afkomstig uit zeer uiteenlopende omgevingen, van oceanen en warmwaterbronnen tot dieren‑darmen en plastica afval. Het werk laat zien hoe rijk de verborgen microbiële wereld van de aarde is aan potentiële nieuwe antimicrobiële middelen en biedt een routekaart om die diversiteit om te zetten in praktische instrumenten voor geneeskunde, voedselveiligheid en milieureiniging. 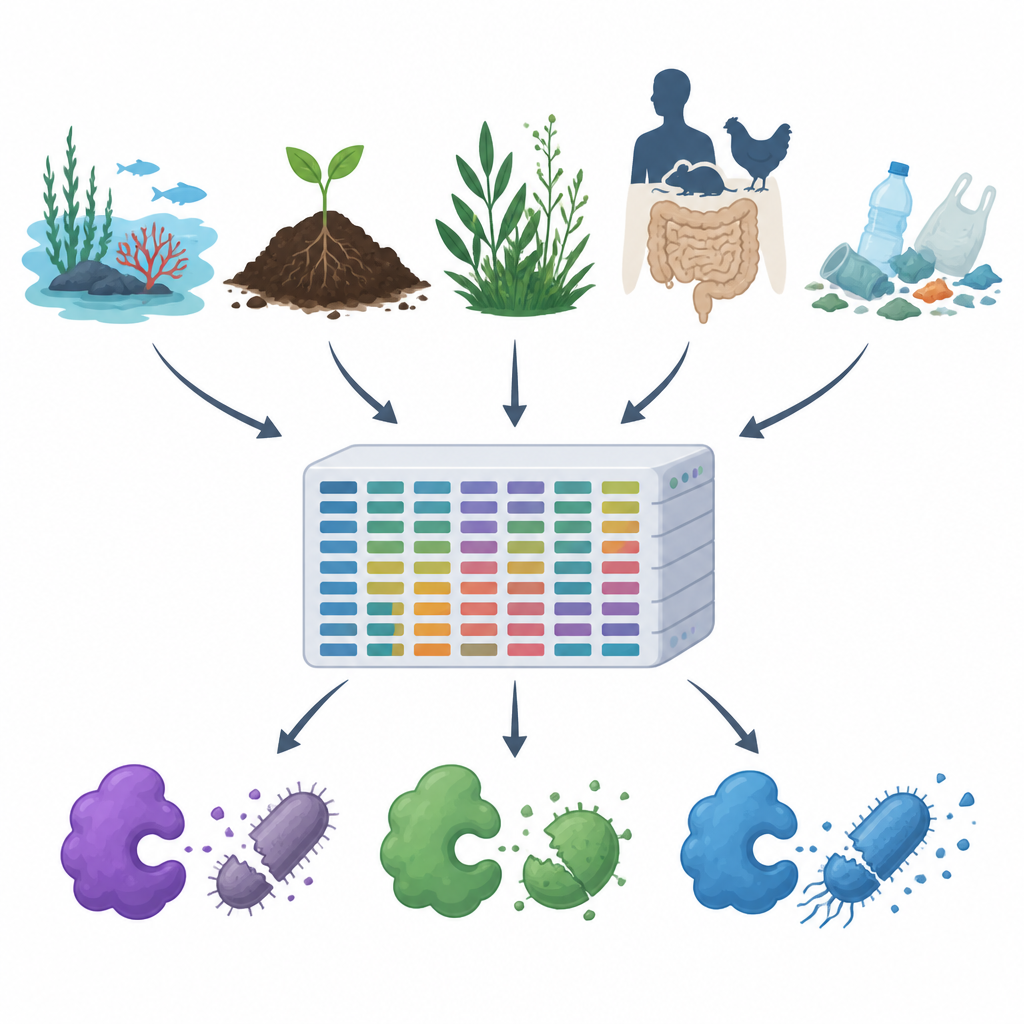
Van microben naar natuurlijke microbe‑doders
Traditionele antibiotica werken vaak als botte instrumenten: ze ruimen zowel nuttige als schadelijke bacteriën op en bevorderen op termijn resistentie. Veel microben gebruiken daarentegen gespecialiseerde enzymen om rivalen met grote precisie aan te vallen, door gaten in celwanden te maken of toxische moleculen precies daar te genereren waar ze nodig zijn. Deze op enzymen gebaseerde antimicrobiële middelen, enzybiotica genoemd, kunnen bacteriële cellen laten barsten, beschermende slijmlaagjes afbreken of overlevingsroutes verstoren. De auteurs maakten het tot doel te achterhalen hoe wijdverbreid zulke enzymen in de natuur zijn en hun genetische blauwdrukken te verzamelen in een enkele, georganiseerde bron die door iedereen te verkennen is.
Het bouwen van een wereldwijde enzymcatalogus
Het team doorzocht eerst openbare eiwitdatabases en wetenschappelijke publicaties om 19 goed bestudeerde antimicrobiële enzymen te verzamelen, waaronder celwand‑knippers, proteolytische enzymen en oxiderende enzymen die schadelijke reactieve moleculen genereren. Ze gebruikten deze bewezen voorbeelden als lokaas om grote DNA‑datasets van 15 zeer verschillende omgevingen te doorzoeken, zoals zeewater, pekelpoelen, riviermondingen, warmwaterbronnen, alpine planten, dieren‑ en menselijke darmen, en met plastic vervuilde bodems en wateren. Met een krachtige computationele pijplijn maakten ze ongeveer 1,2 terabyte aan ruwe DNA‑reads schoon en assembleerden die tot langere fragmenten, voorspelden genen en eiwitten, verwijderden duplicaten en groepeerden verwante sequenties, wat resulteerde in ruwweg 100 miljoen unieke genen en eiwitten.
Verborgen functies in omgevings‑DNA opsporen
Om te begrijpen wat deze genen mogelijk doen, vergeleken de onderzoekers ze met grote functionele databases. Zelfs met moderne hulpmiddelen kon ongeveer 62 procent van de genen geen bekende rol worden toegewezen, wat wijst op een diep reservoir van onontdekte biologie. Onder herkenbare functies waren enzymen die werken op complexe suikers bijzonder veelvoorkomend. Twee families, glycosidehydrolases en glycosyltransferases, vielen op; veel leden daarvan kunnen bacteriële celwanden of biofilms verzwakken. Een gerichte zoekopdracht met een gespecialiseerd instrument bracht bijna 20.000 waarschijnlijke antimicrobiële enzymen aan het licht. De meeste behoorden tot twee hoofdgroepen: hydrolasen, die moleculen doorknippen, en oxidoreductasen, die reacties aandrijven waarbij elektronen betrokken zijn en die reactieve zuurstofsoorten kunnen genereren die microben beschadigen. 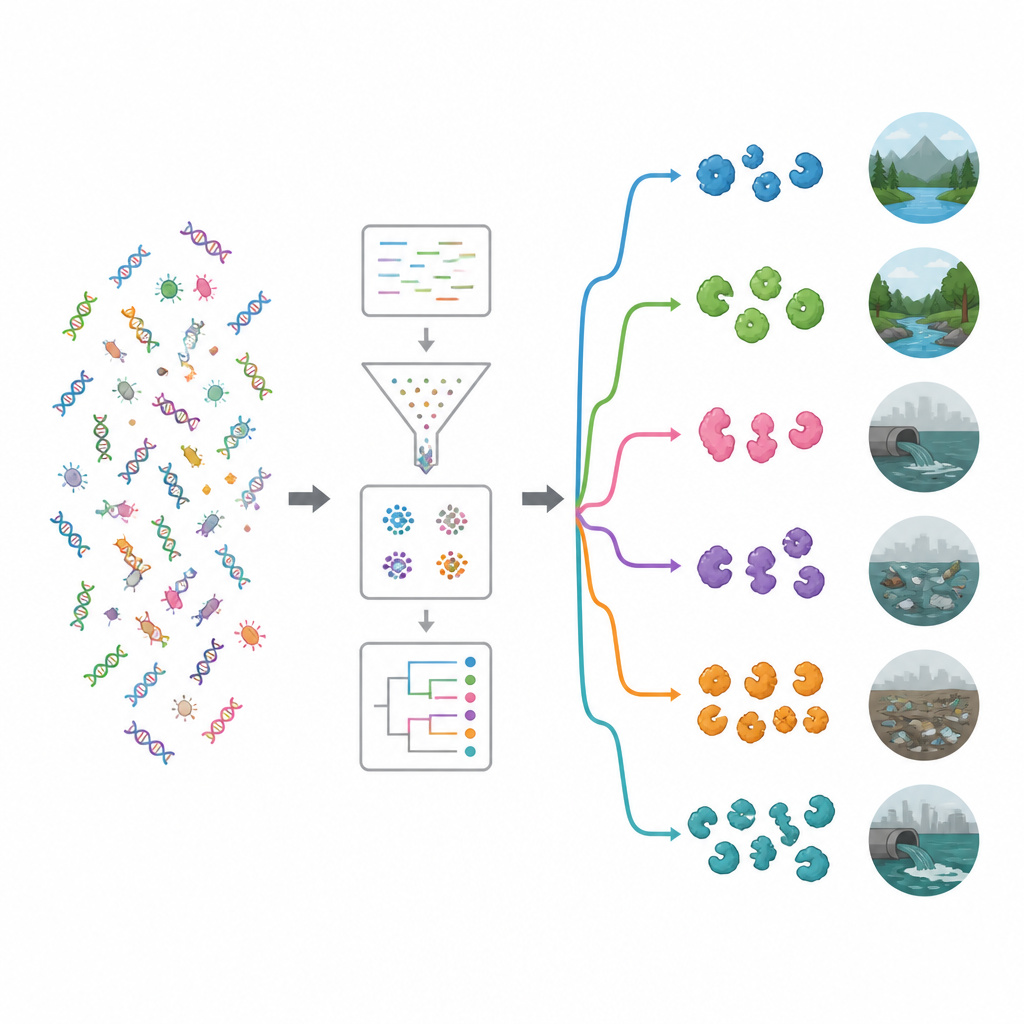
Wie deze enzymen maakt en waar ze floreren
Door genen die enzymen dragen te koppelen aan hun microbiele gastheren, toonde de studie aan dat veel genen afkomstig waren van bacteriegroepen die al bekendstaan om het produceren van natuurlijke antimicrobiële middelen, met name Pseudomonadota en Bacillota, evenals actinomyceten zoals Streptomyces. Het team onderzocht vervolgens welke bacteriën in elk milieu overvloedig aanwezig waren en gebruikte clustering en machine learning om de locaties in ecologische groepen te verdelen. Eén cluster bevatte relatief ongerepte omgevingen zoals rivieren, grondwater, vegetatie, pekel en warmwaterbronnen. De andere cluster omvatte meer door mensen beïnvloede habitats, waaronder door plastic vervuilde locaties, rioolwater, reservoirs, kusten nabij landbouwgebieden en fecale monsters. Verontreinigde omgevingen herbergden over het algemeen een rijker en diverser aanbod aan enzybiotische genen, wat suggereert dat intense competitie en chemische stress microben bevoordelen die sterk investeren in microbe‑bestrijdende middelen.
Wat dit betekent voor gezondheid en milieu
MiGPC is meer dan een gigantische genenlijst; het is een kaart die specifieke enzymen, microben en omgevingen koppelt. Voor niet‑specialisten is de conclusie dat zowel aangetaste als ongerepte habitats op aarde vol zitten met natuurlijke moleculen die gevaarlijke bacteriën kunnen bestrijden, inclusief diegenen die niet langer goed reageren op standaardantibiotica. Veel van deze enzymen zijn nog functioneel onduidelijk, maar deze catalogus maakt het veel eenvoudiger voor onderzoekers om ze te vinden, te testen en te ontwerpen. Na verloop van tijd kan MiGPC de ontwikkeling van nieuwe op enzymen gebaseerde behandelingen, veiligere voedselconserveringsmiddelen en instrumenten om schadelijke microben op boerderijen en verontreinigde locaties te beheersen, begeleiden en zo de samenleving helpen reageren op antimicrobiële resistentie zonder zich uitsluitend op traditionele geneesmiddelen te verlaten.
Bronvermelding: Afshar Jahanshahi, D., Ariaeenejad, A., Hasannejad, A. et al. MiGPC: a comprehensive catalog of enzybiotics from environmental metagenomes. Sci Rep 16, 15153 (2026). https://doi.org/10.1038/s41598-026-44250-9
Trefwoorden: enzybiotica, antimicrobiële enzymen, metagenomica, microbiële ecologie, antibioticaresistentie