Clear Sky Science · de
MiGPC: ein umfassender Katalog von Enzybiotika aus Umwelt-Metagenomen
Warum winzige Enzyme für unsere Zukunft wichtig sind
Da die Antibiotikaresistenz zunimmt und Kunststoffe sowie Schadstoffe in Luft, Wasser und Boden verbreitet sind, suchen Wissenschaftler nach neuen Wegen, schädliche Mikroben zu kontrollieren, ohne den Rest der Umwelt zu schädigen. Diese Studie stellt MiGPC vor, einen umfangreichen Katalog natürlicher keimtötender Enzyme, der aus vielen unterschiedlichen Umgebungen stammt — von Ozeanen und heißen Quellen bis hin zu Tiermägen und Plastikmüll. Er zeigt, wie reich die verborgene mikrobielle Welt der Erde an potenziell neuen Antimikrobiotika ist, und liefert eine Landkarte, wie diese Vielfalt in praktische Werkzeuge für Medizin, Lebensmittelsicherheit und Umweltreinigung überführt werden kann. 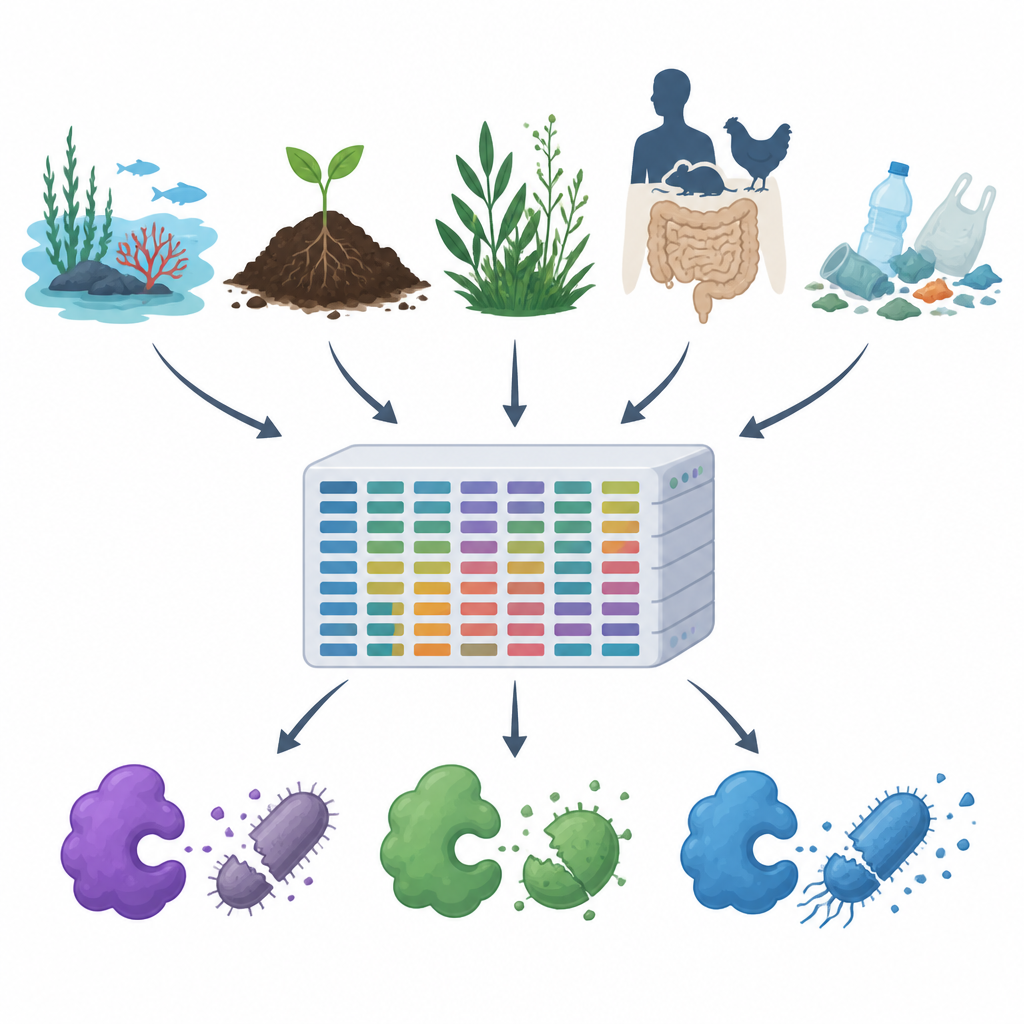
Von Mikroben zu natürlichen Keimkillern
Traditionelle Antibiotika wirken oft wie grobe Werkzeuge: Sie beseitigen nützliche Bakterien ebenso wie schädliche und fördern über die Zeit Resistenzen. Viele Mikroben hingegen nutzen spezialisierte Enzyme, um Konkurrenten sehr präzise anzugreifen — sie stechen Löcher in Zellwände oder erzeugen toxische Moleküle genau dort, wo sie gebraucht werden. Diese enzymbasierten Antimikrobiotika, Enzybiotika genannt, können bakterielle Zellen zum Platzen bringen, schützende Schleimschichten abbauen oder Überlebenswege stören. Die Autorinnen und Autoren wollten herausfinden, wie weit verbreitet solche Enzyme in der Natur sind, und ihre genetischen Baupläne in einer einzigen, organisierten Ressource zusammenführen, die für alle zugänglich ist.
Aufbau eines globalen Enzymkatalogs
Das Team durchforstete zunächst öffentliche Protein-Datenbanken und wissenschaftliche Publikationen, um 19 gut untersuchte antimikrobielle Enzyme zusammenzutragen — darunter Zellwandspaltende Enzyme, proteolytische Enzyme und oxidierende Enzyme, die schädliche reaktive Moleküle erzeugen. Diese bewährten Beispiele dienten als Köder, um große DNA-Datensätze aus 15 sehr unterschiedlichen Umgebungen zu durchsuchen, etwa Meerwasser, Salzseen, Flussmündungen, heiße Quellen, alpine Pflanzen, Tier- und menschliche Darmflora sowie plastikkontaminierte Böden und Gewässer. Mithilfe einer leistungsstarken Rechenpipeline bereinigten und assemblerten sie etwa 1,2 Terabyte Roh-DNA-Reads zu längeren Fragmenten, sagten Gene und Proteine voraus, entfernten Duplikate und gruppierten verwandte Sequenzen — am Ende standen ungefähr 100 Millionen einzigartige Gene und Proteine.
Verborgene Funktionen in Umwelt-DNA entdecken
Um zu verstehen, was diese Gene möglicherweise tun, verglichen die Forschenden sie mit wichtigen Funktionsdatenbanken. Selbst mit modernen Werkzeugen ließ sich bei etwa 62 Prozent der Gene keine bekannte Rolle zuordnen, was auf ein großes Reservoir unerforschter Biologie hindeutet. Unter den erkennbaren Funktionen waren Enzyme, die an komplexen Zuckern arbeiten, besonders häufig. Zwei Familien — Glycosid-Hydrolasen und Glycosyltransferasen — fielen auf, von denen viele bakterielle Zellwände oder Biofilme schwächen können. Eine gezielte Suche mit einem spezialisierten Tool förderte fast 20.000 potenzielle antimikrobielle Enzyme zutage. Die meisten gehörten zu zwei Hauptgruppen: Hydrolasen, die Moleküle aufspalten, und Oxidoreduktasen, die Elektronenübertragungen antreiben und reaktive Sauerstoffspezies erzeugen können, die Mikroben schädigen. 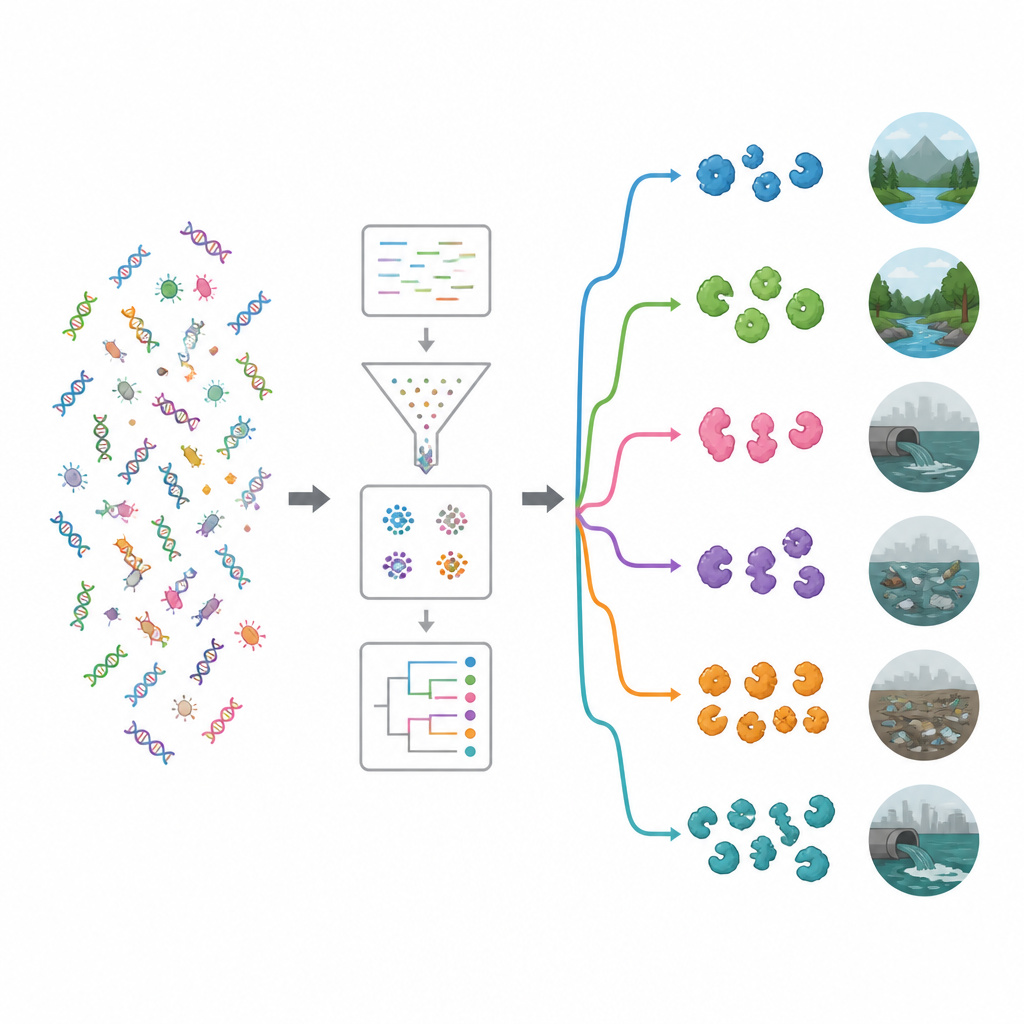
Wer diese Enzyme produziert und wo sie florieren
Durch das Zuordnen der enzymauslösenden Gene zu ihren mikrobiellen Wirten zeigten die Autorinnen und Autoren, dass viele Gene von Bakteriengruppen stammen, die bereits als Produzenten natürlicher Antimikrobiotika bekannt sind, insbesondere Pseudomonadota und Bacillota sowie Actinomyceten wie Streptomyces. Anschließend untersuchten sie, welche Bakterien in den einzelnen Umgebungen häufig vorkommen, und nutzten Clustering und maschinelles Lernen, um die Standorte in ökologische Gruppen zu sortieren. Ein Cluster umfasste relativ ungestörte Umgebungen wie Flüsse, Grundwasser, Vegetation, Salzseen und heiße Quellen. Der andere Cluster enthielt stärker vom Menschen beeinflusste Lebensräume, darunter plastikverschmutzte Stellen, Abwasser, Reservoirs, Meeresgebiete in der Nähe von Landwirtschaften und Fäkalproben. Verschmutzte Umgebungen wiesen tendenziell einen reicheren und vielfältigeren Satz enzybiotischer Gene auf, was darauf hindeutet, dass intensiver Wettbewerb und chemischer Stress Mikroben begünstigen, die stark in keimtötende Werkzeuge investieren.
Was das für Gesundheit und Umwelt bedeutet
MiGPC ist mehr als eine riesige Genliste; es ist eine Karte, die spezifische Enzyme, Mikroben und Umgebungen verknüpft. Für Nichtfachleute lautet die Botschaft, dass sowohl belastete als auch unberührte Lebensräume der Erde voller natürlicher Moleküle sind, die gefährliche Bakterien bekämpfen können — auch solche, die auf herkömmliche Antibiotika nicht mehr zuverlässig ansprechen. Viele dieser Enzyme sind funktionell noch rätselhaft, doch dieser Katalog erleichtert Forschenden erheblich das Auffinden, Testen und Ingenieurmäßige Anpassen. Mit der Zeit könnte MiGPC die Entwicklung neuer enzymbasierter Therapien, sichererer Lebensmittelkonservierungsmittel und Werkzeuge zur Kontrolle schädlicher Mikroben in Landwirtschaft und verschmutzten Gebieten leiten und der Gesellschaft helfen, auf antimikrobielle Resistenzen zu reagieren, ohne sich ausschließlich auf traditionelle Arzneimittel zu stützen.
Zitation: Afshar Jahanshahi, D., Ariaeenejad, A., Hasannejad, A. et al. MiGPC: a comprehensive catalog of enzybiotics from environmental metagenomes. Sci Rep 16, 15153 (2026). https://doi.org/10.1038/s41598-026-44250-9
Schlüsselwörter: Enzybiotika, antimikrobielle Enzyme, Metagenomik, mikrobielle Ökologie, Antibiotikaresistenz