Clear Sky Science · ja
MiGPC:環境メタゲノム由来のエンザイオティクスの包括的カタログ
なぜ小さな酵素が今後重要なのか
抗生物質耐性の増加やプラスチックや汚染物質の拡散が空気・水・土壌に広がる中で、研究者たちは自然環境を傷つけずに有害な微生物を制御する新しい方法を模索しています。本研究はMiGPCを紹介します。これは海洋や温泉から動物の腸やプラスチックごみまで、多様な環境から採取した天然の抗菌酵素を網羅した大規模なカタログです。本研究は地球の隠れた微生物世界がいかに多くの潜在的抗菌物質を含むかを示し、その多様性を医療、食品安全、環境浄化の実用的な道具に変えるためのロードマップを提供します。 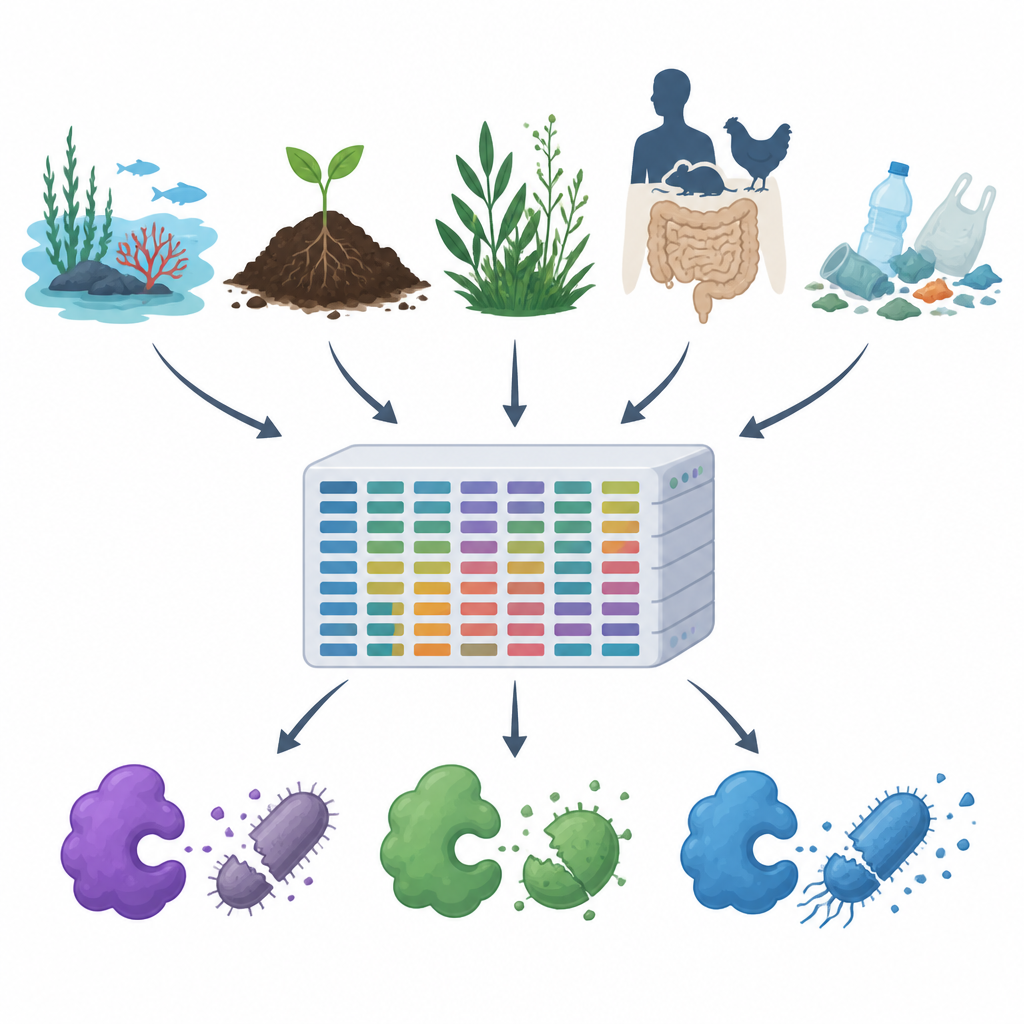
微生物から天然の殺菌因子へ
従来の抗生物質はしばしばぶん殴る道具のように働き、有益な細菌も有害な細菌とともに排除し、時間とともに耐性を助長します。対照的に、多くの微生物は特殊な酵素を使って競合相手を精密に攻撃し、細胞壁に穴をあけたり、必要な場所で毒性分子を生成したりします。これらの酵素ベースの抗菌物質、すなわちエンザイオティクスは、細菌細胞を破裂させたり、保護的な粘性層を分解したり、生存経路を撹乱したりできます。著者らは、こうした酵素が自然界にどれほど広く存在するかを突き止め、それらの遺伝的設計図を誰でも探せる単一の整理された資源に集めることを目指しました。
グローバルな酵素カタログの構築
研究チームはまず、公開タンパク質データベースや学術論文を精査して、細胞壁を切る酵素、タンパク質分解酵素、有害な反応性分子を生成する酸化酵素など、19種類のよく研究された抗菌酵素を収集しました。次に、これらの実証済み例をベイトとして用い、海水、塩水湖、河口、温泉、高山植物、動物・ヒトの腸、プラスチック汚染土壌や水域など15の非常に異なる環境から得られた大規模なDNAデータセットをスキャンしました。高性能な計算パイプラインを使い、約1.2テラバイトの生のDNAリードをクリーニングして組み立て、遺伝子とタンパク質を予測し、重複を除去し、関連配列をグループ化した結果、約1億のユニークな遺伝子とタンパク質を得ました。
環境DNAに潜む機能の発見
これらの遺伝子が何をするかを理解するために、研究者たちは主要な機能データベースと比較しました。現代のツールを用いても約62%の遺伝子は既知の役割に割り当てられず、未踏の生物学の深い井戸を示唆しました。認識可能な機能の中では、複雑な糖に作用する酵素が特に一般的でした。グリコシド加水分解酵素やグリコシルトランスフェラーゼの二つのファミリーが際立ち、その多くは細菌の細胞壁やバイオフィルムを弱める可能性があります。特殊なツールによるターゲット検索で、約2万に近い抗菌酵素候補を検出しました。大部分は分解酵素(分子を切り離す加水分解酵素)と酸化還元酵素(電子を伴う反応を駆動し、微生物を損傷する活性酸素種を生成し得る)の二大グループに属していました。 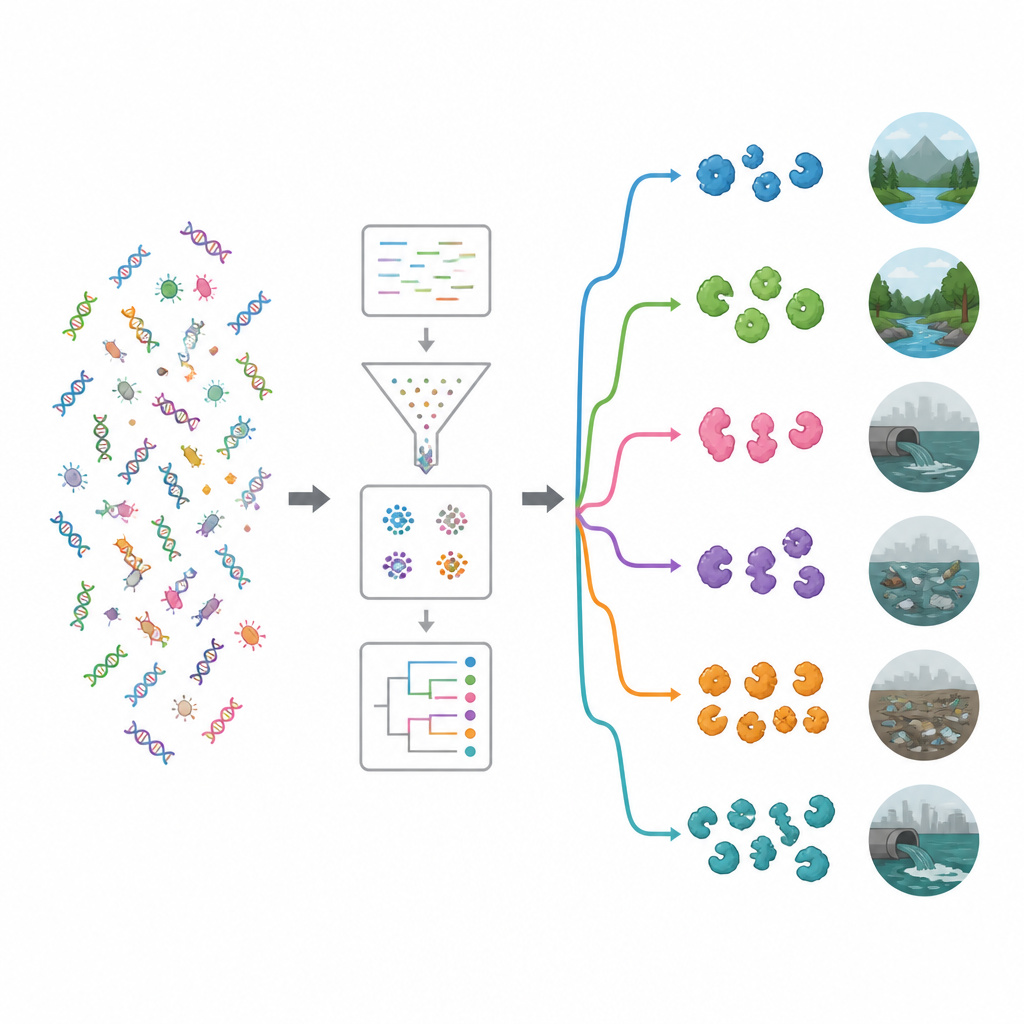
これらの酵素を作る生物と生育環境
酵素をもつ遺伝子を微生物の宿主に結び付けることで、本研究は多くが既に天然抗菌物質を生産することが知られる細菌群、特にシュードモナドータ(Pseudomonadota)やバチロータ(Bacillota)、およびストレプトマイセスのような放線菌から来ていることを示しました。次にチームは各環境で豊富な細菌群を調べ、クラスタリングと機械学習を用いてサイトを生態学的グループに分類しました。あるクラスタは河川、地下水、植生、塩水、温泉のような比較的手つかずの環境を含んでいました。別のクラスタはプラスチック汚染サイト、廃水、貯水池、農地付近の海域、糞便サンプルなど、より人為的影響の強い生息地を含んでいました。汚染された環境は、より豊かで多様なエンザイオティクス遺伝子群を抱える傾向があり、激しい競争と化学的ストレスが殺菌道具に注力する微生物を有利にしていることを示唆します。
健康と環境への意味
MiGPCは単なる巨大な遺伝子リスト以上の存在で、特定の酵素、微生物、環境を結び付ける地図です。非専門家への要点は、地球のストレスを受けた環境も手つかずの環境もいずれも、従来の抗生物質に十分反応しない危険な細菌と戦う天然分子に満ちているということです。多くの酵素はまだ機能的に謎が残っていますが、このカタログにより研究者がそれらを見つけ、試験し、改変するのがはるかに容易になります。長期的には、MiGPCは新しい酵素ベースの治療法、より安全な食品保存料、農場や汚染現場で有害微生物を管理するためのツールの開発を導き、従来薬にのみ依存しない抗菌耐性への対応を助ける可能性があります。
引用: Afshar Jahanshahi, D., Ariaeenejad, A., Hasannejad, A. et al. MiGPC: a comprehensive catalog of enzybiotics from environmental metagenomes. Sci Rep 16, 15153 (2026). https://doi.org/10.1038/s41598-026-44250-9
キーワード: エンザイオティクス, 抗菌酵素, メタゲノミクス, 微生物生態学, 抗生物質耐性