Clear Sky Science · tr
Doku tipine göre çözümleme için DNA metilasyon referans panellerinin optimize edilmesine ilişkin yönergeler
Karışık Dokuların İçine Bakmak
Güncel sağlık ve hastalık çalışmaları genellikle DNA’mızdaki kimyasal işaretleri ölçüyor; çevre ve yaşam tarzının genlerimizde nasıl iz bıraktığını görmek istiyorlar. Ancak çoğu test, kan gibi birçok hücre türü içeren karışık dokular üzerinde yapılır. Hangi hücre tipinden ne kadar bulunduğunu bilemezsek, hücre karışımındaki bir değişikliği gerçek bir hastalık sinyali zannetme riski vardır. Bu makale, bilim insanlarının DNA metilasyon verilerinden hücre karışımlarını doğru biçimde tahmin etmelerini sağlayan daha iyi “referans paneller” nasıl oluşturulacağını açıklıyor; bu da sonuçların daha açık ve güvenilir olmasına yol açar. 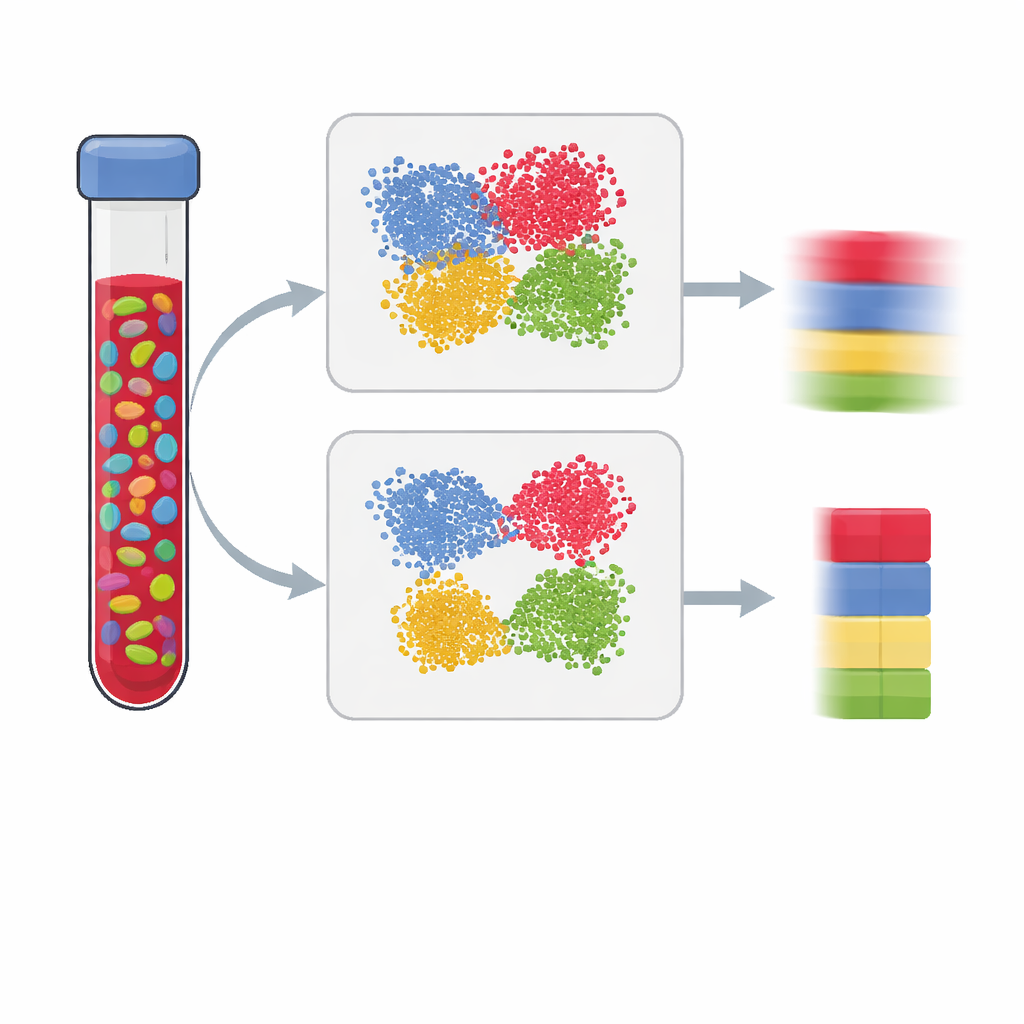
Neden Hücre Karışımı Önemli?
Epigenom çapında ilişki çalışmaları, bir hastalık gibi bir özellik taşıyan ve taşımayan kişiler arasında DNA metilasyonu—gen aktivitesini kontrollemeye yardımcı olan küçük kimyasal eklemeler—farklılıklarını arar. Metilasyon desenleri hücre tipleri arasında çok farklı olduğundan, toplu kan ölçümleri yanıltıcı olabilir: bir bağışıklık hücresi tipinden diğerine olan kayma, her bir hücre tipinde gerçek bir değişiklik olmasa bile hastalık etkisini taklit edebilir. Bunu düzeltmek için araştırmacılar, saflaştırılmış hücrelerden veya tek hücrelerden oluşturulmuş bir referans panel kullanarak ana hücre tiplerinin (T hücreleri, B hücreleri, doğal öldürücü hücreler gibi) oranlarını tahmin ederler. O panelin kalitesi, bir örneği ne kadar iyi “ayırabildiğimizi” ve dolayısıyla çalışmanın çıkarımlarının ne kadar güvenilir olduğunu büyük ölçüde belirler.
Basit İstatistiklerden Daha Akıllı Belirteçlere
Geleneksel olarak, bilim insanları bu paneller için DNA konumlarını standart istatistiksel testlerle seçiyordu. Bir hücre tipinin tüm diğerlerinden anlamlı biçimde farklı olduğu pozisyonları arayıp t-istatistiğine göre sıralıyorlardı. Son zamanlarda IDOL, Elastic Net ve Random Forests gibi optimizasyon ve makine öğrenimi yöntemleri bu seçimleri iyileştirmek için kullanıldı. Yeni çalışma, bu yaklaşımların özellikle yalnızca birkaç saflaştırılmış örnek mevcut olduğunda, hücre tipleri arasındaki gerçek dünya farkları küçük olan belirteçleri tercih etme eğiliminde olduğunu gösteriyor. Bu tür “düşük etki büyüklüğüne” sahip belirteçler eğitim verisinde ikna edici görünebilir, ancak yeni veri setlerinde başarısız olabilir ve hücre tipi tahminlerinin doğruluğunu ince ince bozabilir.
Hücre Tipleri Arasında Net Boşluklar Bulmak
Yazarlar, bir belirtecin ne kadar yararlı olduğunu değerlendirmek için daha doğrudan bir yol öneriyor: “boşluk özgüllük skoru.” Bu skor yalnızca istatistiksel anlamlılığa odaklanmak yerine, bir DNA konumunun bir hücre tipini diğer tüm hücrelerden ne kadar temiz ayırdığını ölçer; hedef hücredeki en yüksek değerin diğer hücrelerdeki en düşük değerden (veya düşük değerler için tersine) olan boşluğuna bakar. Büyük pozitif boşluklara sahip belirteçler hem özgül hem de sağlamdır. Mevcut bağışıklık hücresi verilerini kullanarak araştırmacılar, bu skora göre sıralamanın geleneksel yöntemden çok daha büyük hücre tipi farklarına sahip DNA konumları verdiğini gösterdiler. Bu boşluk temelli belirteçlerle oluşturulan paneller, özellikle bellek CD4 T hücreleri gibi çözülmesi daha zor popülasyonlar için birçok bağışıklık alt kümesi arasında hücre-fraksiyon tahminlerinde daha yüksek doğruluk sağladı. 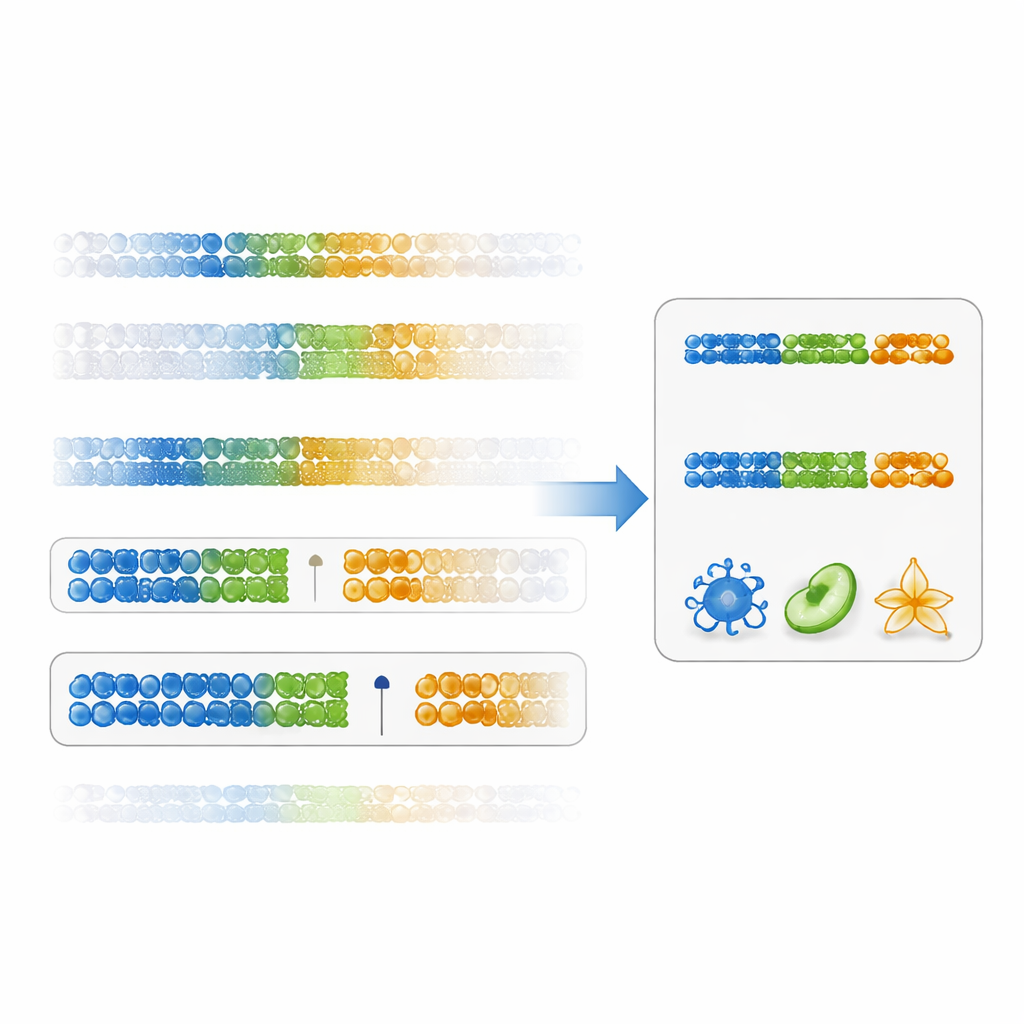
Neden Düşük İşaretler ve Aşırı Uydurma Zararlı?
Araştırma ekibi ayrıca gelişmiş optimizasyon araçlarının veya makine öğrenimi modellerinin kendi boşluk temelli yaklaşımlarını geliştirip geliştiremeyeceğini test etti. Bunun yerine tam tersi bulundu. IDOL, Elastic Net ve Random Forest gibi yöntemler genellikle daha küçük etki büyüklüğüne sahip özellikleri seçme eğilimindeydi ve bağımsız karışımlarda veya bilinen hücre sayıları olan gerçek kan örneklerinde daha kötü performans gösterdiler. Bu, yalnızca birkaç düzine eğitim örneğiyle karmaşık modellerin verinin tuhaflıklarına aşırı uydurma yapıp genel desenleri yakalamadığına işaret ediyor. Buna karşılık, yüksek boşluk skorlarına sahip güçlü hipometile belirteçlerden oluşan paneller sadece çözümleme doğruluğunu artırmakla kalmadı, aynı zamanda doğal öldürücü hücrelerin yaşa bağlı artışı gibi bilinen biyolojik eğilimleri de daha iyi yakaladı.
Daha İyi Panellerle Daha Net Hastalık Sinyalleri
Bu iyileştirmelerin pratikte nasıl sonuç verdiğini görmek için yazarlar şizofreni ve tip 1 diyabetin büyük çalışmalarını yeniden analiz ettiler. Optimize edilmiş referans panellerini kullanmak tahmin edilen hücre fraksiyonlarını yalnızca hafifçe değiştirdi, ancak bu küçük kaymalar sonraki bulguları keskinleştirdi. Hastalıkla ilişkili metilasyon değişiklikleri, inflamasyon ve otoimmünitede daha önce ilişkilendirilmiş yollar için daha fazla zenginleşti ve immün sinyal ile ilişkili belirli genler daha belirgin hale geldi. Başka bir deyişle, daha iyi belirteç seçimi gürültüyü azalttı ve biyolojik hikâyeyi daha tutarlı hale getirdi.
Gelecek Çalışmalar İçin Ne Anlama Geliyor
Uzman olmayanlar için ana mesaj, tüm istatistiksel olarak anlamlı sinyallerin eşit derecede faydalı olmadığıdır. Karışık dokuları çözmeye çalışırken en önemli olan, bir belirtecin bir hücre tipini diğerinden ne kadar net ayırdığıdır; yalnızca P-değerinin etkileyici görünmesi yeterli değildir. Hücre tipleri arasında büyük, temiz boşluklara sahip DNA konumlarını—özellikle belirli bir hücrede tek özgün şekilde metile edilmemiş olanları—tercih ederek, araştırmacılar küçük veri setlerinden bile daha güvenilir referans paneller oluşturabilirler. Yazarlar, bu panelleri oluşturmak için araçları EpiDISH yazılımına eklediler ve bu da gelecekteki çalışmaların DNA metilasyon verilerinden daha doğru ve biyolojik olarak anlamlı sonuçlar çıkarmasına yardımcı olacaktır.
Atıf: Guo, X., Teschendorff, A.E. Guidelines on optimizing DNA methylation reference panels for cell-type deconvolution. Commun Biol 9, 454 (2026). https://doi.org/10.1038/s42003-026-09745-1
Anahtar kelimeler: DNA metilasyonu, hücre tipi çözümleme, epigenomik, bağışıklık hücreleri, referans paneller