Clear Sky Science · tr
CircRNA dizilim ve ağ bilgilerini birleştirerek circRNA alt-hücre yeri tahmini
Neden küçük RNA halkaları ve adresleri önemli
Her insan hücresinde, hangi genlerin açılıp kapanacağını kontrol etmeye yardımcı olan çok sayıda RNA molekülü yoğun biçimde bulunur. Bunların arasında dairesel RNA’lar veya circRNA’lar vardır—alışılmadık halka biçiminde, şaşırtıcı derecede stabil ve kanserler dahil birçok hastalıkla yakından ilişkili RNA parçaları. Bu moleküllerin ne işe yaradığını anlamak için bilim insanlarının bilmesi gereken temel bir gerçek var: hücre içinde nerede bulundukları. Geleneksel laboratuvar deneyleriyle circRNA’ların “adreslerini” haritalamak yavaş, maliyetli ve eksik kalıyor. Bu çalışma, dizilerinden ve yer aldıkları karmaşık biyolojik ağlardan gelen bilgileri birleştirerek circRNA’ların hücre içindeki yerlerini tahmin eden yeni bir bilgisayar tabanlı yöntem olan CircLoc’u sunuyor.
Büyük biyolojik rollere sahip küçük halkalar
Bir zamanlar gen işlenmesinin zararsız artık parçaları olarak göz ardı edilen circRNA’ların artık hücre farklılaşması gibi temel süreçlerden gen düzenlenmesine kadar birçok hayati süreci etkilediği biliniyor. Dairesel şekilleri onları pek çok diğer RNA’dan daha kararlı kılar; bu da onları hastalık teşhisinde potansiyel biyobelirteçler olarak çekici yapar. CircRNA’lar proteinlere bağlanabilir ve gen aktivitesini normalde baskılayan küçük düzenleyiciler olan mikroRNA’ları tutarak hücresel davranışı yeniden şekillendirebilir. Birçok molekül sadece çekirdek, sitoplazma veya zarlar gibi hücrenin belirli bölgelerinde etki gösterdiği için bir circRNA’nın alt-hücre konumunu bilmek, işlevi ve sağlık ile hastalıkta olası rolü hakkında önemli ipuçları verir.
Dağınık verileri bir eğitim alanına dönüştürmek
Yazarlar işe, yerleri bilinen insan circRNA’larının birkaç halka açık veritabanından titizlikle küratörlüğünü yaparak derlenmesiyle başladı. Nadir kategoriler ve aşırı dengesiz gruplar çıkarıldıktan sonra çekirdek, nükleolus, nükleoplazma, sitoplazma, sitozol, kromatin ve zarlar dahil yedi ana hücresel bölgeye odaklandılar. Toplamda, güvenilir dizi bilgisine ve en az bir bilinen konuma sahip 1.486 circRNA topladılar; birçoğu aynı anda birden fazla bölgeye aitti ve bu da görevi gerçek bir çoklu-etiket tahmin problemi hâline getirdi. Daha önceki veritabanı sürümlerinden ve büyük bir kanser odaklı koleksiyondan alınan ek veri kümeleri bağımsız testler için ayrıldı; bu, ekibin modellerinin yeni rapor edilen circRNA’lara ne kadar genelleştirilebileceğini incelemesine olanak tanıdı.
Dizi desenlerini hücresel etkileşim haritalarıyla harmanlamak
CircLoc’un temel fikri, bir circRNA’nın adresinin yalnızca kendi dizisi tarafından değil, aynı zamanda ilişkide bulunduğu çevre tarafından da şekillendiğidir. Dizi tarafında model kısa dizi parçalarına (k-merler ve bunların ters tamamlayıcıları) ve RNAErnie adındaki büyük RNA odaklı bir dil modeli tarafından öğrenilmiş daha zengin desenlere bakar; RNAErnie çok büyük RNA veri kümeleri üzerinde eğitilerek ince düzenlilikleri yakalayacak şekilde geliştirildi. Ağ tarafında ise yazarlar circRNA’ların birbirleriyle ve ilişkili biyolojik varlıklarla nasıl bağlandığını gösteren birkaç harita inşa ettiler: örtüşen diziler, ilişkili hastalıklar, ilaç yanıtları, etkileşen mikroRNA’lar ve bağlanan proteinler. Node2vec adlı bir ağ gömme aracı her haritanın yapısını sayısal özelliklere dönüştürür ve ardından bir grafik dikkatli oto-enkoder (GATE) bunları benzer davranış gösteren circRNA’lar arasındaki bağlantılara ağırlık vererek rafine eder; bu, ağ kaynaklı sinyallerin gürültüsünü azaltıp zenginleştirmeye yarar.
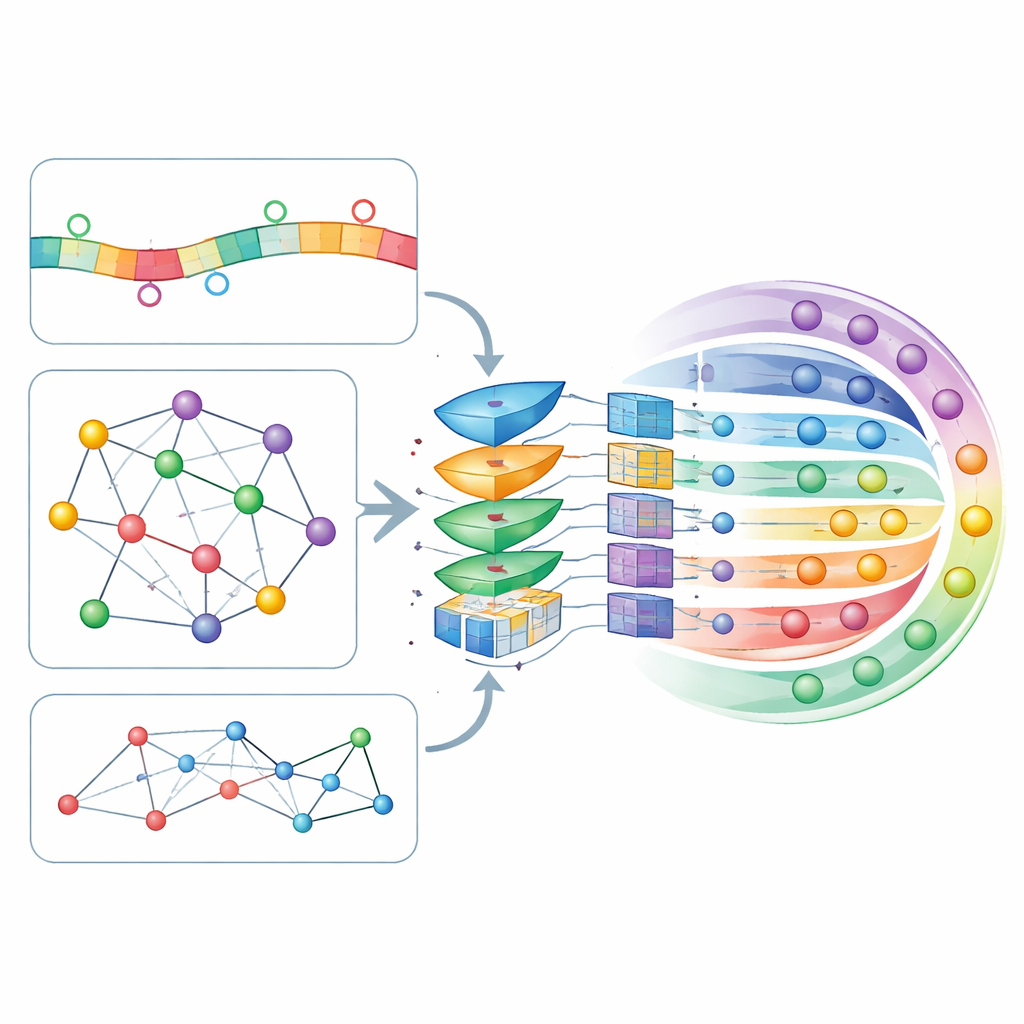
Modelin en çok neyin önemli olduğuna karar vermesine izin vermek
Tüm bu dizi ve ağ tabanlı özellikler her circRNA için tek bir profile dikilir ve modelin hangi özellik kombinasyonlarının kararlarını en güçlü şekilde etkilemesi gerektiğini öğrenmesine izin veren bir kendi-kendine dikkat (self-attention) katmanından geçirilir. Rafine edilmiş profiller daha sonra yedi olası konumun her biri için bir olasılık üreten derin, tamamen bağlı bir sinir ağına girer. Yazarlar modelin çok sayıda ayarını on katlı çapraz doğrulama kullanarak ayarladı; bu, veriyi tekrar tekrar eğitim ve test bölümlerine ayıran titiz bir prosedürdür. CircLoc standart bir başarı ölçüsünde (AUC) yaklaşık 0,79 ortalama puan elde etti ve aynı özelliklerle eğitilmiş klasik çoklu-etiket yöntemler ve mikroRNA’lar için tasarlanmış önceki yaklaşımları açıkça geride bıraktı. Belirli özellikleri veya modülleri çıkarmaya yönelik deneyler, ağ bilgisinin ve GATE rafinasyonunun özellikle önemli olduğunu, dizi özelliklerinin ise daha küçük ama yine de faydalı katkılar sağladığını gösterdi.
Model yeni circRNA’larla ne kadar iyi başa çıkıyor?
Gerçek dünyadaki kullanışlılığı sınamak için ekip CircLoc’u lokalizasyon veritabanının bir sürümü üzerinde eğitti ve yalnızca daha sonraki bir sürümde görünen circRNA’lar ile ayrı bir kanser odaklı kaynağı üzerinde test etti. Farklı kaynaklardan gelen gerçekten yeni veriyle karşılaşıldığında beklenildiği gibi performans azaldı, ancak saygın düzeyde kaldı: ortalama puanlar makul bir düşüş gösterse de anlamlı öngörü gücünü korudu. Bu testler ve diğer yöntemlerle yapılan karşılaştırmalar, CircLoc’un bazı destekleyici bilgilerin—örneğin ayrıntılı hastalık veya ilaç ilişkileri—eksik olduğu durumlarda bile yeni keşfedilen circRNA’ların konumları için makul ilk tahminler sağlayabileceğini gösteriyor.
Gelecek RNA araştırmaları için bunun anlamı
Bu çalışma, doğrudan dizi bilgisi ile zengin etkileşim ağlarını birleştirmenin, hesaplamalı modellerin circRNA’ların hücre içinde muhtemelen nerede bulunacağını tahmin etmesine yardımcı olabileceğini gösteriyor. Deneysel biyologlar için CircLoc, hangi circRNA’ların hangi hücresel kompartımanlarda incelenmeye öncelik verilmesi gerektiğini belirlemede zaman ve kaynak tasarrufu sağlayabilecek bir yol sunuyor. Yöntem henüz laboratuvar ölçümlerinin yerini alamasa da ve yaratıcıları eksik veriler ve bazı test kümelerinde sınırlı performans gibi kısıtları not etse de, RNA molekülleri için büyük ölçekli, in silico “adres defterleri”ne doğru atılmış önemli bir adımı temsil ediyor. Veritabanları büyüdükçe ve modelleme teknikleri ilerledikçe, bu tür araçlar deneylerin rutin destekçileri haline gelebilir ve hastalık ve tedavi açısından en önemli circRNA’ları bulma çabalarını yönlendirebilir.
Atıf: Chen, L., Hu, J. & Zhou, B. Predicting circRNA subcellular localization by fusing circRNA sequence and network information. Sci Rep 16, 12775 (2026). https://doi.org/10.1038/s41598-026-43808-x
Anahtar kelimeler: dairesel RNA, alt-hücre lokalizasyonu, hesaplamalı biyoloji, makine öğrenimi, RNA ağları