Clear Sky Science · tr
mViSE: Çoklu IHC beyin doku görüntülerini (uzamsal proteomik) analiz etmek için görsel arama motoru
Beyindeki Desenleri Görmek
Modern mikroskoplar artık tüm beyin dilimlerinin nefes kesici ayrıntıda görüntülerini yakalayabiliyor ve aynı anda onlarca farklı proteini gösterebiliyor. Bu “çoklu” görüntüler, beyin hücrelerinin nasıl düzenlendiği, birbirleriyle nasıl iletişim kurduğu ve hastalığın bu düzenleri nasıl bozduğu konusunda ipuçları vaat ediyor. Ancak görüntüler o kadar büyük ve karmaşık ki, güçlü bilgisayarlar bile bunları anlamakta zorlanıyor. Bu makale, araştırmacıların özel kod yazmak yerine ilgi duydukları hücrelere ve komşuluklara tıklayarak bu geniş beyin görüntülerini keşfetmelerine olanak sağlayan mViSE adlı görsel arama motorunu tanıtıyor.
Neden Büyük Beyin Görüntüleri Kullanması Zor?
Her bir çoklu beyin görüntüsü, her bina, sokak ve altyapı hattının aynı anda birçok renkle etiketlendiği devasa bir şehir haritasına benzer. Farklı proteinler farklı hücre tiplerini, hücre durumlarını, kan damarlarını ve bağlantı desenlerini işaretler. Geleneksel analiz hatları bu haritayı uzun bir programlı adım zincirine böler: görüntüyü temizle, hücreleri tespit et, segmentle, hücre tiplerini etiketle ve sonra bölge bazında özetle. Güçlü olsa da, bu yaklaşım esnek değildir ve yeni sorular ortaya çıktığında uyum sağlamak zordur—özellikle nöronlar, glia hücreleri ve kan damarlarının karışımının muazzam moleküler ve mekânsal karmaşıklığa sahip olduğu beyin için. Bilim insanları, bu verilere tam zamanlı programcı olmadan yeni sorular sorabilmek için giderek daha esnek, etkileşimli bir yol arıyorlar.
Beyin Hücreleri için Bir Arama Motoru
mViSE bir beyin görüntüsünü statik bir veri kümesi yerine çevrimiçi bir fotoğraf kütüphanesi gibi ele alıyor. Her analiz adımını önceden tanımlamak yerine kullanıcı ilginç görünen bir hücreye veya küçük bir doku parçasına tıklar. Sistem daha sonra tüm beyin görüntüsünde birçok protein kanalında benzer görünüşe ve “davranışa” sahip hücreleri veya komşulukları arar. Eşleşmeler tüm beyin görünümünde doğrudan vurgulanır ve protein ekspresyon profilleri olarak özetlenebilir. Bu, araştırmacıların benzer hücrelerin veya mikroçevrelerin nerelerde ortaya çıktığını hızla keşfetmesini, beyin bölgelerini ve kortikal katmanları belirlemesini ve farklı beyin parçaları arasındaki desenleri karşılaştırmasını sağlar—tümü görsel sorgularla, koda gerek olmadan. 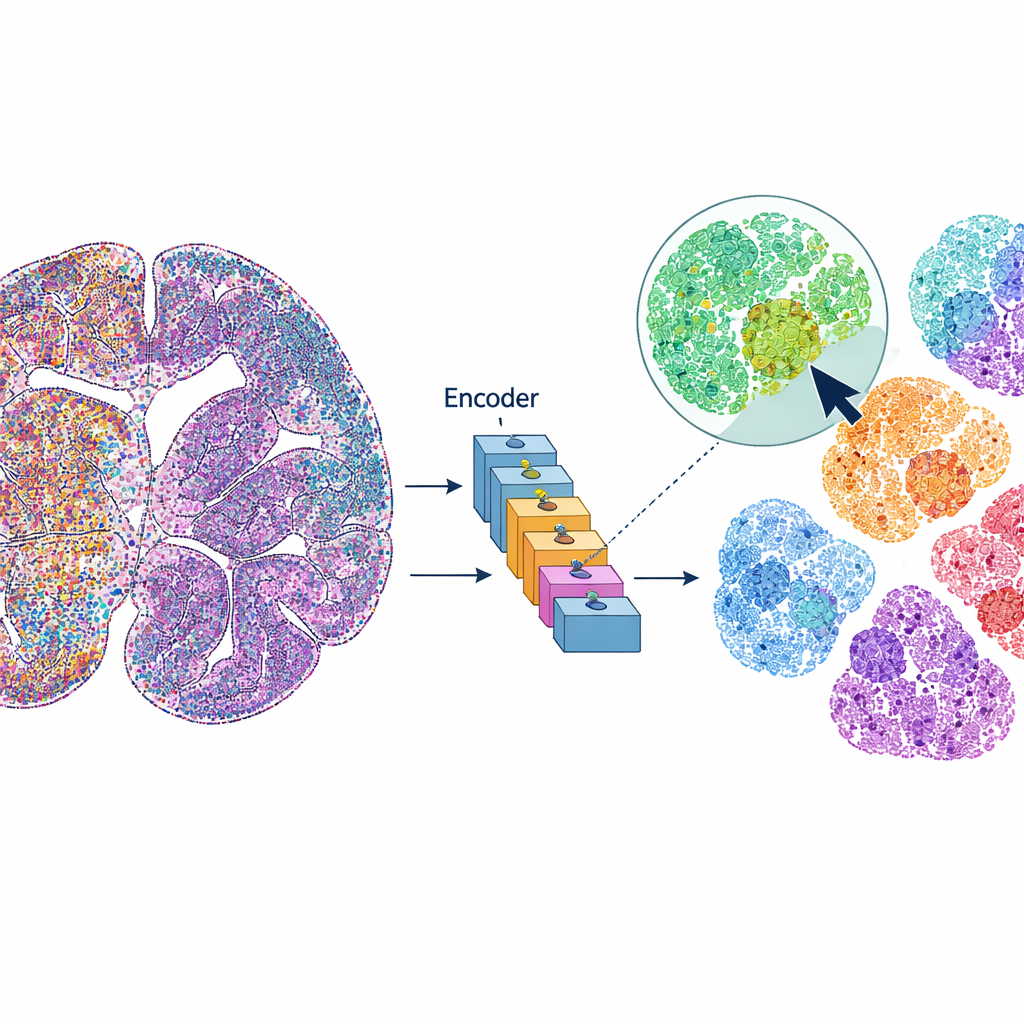
Bilgisayara Dokuyu Anlamayı Öğretmek
Bunun çalışması için mViSE önce tamamen arka planda bir öğrenme aşamasından geçer. Yazarlar birçok protein kanalını hücre tiplerini, glial hücreleri, sinir liflerini veya kan damarlarını vurgulayan belirleyiciler gibi biologik olarak anlamlı panellere böler. Her panel için güçlü bir görsel transformer—modern bir derin öğrenme modeli—beynin birçok küçük yama görüntüsüne bakar ve her yama için yüksek boyutlu bir “özellik uzayında” bir nokta olarak temsil etmeyi öğrenir. Benzer görünen ve davranan yamalar bu uzayda birbirine yakın olmalıdır. Bilgi teorisine dayalı bir topluluk tespit yöntemi daha sonra yakın noktaları doku mimarisinin tekrarlayan desenlerini yansıtan topluluklar halinde gruplar. Önemli olarak, bu öğrenme kendinden denetimli şekilde gerçekleşir: insan etiketlemesi gerektirmez, ancak bilinen katmanların ve bölgelerin yakalandığını görsel olarak doğrulayan renk kodlu haritalar üretir.
Hücrelere ve Komşuluklara Yakınlaştırma
Eğitildikten sonra mViSE farklı türde sorgulara yanıt verebilir. Tek hücre içeren çok küçük yamalar için, tüm beyinde en benzer hücreleri getirir ve bunların nerede bulunduğunu gösterir. Yazarlar sistemin nöronlar, astrositler, oligodendrositler, mikroglia ve vasküler hücreler gibi ana beyin hücre tiplerini, daha spesifik nöronal alt tipleri ve hatta kan damarlarının yanında yer alan hücre çiftlerini güvenilir şekilde bulduğunu gösterir. Birden çok hücre ve yerel bağlantıyı içeren daha büyük yamalar için mViSE benzer komşulukların tamamını döndürür; genellikle bilinen beyin bölgelerini veya yolları izler. Birden fazla belirteç panelinden gelen bilgileri birleştirerek kortikal katmanlar arasındaki ve aksi takdirde ayırt edilmesi zor küçük alt bölgeler arasındaki ince farkları da ayırabilir.
Genel Amaçlı Yapay Zeka Modellerini Geride Bırakmak
Araştırmacılar mViSE’yi doğal veya patoloji görüntülerinden oluşan büyük koleksiyonlar üzerinde eğitilmiş birkaç son teknoloji “foundation” modeliyle karşılaştırdı. Bu modeller basit üç renkli görüntüler beklediğinden, çok sayıda protein kanalı kırmızı, yeşil ve maviye sıkıştırılmak zorunda kaldı; bu da bilgi kaybına yol açtı. Bu uyarlamadan sonra bile, bu genel modeller katmanlar arasındaki sınırları daha belirsiz gösterdi ve ince taneli alt bölgeleri kaçırdı. Buna karşılık birçok kanalı doğrudan işleyebilecek şekilde tasarlanmış ve her kanalı ayrı kodlayıp sonra birleştiren mViSE, bilinen beyin atlası bölgelerini eşlemede daha yüksek doğruluk elde etti. Kortikal katmanların daha keskin haritalarını ve benzer yamaların daha tutarlı topluluklarını üretti; bu da temsilinin gerçek biyolojik organizasyonu daha iyi yansıttığını gösteriyor. 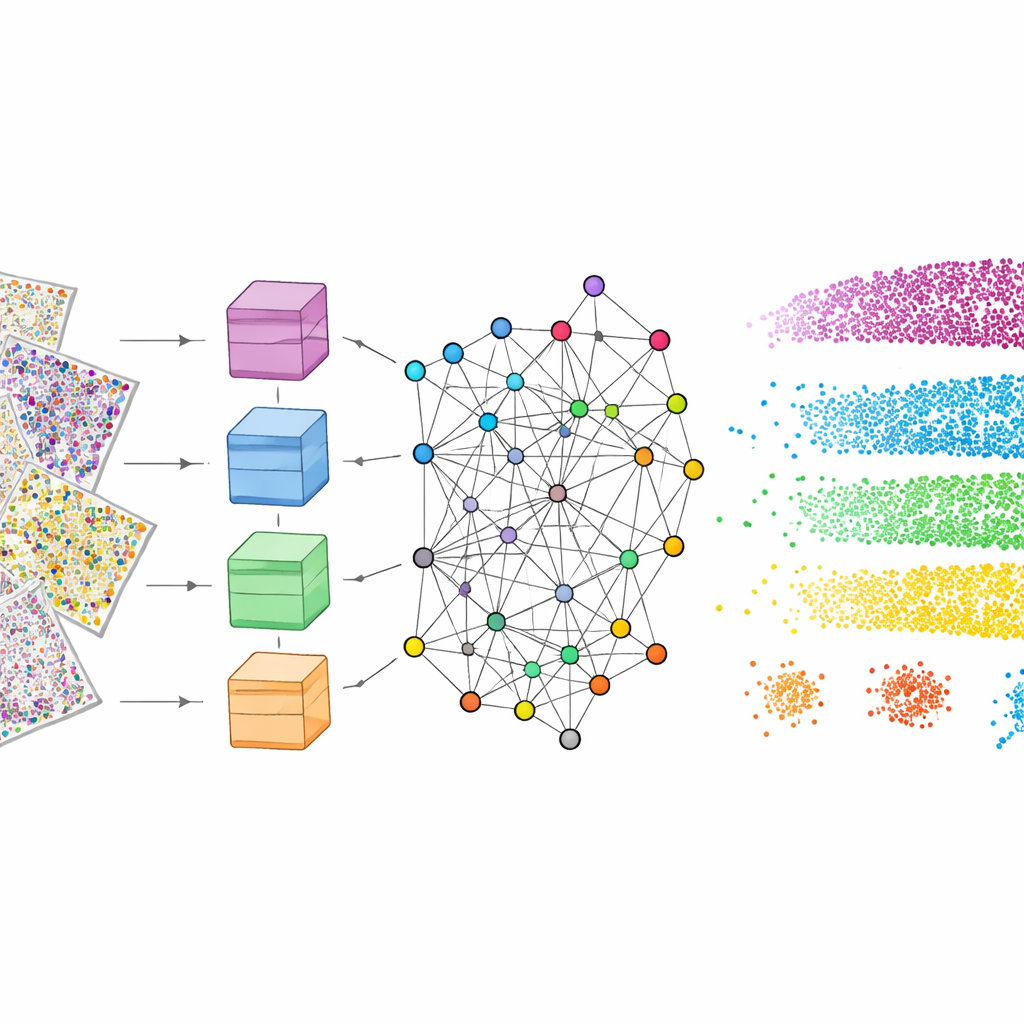
Canlı Haritayı Keşfetmenin Yeni Bir Yolu
Özünde mViSE, devasa, çok renkli beyin görüntülerini araştırmacıların görsel olarak arayabileceği etkileşimli bir haritaya dönüştürüyor. Her analizi zahmetle betimlemek yerine bilim insanları gözlerini çeken hücrelere veya mikroçevrelere tıklayıp benzer yapıların nerede göründüğünü ve protein profillerinin nasıl karşılaştırıldığını anında görebilir. Yöntem eğitim sırasında manuel açıklama gerektirmez ve çok büyük veri kümelerine ölçeklenir; bu da onu uzamsal proteomik araç setine pratik bir katkı haline getirir. Görüntüleme teknolojileri daha fazla moleküler kanal ekledikçe ve benzer yaklaşımlar hastalıklı beyinlere ve diğer organlara genişletildikçe, mViSE benzeri araçlar ham görüntü karmaşıklığını doku mimarisinin sezgisel, gezilebilir görünümlerine dönüştürmeye yardımcı olabilir—bizi beynin karmaşık moleküler atlasını aranabilir bir harita gibi okumaya daha da yaklaştırır.
Atıf: Huang, L., Mills, R., Mandula, S. et al. mViSE: A visual search engine for analyzing multiplex IHC brain tissue images (spatial proteomics). Sci Rep 16, 10245 (2026). https://doi.org/10.1038/s41598-026-40620-5
Anahtar kelimeler: uzamsal proteomik, beyin görüntüleme, görsel arama motoru, çoklu mikroskopi, hesaplamalı patoloji