Clear Sky Science · ru
mViSE: Визуальная поисковая система для анализа мультиплексных IHC-изображений мозга (пространственная протеомика)
Увидеть закономерности в мозге
Современные микроскопы теперь способны получать невероятно детализированные изображения целых срезов мозга, одновременно показывая десятки разных белков. Эти «мультиплексные» изображения обещают подсказать, как организованы клетки мозга, как они взаимодействуют и как заболевания нарушают эти закономерности. Но изображения настолько огромны и сложны, что даже мощным компьютерам трудно их осмыслить. В этой статье представлен mViSE — визуальная поисковая система, которая позволяет исследователям исследовать такие обширные изображения мозга простым щелчком по клетке или интересующему участку ткани, а не написанием специального кода.
Почему большие изображения мозга трудно использовать
Каждое мультиплексное изображение мозга похоже на гигантскую карту города, где каждый дом, улица и коммуникация помечены множеством цветов одновременно. Разные белки отмечают разные типы клеток, состояния клеток, кровеносные сосуды и проводящие структуры. Традиционные аналитические конвейеры разбивают эту карту на длинную цепочку программных шагов: очистить изображение, обнаружить клетки, сегментировать их, присвоить типы клеток и затем суммировать результаты по регионам. Хотя такой подход мощный, он жесткий и трудно адаптируется под новые вопросы — особенно для мозга, где смешение нейронов, глии и сосудов обладает огромной молекулярной и пространственной сложностью. Ученым все чаще нужна более гибкая, интерактивная возможность задавать новые вопросы к этим данным, не становясь программистами на полный рабочий день.
Поисковая система для клеток мозга
mViSE рассматривает изображение мозга скорее как онлайн-библиотеку фотографий, а не как статичный набор данных. Вместо того чтобы заранее определять каждый шаг анализа, пользователь щелкает по клетке или небольшому участку ткани, который кажется интересным. Система затем ищет по всему изображению мозга клетки или микроокружения, которые выглядят и «ведут себя» похоже по многим белковым каналам. Совпадения выделяются непосредственно на обзоре всего мозга и могут быть суммированы в виде профилей экспрессии белков. Это позволяет исследователям быстро выявлять, где появляются похожие клетки или микроокружения, очерчивать регионы мозга и корковые слои и сравнивать закономерности в разных частях мозга — все это управляется визуальными запросами, а не кодом. 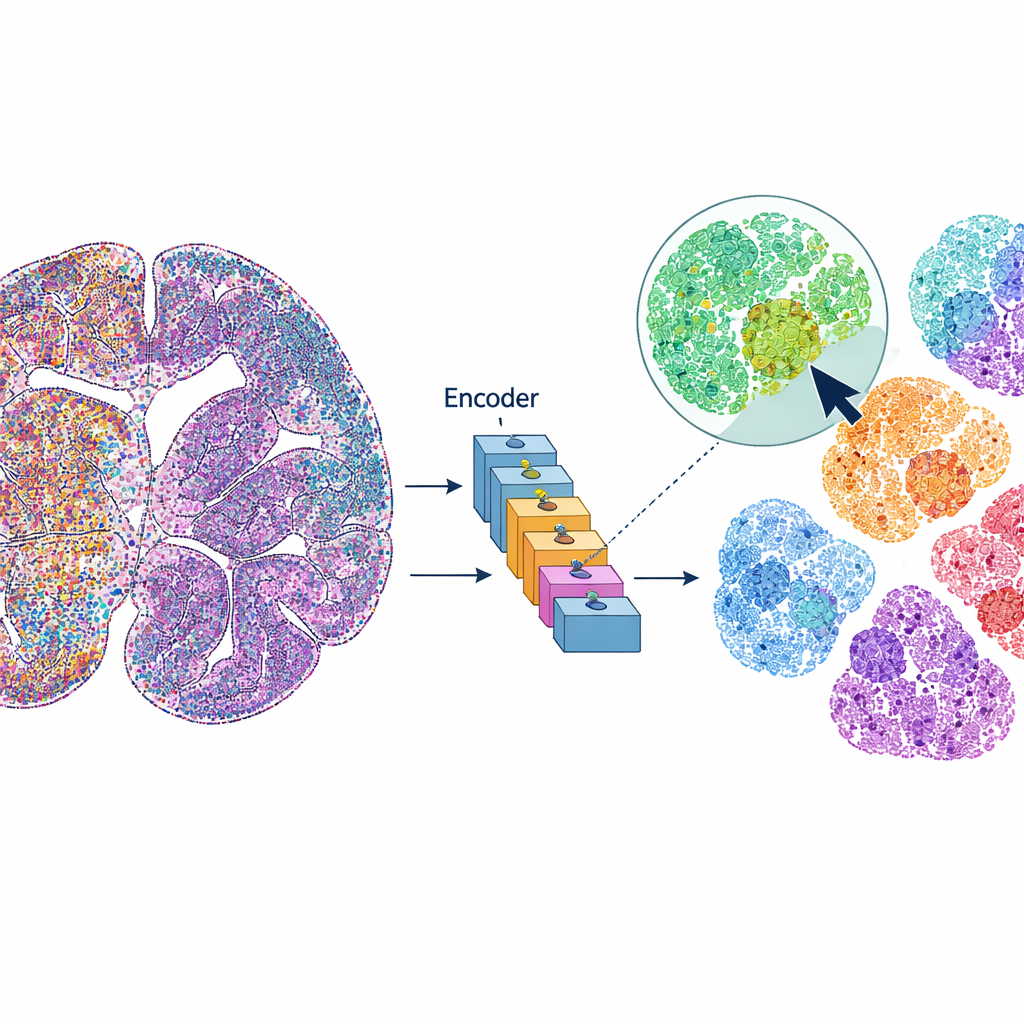
Обучение компьютера понимать ткань
Чтобы это работало, mViSE сначала проходит фазу обучения полностью в фоновом режиме. Авторы делят многочисленные белковые каналы на биологически осмысленные панели, такие как маркеры, выделяющие типы клеток, глиальные клетки, нервные волокна или кровеносные сосуды. Для каждой панели мощный vision transformer — современная модель глубокого обучения — просматривает множество небольших участков по всему мозгу и учится представлять каждый фрагмент как точку в многомерном «пространстве признаков». Фрагменты, которые выглядят и ведут себя похоже, должны оказаться близкими друг к другу в этом пространстве. Затем информационно-теоретический метод обнаружения сообществ группирует близкие точки в сообщества, отражающие повторяющиеся шаблоны архитектуры ткани. Важно, что это обучение самоподсмотренное: оно не требует ручной разметки, но при этом дает цветовые карты, которые визуально подтверждают, что известные слои и регионы захватываются.
Приближение к клеткам и микроокружениям
После обучения mViSE может отвечать на разные типы запросов. Для очень маленьких фрагментов, содержащих отдельные клетки, система находит наиболее похожие клетки по всему мозгу и показывает, где они расположены. Авторы демонстрируют, что система надежно обнаруживает основные типы клеток мозга — такие как нейроны, астроциты, олигодендроциты, микроглия и сосудистые клетки — а также более специфические нейронные подтипы и даже пары клеток рядом с кровеносными сосудами. Для больших фрагментов, включающих несколько клеток и локальные проводящие структуры, mViSE возвращает полное сообщество похожих микроокружений, часто очерчивая известные регионы мозга или тракты. Объединяя информацию из нескольких панелей маркеров одновременно, система также может различать тонкие отличия между корковыми слоями и небольшими подрегионами, которые иначе трудно разделить.
Превосходство над универсальными моделями ИИ
Исследователи сравнили mViSE с несколькими современными «фундаментальными» моделями, изначально обученными на больших коллекциях естественных или патологических изображений. Поскольку эти модели ожидают простые трехцветные изображения, многочисленные белковые каналы приходилось сжимать в красный, зеленый и синий, что приводило к потере информации. Даже после такой адаптации эти общие модели давали более размытые границы между слоями и упускали мелкомасштабные подрегионы. В отличие от них, mViSE, спроектированный для работы с множеством каналов напрямую и кодирующий каждый канал отдельно перед объединением, показал более высокую точность в сопоставлении с известными регионами атласа мозга. Он создал более четкие карты корковых слоев и более согласованные сообщества похожих фрагментов, что указывает на то, что его представления лучше отражают истинную биологическую организацию. 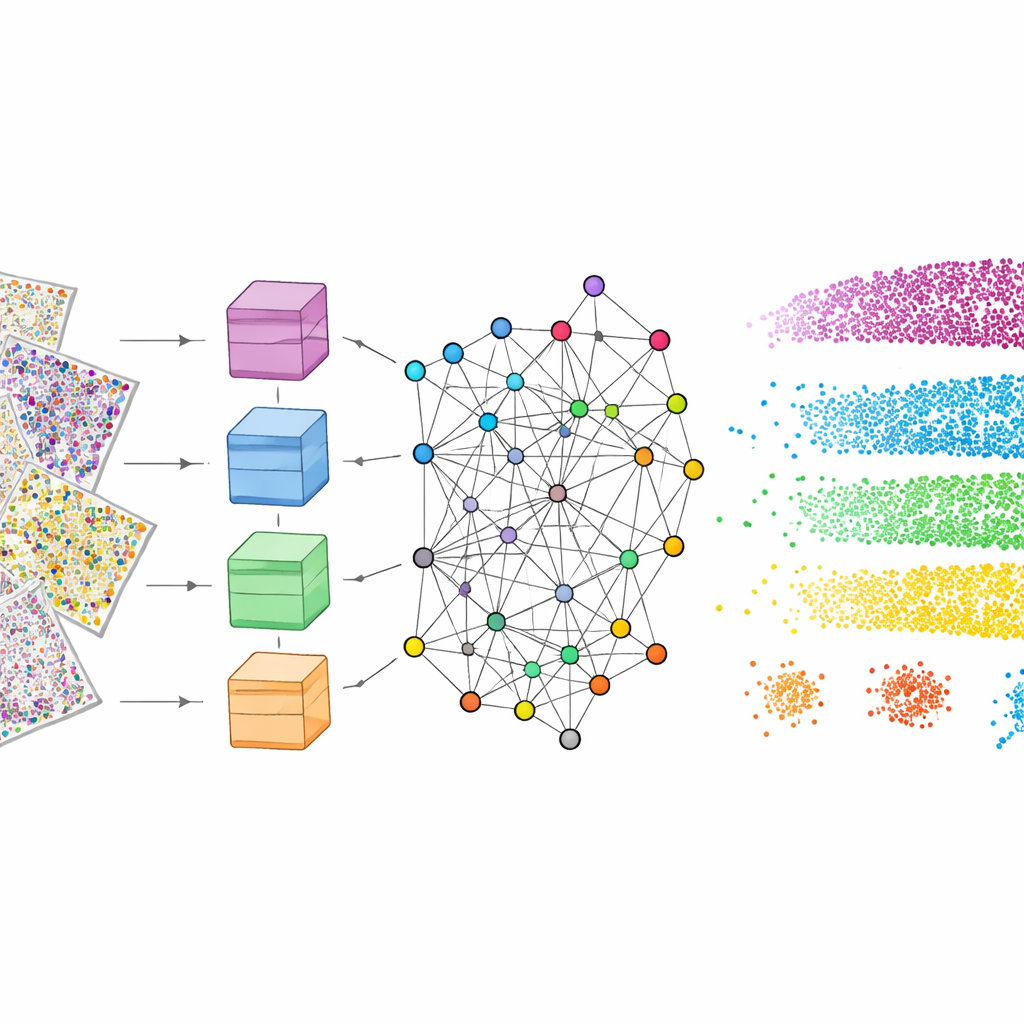
Новый способ исследовать живую карту
По сути, mViSE превращает огромные, многоцветные изображения мозга в интерактивную карту, которую исследователи могут искать визуально. Вместо утомительного написания скриптов для каждого анализа ученые могут щелкнуть по клеткам или микроокружениям, которые привлекают их внимание, и мгновенно увидеть, где появляются похожие структуры и как сравниваются их белковые профили. Метод не требует ручной аннотации во время обучения и масштабируется на очень большие наборы данных, что делает его практичным дополнением к инструментарию пространственной протеомики. По мере того как методы визуализации будут добавлять еще больше молекулярных каналов, а подобные подходы будут распространяться на пораженные заболеваниями мозги и другие органы, такие инструменты, как mViSE, могут помочь превратить сырую сложность изображений в интуитивно понятные, удобные для навигации представления архитектуры ткани — приближая нас к тому, чтобы читать сложный молекулярный атлас мозга как поисковую карту.
Цитирование: Huang, L., Mills, R., Mandula, S. et al. mViSE: A visual search engine for analyzing multiplex IHC brain tissue images (spatial proteomics). Sci Rep 16, 10245 (2026). https://doi.org/10.1038/s41598-026-40620-5
Ключевые слова: пространственная протеомика, изображение мозга, визуальная поисковая система, мультиплексная микроскопия, вычислительная патология