Clear Sky Science · es
mViSE: Un motor de búsqueda visual para analizar imágenes cerebrales IHC multiplex (proteómica espacial)
Detectando patrones en el cerebro
Los microscopios modernos pueden capturar ahora imágenes de rebanadas cerebrales con un nivel de detalle asombroso, mostrando decenas de proteínas diferentes a la vez. Estas imágenes “multiplex” prometen pistas sobre cómo se organizan las células cerebrales, cómo se comunican entre sí y cómo la enfermedad altera esos patrones. Pero las imágenes son tan grandes y complejas que incluso equipos informáticos potentes tienen dificultades para interpretarlas. Este artículo presenta mViSE, un motor de búsqueda visual que permite a los investigadores explorar estas inmensas imágenes cerebrales simplemente haciendo clic en células y vecindarios de interés, en lugar de escribir código personalizado.
Por qué las imágenes cerebrales grandes son difíciles de usar
Cada imagen cerebral multiplex es como un mapa urbano gigantesco donde cada edificio, calle y línea de servicio aparece etiquetado en muchos colores a la vez. Diferentes proteínas marcan distintos tipos celulares, estados celulares, vasos sanguíneos y patrones de conexión. Las canalizaciones de análisis tradicionales dividen este mapa en una larga cadena de pasos programados: limpiar la imagen, detectar células, segmentarlas, etiquetar los tipos celulares y luego resumir los resultados por región. Aunque potentes, este enfoque es rígido y difícil de adaptar cuando surgen nuevas preguntas, sobre todo en el cerebro, cuya mezcla de neuronas, glía y vasos tiene una complejidad molecular y espacial enorme. Cada vez más, los científicos necesitan una forma interactiva y flexible de plantear nuevas preguntas a estos datos sin convertirse en programadores a tiempo completo.
Un motor de búsqueda para las células del cerebro
mViSE trata una imagen cerebral más como una librería de fotos en línea que como un conjunto de datos estático. En lugar de predefinir cada paso de análisis, el usuario hace clic en una célula o en un pequeño parche de tejido que le resulte interesante. El sistema busca entonces en toda la imagen cerebral las células o vecindarios que se parezcan y “se comporten” de forma similar a través de muchos canales proteicos. Las coincidencias se resaltan directamente en la vista del cerebro completo y pueden resumirse como perfiles de expresión proteica. Esto permite a los investigadores descubrir rápidamente dónde aparecen células o microambientes similares, delinear regiones cerebrales y capas corticales, y comparar patrones entre distintas partes del cerebro—todo impulsado por consultas visuales, no por código. 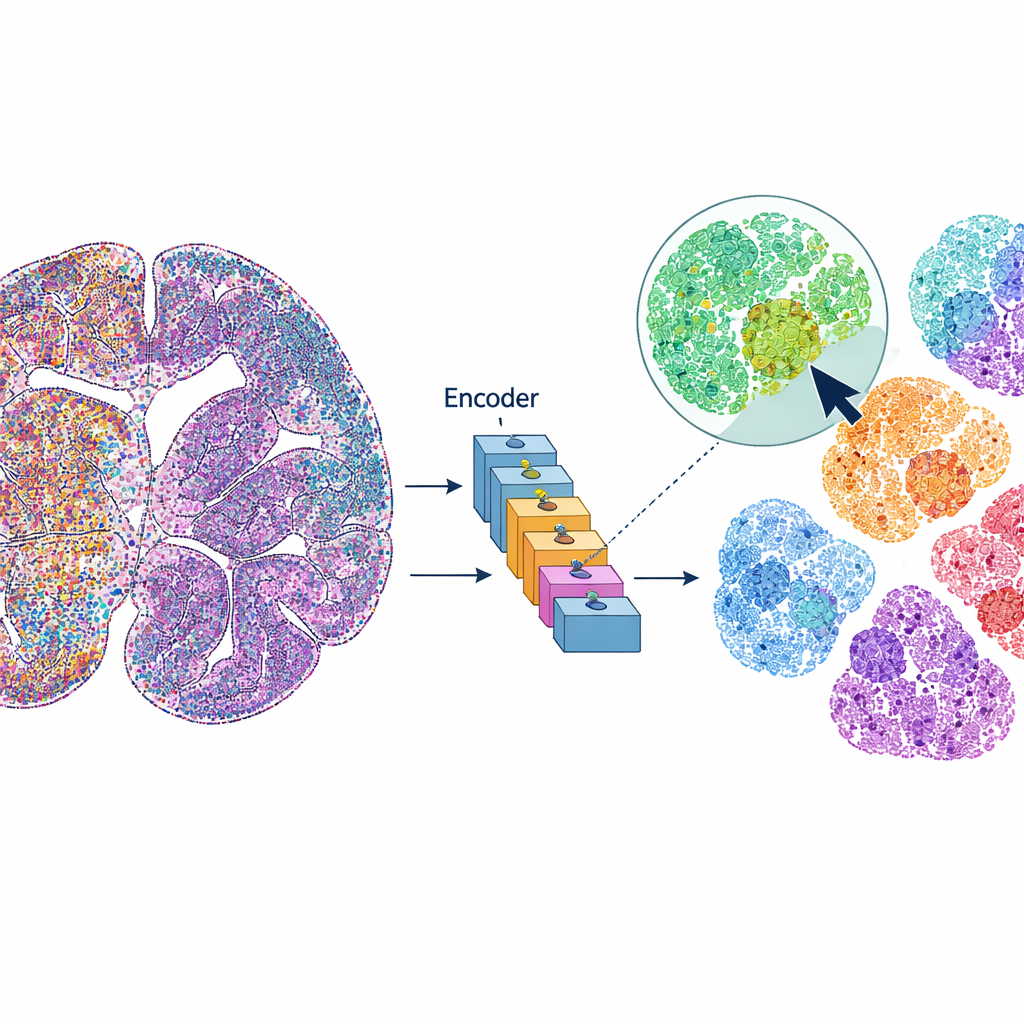
Enseñar al ordenador a entender el tejido
Para que esto funcione, mViSE primero pasa por una fase de aprendizaje que se ejecuta completamente en segundo plano. Los autores dividen los muchos canales proteicos en paneles biológicamente significativos, por ejemplo marcadores que resaltan tipos celulares, células gliales, fibras nerviosas o vasos sanguíneos. Para cada panel, un transformer de visión potente—un modelo moderno de aprendizaje profundo—observa muchos pequeños parches repartidos por el cerebro y aprende a representar cada parche como un punto en un espacio de características de alta dimensión. Los parches que se parecen y actúan de forma similar deberían terminar próximos en ese espacio. Un método de detección de comunidades basado en teoría de la información agrupa después puntos cercanos en comunidades que reflejan patrones repetidos de arquitectura tisular. Es importante destacar que este aprendizaje es auto-supervisado: no requiere etiquetado humano, pero aun así produce mapas codificados por colores que confirman visualmente que se capturan capas y regiones conocidas.
Acercándose a células y vecindarios
Una vez entrenado, mViSE puede responder a distintos tipos de consultas. Para parches muy pequeños que contienen células individuales, recupera las células más similares en todo el cerebro y muestra dónde están ubicadas. Los autores demuestran que el sistema encuentra de forma fiable los principales tipos celulares cerebrales—como neuronas, astrocitos, oligodendrocitos, microglía y células vasculares—además de subtipos neuronales más específicos e incluso pares de células situadas junto a vasos sanguíneos. Para parches mayores que incluyen múltiples células y conexiones locales, mViSE devuelve la comunidad completa de vecindarios similares, trazando a menudo regiones conocidas o tractos cerebrales. Al combinar información de varios paneles de marcadores a la vez, también puede distinguir diferencias sutiles entre capas corticales y pequeñas subregiones que de otro modo son difíciles de separar.
Rendimiento superior frente a modelos de IA de propósito general
Los investigadores compararon mViSE con varios modelos “foundation” de última generación entrenados originalmente con grandes colecciones de imágenes naturales o de patología. Debido a que esos modelos esperan imágenes sencillas de tres colores, los muchos canales proteicos tuvieron que comprimirse en rojo, verde y azul, lo que provocó pérdida de información. Incluso después de esa adaptación, esos modelos generales produjeron límites más difusos entre capas y pasaron por alto subregiones finas. En contraste, mViSE, diseñado para manejar directamente muchos canales y que codifica cada canal por separado antes de combinarlos, alcanzó mayor precisión al coincidir con regiones conocidas de atlas cerebrales. Generó mapas más nítidos de las capas corticales y comunidades más coherentes de parches similares, lo que indica que sus representaciones reflejan mejor la organización biológica real. 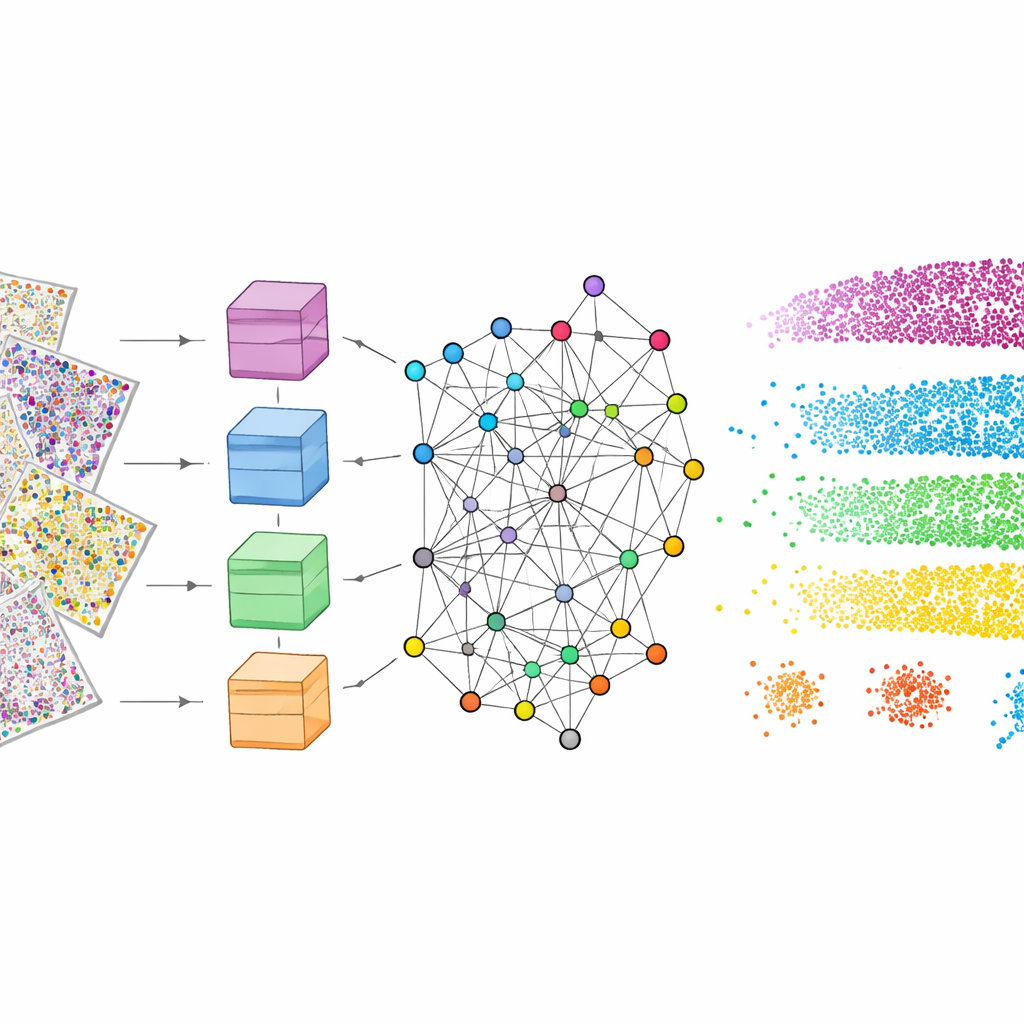
Una nueva forma de explorar el mapa vivo
En esencia, mViSE convierte imágenes cerebrales enormes y multicolores en un mapa interactivo que los investigadores pueden buscar visualmente. En lugar de programar laboriosamente cada análisis, los científicos pueden hacer clic en células o microambientes que llamen su atención y ver al instante dónde aparecen estructuras similares y cómo se comparan sus perfiles proteicos. El método no requiere anotación manual durante el entrenamiento y escala a conjuntos de datos muy grandes, lo que lo convierte en una adición práctica al conjunto de herramientas de la proteómica espacial. A medida que las tecnologías de imagen incorporen aún más canales moleculares y enfoques similares se extiendan a cerebros enfermos y otros órganos, herramientas como mViSE podrían ayudar a convertir la complejidad cruda de las imágenes en vistas intuitivas y navegables de la arquitectura tisular—acercándonos a leer el intrincado atlas molecular del cerebro como un mapa buscable.
Cita: Huang, L., Mills, R., Mandula, S. et al. mViSE: A visual search engine for analyzing multiplex IHC brain tissue images (spatial proteomics). Sci Rep 16, 10245 (2026). https://doi.org/10.1038/s41598-026-40620-5
Palabras clave: proteómica espacial, imagen cerebral, motor de búsqueda visual, microscopía multiplex, patología computacional