Clear Sky Science · fr
mViSE : un moteur de recherche visuel pour analyser des images cérébrales IHC multiplex (protéomique spatiale)
Voir les motifs dans le cerveau
Les microscopes modernes peuvent désormais capturer des images d'une précision époustouflante de tranches cérébrales entières, montrant des dizaines de protéines différentes simultanément. Ces images « multiplex » offrent des indices sur l'organisation des cellules cérébrales, leurs interactions et la manière dont la maladie perturbe ces motifs. Mais les images sont si énormes et complexes que même des ordinateurs puissants peinent à en extraire du sens. Cet article présente mViSE, un moteur de recherche visuel qui permet aux chercheurs d’explorer ces vastes images cérébrales en cliquant simplement sur des cellules ou des voisinages d’intérêt, plutôt qu’en écrivant du code personnalisé.
Pourquoi les grandes images cérébrales sont difficiles à utiliser
Chaque image cérébrale multiplex ressemble à une immense carte urbaine où chaque bâtiment, rue et réseau utilitaire est étiqueté par de nombreuses couleurs à la fois. Différentes protéines marquent différents types cellulaires, états cellulaires, vaisseaux sanguins et schémas de câblage. Les pipelines d’analyse traditionnels fragmentent cette carte en une longue chaîne d’étapes programmées : nettoyage de l’image, détection des cellules, segmentation, attribution des types cellulaires, puis synthèse des résultats par région. Bien que puissante, cette approche est rigide et difficile à adapter quand surgissent de nouvelles questions—surtout pour le cerveau, dont le mélange de neurones, cellules gliales et vaisseaux présente une immense complexité moléculaire et spatiale. Les scientifiques ont de plus en plus besoin d’un mode d’interrogation flexible et interactif de ces données sans devenir des programmeurs à plein temps.
Un moteur de recherche pour les cellules cérébrales
mViSE considère une image cérébrale plus comme une bibliothèque de photos en ligne que comme un jeu de données statique. Plutôt que de pré-définir chaque étape d’analyse, l’utilisateur clique sur une cellule ou un petit patch de tissu qui paraît intéressant. Le système recherche alors dans l’ensemble de l’image les cellules ou voisinages qui ressemblent et « se comportent » de façon similaire à travers de nombreuses voies protéiques. Les correspondances sont mises en évidence directement sur la vue globale du cerveau et peuvent être résumées sous forme de profils d’expression protéique. Cela permet aux chercheurs de découvrir rapidement où apparaissent des cellules ou microenvironnements similaires, de délimiter des régions cérébrales et des couches corticales, et de comparer des motifs entre différentes parties du cerveau—le tout piloté par des requêtes visuelles, sans code. 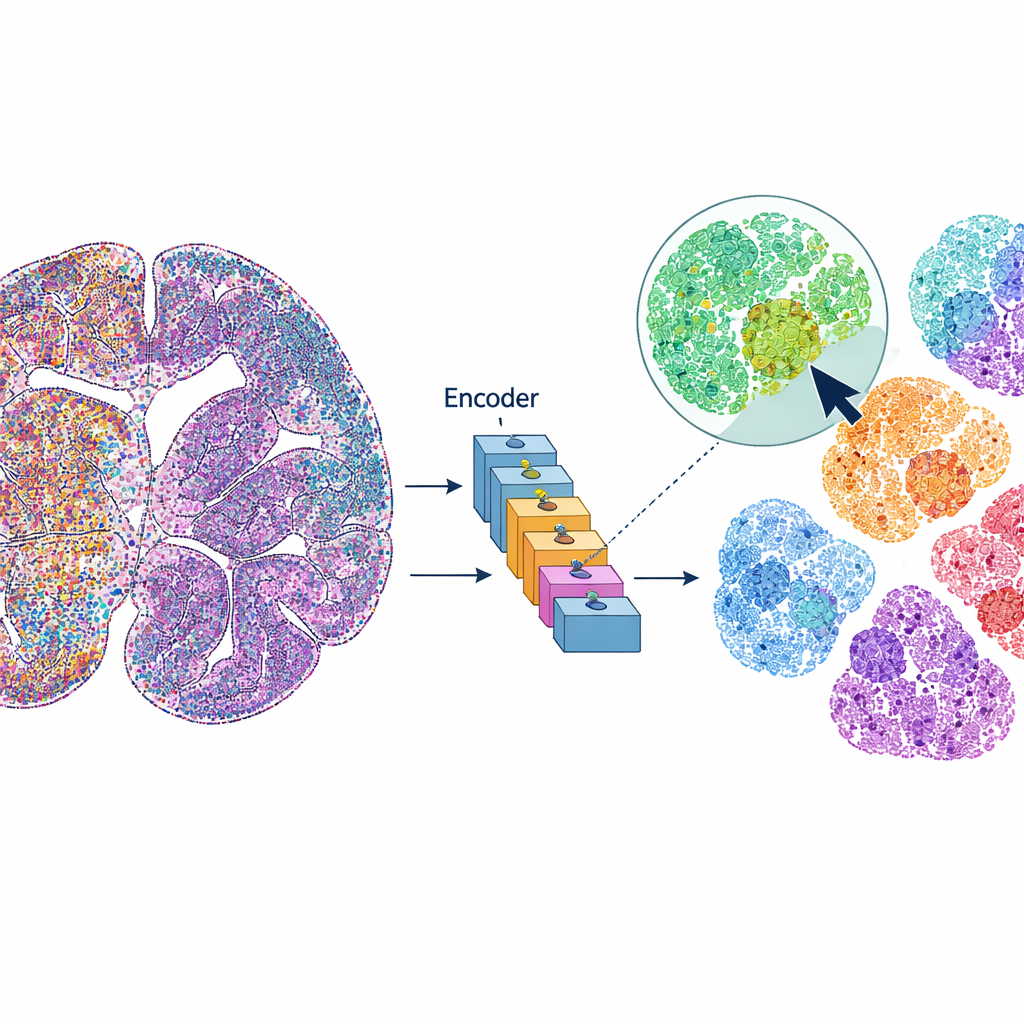
Apprendre à l’ordinateur à comprendre le tissu
Pour que cela fonctionne, mViSE passe d’abord par une phase d’apprentissage entièrement en arrière-plan. Les auteurs divisent les nombreuses voies protéiques en panneaux biologiquement pertinents, tels que des marqueurs mettant en évidence les types cellulaires, les cellules gliales, les fibres nerveuses ou les vaisseaux sanguins. Pour chaque panneau, un puissant transformeur de vision—un modèle d’apprentissage profond moderne—analyse de nombreux petits patches à travers le cerveau et apprend à représenter chaque patch comme un point dans un « espace de caractéristiques » de haute dimension. Les patches qui se ressemblent et fonctionnent de la même manière doivent se retrouver proches dans cet espace. Une méthode de détection de communautés fondée sur la théorie de l’information regroupe ensuite les points voisins en communautés reflétant des motifs répétitifs d’architecture tissulaire. Fait important, cet apprentissage est auto-supervisé : il ne nécessite pas d’annotations humaines, tout en produisant des cartes colorées qui confirment visuellement que des couches et régions connues sont bien capturées.
Zoom sur les cellules et les voisinages
Une fois entraîné, mViSE peut répondre à différents types de requêtes. Pour des patches très petits contenant des cellules uniques, il récupère les cellules les plus similaires à travers le cerveau et montre où elles se situent. Les auteurs démontrent que le système retrouve de façon fiable les principaux types cellulaires du cerveau—comme les neurones, astrocytes, oligodendrocytes, microglies et cellules vasculaires—ainsi que des sous-types neuronaux plus spécifiques, et même des paires de cellules situées à côté de vaisseaux sanguins. Pour des patches plus grands incluant plusieurs cellules et le câblage local, mViSE renvoie la communauté complète de voisinages similaires, retraçant souvent des régions cérébrales ou des faisceaux connus. En combinant l’information de plusieurs panneaux de marqueurs à la fois, il peut aussi distinguer des différences subtiles entre couches corticales et petites sous-régions difficilement séparables autrement.
Surpasser les modèles d’IA à usage général
Les chercheurs ont comparé mViSE à plusieurs modèles « fondation » de pointe initialement entraînés sur de larges collections d’images naturelles ou pathologiques. Parce que ces modèles s’attendent à des images simples en trois couleurs, les nombreuses voies protéiques ont dû être compressées en rouge, vert et bleu, entraînant une perte d’information. Même après cette adaptation, ces modèles généraux produisaient des frontières plus floues entre les couches et manquaient des sous-régions fines. En revanche, mViSE, conçu pour gérer directement de nombreux canaux et encodant chaque canal séparément avant de les combiner, a obtenu une meilleure précision dans l’identification des régions d’atlas cérébral connues. Il a produit des cartes de couches corticales plus nettes et des communautés de patches plus cohérentes, indiquant que ses représentations reflètent mieux l’organisation biologique réelle. 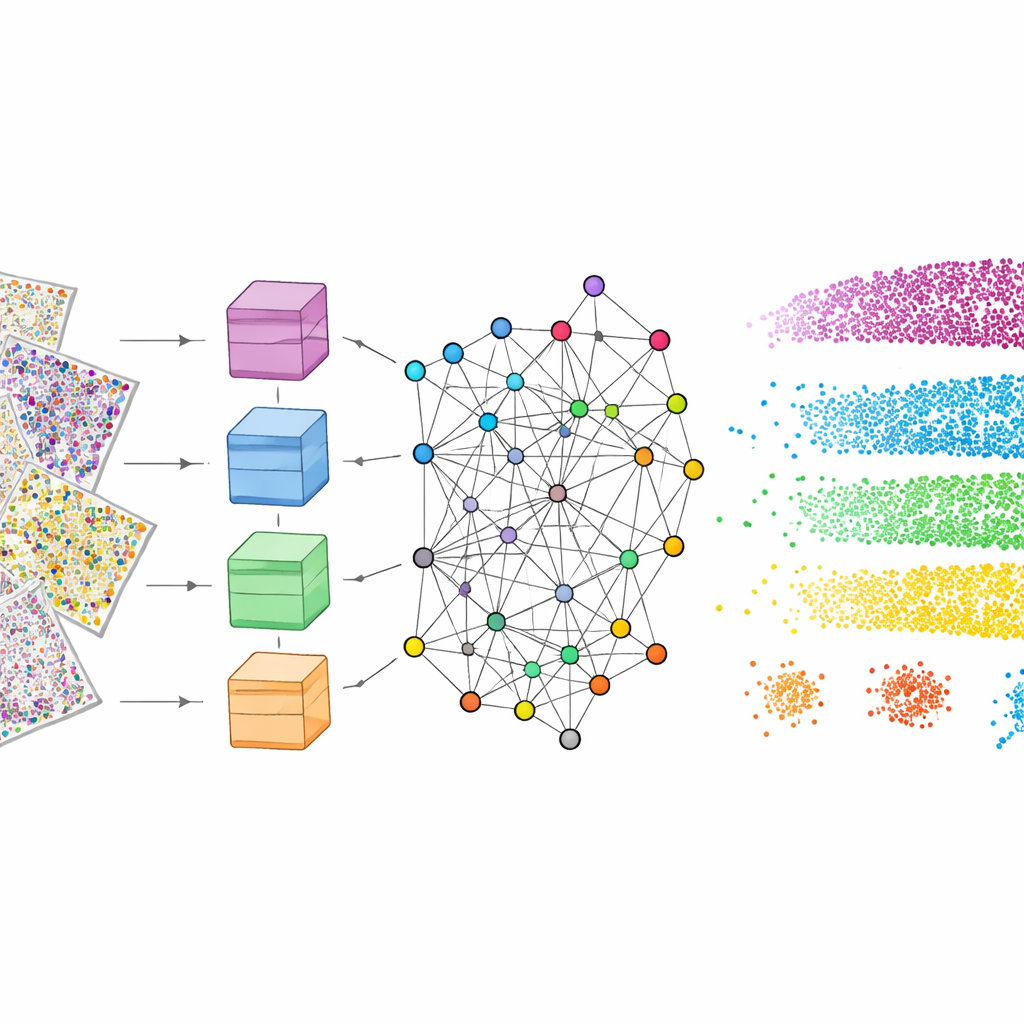
Une nouvelle façon d’explorer la carte vivante
En substance, mViSE transforme d’immenses images cérébrales multicolores en une carte interactive que les chercheurs peuvent interroger visuellement. Au lieu de rédiger laborieusement chaque analyse, les scientifiques peuvent cliquer sur des cellules ou microenvironnements qui attirent leur attention et voir instantanément où des structures similaires apparaissent et comment leurs profils protéiques se comparent. La méthode ne requiert aucune annotation manuelle lors de l’entraînement et s’adapte à des jeux de données très volumineux, ce qui en fait un ajout pratique à la boîte à outils de la protéomique spatiale. À mesure que les technologies d’imagerie ajoutent encore plus de canaux moléculaires, et que des approches similaires sont étendues aux cerveaux malades et à d’autres organes, des outils comme mViSE pourraient aider à convertir la complexité brute des images en vues intuitives et navigables de l’architecture tissulaire—nous rapprochant de la lecture de l’atlas moléculaire complexe du cerveau comme d’une carte consultable.
Citation: Huang, L., Mills, R., Mandula, S. et al. mViSE: A visual search engine for analyzing multiplex IHC brain tissue images (spatial proteomics). Sci Rep 16, 10245 (2026). https://doi.org/10.1038/s41598-026-40620-5
Mots-clés: protéomique spatiale, imagerie cérébrale, moteur de recherche visuel, microscopie multiplex, pathologie computationnelle