Clear Sky Science · sv
mViSE: En visuell sökmotor för analys av multiplex IHC-hjärnvävnadsbilder (rumslig proteomik)
Att se mönster i hjärnan
Moderna mikroskop kan nu fånga hisnande detaljerade bilder av hela hjärnskivor och samtidigt visa många olika proteiner. Dessa ”multiplex”-bilder lovar insikter om hur hjärnceller är organiserade, hur de kommunicerar och hur sjukdom stör dessa mönster. Men bilderna är så stora och komplexa att även kraftfulla datorer har svårt att tolka dem. Denna artikel presenterar mViSE, en visuell sökmotor som låter forskare utforska dessa enorma hjärnbilder genom att helt enkelt klicka på celler och intressanta närområden istället för att skriva specialanpassad kod.
Varför stora hjärnbilder är svåra att använda
Varje multiplex-hjärnbild är som en jättelik stadsplan där varje byggnad, gata och ledning är märkta i många färger samtidigt. Olika proteiner markerar olika celltyper, celltillstånd, blodkärl och nervdragningar. Traditionella analyskedjor delar upp denna karta i en lång rad förprogrammerade steg: rengör bilden, detektera celler, segmentera dem, märk upp celltyper och summera resultat per region. Trots sin kraft är detta tillvägagångssätt stelt och svårt att anpassa när nya frågor uppstår—särskilt för hjärnan, vars blandning av neuroner, gliaceller och blodkärl har enorm molekylär och rumslig komplexitet. Forskare behöver i allt högre grad ett mer flexibelt, interaktivt sätt att ställa nya frågor till dessa data utan att bli heltidsprogrammerare.
En sökmotor för hjärnceller
mViSE behandlar en hjärnbild mer som ett online-fotobibliotek än som en statisk datamängd. Istället för att fördefiniera varje analyssteg klickar användaren på en cell eller en liten vävnadsfläck som ser intressant ut. Systemet söker sedan igenom hela hjärnbilden efter celler eller närområden som ser och ”beter sig” likadant över många proteinkanaler. Träffarna markeras direkt i helbildsvyn och kan sammanfattas som proteinuttrycksprofiler. Det låter forskare snabbt upptäcka var liknande celler eller mikroomgivningar förekommer, avgränsa hjärnregioner och kortikala lager samt jämföra mönster i olika delar av hjärnan—allt styrt av visuella förfrågningar, inte kod. 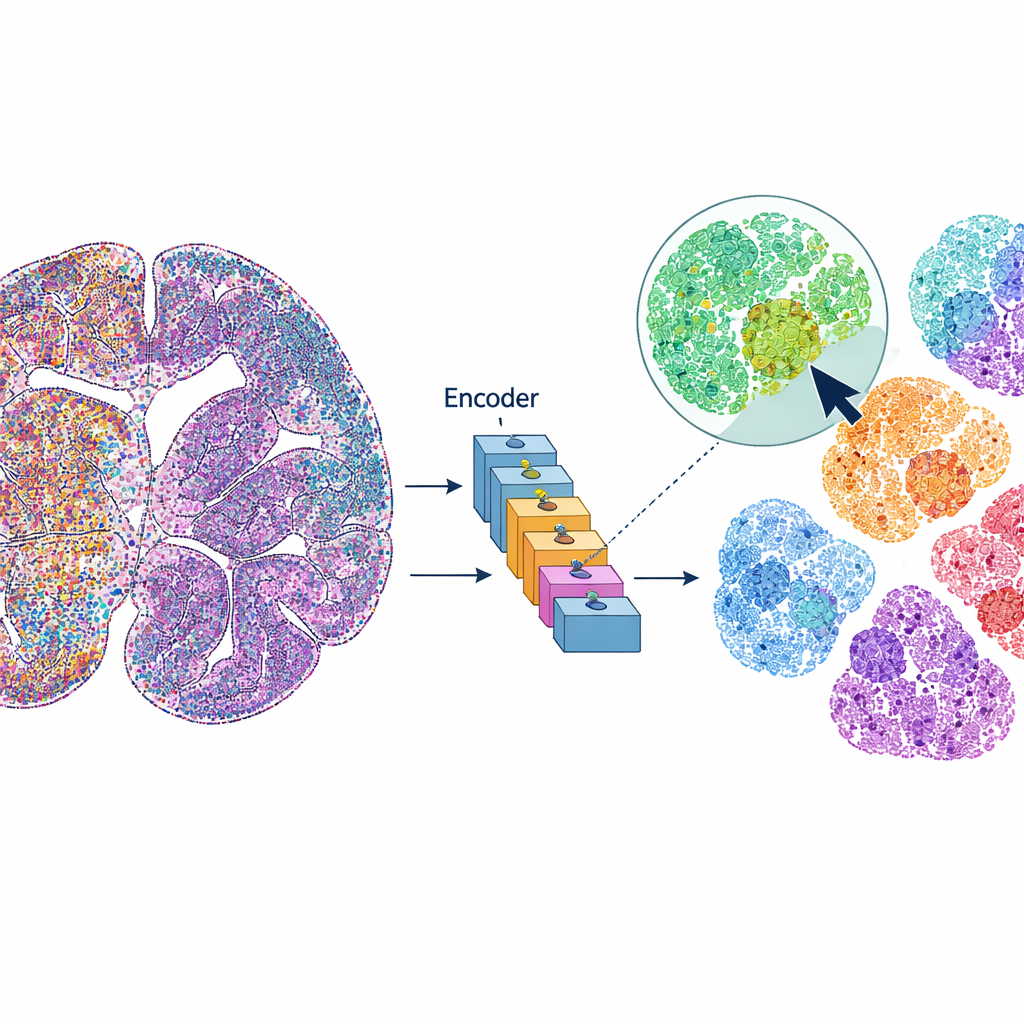
Att lära datorn förstå vävnad
För att detta ska fungera genomgår mViSE först en inlärningsfas helt i bakgrunden. Författarna delar upp de många proteinkanalerna i biologiskt meningsfulla paneler, såsom markörer som framhäver celltyper, gliaceller, nervfibrer eller blodkärl. För varje panel ser en kraftfull vision transformer—en modern djupinlärningsmodell—på många små fläckar över hjärnan och lär sig representera varje fläck som en punkt i ett högdimensionellt ”funktionsutrymme”. Fläckar som ser och uppträder lika bör hamna nära varandra i detta rum. En informationsteoretisk community-detekteringsmetod grupperar sedan närliggande punkter i gemenskaper som speglar återkommande mönster i vävnadsarkitekturen. Viktigt är att denna inlärning är självövervakad: den kräver ingen mänsklig märkning men producerar ändå färgkodade kartor som visuellt bekräftar att kända lager och regioner fångas upp.
Zooma in på celler och närområden
När modellen är tränad kan mViSE svara på olika typer av förfrågningar. För mycket små fläckar som innehåller enstaka celler återfinns de mest liknande cellerna i hela hjärnan och deras placering visas. Författarna visar att systemet pålitligt hittar huvudtyper av hjärnceller—såsom neuroner, astrocyter, oligodendrocyter, mikroglia och vaskulära celler—såväl som mer specifika neuronal undergrupper, och till och med cellpar belägna intill blodkärl. För större fläckar som inkluderar flera celler och lokal nervkoppling returnerar mViSE hela gemenskapen av liknande närområden, ofta så att kända hjärnregioner eller banor framträder. Genom att kombinera information från flera markörpaneler samtidigt kan det också urskilja subtila skillnader mellan kortikala lager och små subregioner som annars är svåra att särskilja.
Överträffar allmänna AI-modeller
Forskarna jämförde mViSE med flera ledande ”foundation”-modeller som ursprungligen tränats på stora samlingar av naturliga eller patologiska bilder. Eftersom dessa modeller förväntar sig enkla trefärgade bilder var man tvungen att pressa de många proteinkanalerna in i rött, grönt och blått, vilket ledde till informationsförlust. Även efter denna anpassning gav de generella modellerna suddigare gränser mellan lager och missade finfördelade subregioner. I kontrast nådde mViSE, som utformats för att hantera många kanaler direkt och kodar varje kanal separat innan de kombineras, högre noggrannhet vid matchning mot kända hjärnatlasregioner. Den producerade skarpare kartor över kortikala lager och mer sammanhängande gemenskaper av liknande fläckar, vilket indikerar att dess representationer bättre speglar verklig biologisk organisation. 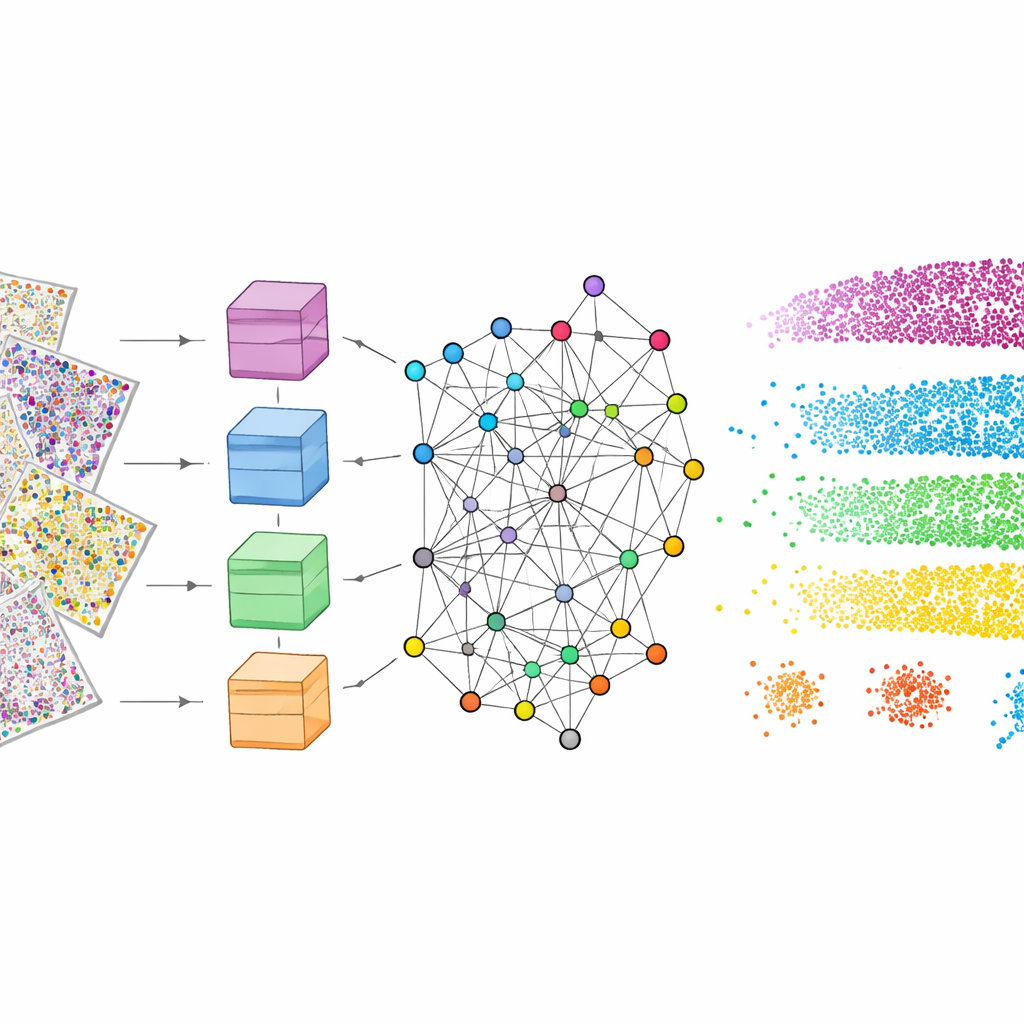
Ett nytt sätt att utforska den levande kartan
I grunden förvandlar mViSE enorma, mångfärgade hjärnbilder till en interaktiv karta som forskare kan söka visuellt. Istället för att tidsödande skripta varje analys kan forskare klicka på celler eller mikroomgivningar som fångar deras intresse och omedelbart se var liknande strukturer förekommer och hur deras proteinprofiler jämförs. Metoden kräver ingen manuell annotering under träning och skalar till mycket stora datamängder, vilket gör den till ett praktiskt tillskott i verktygslådan för rumslig proteomik. När bildtekniker lägger till ännu fler molekylära kanaler, och när liknande angreppssätt utvidgas till sjuka hjärnor och andra organ, kan verktyg som mViSE hjälpa till att omvandla rå bildkomplexitet till intuitiva, navigerbara vyer över vävnadsarkitektur—vilket för oss närmare att läsa hjärnans intrikata molekylära atlas som en sökbar karta.
Citering: Huang, L., Mills, R., Mandula, S. et al. mViSE: A visual search engine for analyzing multiplex IHC brain tissue images (spatial proteomics). Sci Rep 16, 10245 (2026). https://doi.org/10.1038/s41598-026-40620-5
Nyckelord: rumslig proteomik, hjärnavbildning, visuell sökmotor, multiplexmikroskopi, beräkningspatologi