Clear Sky Science · nl
mViSE: Een visuele zoekmachine voor het analyseren van multiplex IHC-hersenweefselbeelden (ruimtelijke proteomica)
Patronen zien in de hersenen
Moderne microscopen kunnen nu verbluffend gedetailleerde beelden vastleggen van volledige hersenplakjes, waarin tientallen verschillende eiwitten tegelijk zichtbaar zijn. Deze “multiplex”-beelden bieden aanwijzingen over hoe hersencellen zijn georganiseerd, hoe ze met elkaar communiceren en hoe ziekten deze patronen verstoren. Maar de beelden zijn zo groot en complex dat zelfs krachtige computers moeite hebben ze te begrijpen. Dit artikel introduceert mViSE, een visuele zoekmachine waarmee onderzoekers deze omvangrijke hersenbeelden kunnen verkennen door simpelweg op interessante cellen en buurten te klikken, in plaats van aangepaste code te schrijven.
Waarom grote hersenbeelden moeilijk te gebruiken zijn
Elk multiplex hersenbeeld is als een gigantische stadskaart waarop elk gebouw, elke straat en elke nutsleiding tegelijk in veel kleuren is gemarkeerd. Verschillende eiwitten wijzen op verschillende celtypes, celtoestanden, bloedvaten en bedradingpatronen. Traditionele analyseketens splitsen deze kaart op in een lange reeks geprogrammeerde stappen: het beeld opschonen, cellen detecteren, segmenteren, celtypes labelen en vervolgens resultaten per regio samenvatten. Hoewel krachtig, is deze aanpak star en moeilijk aanpasbaar wanneer nieuwe vragen opkomen—vooral voor de hersenen, waarvan de mix van neuronen, glia en bloedvaten enorme moleculaire en ruimtelijke complexiteit heeft. Wetenschappers hebben steeds vaker behoefte aan een flexibelere, interactieve manier om nieuwe vragen aan deze data te stellen zonder fulltime programmeur te hoeven worden.
Een zoekmachine voor hersencellen
mViSE behandelt een hersenbeeld meer als een online fotobibliotheek dan als een statische dataset. In plaats van elke analysetrap vooraf te definiëren, klikt de gebruiker op een cel of een klein weefselvlakje dat er interessant uitziet. Het systeem zoekt vervolgens in het hele hersenbeeld naar cellen of buurten die er visueel en functioneel vergelijkbaar uitzien over vele eiwitkanalen. De overeenkomsten worden direct in de hele-hersenen-weergave gemarkeerd en kunnen worden samengevat als eiwitexpressieprofielen. Dit stelt onderzoekers in staat snel te ontdekken waar vergelijkbare cellen of micro-omgevingen voorkomen, hersengebieden en corticale lagen af te bakenen en patronen tussen verschillende delen van de hersenen te vergelijken—alles gestuurd door visuele queries, niet door code. 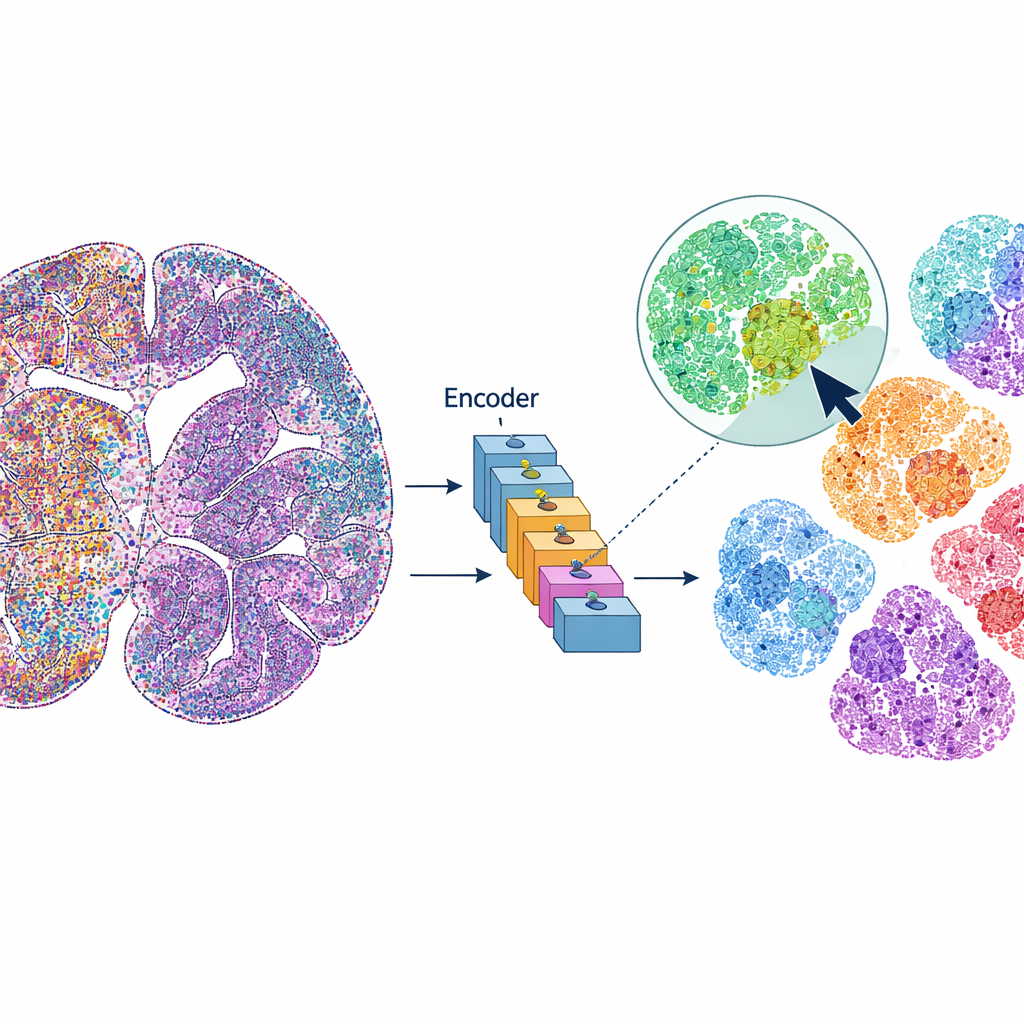
De computer leren weefsel te begrijpen
Om dit mogelijk te maken doorloopt mViSE eerst een leercyclus die volledig op de achtergrond plaatsvindt. De auteurs verdelen de vele eiwitkanalen in biologisch betekenisvolle panelen, zoals markers die celtypen, gliale cellen, zenuwvezels of bloedvaten benadrukken. Voor elk paneel kijkt een krachtige vision transformer—een modern diepleermodel—naar vele kleine vlakjes door de hersenen en leert elk vlakje te representeren als een punt in een hoge-dimensionale “kenmerkruimte”. Vlakjes die er hetzelfde uitzien en zich hetzelfde gedragen, zouden dicht bij elkaar in die ruimte moeten eindigen. Een informatie-theoretische community-detectiemethode groepeert vervolgens nabije punten in gemeenschappen die terugkerende patronen van weefselarchitectuur weerspiegelen. Belangrijk is dat dit leerproces zelfgesuperviseerd is: het vereist geen menselijke labeling, maar levert toch kleurgecodeerde kaarten op die visueel bevestigen dat bekende lagen en regio’s worden vastgelegd.
Inzoomen op cellen en buurten
Eenmaal getraind kan mViSE reageren op verschillende soorten queries. Voor zeer kleine vlakjes die individuele cellen bevatten, haalt het systeem de meest vergelijkbare cellen in de hele hersenen op en toont waar ze zich bevinden. De auteurs tonen aan dat het systeem betrouwbaar grote hersenceltypes vindt—zoals neuronen, astrocyten, oligodendrocyten, microglia en vasculaire cellen—maar ook specifiekere neuronale subtypes en zelfs celparen naast bloedvaten. Voor grotere vlakjes met meerdere cellen en lokale bedrading geeft mViSE de volledige gemeenschap van vergelijkbare buurten terug, die vaak bekende hersengebieden of banen volgen. Door informatie uit meerdere markerpanelen tegelijk te combineren, kan het ook subtiele verschillen tussen corticale lagen en kleine subregio’s onderscheiden die anders moeilijk te scheiden zijn.
Overtreft algemene AI-modellen
De onderzoekers vergeleken mViSE met verschillende state-of-the-art “foundation”-modellen die oorspronkelijk op grote verzamelingen natuurlijke of pathologiebeelden waren getraind. Omdat die modellen eenvoudige driekleurige beelden verwachten, moesten de vele eiwitkanalen worden samengedrukt tot rood, groen en blauw, wat verlies van informatie veroorzaakte. Zelfs na deze aanpassing produceerden die algemene modellen vager afgebakende lagen en misten fijnmazige subregio’s. In tegenstelling daarmee, mViSE—dat is ontworpen om vele kanalen direct te verwerken en elk kanaal afzonderlijk te coderen voordat ze worden gecombineerd—bereikte hogere nauwkeurigheid bij het matchen van bekende hersenatlas-regio’s. Het leverde scherpere kaarten van corticale lagen en meer coherente gemeenschappen van vergelijkbare vlakjes, wat aangeeft dat zijn representaties de echte biologische organisatie beter weerspiegelen. 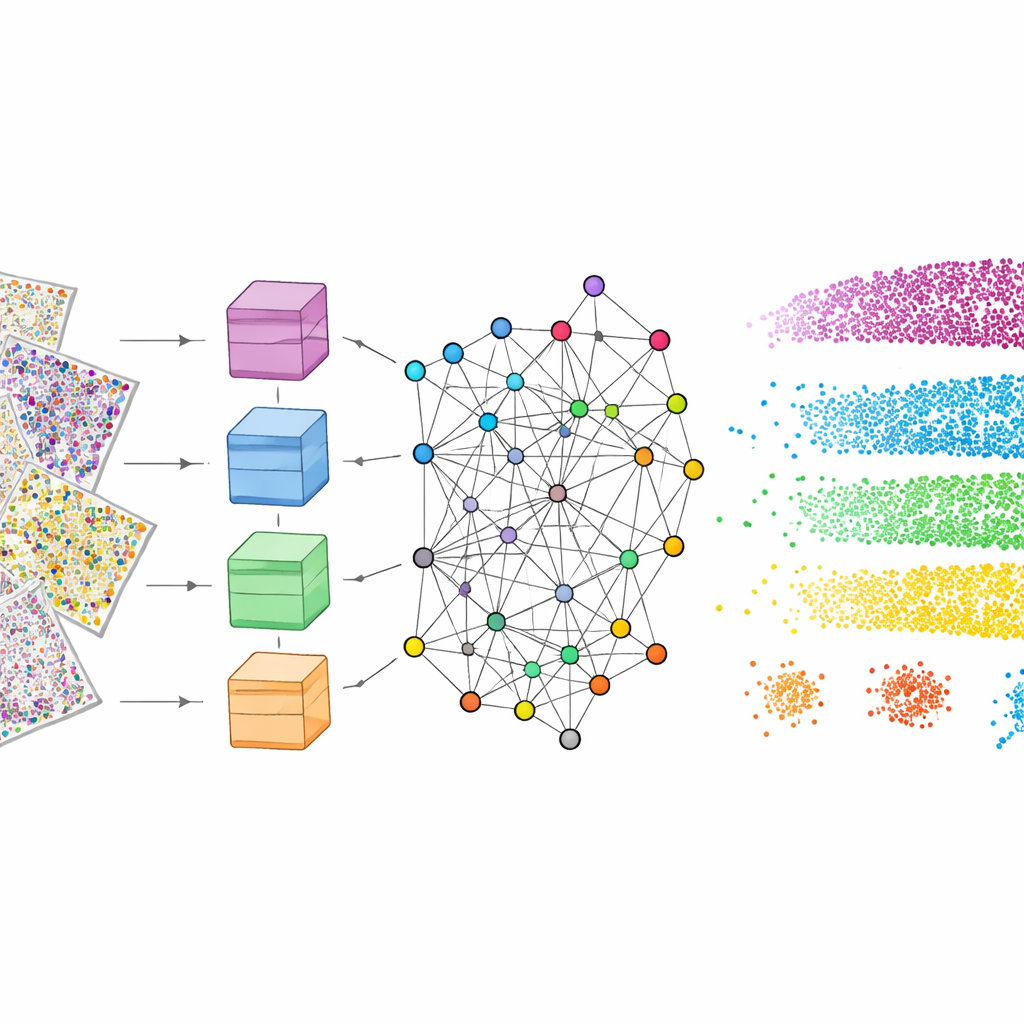
Een nieuwe manier om de levende kaart te verkennen
In wezen verandert mViSE enorme, veelkleurige hersenbeelden in een interactieve kaart die onderzoekers visueel kunnen doorzoeken. In plaats van elke analyse zorgvuldig te scripten, kunnen wetenschappers klikken op cellen of micro-omgevingen die hun aandacht trekken en onmiddellijk zien waar vergelijkbare structuren voorkomen en hoe hun eiwitprofielen zich verhouden. De methode vereist geen handmatige annotatie tijdens de training en schaalt naar zeer grote datasets, wat het tot een praktische aanvulling op het ruimtelijke proteomica-gereedschap maakt. Naarmate beeldvormingstechnologieën nog meer moleculaire kanalen toevoegen en vergelijkbare benaderingen worden uitgebreid naar zieke hersenen en andere organen, kunnen tools zoals mViSE helpen ruwe beeldcomplexiteit om te zetten in intuïtieve, navigeerbare weergaven van weefselarchitectuur—en ons dichter brengen bij het lezen van de ingewikkelde moleculaire atlas van de hersenen als een doorzoekbare kaart.
Bronvermelding: Huang, L., Mills, R., Mandula, S. et al. mViSE: A visual search engine for analyzing multiplex IHC brain tissue images (spatial proteomics). Sci Rep 16, 10245 (2026). https://doi.org/10.1038/s41598-026-40620-5
Trefwoorden: ruimtelijke proteomica, hersenbeeldvorming, visuele zoekmachine, multiplexmicroscopie, computationele pathologie