Clear Sky Science · it
mViSE: un motore di ricerca visivo per analizzare immagini di tessuto cerebrale con IHC multiplex (proteomica spaziale)
Vedere i pattern nel cervello
I microscopi moderni possono ora acquisire immagini straordinariamente dettagliate di intere sezioni cerebrali, mostrando decine di proteine diverse contemporaneamente. Queste immagini “multiplex” promettono indizi su come le cellule cerebrali sono organizzate, come comunicano tra loro e come le malattie alterano questi schemi. Ma le immagini sono così grandi e complesse che anche i computer potenti faticano a interpretarle. Questo articolo presenta mViSE, un motore di ricerca visivo che permette ai ricercatori di esplorare queste vaste immagini cerebrali cliccando semplicemente sulle cellule e sui vicinati di interesse, anziché scrivere codice personalizzato.
Perché le grandi immagini cerebrali sono difficili da usare
Ogni immagine cerebrale multiplex è come una grande mappa cittadina in cui ogni edificio, strada e linea di servizio è etichettata in molti colori contemporaneamente. Proteine diverse segnalano tipi cellulari differenti, stati cellulari, vasi sanguigni e schemi di connessione. Le pipeline di analisi tradizionali spezzettano questa mappa in una lunga catena di passaggi programmati: pulire l’immagine, rilevare le cellule, segmentarle, etichettare i tipi cellulari e poi riassumere i risultati per regione. Pur essendo potenti, questi approcci sono rigidi e difficili da adattare quando sorgono nuove domande—soprattutto per il cervello, la cui mescolanza di neuroni, cellule gliali e vasi ha un’enorme complessità molecolare e spaziale. I ricercatori hanno sempre più bisogno di un modo interattivo e flessibile per porre nuove domande a questi dati senza diventare programmatori a tempo pieno.
Un motore di ricerca per le cellule cerebrali
mViSE tratta un’immagine cerebrale più come una libreria fotografica online che come un dataset statico. Invece di predefinire ogni passaggio di analisi, l’utente clicca su una cellula o su una piccola porzione di tessuto che sembra interessante. Il sistema quindi cerca nell’intera immagine cerebrale cellule o vicinati che appaiono e “comportano” in modo simile attraverso molti canali proteici. Le corrispondenze vengono evidenziate direttamente nella vista dell’intero cervello e possono essere riassunte come profili di espressione proteica. Questo permette ai ricercatori di scoprire rapidamente dove compaiono cellule o microambienti simili, delineare regioni cerebrali e strati corticali e confrontare schemi in diverse parti del cervello—il tutto guidato da query visive, non da codice. 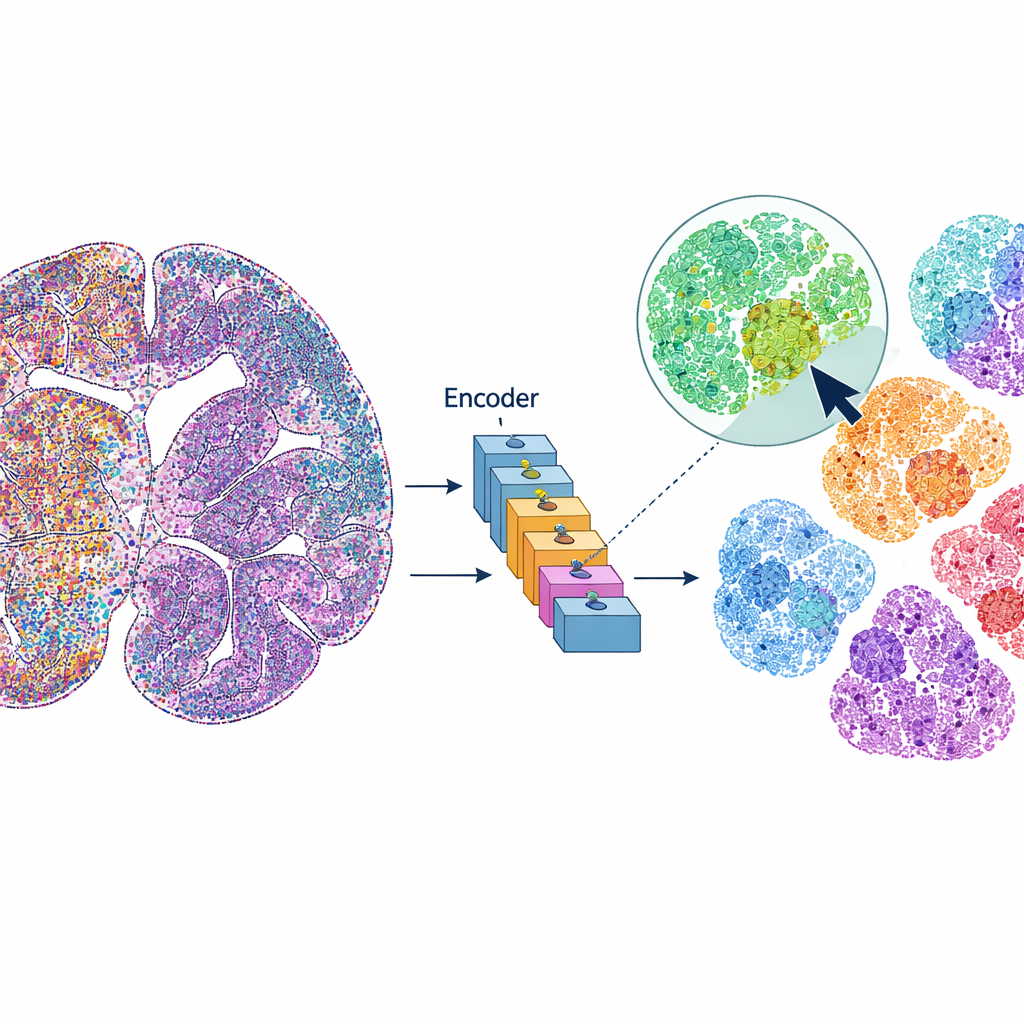
Insegnare al computer a comprendere il tessuto
Per farlo funzionare, mViSE passa prima attraverso una fase di apprendimento interamente in background. Gli autori suddividono i numerosi canali proteici in pannelli biologicamente significativi, come marcatori che evidenziano tipi cellulari, cellule gliali, fibre nervose o vasi sanguigni. Per ciascun pannello, un potente transformer visivo—un moderno modello di deep learning—analizza molte piccole patch in tutto il cervello e impara a rappresentare ogni patch come un punto in uno spazio di caratteristiche ad alta dimensionalità. Le patch che appaiono e si comportano in modo simile dovrebbero ritrovarsi vicine in questo spazio. Un metodo di rilevamento di comunità basato sull’informazione raggruppa poi i punti vicini in comunità che riflettono pattern ripetuti nell’architettura tissutale. È importante che questo apprendimento sia self-supervised: non richiede etichettature umane, ma produce comunque mappe codificate a colori che confermano visivamente che strati e regioni note vengono catturati.
Zoom su cellule e vicinati
Una volta addestrato, mViSE può rispondere a diversi tipi di query. Per patch molto piccole contenenti singole cellule, recupera le cellule più simili in tutto il cervello e mostra dove sono localizzate. Gli autori dimostrano che il sistema trova in modo affidabile i principali tipi cellulari cerebrali—come neuroni, astrociti, oligodendrociti, microglia e cellule vascolari—nonché sottotipi neuronali più specifici e persino coppie di cellule situate accanto ai vasi sanguigni. Per patch più grandi che includono più cellule e circuiti locali, mViSE restituisce l’intera comunità di vicinati simili, spesso tracciando regioni cerebrali o tratti noti. Combinando informazioni provenienti da diversi pannelli di marcatori contemporaneamente, può anche discriminare sottili differenze tra strati corticali e piccole subregioni che altrimenti sono difficili da distinguere.
Superare i modelli di IA di uso generale
I ricercatori hanno confrontato mViSE con diversi modelli “foundation” all’avanguardia originariamente addestrati su grandi raccolte di immagini naturali o di patologia. Poiché quei modelli si aspettano immagini a tre colori, i molti canali proteici hanno dovuto essere compressi in rosso, verde e blu, causando perdita di informazione. Anche dopo questa adattazione, questi modelli generali hanno prodotto confini meno definiti tra gli strati e hanno mancato subregioni fini. Al contrario, mViSE, progettato per gestire molti canali direttamente e a codificare ciascun canale separatamente prima di combinarli, ha raggiunto una maggiore accuratezza nell’abbinamento con regioni note dell’atlas cerebrale. Ha prodotto mappe più nitide degli strati corticali e comunità di patch più coerenti, indicando che le sue rappresentazioni riflettono meglio l’organizzazione biologica reale. 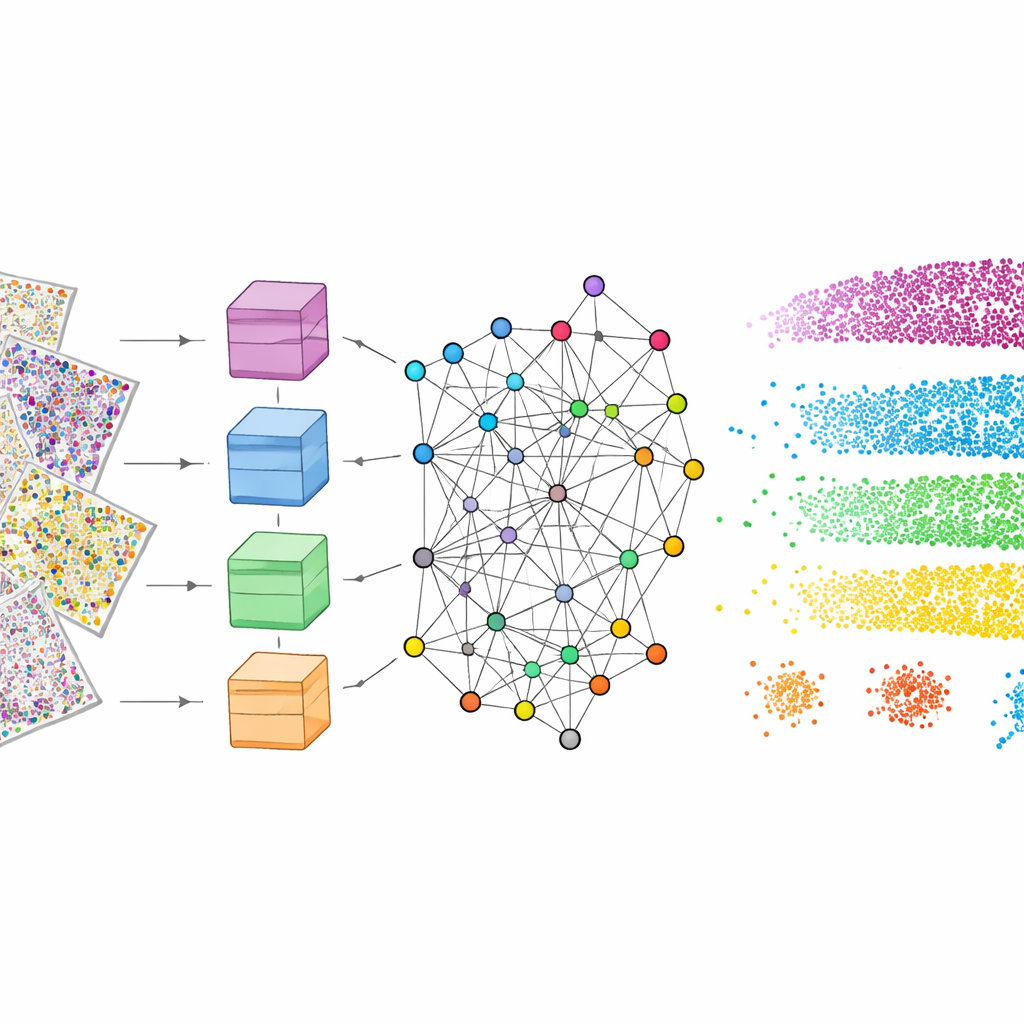
Un nuovo modo di esplorare la mappa vivente
In sostanza, mViSE trasforma immagini cerebrali enormi e multicolore in una mappa interattiva che i ricercatori possono esplorare visivamente. Invece di scrivere laboriosamente ogni analisi, gli scienziati possono cliccare su cellule o microambienti che attirano la loro attenzione e vedere istantaneamente dove compaiono strutture simili e come si confrontano i loro profili proteici. Il metodo non richiede annotazioni manuali durante l’addestramento e scala a dataset molto grandi, rendendolo un'aggiunta pratica agli strumenti della proteomica spaziale. Man mano che le tecnologie di imaging aggiungeranno ancora più canali molecolari e che approcci simili verranno estesi a cervelli malati e altri organi, strumenti come mViSE potrebbero contribuire a convertire la complessità grezza delle immagini in viste intuitive e navigabili dell’architettura tissutale—avvicinandoci alla lettura dell’intricata mappa molecolare del cervello come se fosse una mappa ricercabile.
Citazione: Huang, L., Mills, R., Mandula, S. et al. mViSE: A visual search engine for analyzing multiplex IHC brain tissue images (spatial proteomics). Sci Rep 16, 10245 (2026). https://doi.org/10.1038/s41598-026-40620-5
Parole chiave: proteomica spaziale, imaging cerebrale, motore di ricerca visivo, microscopia multiplex, patologia computazionale