Clear Sky Science · ja
mViSE: 多重IHC脳組織画像(空間プロテオミクス)を解析するビジュアル検索エンジン
脳におけるパターンの可視化
現代の顕微鏡は、数十種類のタンパク質を同時に示す、脳スライス全体の驚くほど詳細な画像を取得できるようになりました。こうした「多重」画像は、脳細胞の配置や相互作用、病気がどのようにこれらのパターンを乱すかについての手がかりを与えてくれます。しかし画像は非常に巨大で複雑なため、強力なコンピュータでも理解するのが難しいことが多いのです。本稿は mViSE を紹介します。これは研究者がカスタムコードを書く代わりに、関心のある細胞や周辺領域をクリックするだけで広大な脳画像を探索できるビジュアル検索エンジンです。
なぜ大規模な脳画像は扱いにくいのか
各多重脳画像は、色とりどりにラベル付けされた建物、道路、インフラが満載の巨大な都市地図のようなものです。異なるタンパク質は異なる細胞型、細胞状態、血管、配線パターンを示します。従来の解析パイプラインはこの地図を一連の手続きに分解します:画像を整え、細胞を検出し、セグメント化して細胞型をラベリングし、領域ごとに結果を要約する。強力ではありますが、このアプローチは堅牢性に欠け、新しい問いが生じたときに適応しにくい、特にニューロン、グリア、血管が入り混じる脳では分子的・空間的複雑性が極めて高いためです。研究者はフルタイムのプログラマにならずにこれらのデータに対して新しい問いを柔軟に投げかけられる、より対話的な手法をますます必要としています。
脳細胞のための検索エンジン
mViSE は脳画像を静的データセットというよりもオンライン写真ライブラリのように扱います。すべての解析ステップを事前定義するのではなく、ユーザーが興味のある細胞や小さな組織パッチをクリックします。システムはその後、全脳画像を検索して多くのタンパク質チャネルにわたって見た目や“振る舞い”が類似する細胞や近傍を探します。マッチした箇所は全脳ビュー上で直接ハイライトされ、タンパク質発現プロファイルとして要約できます。これにより、研究者は類似した細胞や微小環境がどこに現れるかを迅速に突き止め、脳領域や皮質層を区切り、脳の異なる部分間でパターンを比較できます——コードではなく視覚的クエリで駆動されるのです。 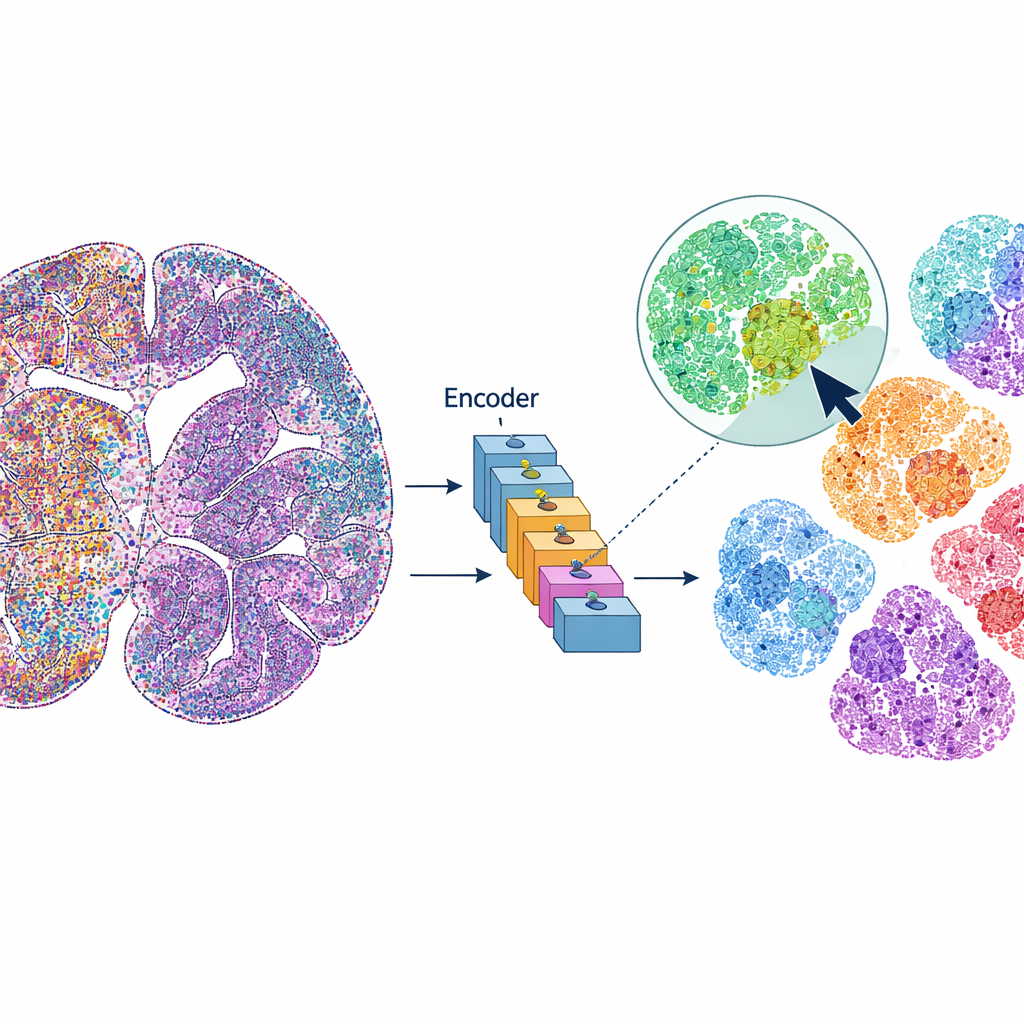
組織を理解するようコンピュータを教える
これを実現するために、mViSE はまずバックグラウンドで学習フェーズを実行します。著者らは多くのタンパク質チャネルを、生物学的に意味のあるパネル(細胞型を示すマーカー、グリア、神経線維、血管など)に分けます。各パネルについて、強力なビジョントランスフォーマー(現代の深層学習モデル)が脳全体の多くの小さなパッチを観察し、各パッチを高次元の“特徴空間”の点として表現する方法を学びます。見た目や振る舞いが似たパッチはこの空間で互いに近くなるはずです。情報理論に基づくコミュニティ検出法は、近接する点を組織内の繰り返しパターンを反映するコミュニティにまとめます。重要なのは、この学習が自己教師ありで行われ、人手によるラベル付けを必要としない一方で、既知の層や領域が捉えられていることを視覚的に確認できる色分けマップを生成する点です。
細胞と近傍へのズーム
一度学習されると、mViSE はさまざまなタイプのクエリに応答できます。単一細胞を含む非常に小さなパッチでは、脳全体から最も類似した細胞を取得してその配置を示します。著者らは、このシステムがニューロン、アストロサイト、オリゴデンドロサイト、ミクログリア、血管細胞といった主要な脳細胞型を確実に見つけること、さらにより特定の神経サブタイプや血管隣接の細胞ペアさえ検出することを示しています。複数の細胞と局所配線を含むより大きなパッチでは、mViSE は類似した近隣の完全なコミュニティを返し、既知の脳領域や神経路をたどることが多いです。複数のマーカーパネルからの情報を同時に組み合わせることで、皮質層間や小さなサブ領域の微妙な差異を判別することも可能になります。
汎用AIモデルを上回る性能
研究者らは mViSE を、多数の自然画像や病理画像で事前学習された最新の“ファンデーション”モデル数種と比較しました。これらのモデルは三色の単純な画像を想定しているため、多数のタンパク質チャネルを赤・緑・青に圧縮する必要があり、情報の損失が生じます。この適応を行っても、汎用モデルは層間の境界がぼやけ、小領域の微細な違いを見逃す傾向がありました。これに対して mViSE は、多数チャネルを直接扱うよう設計され、各チャネルを個別に符号化してから統合するため、既知の脳アトラス領域とのマッチング精度が高くなりました。皮質層のより鮮明なマップと一貫性のある類似パッチ群を生成し、その表現が生物学的な組織をより正確に反映していることを示しています。 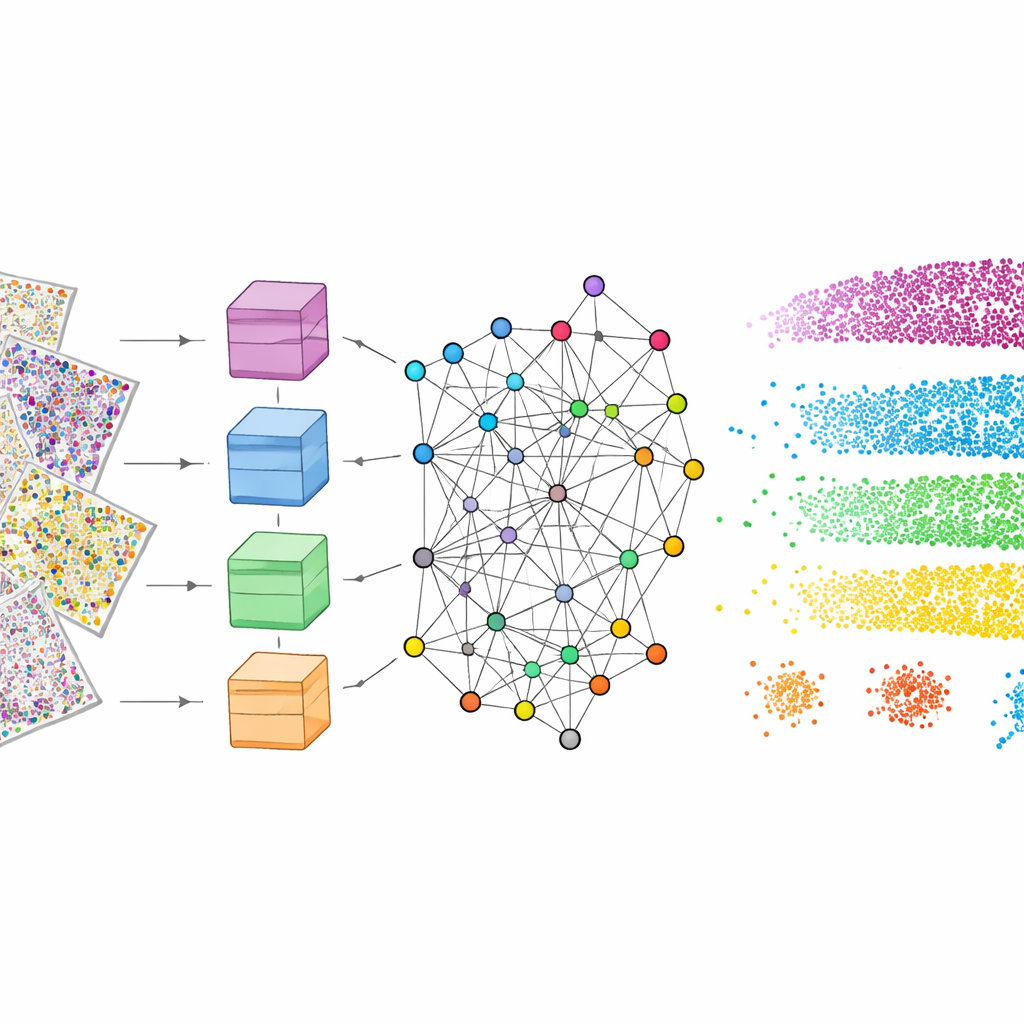
生きた地図を探索する新しい方法
本質的に、mViSE は巨大で多色の脳画像を研究者が視覚的に検索できるインタラクティブな地図に変換します。すべての解析を手作業でスクリプト化する代わりに、研究者は目を引く細胞や微小環境をクリックし、類似構造がどこに現れるか、タンパク質プロファイルがどう比較されるかを瞬時に確認できます。訓練時に手動注釈を必要とせず、非常に大きなデータセットに拡張可能であるため、空間プロテオミクスのツールキットに実用的に追加できる方法です。イメージング技術がさらに多くの分子チャネルを追加し、同様の手法が疾患脳や他の臓器にも拡張されるにつれて、mViSE のようなツールは生の画像の複雑さを直感的でナビゲートしやすい組織地図に変換する助けとなり、複雑な分子アトラスを検索可能な地図として読み解くことに近づけるでしょう。
引用: Huang, L., Mills, R., Mandula, S. et al. mViSE: A visual search engine for analyzing multiplex IHC brain tissue images (spatial proteomics). Sci Rep 16, 10245 (2026). https://doi.org/10.1038/s41598-026-40620-5
キーワード: 空間プロテオミクス, 脳イメージング, ビジュアル検索エンジン, 多重顕微鏡法, 計算病理学