Clear Sky Science · pt
mViSE: Um mecanismo de busca visual para analisar imagens cerebrais multiplex de IHC (proteômica espacial)
Vendo Padrões no Cérebro
Microscópios modernos conseguem capturar imagens de fatias cerebrais inteiras com nível de detalhe impressionante, mostrando dezenas de proteínas diferentes ao mesmo tempo. Essas imagens “multiplex” prometem pistas sobre como as células cerebrais se organizam, como se comunicam e como doenças perturbam esses padrões. Mas as imagens são tão grandes e complexas que mesmo computadores potentes têm dificuldade em interpretá-las. Este artigo apresenta o mViSE, um mecanismo de busca visual que permite aos pesquisadores explorar essas vastas imagens cerebrais clicando em células e vizinhanças de interesse, em vez de escrever código personalizado.
Por que Imagens Cerebrais Grandes São Difíceis de Usar
Cada imagem cerebral multiplex é como um mapa urbano gigantesco onde cada edifício, rua e infraestrutura aparece rotulado em muitas cores ao mesmo tempo. Diferentes proteínas marcam tipos celulares, estados celulares, vasos sanguíneos e padrões de conexões. Pipelines analíticos tradicionais quebram esse mapa em uma longa cadeia de etapas programadas: limpar a imagem, detectar células, segmentá-las, rotular tipos celulares e então resumir resultados por região. Embora poderosa, essa abordagem é rígida e difícil de adaptar quando surgem novas perguntas—especialmente no cérebro, cuja mistura de neurônios, glia e vasos sanguíneos tem imensa complexidade molecular e espacial. Cientistas precisam cada vez mais de uma forma interativa e flexível de formular novas perguntas a esses dados sem se tornarem programadores em tempo integral.
Um Mecanismo de Busca para Células Cerebrais
O mViSE trata uma imagem cerebral mais como uma biblioteca online de fotos do que como um conjunto de dados estático. Em vez de pré-definir cada etapa da análise, o usuário clica em uma célula ou em um pequeno pedaço de tecido que pareça interessante. O sistema então procura na imagem cerebral inteira por células ou vizinhanças que se pareçam e “se comportem” de maneira semelhante através de muitos canais proteicos. As correspondências são destacadas diretamente na visão de todo o cérebro e podem ser resumidas como perfis de expressão proteica. Isso permite que os pesquisadores descubram rapidamente onde células ou microambientes semelhantes aparecem, delineiem regiões cerebrais e camadas corticais e comparem padrões em diferentes partes do cérebro—tudo guiado por consultas visuais, não por código. 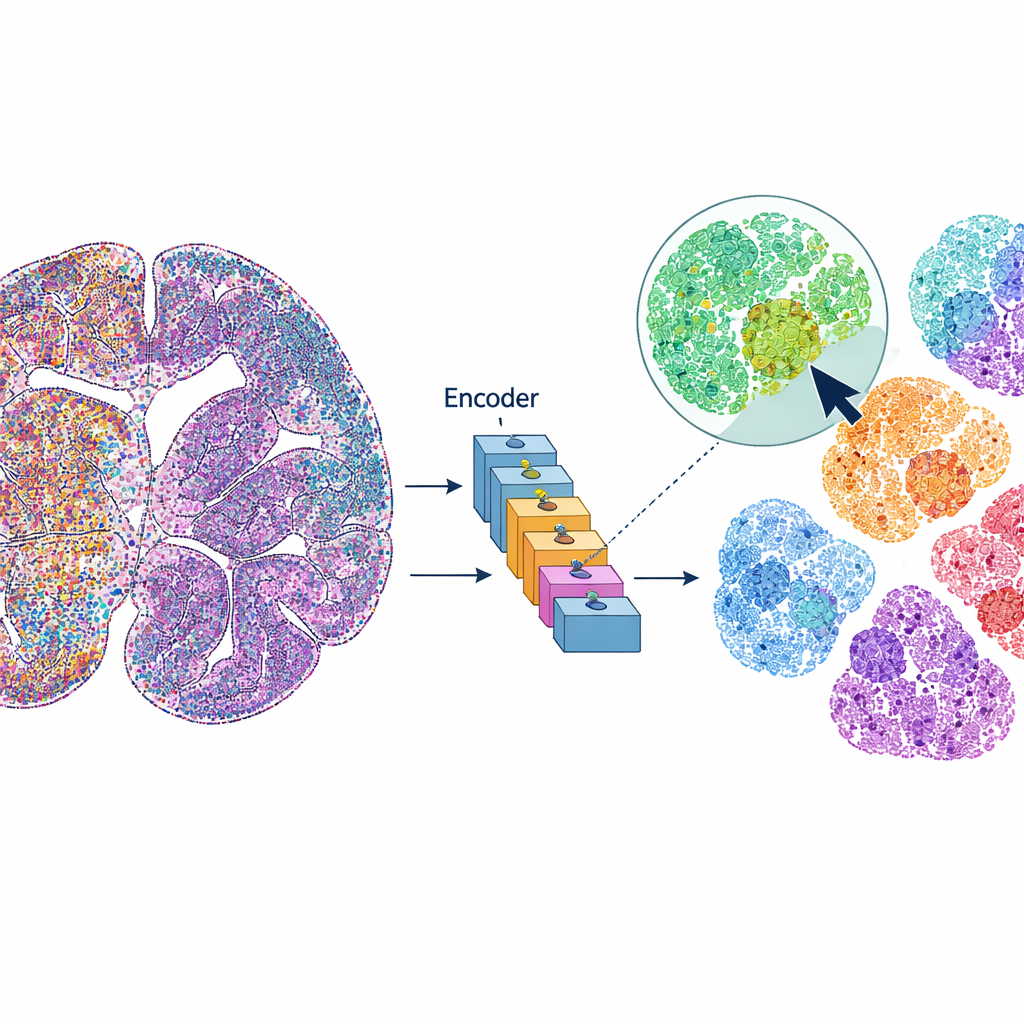
Ensinando o Computador a Entender o Tecido
Para que isso funcione, o mViSE primeiro passa por uma fase de aprendizado inteiramente em segundo plano. Os autores dividem os muitos canais proteicos em painéis biologicamente significativos, como marcadores que destacam tipos celulares, células gliais, fibras nervosas ou vasos sanguíneos. Para cada painel, um vision transformer poderoso—um modelo moderno de deep learning—analisa muitos pequenos patchs por todo o cérebro e aprende a representar cada patch como um ponto em um “espaço de características” de alta dimensão. Patchs que se parecem e se comportam de forma semelhante tendem a ficar próximos nesse espaço. Um método de detecção de comunidades baseado em teoria da informação agrupa então pontos próximos em comunidades que refletem padrões repetitivos da arquitetura do tecido. Importante: esse aprendizado é auto-supervisionado—não requer rotulagem humana—mas ainda produz mapas coloridos que confirmam visualmente que camadas e regiões conhecidas estão sendo capturadas.
Dando Zoom em Células e Vizinhanças
Uma vez treinado, o mViSE pode responder a diferentes tipos de consultas. Para patchs muito pequenos contendo células individuais, ele recupera as células mais semelhantes por todo o cérebro e mostra onde estão localizadas. Os autores demonstram que o sistema encontra de forma confiável os principais tipos celulares cerebrais—como neurônios, astrócitos, oligodendrócitos, micróglias e células vasculares—além de subtipos neuronais mais específicos e até pares de células localizados próximos a vasos sanguíneos. Para patchs maiores que incluem múltiplas células e conexões locais, o mViSE retorna a comunidade completa de vizinhanças semelhantes, muitas vezes traçando regiões cerebrais ou tratos conhecidos. Ao combinar informações de vários painéis de marcadores ao mesmo tempo, ele também consegue distinguir diferenças sutis entre camadas corticais e pequenas sub-regiões que seriam difíceis de separar de outra forma.
Superando Modelos de IA de Uso Geral
Os pesquisadores compararam o mViSE com vários modelos de “foundation” de última geração originalmente treinados em grandes coleções de imagens naturais ou de patologia. Como esses modelos esperam imagens simples com três cores, os muitos canais proteicos tiveram que ser comprimidos em vermelho, verde e azul, causando perda de informação. Mesmo após essa adaptação, esses modelos gerais produziram limites mais difusos entre camadas e perderam sub-regiões finamente definidas. Em contraste, o mViSE, projetado para lidar com muitos canais diretamente e que codifica cada canal separadamente antes de combiná-los, alcançou maior precisão ao corresponder regiões conhecidas de atlas cerebrais. Ele gerou mapas mais nítidos das camadas corticais e comunidades mais coerentes de patchs semelhantes, indicando que suas representações refletem melhor a organização biológica real. 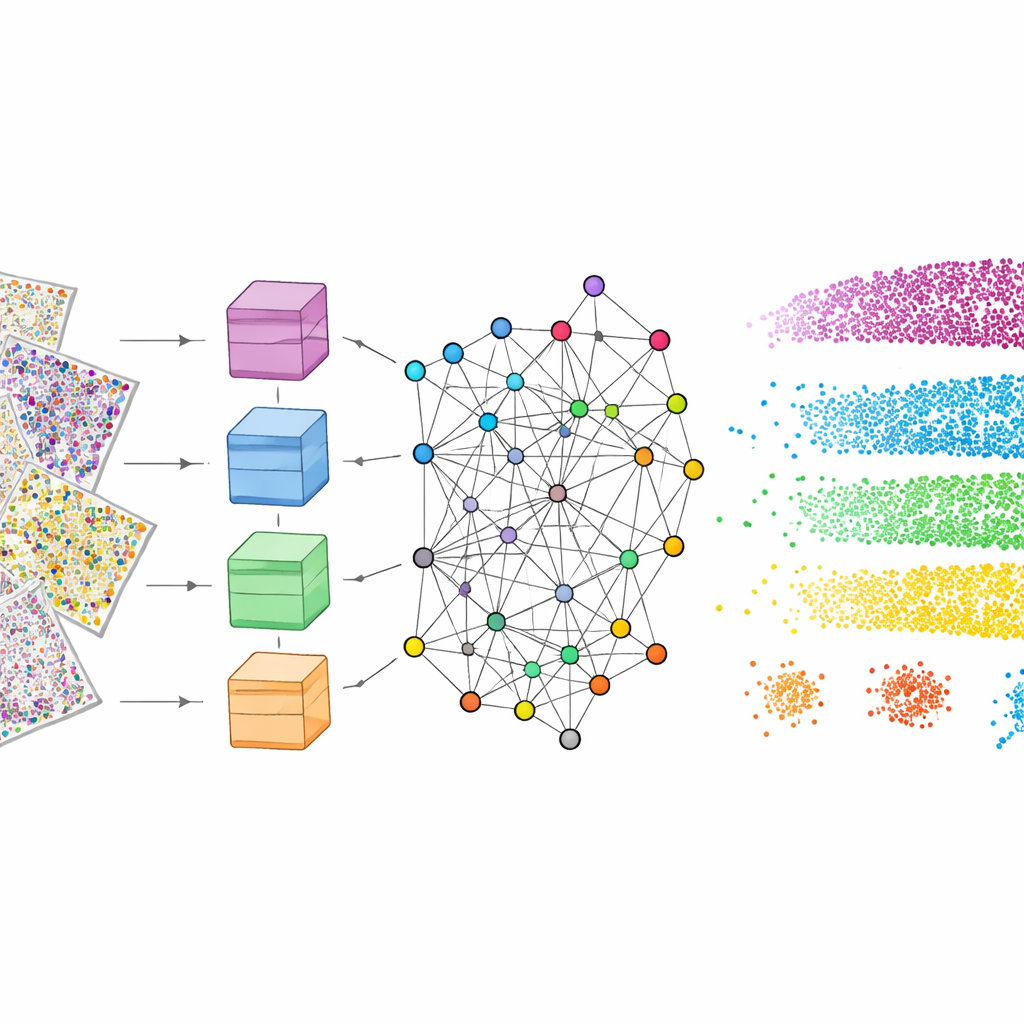
Uma Nova Forma de Explorar o Mapa Vivo
Em essência, o mViSE transforma imagens cerebrais enormes e multicoloridas em um mapa interativo que os pesquisadores podem buscar visualmente. Em vez de escrever exaustivamente scripts para cada análise, os cientistas podem clicar em células ou microambientes que chamem a atenção e ver instantaneamente onde estruturas semelhantes aparecem e como seus perfis proteicos se comparam. O método não requer anotação manual durante o treinamento e escala para conjuntos de dados muito grandes, tornando-se uma adição prática ao conjunto de ferramentas da proteômica espacial. À medida que as tecnologias de imagem adicionam ainda mais canais moleculares, e abordagens semelhantes são estendidas a cérebros doentes e outros órgãos, ferramentas como o mViSE poderão ajudar a converter a complexidade bruta das imagens em visões intuitivas e navegáveis da arquitetura do tecido—aproximando-nos de ler o intricado atlas molecular do cérebro como um mapa pesquisável.
Citação: Huang, L., Mills, R., Mandula, S. et al. mViSE: A visual search engine for analyzing multiplex IHC brain tissue images (spatial proteomics). Sci Rep 16, 10245 (2026). https://doi.org/10.1038/s41598-026-40620-5
Palavras-chave: proteômica espacial, imagens cerebrais, mecanismo de busca visual, microscopia multiplex, patologia computacional