Clear Sky Science · pl
mViSE: Wyszukiwarka wizualna do analizy wieloparametrowych obrazów mózgu z IHC (proteomika przestrzenna)
Dostrzeganie wzorców w mózgu
Nowoczesne mikroskopy potrafią dziś rejestrować zapierająco szczegółowe obrazy całych przekrojów mózgu, pokazując jednocześnie dziesiątki różnych białek. Te „multipleksowe” obrazy obiecują wskazówki dotyczące organizacji komórek mózgowych, sposobów ich komunikacji oraz tego, jak choroba zaburza te wzorce. Jednak obrazy są tak ogromne i złożone, że nawet wydajne komputery mają trudności z ich interpretacją. W artykule przedstawiono mViSE — wyszukiwarkę wizualną, która pozwala badaczom eksplorować te rozległe obrazy mózgu przez proste klikanie komórek i interesujących obszarów tkanki, zamiast pisania specjalistycznego kodu.
Dlaczego duże obrazy mózgu są trudne w użyciu
Każdy multipleksowy obraz mózgu przypomina olbrzymią mapę miasta, na której każdy budynek, ulica i sieć jest oznaczona wieloma kolorami jednocześnie. Różne białka oznaczają rozmaite typy komórek, stany komórkowe, naczynia krwionośne i wzory połączeń. Tradycyjne pipeline’y analityczne rozbijają tę mapę na długi łańcuch zaprogramowanych kroków: oczyszczanie obrazu, wykrywanie komórek, segmentacja, oznaczanie typów komórek i podsumowanie wyników według regionów. Choć to potężne podejście, jest sztywne i trudne do adaptacji przy nowych pytaniach — zwłaszcza w przypadku mózgu, którego mieszanka neuronów, gleju i naczyń ma ogromną złożoność molekularną i przestrzenną. Naukowcy coraz częściej potrzebują bardziej elastycznego, interaktywnego sposobu zadawania pytań tym danym, bez konieczności zostawania programistami na pełen etat.
Wyszukiwarka komórek mózgu
mViSE traktuje obraz mózgu bardziej jak internetową bibliotekę zdjęć niż statyczny zestaw danych. Zamiast uprzednio definiować każdy krok analizy, użytkownik klika komórkę lub mały fragment tkanki, który wydaje się interesujący. System wyszukuje wówczas w całym obrazie komórki lub otoczenia, które wyglądają i „zachowują się” podobnie w wielu kanałach białkowych. Dopasowania są podświetlane bezpośrednio na widoku całego mózgu i można je podsumować jako profile ekspresji białek. Pozwala to badaczom szybko odkryć, gdzie pojawiają się podobne komórki lub mikrośrodowiska, wyznaczać regiony mózgu i warstwy korowe oraz porównywać wzorce w różnych częściach mózgu — wszystko sterowane zapytaniami wizualnymi, nie kodem. 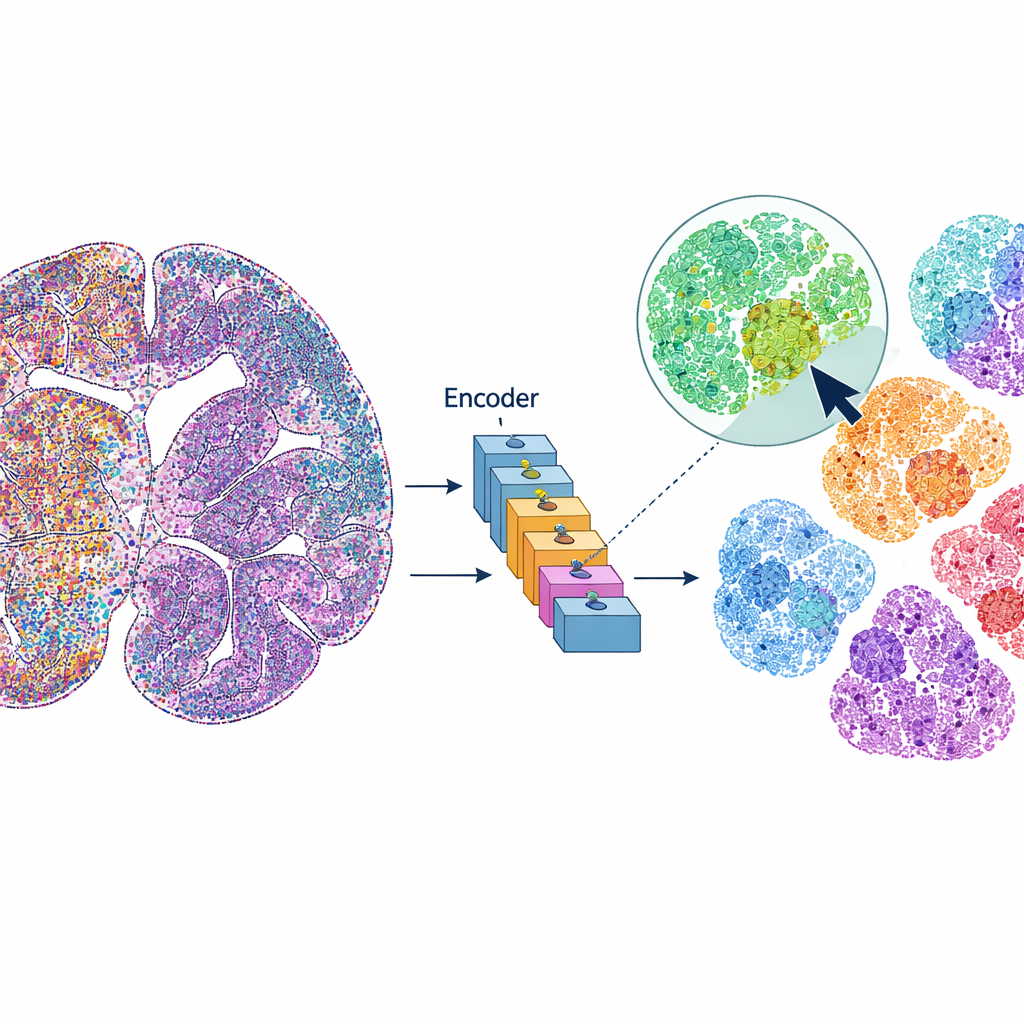
Nauczanie komputera rozumienia tkanki
Aby to zadziałało, mViSE najpierw przechodzi etap uczenia całkowicie w tle. Autorzy dzielą liczne kanały białkowe na biologicznie znaczące panele, takie jak markery uwidaczniające typy komórek, komórki glejowe, włókna nerwowe czy naczynia krwionośne. Dla każdego panelu potężny vision transformer — nowoczesny model głębokiego uczenia — analizuje wiele małych fragmentów w całym mózgu i uczy się reprezentować każdy fragment jako punkt w wysokowymiarowej „przestrzeni cech”. Fragmenty, które wyglądają i zachowują się podobnie, powinny znaleźć się blisko siebie w tej przestrzeni. Metoda wykrywania wspólnot oparta na teorii informacji grupuje następnie pobliskie punkty w wspólnoty odzwierciedlające powtarzające się wzorce architektury tkanki. Co ważne, to uczenie jest samonadzorowane: nie wymaga ręcznego oznaczania przez ludzi, a mimo to generuje mapy kolorystyczne, które wizualnie potwierdzają, że znane warstwy i regiony są wychwytywane.
Zbliżanie się do komórek i sąsiedztw
Po treningu mViSE potrafi odpowiadać na różne typy zapytań. Dla bardzo małych fragmentów zawierających pojedyncze komórki wyszukuje najbardziej podobne komórki w całym mózgu i pokazuje, gdzie się znajdują. Autorzy wykazują, że system niezawodnie znajduje główne typy komórek mózgowych — takie jak neurony, astrocyty, oligodendrocyty, mikroglej i komórki naczyniowe — oraz bardziej specyficzne podtypy neuronalne, a nawet pary komórek położone obok naczyń krwionośnych. Dla większych fragmentów obejmujących wiele komórek i lokalne połączenia mViSE zwraca całą wspólnotę podobnych sąsiedztw, często wyznaczając znane regiony mózgu lub pasma. Łącząc informacje z kilku paneli markerów jednocześnie, potrafi też rozróżnić subtelne różnice między warstwami korowymi i małymi podregionami, które w innym wypadku trudno odróżnić.
Przewyższając ogólnego przeznaczenia modele AI
Naukowcy porównali mViSE z kilkoma nowoczesnymi modelami „foundation” pierwotnie trenowanymi na dużych zbiorach zdjęć naturalnych lub patologicznych. Ponieważ te modele oczekują prostych, trójkolorowych obrazów, liczne kanały białkowe musiały zostać skompresowane do czerwonego, zielonego i niebieskiego, co powodowało utratę informacji. Nawet po takiej adaptacji te ogólne modele generowały bardziej rozmyte granice między warstwami i pomijały drobne podregiony. W przeciwieństwie do nich mViSE, zaprojektowany do obsługi wielu kanałów bezpośrednio i kodujący każdy kanał osobno przed ich połączeniem, osiągnął wyższą dokładność w dopasowywaniu znanych regionów z atlasu mózgu. Wygenerował ostrzejsze mapy warstw korowych i bardziej spójne wspólnoty podobnych fragmentów, co wskazuje, że jego reprezentacje lepiej odzwierciedlają rzeczywistą organizację biologiczną. 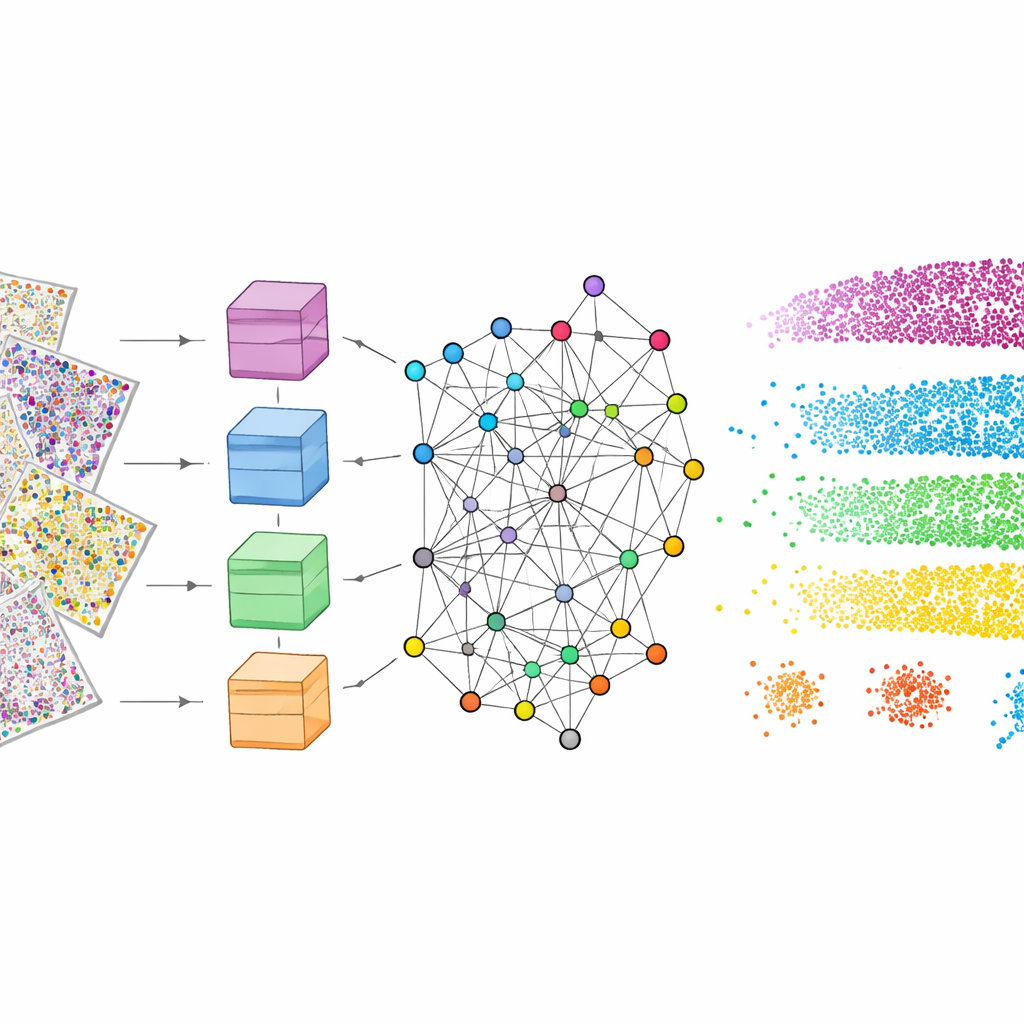
Nowy sposób eksploracji żywej mapy
W istocie mViSE zamienia olbrzymie, wielokolorowe obrazy mózgu w interaktywną mapę, którą badacze mogą przeszukiwać wzrokowo. Zamiast mozolnie skryptować każdą analizę, naukowcy mogą klikać komórki lub mikrośrodowiska, które przyciągną ich uwagę, i natychmiast zobaczyć, gdzie podobne struktury występują oraz jak porównują się ich profile białkowe. Metoda nie wymaga ręcznej adnotacji podczas treningu i skaluje się do bardzo dużych zestawów danych, co czyni ją praktycznym dodatkiem do narzędzi proteomiki przestrzennej. W miarę jak technologie obrazowania dodadzą jeszcze więcej kanałów molekularnych, a podobne podejścia będą rozszerzane na mózgi w stanie chorobowym i inne organy, narzędzia takie jak mViSE mogą pomóc przekształcić surową złożoność obrazów w intuicyjne, nawigowalne widoki architektury tkanek — przybliżając nas do odczytywania skomplikowanego molekularnego atlasu mózgu jak wyszukiwalnej mapy.
Cytowanie: Huang, L., Mills, R., Mandula, S. et al. mViSE: A visual search engine for analyzing multiplex IHC brain tissue images (spatial proteomics). Sci Rep 16, 10245 (2026). https://doi.org/10.1038/s41598-026-40620-5
Słowa kluczowe: proteomika przestrzenna, obrazowanie mózgu, wyszukiwarka wizualna, mikroskopia multipleksowa, patologia obliczeniowa